Clear Sky Science · es
Investigando las interacciones de la proteína de inmunidad Colicin E9 de Escherichia coli con la girasa de ADN de Pseudomonas aeruginosa: enfoque computacional avanzado para desarrollar nuevas estrategias antimicrobianas
Convertir las armas bacterianas en nuevos medicamentos
A medida que la resistencia a los antibióticos se extiende, los médicos se quedan sin herramientas para detener infecciones peligrosas. Algunos de los agentes más persistentes, como Pseudomonas aeruginosa, pueden resistir muchos fármacos. Este estudio busca en las propias bacterias ideas innovadoras, explorando cómo la proteína protectora incorporada de un microbio podría reutilizarse para desactivar una enzima vital en otro microbio. Mediante avanzadas simulaciones por ordenador, los investigadores muestran cómo una pequeña proteína “de inmunidad” puede adherirse firmemente a una enzima bacteriana clave, sugiriendo una nueva vía para futuros antimicrobianos.
Un pequeño escudo frente a una toxina letal
Ciertos cepas de Escherichia coli producen potentes toxinas proteicas llamadas colicinas que pueden matar a bacterias vecinas. Para evitar envenenarse, estas bacterias también fabrican proteínas de inmunidad complementarias. Una de esas protectoras, conocida como la proteína de inmunidad Colicin E9 (a menudo llamada Im9), se une al dominio cortante de la toxina e impide que dañe el ADN del hospedador. Debido a que esta asociación es tan específica y fuerte, los científicos llevan tiempo sospechando que comprenderla en detalle podría revelar maneras nuevas de controlar bacterias nocivas. En este trabajo, los autores se preguntan si Im9 también podría engancharse a la girasa de ADN, una enzima esencial en Pseudomonas aeruginosa que gestiona cómo se enrolla y copia su ADN.
Apuntar a una enzima vulnerable en un germen difícil de tratar
Pseudomonas aeruginosa es un patógeno hospitalario importante, capaz de sobrevivir en entornos adversos y resistente a muchos fármacos. La girasa de ADN es una de sus enzimas más relevantes, responsable de mantener las largas cadenas de ADN de la bacteria debidamente torsionadas para que puedan replicarse. Como bloquear esta enzima puede detener el crecimiento bacteriano, ya es un objetivo probado para algunos antibióticos. Los autores emplearon una herramienta de aprendizaje profundo para analizar la estructura tridimensional de la girasa de Pseudomonas y señalar probables “puntos calientes”: agrupaciones de aminoácidos en su superficie que son más importantes para unir a otras moléculas. Estas regiones forman el bolsillo activo de la enzima, donde ocurre el procesamiento normal del ADN y donde idealmente se uniría un inhibidor potencial.
Simulando un apretón molecular de manos
Para comprobar si Im9 podría aferrarse a esos puntos calientes, los investigadores recurrieron a programas de acoplamiento molecular que virtualmente “encajan” proteínas como rompecabezas 3D. Primero limpiaron y completaron las estructuras disponibles tanto de Im9 como de la girasa, reparando un lazo faltante en la enzima y ejecutando simulaciones cortas para relajar regiones tensas. Luego utilizaron dos herramientas de docking complementarias, ClusPro y LightDock, para generar muchos complejos candidatos. A partir de estos, seleccionaron los arreglos más prometedores y los sometieron a largas simulaciones de dinámica molecular que abarcaron cientos de nanosegundos. Estas películas con resolución temporal les permitieron observar cómo las dos proteínas se ajustaban, flexionaban y asentaban en formas más estables cuando estaban unidas.
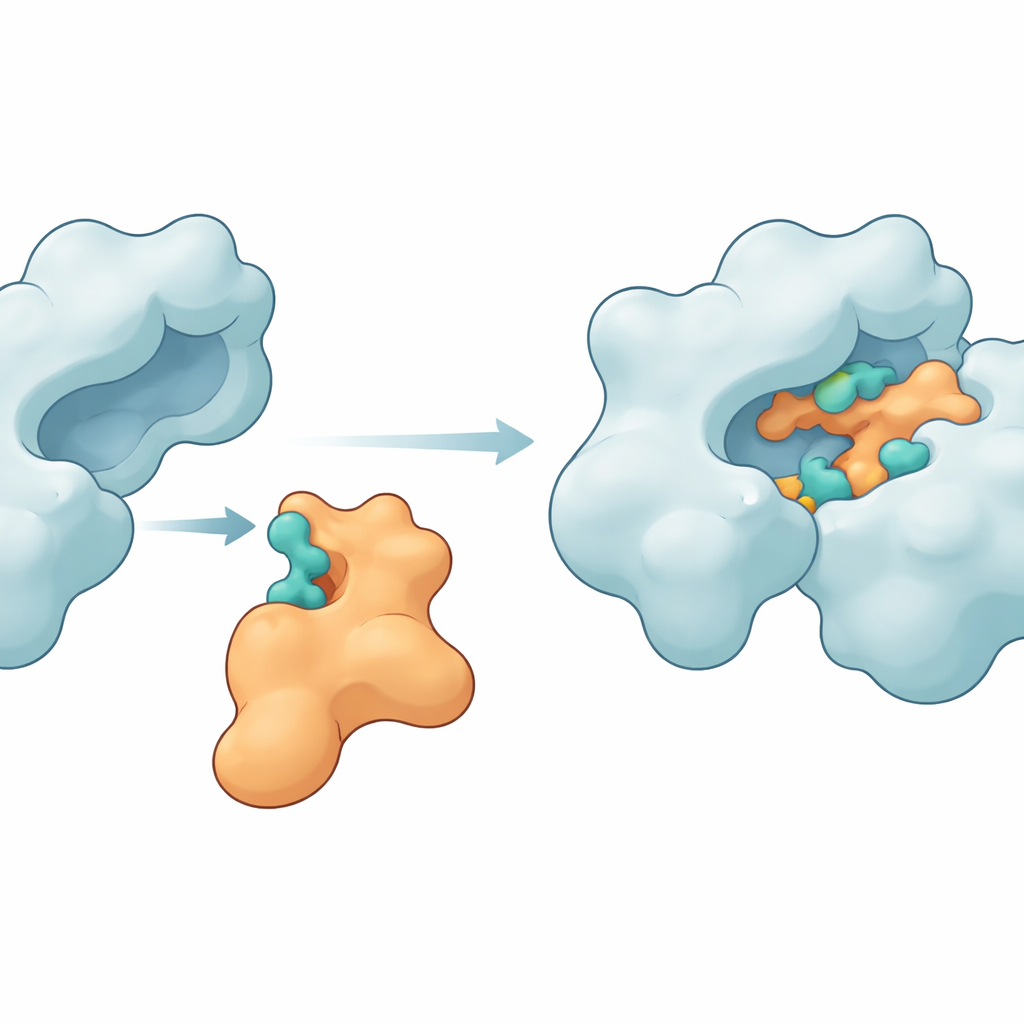
Puntos clave de contacto que mantienen unidas a las proteínas
Las simulaciones revelaron que Im9 puede, en efecto, formar un complejo compacto y persistente con la girasa de ADN. Varios aminoácidos en la enzima—como MET27, ASP47, LYS105, LEU198, ASN199, ARG191 y GLU194—formaron repetidamente enlaces de hidrógeno y otras fuerzas atractivas con sitios coincidentes en Im9. En uno de los modelos principales, los dos socios mantuvieron entre seis y diez enlaces de hidrógeno durante la mayor parte de la simulación, señal de una interfaz fuerte y bien organizada. Otras medidas estructurales, incluidas la compacidad de las proteínas y la amplitud de sus fluctuaciones conformacionales, mostraron que la enzima permaneció íntegra mientras la proteína de inmunidad se flexionaba lo justo para moldearse alrededor de la superficie de la girasa. Cálculos energéticos mediante el método MM-GBSA respaldaron además la idea de que estos contactos generan una energía libre de unión favorable, aunque modesta, dominada por contribuciones electrostáticas y de van der Waals.
De modelos computacionales a futuros antimicrobianos
En conjunto, los resultados sugieren que la proteína de inmunidad Colicin E9 puede unirse de forma estable a la región activa de la girasa de ADN de Pseudomonas, formando un complejo de larga duración que, en principio, podría bloquear la función normal de la enzima en el manejo del ADN. Aunque estos hallazgos se basan enteramente en modelos computacionales y aún requieren validación experimental, proporcionan un plano detallado de dónde y cómo podría adherirse un inhibidor basado en proteínas. Para el público no especialista, el mensaje clave es que las propias armas y escudos bacterianos de la naturaleza pueden inspirar nuevas estrategias contra infecciones difíciles de tratar. Al entender este apretón microscópico de manos con detalle atómico, los científicos avanzan un paso más hacia el diseño de nuevos antimicrobianos que inhabiliten enzimas bacterianas cruciales sin dañar las células humanas.
Cita: Alfaraj, R., Alkathiri, F. & Chikhale, R. Investigating Escherichia coli Colicin E9 immunity protein interactions with DNA gyrase of Pseudomonas aeruginosa: advanced computational approach for developing novel antimicrobial strategies. Sci Rep 16, 10786 (2026). https://doi.org/10.1038/s41598-026-44427-2
Palabras clave: resistencia a los antibióticos, girasa de ADN, interacciones proteína–proteína, diseño computacional de fármacos, Pseudomonas aeruginosa