Clear Sky Science · es
Genómica comparativa de los plastidios de Hippophae revela relaciones filogenéticas y propone marcadores de ADN candidatos para identificación taxonómica
Por qué importa este arbusto resistente
El espino amarillo es un arbusto resistente que prospera donde muchas otras plantas fracasan: en laderas frías, secas y expuestas al viento del altiplano Qinghai–Tíbet y más allá. Sus brillantes bayas naranjas se promocionan en todo el mundo como “súperfrutas” y la planta se usa ampliamente para estabilizar suelos y recuperar terrenos degradados. Sin embargo, incluso los especialistas tienen dificultades para distinguir a simple vista entre sus especies y subespecies estrechamente emparentadas. Este estudio plantea una pregunta simple pero importante: ¿podemos leer el manual de instrucciones interno de la planta—su ADN—para aclarar quién es quién y, al hacerlo, ofrecer a criadores y conservacionistas una herramienta potente para gestionar este recurso valioso?
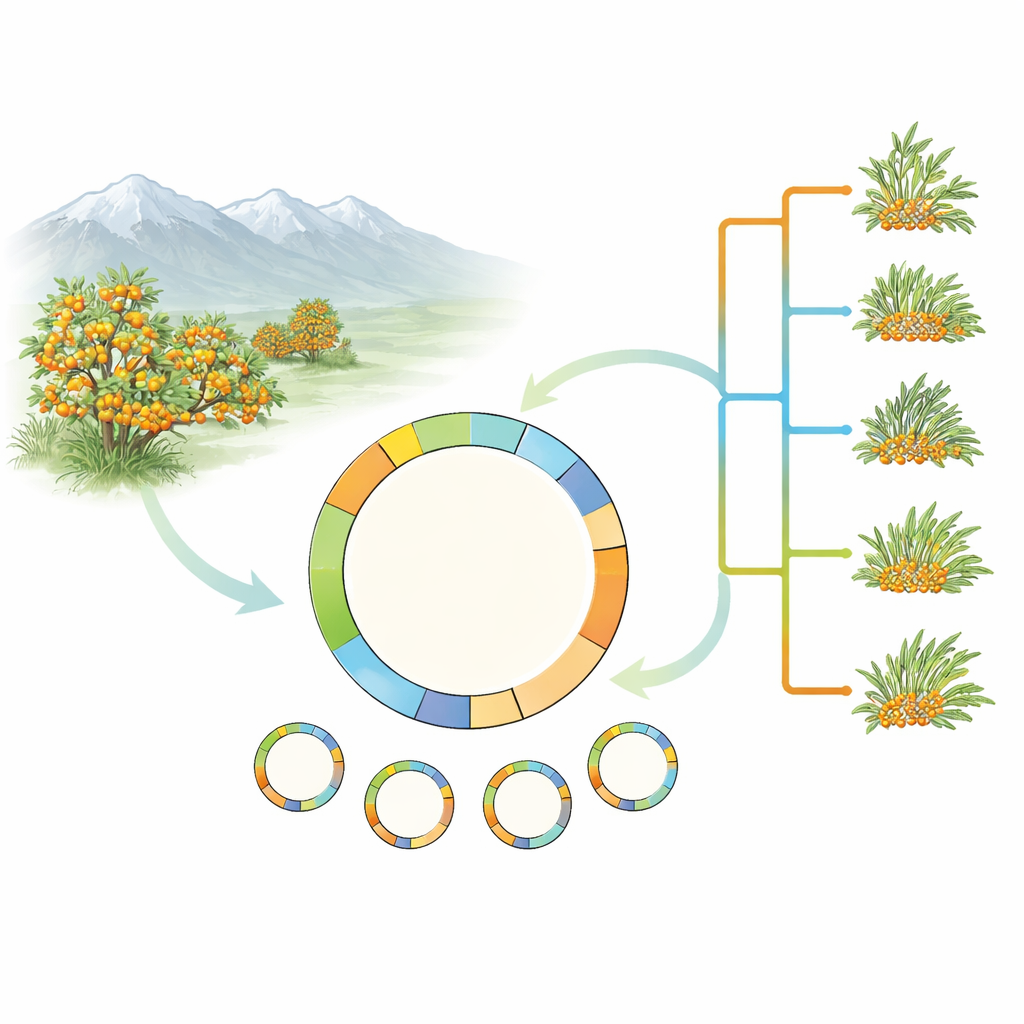
Mirando dentro de los motores verdes de la planta
En lugar de abordar la complejidad completa del genoma del espino amarillo, los investigadores se centraron en los plastidios de la planta—pequeños compartimentos verdes dentro de las células que realizan la fotosíntesis. Los plastidios tienen su propia molécula de ADN circular y pequeña, heredada mayoritariamente de la madre, que ha resultado extremadamente útil para trazar árboles genealógicos de plantas. El equipo recogió y secuenció genomas plastidiales completos de 17 muestras que representan cinco especies de espino amarillo y varias formas del extendido Hippophae rhamnoides. También añadieron un genoma plastidial recién ensamblado de un tipo cultivado importante, H. rhamnoides subsp. mongolica cv. Prevoskhodnaya, y revisaron cuidadosamente entradas previas en bases de datos para corregir errores.
Un plano compartido con diferencias reveladoras
A primera vista, el ADN plastidial de todas las muestras de espino amarillo parecía notablemente similar. Cada genoma tenía alrededor de 155 000 a 156 000 “letras” y seguía la misma disposición en cuatro partes que se encuentra en muchas plantas con flores: dos regiones de copia única separadas por un par de segmentos duplicados. Estaba presente el mismo conjunto de genes, dispuestos en el mismo orden, e incluso el balance global de las cuatro letras del ADN variaba muy poco. Esta estabilidad estructural sugiere que, a lo largo del tiempo evolutivo, el plano plastidial en Hippophae se ha conservado. Sin embargo, cuando los investigadores examinaron detalles más finos—como la frecuencia con que ciertos “codones” se usan para deletrear el mismo aminoácido—hallaron patrones sutiles específicos de linajes que apuntan a una modelación lenta y a largo plazo del código en distintas ramas del género.
Desenredando el árbol familiar
Usando 78 genes codificadores de proteínas del ADN plastidial, el equipo construyó árboles evolutivos que sitúan al espino amarillo dentro de la amplia familia de las rosáceas y luego se centran en las relaciones dentro de Hippophae. Los análisis confirmaron que el espino amarillo, como grupo, forma una única línea natural, y que H. rhamnoides y sus subespecies también están estrechamente emparentadas. De forma intrigante, una especie, H. tibetana, cae consistentemente dentro del grupo de H. rhamnoides en el árbol plastidial, aunque trabajos anteriores con ADN nuclear la habían situado más cerca de la base del género. Esta discrepancia entre las historias nuclear y plastidial sugiere hibridación pasada u otros eventos evolutivos complejos y subraya la necesidad de futuros estudios que combinen conjuntos de datos nucleares y plastidiales completos.
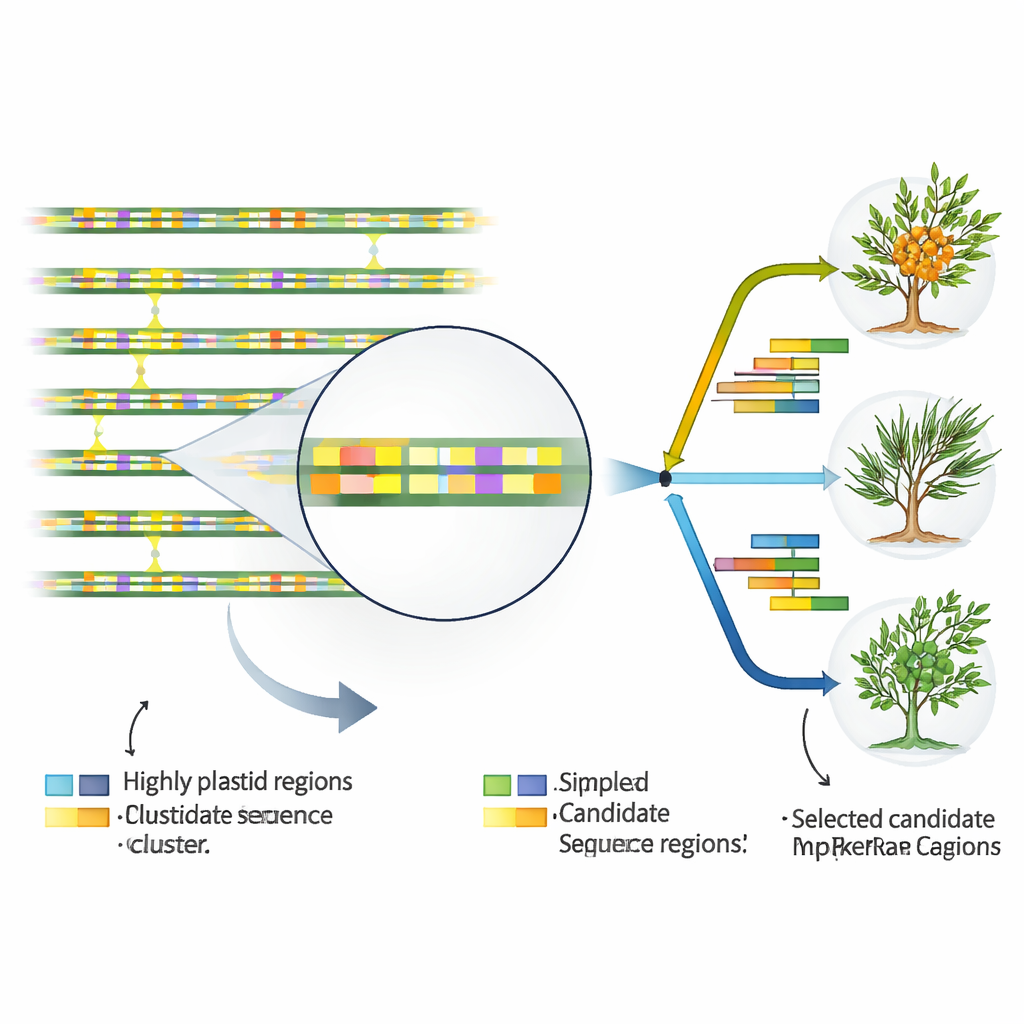
Encontrando los puntos calientes genómicos que marcan la identidad
Para transformar el ADN plastidial en herramientas prácticas para taxónomos y criadores, los autores buscaron tramos de secuencia que cambian más rápido que el resto. Comparando los 17 genomas plastidiales, identificaron 46 regiones especialmente variables, casi todas situadas entre genes o dentro de intrones no codificantes más que en los propios cuerpos de los genes. También cartografiaron docenas de pequeños motivos repetidos conocidos como repeticiones simples en tándem (SSRs), que son particularmente ricos en las letras A y T y se agrupan en regiones no codificantes. Algunas de estas repeticiones y segmentos variables mostraron diferencias claras entre especies e incluso entre subespecies de H. rhamnoides. Unas pocas regiones destacaron como puntos calientes tanto en comparaciones a nivel de especie como de subespecie, lo que las convierte en candidatas principales para marcadores de ADN prácticos que se pueden detectar con pruebas de laboratorio sencillas.
De los patrones de ADN a aplicaciones en el mundo real
Trazando tanto el marco estable como las pequeñas pero informativas diferencias en los genomas plastidiales del espino amarillo, este estudio proporciona una caja de herramientas para una identificación fiable basada en ADN. Las regiones marcadoras propuestas podrían ayudar a distinguir especies de aspecto similar, verificar el origen de productos comerciales de las bayas, proteger la diversidad genética salvaje y guiar la selección de progenitores en programas de cría destinados a la nutrición, la medicina y la restauración de tierras. En términos sencillos, los autores demuestran que un manual de instrucciones del cloroplasto leído con cuidado puede revelar quién es quién en la familia ampliada de este arbusto resistente, allanando el camino para una conservación más inteligente y un uso más específico de uno de los cultivos de fruto más resistentes del mundo.
Cita: Asakura, N., Noda, M., Takahashi, Y. et al. Comparative plastid genomics of Hippophae reveals phylogenetic relationships and provides candidate DNA markers for taxonomic identification. Sci Rep 16, 7943 (2026). https://doi.org/10.1038/s41598-026-40776-0
Palabras clave: espino amarillo, genoma del plastidio, marcadores de ADN, taxonomía vegetal, diversidad genética