Clear Sky Science · es
Caracterización genómica de cepas multirresistentes de Escherichia coli identificadas en pacientes con infección del tracto urinario en Egipto
Por qué importan estas infecciones persistentes
Las infecciones del tracto urinario figuran entre las razones más comunes por las que las personas acuden a hospitales y consultas. Muchas las provoca la bacteria Escherichia coli y, por lo general, son tratables con antibióticos estándar. Pero en todo el mundo, incluido Egipto, algunas cepas de E. coli han desarrollado tanta resistencia a los fármacos que los médicos se están quedando sin opciones. Este estudio examina en detalle el material genético de dos de estas cepas difíciles de tratar procedentes de pacientes egipcias para entender cómo eluden múltiples fármacos y con qué facilidad podría propagarse su resistencia.
Dos pacientes, dos gérmenes peligrosos
Los investigadores se centraron en dos cepas de E. coli, denominadas UPE7 y UPE139, aisladas de mujeres con infecciones del tracto urinario en un hospital de Mansura, Egipto. Al someterlas a pruebas frente a una amplia gama de antibióticos, ambas resistieron muchos de los fármacos que los médicos suelen prescribir, incluidos varios medicamentos de último recurso. Mostraron resistencia a penicilinas y cefalosporinas comunes, a carbapenémicos potentes, a fluoroquinolonas de uso extendido y a otras clases de fármacos. Este patrón las sitúa claramente en la categoría de bacterias multirresistentes, lo que hace que las infecciones sean difíciles y costosas de tratar y aumenta el riesgo de complicaciones.
Leyendo el manual genético de las bacterias
Para averiguar cómo se volvieron tan resistentes, el equipo secuenció sus genomas completos mediante tecnología de secuenciación de nueva generación. Después utilizaron herramientas informáticas especializadas para buscar en los genomas genes asociados a la resistencia a antibióticos y rasgos que ayudan a las bacterias a causar enfermedad. Ambas cepas portaban numerosos genes de resistencia que concordaban con su comportamiento en el laboratorio. Por ejemplo, albergaban múltiples genes de “beta‑lactamasa” que desactivan antibióticos clave, así como genes que confieren protección frente a fármacos como aminoglucósidos, tetraciclinas, macrólidos, sulfonamidas y trimetoprim. Alteraciones en enzimas centrales que manejan el ADN, los blancos de las fluoroquinolonas, se correspondían con su marcada resistencia a la levofloxacina. Ambas cepas también poseían un operón conocido por modificar su superficie externa de modo que reduce la eficacia de los antibióticos polimixina.
Ayudantes ocultos que difunden la resistencia
Más allá de los genes individuales de resistencia, el estudio pone de relieve los vehículos genéticos que movilizan estos rasgos. Muchos de los genes de resistencia estaban junto a elementos genéticos móviles, como secuencias de inserción y transposones —pequeñas unidades de ADN que pueden saltar entre ubicaciones—, y en plásmidos, moléculas circulares de ADN que las bacterias comparten entre sí. Por ejemplo, un gen de beta‑lactamasa de espectro extendido muy difundido, CTX‑M‑15, se vinculó a estos elementos móviles en ambas cepas, mientras que UPE139 también portaba OXA‑244, una enzima que degrada carbapenémicos e integrada entre segmentos de ADN saltantes en el cromosoma. Los mismos tipos de plásmidos encontrados aquí se han asociado en otros lugares a cúmulos de genes de resistencia, lo que genera preocupación de que estas cepas puedan transferir sus defensas a otras bacterias en hospitales y en la comunidad.
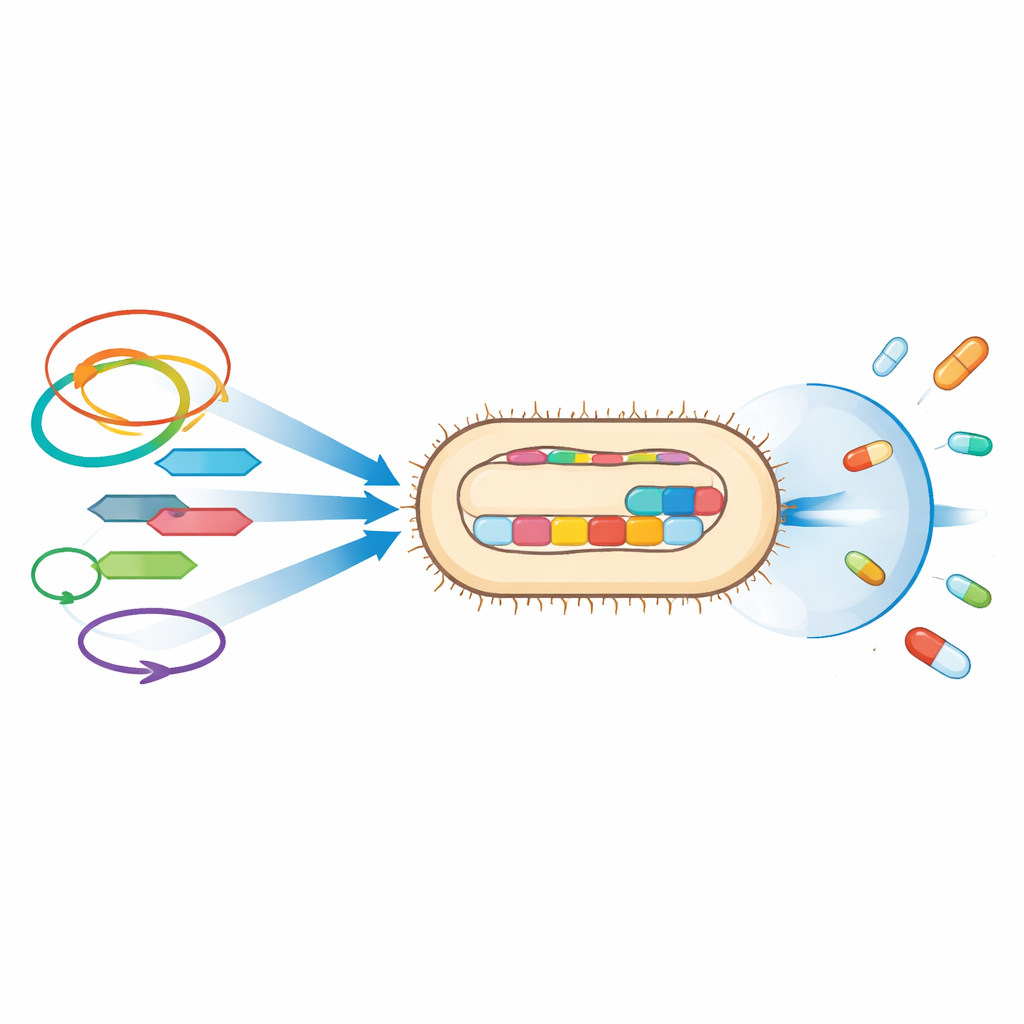
Herramientas para la infección y la supervivencia
El análisis genético también desveló numerosos rasgos que ayudan a estas cepas de E. coli a colonizar el tracto urinario y dañar los tejidos del huésped. Tanto UPE7 como UPE139 portaban múltiples estructuras de adhesión que les permiten adherirse a las células y formar biopelículas, comunidades protectoras que son más resistentes a los fármacos y al sistema inmunitario. Codificaban toxinas como la hemolisina, que puede dañar células del huésped, y sistemas de captación de hierro que permiten a las bacterias prosperar en el entorno pobre en hierro del organismo. UPE139, en particular, poseía genes adicionales relacionados con la formación de cápsula, la invasión y la evasión inmune, lo que sugiere que puede tener una capacidad especialmente fuerte para persistir y propagarse dentro de los pacientes.
Qué significa esto para pacientes y médicos
Al combinar las pruebas tradicionales de sensibilidad a los fármacos con la secuenciación completa del genoma, este estudio muestra cómo un pequeño conjunto de genes y elementos móviles puede convertir bacterias urinarias comunes en patógenos multirresistentes formidables. También revela que estos rasgos peligrosos residen en fragmentos de ADN bien adaptados para transferirse a otras cepas, lo que aumenta el riesgo de una difusión más amplia a nivel local y regional. Para los pacientes, esto significa que algunas infecciones comunes pueden volverse más difíciles de curar. Para los clínicos y las autoridades sanitarias, el trabajo subraya la necesidad de una vigilancia genómica continua, un uso prudente de los antibióticos y estudios más amplios sobre un mayor número de aislados para rastrear clones de alto riesgo, afinar las guías de tratamiento y frenar el avance de la resistencia.
Cita: El Halfawy, N.M., Gouda, M.K., Elgayar, F.A. et al. Genomic characterization of multidrug-resistant Escherichia coli strains identified from patients with urinary tract infection in Egypt. Sci Rep 16, 8958 (2026). https://doi.org/10.1038/s41598-026-40536-0
Palabras clave: resistencia a los antibióticos, infección del tracto urinario, Escherichia coli, secuenciación del genoma, elementos genéticos móviles