Clear Sky Science · es
El análisis multi-ómico integrado identifica el gen relacionado con el daño del ADN CLSPN como un biomarcador en el cáncer gástrico
Por qué importa esta investigación
El cáncer de estómago sigue siendo uno de los más letales del mundo, en buena parte porque con frecuencia se detecta tarde y carece de señales de alerta temprana fiables. Este estudio explora en profundidad las “marcas” genéticas que deja el daño del ADN e identifica un gen llamado CLSPN como un marcador prometedor que podría ayudar a los médicos a detectar el cáncer gástrico antes, valorar su agresividad y, potencialmente, personalizar los tratamientos con mayor precisión.
Buscando señales de peligro en los tumores gástricos
Los investigadores partieron de una idea sencilla: si el daño del ADN contribuye al cáncer gástrico, los genes implicados en gestionar ese daño podrían contener pistas importantes sobre quién enferma y cómo progresa la enfermedad. Para comprobarlo, reunieron varios conjuntos de datos grandes. Estos incluyeron secuenciación de ARN a granel, que mide la actividad génica media en muestras tumorales completas; secuenciación de ARN de célula única, que examina miles de células individuales una por una; y transcriptómica espacial, que sitúa la actividad génica en la lámina tisular. También compilaron una lista extensa de genes ya vinculados al daño del ADN. Con estos recursos, preguntaron qué genes relacionados con el daño del ADN estaban más fuertemente asociados con el cáncer gástrico y con la supervivencia de los pacientes.
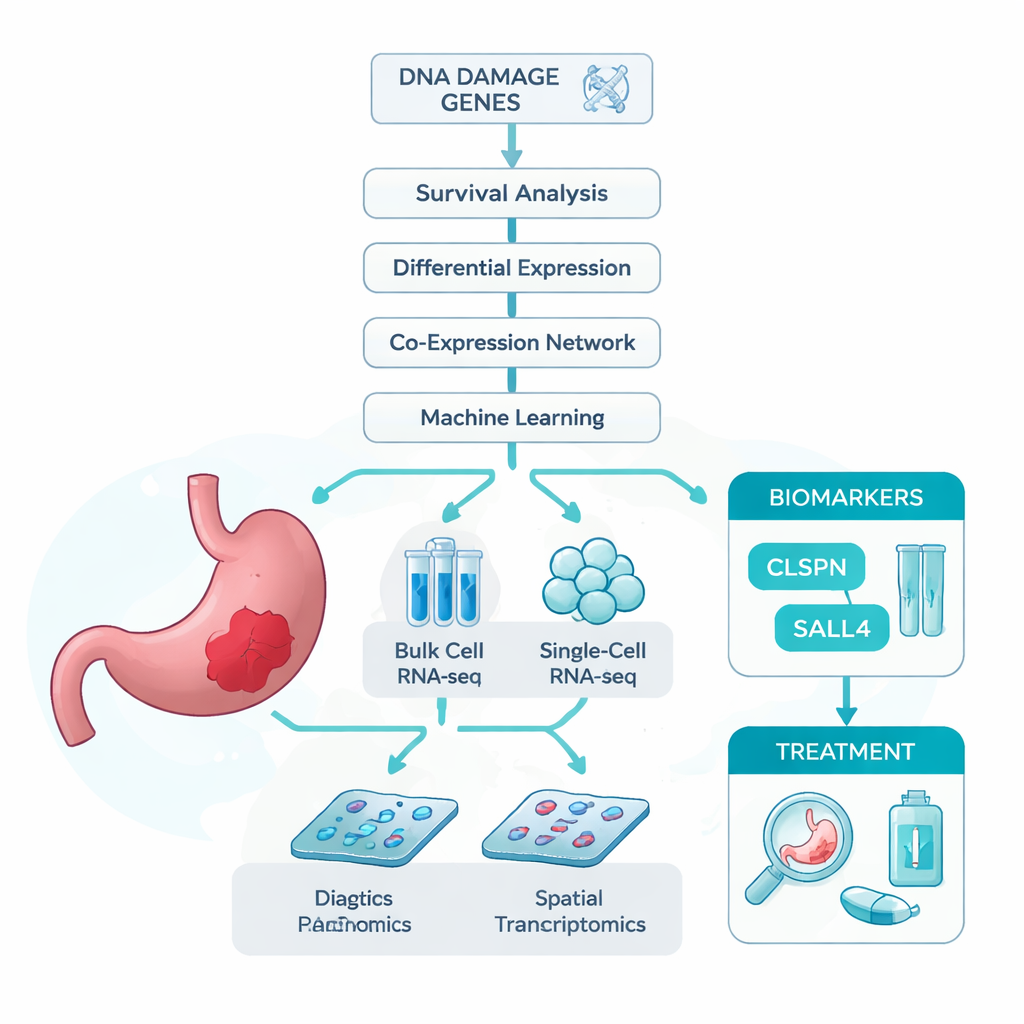
Usando algoritmos inteligentes para encontrar genes clave
Dado que miles de genes cambian en el cáncer, el equipo recurrió a un conjunto de herramientas estadísticas y de aprendizaje automático para reducir el número de candidatos. Primero filtraron los genes que estaban tanto desregulados en tumores como claramente relacionados con la supervivencia de los pacientes. Luego agruparon genes según cómo subían y bajaban de forma conjunta y cotejaron estos grupos con la lista de genes de daño del ADN. Este cribado en varios pasos produjo 13 genes candidatos sólidos. Para ver cuáles de estos eran más útiles para distinguir tejido tumoral del normal, entrenaron siete modelos diferentes de aprendizaje automático, cada uno clasificando los genes según su utilidad para la clasificación. En todos los modelos, dos genes —CLSPN y SALL4— se situaron de forma constante en la cima, con puntuaciones de precisión cercanas o superiores al 97% y áreas bajo la curva ROC por encima de 0,96, lo que sugiere un excelente potencial diagnóstico.
Detallando CLSPN dentro del tumor
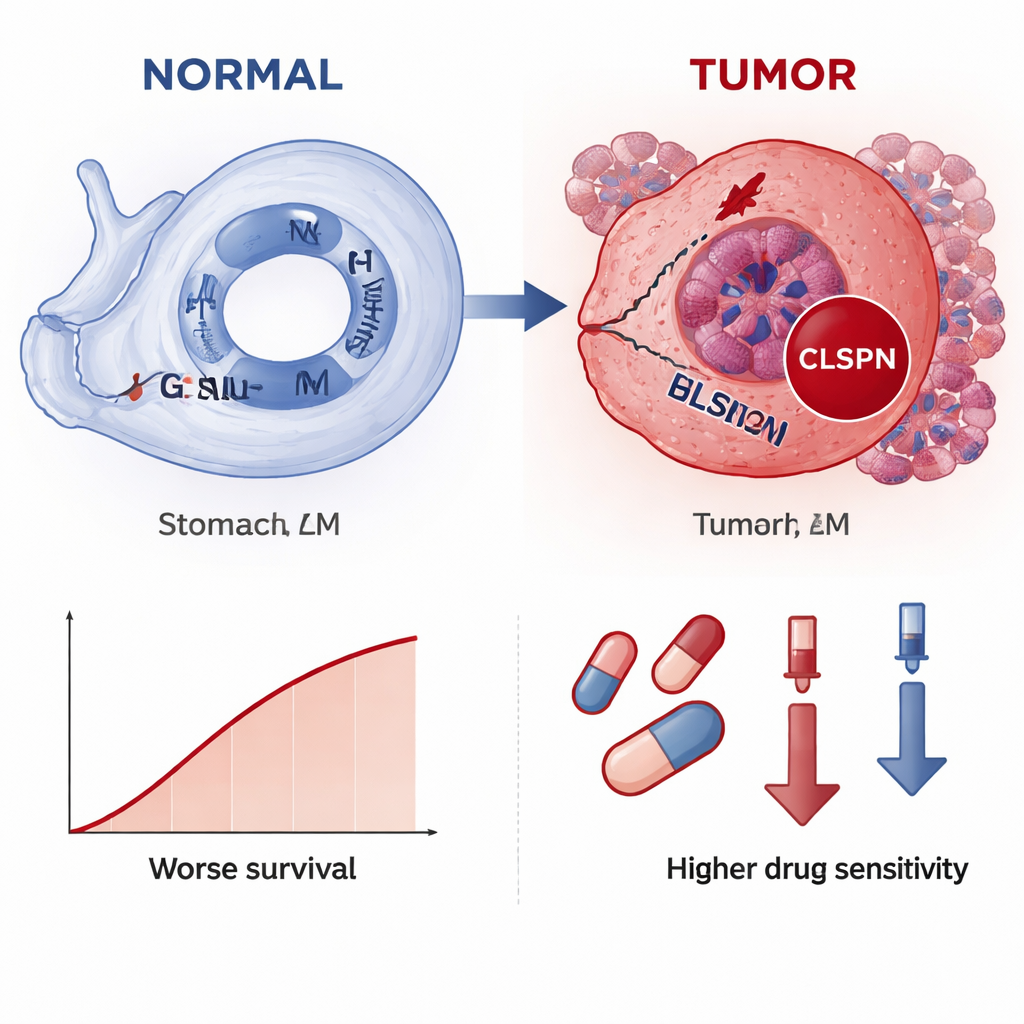
Entre los dos genes principales, CLSPN destacó como el más informativo en conjunto, por lo que los autores lo examinaron con mayor detalle. En datos de célula única de más de 30 000 células, CLSPN mostraba mucha más actividad en las células tumorales que en las células normales adyacentes o en las células de sostén, lo que apunta a un papel específico en el tumor. El mapeo espacial de secciones de tejido de pacientes mostró un patrón similar: la expresión de CLSPN se agrupaba en regiones que los patólogos identificaban como cancerosas. Cuando el equipo dividió las células tumorales en grupos de “CLSPN alto” y “CLSPN bajo”, el grupo con niveles altos mostró mayor actividad en vías relacionadas con la replicación del ADN, la división celular y la reparación —procesos que, cuando están sobreactivados o desregulados, pueden impulsar el crecimiento descontrolado. El análisis de pseudotiempo, que reconstruye cómo cambian las células a lo largo de una línea temporal hipotética, sugirió que a medida que progresa el tumor las concentraciones de CLSPN tienden a aumentar, lo que indica que la subida de CLSPN podría formar parte del cambio hacia un estado más maligno.
Vínculos con el sistema inmunitario y la respuesta al tratamiento
El estudio también exploró cómo se relaciona CLSPN con el microambiente tumoral y con posibles terapias. Los tumores con mayor expresión de CLSPN mostraron mezclas distintas de células inmunitarias, en particular macrófagos y ciertos linfocitos T y NK, lo que sugiere que CLSPN podría contribuir a moldear un entorno inmunosupresor. La modelización de la sensibilidad a fármacos indicó que los cánceres con más CLSPN podrían ser más vulnerables a varios agentes quimioterápicos y dianas, ya que niveles elevados de CLSPN se asociaron con dosis predichas más bajas necesarias para inhibir el crecimiento. Importante, cuando los autores tiñeron muestras de tejido reales de 70 pacientes, los niveles de proteína CLSPN fueron claramente más altos en el cáncer que en el estómago normal y se relacionaron con tumores más grandes, mayor profundidad de invasión, afectación de ganglios linfáticos y menor supervivencia global.
Qué podría significar esto para los pacientes
En términos prácticos, el estudio sugiere que CLSPN actúa como una luz roja de alarma para el cáncer de estómago: se enciende principalmente en las células tumorales, brilla más en las enfermedades avanzadas y señala un mayor riesgo de mal pronóstico. Dado que puede detectarse tanto a nivel de ARN como mediante técnicas de tinción estándar en hospitales, CLSPN podría convertirse en un biomarcador práctico para ayudar a los patólogos a confirmar el cáncer gástrico, estratificar a los pacientes por riesgo y, quizá, guiar la elección de fármacos. Aunque se necesitan más pruebas clínicas antes de su uso rutinario, este trabajo destaca cómo leer las huellas del daño del ADN a través de múltiples capas de datos puede descubrir nuevas herramientas para un diagnóstico más temprano y un tratamiento más personalizado del cáncer gástrico.
Cita: Ma, Q., Yang, X., Sun, N. et al. Integrating multi-omics analysis identifies DNA damage-related gene CLSPN as a biomarker in gastric cancer. Sci Rep 16, 7789 (2026). https://doi.org/10.1038/s41598-026-39387-6
Palabras clave: cáncer gástrico, daño del ADN, CLSPN, biomarcador, análisis de célula única