Clear Sky Science · es
Nuevos genes marcadores para la detección simultánea de Salmonella, EHEC O157:H7 y Cronobacter
Por qué esto importa para la seguridad alimentaria cotidiana
Desde las hojas de ensalada hasta las hamburguesas y la leche de fórmula para bebés, los alimentos en los que confiamos pueden ocasionalmente contener gérmenes peligrosos. Tres de los culpables más preocupantes —ciertas cepas de E. coli, Salmonella y una bacteria menos conocida llamada Cronobacter— pueden causar enfermedades graves, especialmente en niños pequeños y adultos vulnerables. Este estudio muestra cómo los científicos están usando enormes bases de datos de ADN y pruebas de laboratorio ingeniosas para detectar las tres amenazas a la vez, de forma rápida y precisa, antes de que los alimentos contaminados lleguen a su mesa.
Peligros ocultos en alimentos comunes
Las enfermedades transmitidas por los alimentos han aumentado en la última década, impulsadas en parte por las cadenas de suministro globales y el gran volumen de alimentos procesados y listos para consumir. EHEC O157:H7, una forma altamente tóxica de E. coli, puede provocar diarrea sanguinolenta e insuficiencia renal. Salmonella causa millones de casos de intoxicación alimentaria cada año, y Cronobacter, aunque menos conocida, puede ser letal para los recién nacidos, sobre todo en relación con la fórmula infantil en polvo. Los métodos de laboratorio tradicionales suelen centrarse en un solo germen a la vez y requieren días de cultivo, lo que ralentiza la investigación de brotes y los cribados rutinarios. Los autores se propusieron desarrollar pruebas basadas en ADN más rápidas que pudieran detectar estos tres patógenos juntos en un único procedimiento simplificado.
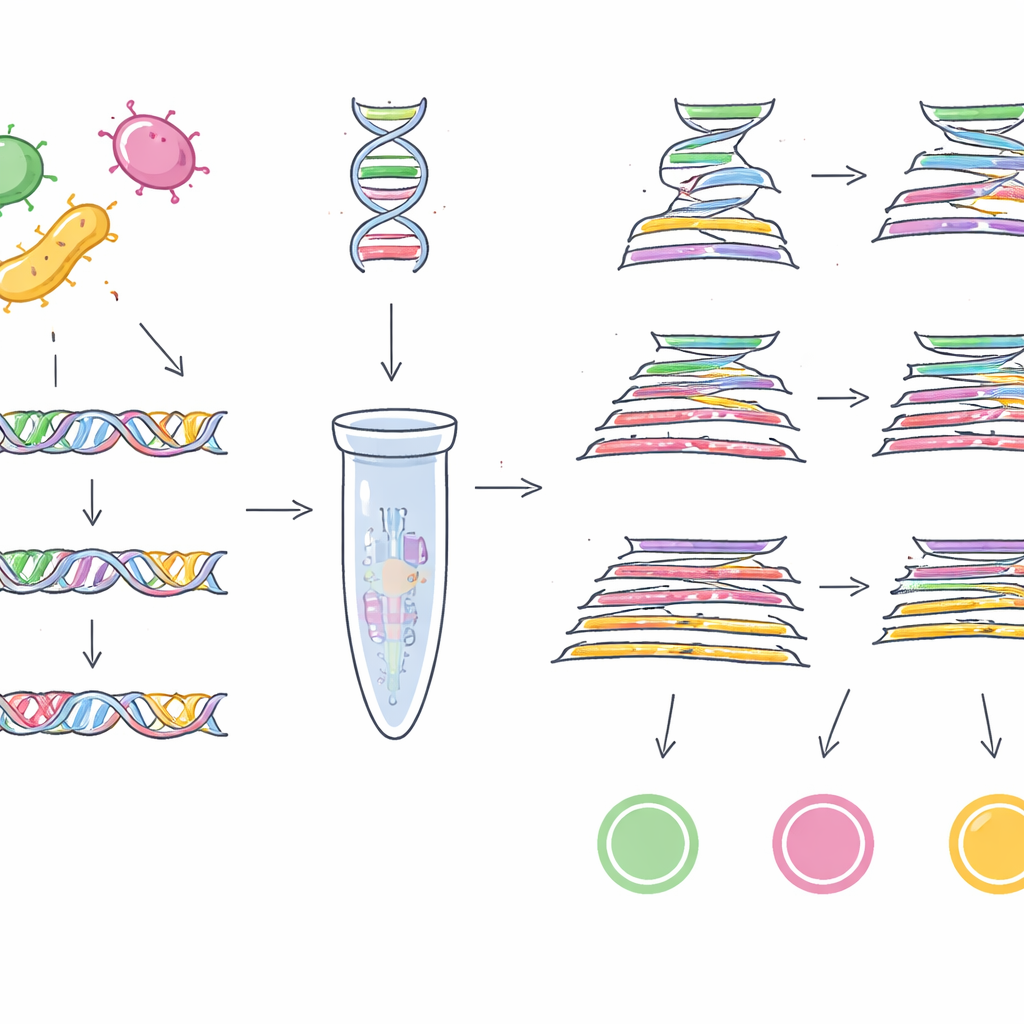
Encontrar “códigos de barras” en un mar de ADN
Para ello, el equipo primero necesitó “códigos de barras” genéticos fiables: fragmentos cortos de ADN que estén presentes en casi todas las cepas de un germen objetivo pero ausentes en otros. En lugar de buscar en unas pocas genomas, recurrieron a una enorme colección pública de 1,46 millones de genomas bacterianos de 50 géneros diferentes. Para EHEC O157:H7, compararon miles de genomas de E. coli y analizaron más de 100.000 familias de genes accesorios para encontrar secuencias de ADN exclusivas de este subtipo peligroso. Tras varias rondas de filtrado y comprobaciones cruzadas frente a más de un millón de genomas no pertenecientes a E. coli, llegaron a un gen llamado z0340 como marcador altamente específico de EHEC O157:H7. Usando una estrategia similar sobre más de medio millón de genomas de Salmonella y casi un millón de otros genomas bacterianos, identificaron otro gen, sbcC, como un marcador fiable para el grupo Salmonella en su conjunto.
Convertir marcadores en pruebas aplicables
Con estos dos nuevos códigos de barras en la mano —más un gen específico de Cronobacter, ygcB, que el grupo había descubierto previamente— los investigadores diseñaron pruebas de laboratorio capaces de detectar los tres patógenos a la vez. Construyeron ensayos de PCR múltiple, que actúan como fotocopiadoras moleculares dirigidas a tramos concretos de ADN, y una versión más sensible de PCR cuantitativa TaqMan que mide en tiempo real la cantidad de ADN objetivo presente. Cuando estas pruebas se enfrentaron a 23 cepas de los tres patógenos y a 100 cepas de otras bacterias comunes, identificaron correctamente solo los objetivos previstos en todo momento, mostrando una especificidad del 100 %. La PCR múltiple básica pudo detectar hasta 1 picogramo de ADN por microlitro, mientras que la versión TaqMan descendió hasta 0,5 picogramos, lo que indica una alta sensibilidad.
Poner los métodos a prueba en alimentos
La precisión del laboratorio solo es útil si las pruebas funcionan en muestras desordenadas del mundo real. Para comprobarlo, los científicos contaminaron deliberadamente lechuga, carne picada y fórmula infantil en polvo con cantidades conocidas de EHEC O157:H7, Salmonella o Cronobacter. Tras pasos de enriquecimiento estándar para permitir que cualquier bacteria presente se multiplique, aplicaron sus ensayos de PCR múltiple y qPCR TaqMan. En todos los casos, los métodos detectaron correctamente el patógeno introducido y no produjeron falsas alarmas en los controles negativos. El rendimiento fue consistente en los tres tipos de alimentos, lo que sugiere que las grasas, los componentes vegetales o los ingredientes complejos no interfirieron notablemente con la detección.
Limitaciones y mejoras futuras
A pesar de los resultados sólidos, los autores señalan que su panel de validación sigue representando solo una fracción muy pequeña de la diversidad microbiana que existe en la naturaleza. Por ejemplo, en el laboratorio solo probaron una cepa de EHEC O157:H7, aunque su cribado basado en genomas cubrió decenas de miles de dichas cepas. También trabajaron con niveles de contaminación relativamente altos en comparación con las cantidades extremadamente bajas de bacterias que aún pueden causar enfermedad. Trabajos futuros deberán probar muchos más aislados del mundo real, examinar alimentos contaminados de forma natural y añadir controles internos para protegerse contra sustancias en los alimentos que puedan inhibir la amplificación de ADN.
Qué significa esto para los consumidores
En términos cotidianos, este estudio muestra que los códigos de barras de ADN seleccionados con cuidado permiten a los laboratorios de seguridad alimentaria cribar varios gérmenes de alto riesgo a la vez, con gran exactitud y en menos tiempo que los métodos tradicionales basados en cultivo. Al minar millones de genomas, los investigadores identificaron tres firmas genéticas —una para EHEC O157:H7, otra para Salmonella y otra para Cronobacter— que parecen ser tanto muy específicas como estables. Las pruebas resultantes podrían reforzar la vigilancia rutinaria de alimentos como hojas de ensalada, carnes y fórmulas infantiles, detectando la contaminación antes y con mayor fiabilidad. Más allá de estos tres patógenos, el mismo enfoque basado en genomas podría usarse para diseñar pruebas rápidas para muchos otros microbios peligrosos, ofreciendo una herramienta poderosa para mantener más segura la cadena alimentaria global.
Cita: Zhang, H., Xiong, P., Lu, Z. et al. Novel marker genes for simultaneous detection of Salmonella, EHEC O157:H7, and Cronobacter. Sci Rep 16, 9362 (2026). https://doi.org/10.1038/s41598-026-38990-x
Palabras clave: patógenos transmitidos por alimentos, PCR múltiple, marcadores genómicos, Salmonella y EHEC, detección de Cronobacter