Clear Sky Science · es
Un estudio piloto sobre la consistencia de protocolos y la reproducibilidad de métricas de grafo en conectomas ponderados por microestructura
Por qué el mapa de cableado del cerebro necesita una comprobación de fiabilidad
Médicos y científicos consideran cada vez más el cerebro como un gran mapa de cableado, donde las regiones se comunican entre sí a través de haces de fibras nerviosas. Nuevos métodos basados en la resonancia magnética pueden convertir este cableado en redes matemáticas que podrían revelar signos tempranos de enfermedades como la esclerosis múltiple o el Alzheimer. Pero antes de que tales mediciones puedan orientar el diagnóstico o el tratamiento, necesitamos saber algo básico: si escaneamos el mismo cerebro sano más de una vez, o en distintos escáneres con ajustes ligeramente diferentes, ¿obtenemos esencialmente la misma red?
De la movilidad del agua a mapas de las autopistas cerebrales
Para construir estos mapas de cableado, los autores usan una forma de resonancia magnética que rastrea cómo se mueven las moléculas de agua en el tejido cerebral. En la sustancia blanca, donde largas fibras nerviosas aisladas discurren juntas, el agua prefiere moverse a lo largo de las fibras más que a través de ellas. Midiendo este movimiento sensible a la dirección en muchas orientaciones, los algoritmos informáticos pueden inferir haces de fibras y ensamblar un “conectoma”: una matriz que registra qué regiones de materia gris están conectadas por qué vías de materia blanca. En lugar de limitarse a contar cuántas fibras virtuales se reconstruyen entre regiones, este estudio se centra en conectomas “ponderados por microestructura”, donde cada conexión se caracteriza por propiedades del tejido mismo, como cuán ordenadas están las fibras o cuán densamente empaquetadas parecen.
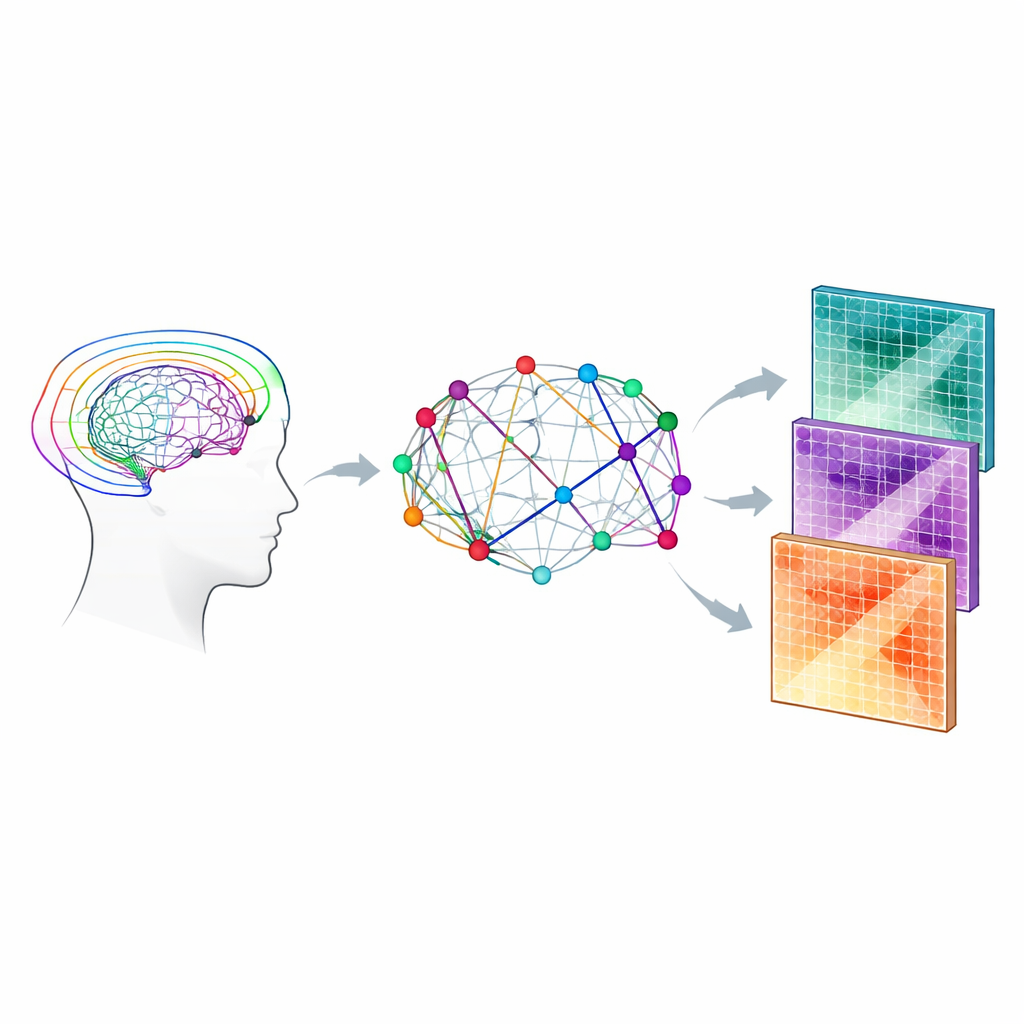
Incorporando detalle biológico a la red
El equipo combinó dos familias de modelos que interpretan la señal de la RM por difusión. El primero, la imagen por tensor de difusión, resume cuán direccional es el movimiento del agua y cuán rápido difunde en promedio. El segundo, denominado Bingham-NODDI, va un paso más allá estimando cuánto de cada pequeño volumen de tejido está compuesto por agua dentro de las neuritas, fuera de ellas o en espacios llenos de líquido. Usando un protocolo de adquisición relativamente rico de “cuatro conchas” diseñado para captar mejor la geometría compleja de las fibras, calcularon varios parámetros microestructurales, incluidos la anisotropía fraccional y la diffusividad media (del modelo tensorial) y las fracciones de volumen intra-neurita y extra-celular (de Bingham-NODDI). Estos parámetros se propagaron a lo largo de cada haz de fibras reconstruido y se combinaron para dar un peso biológicamente informado a cada conexión en la red.
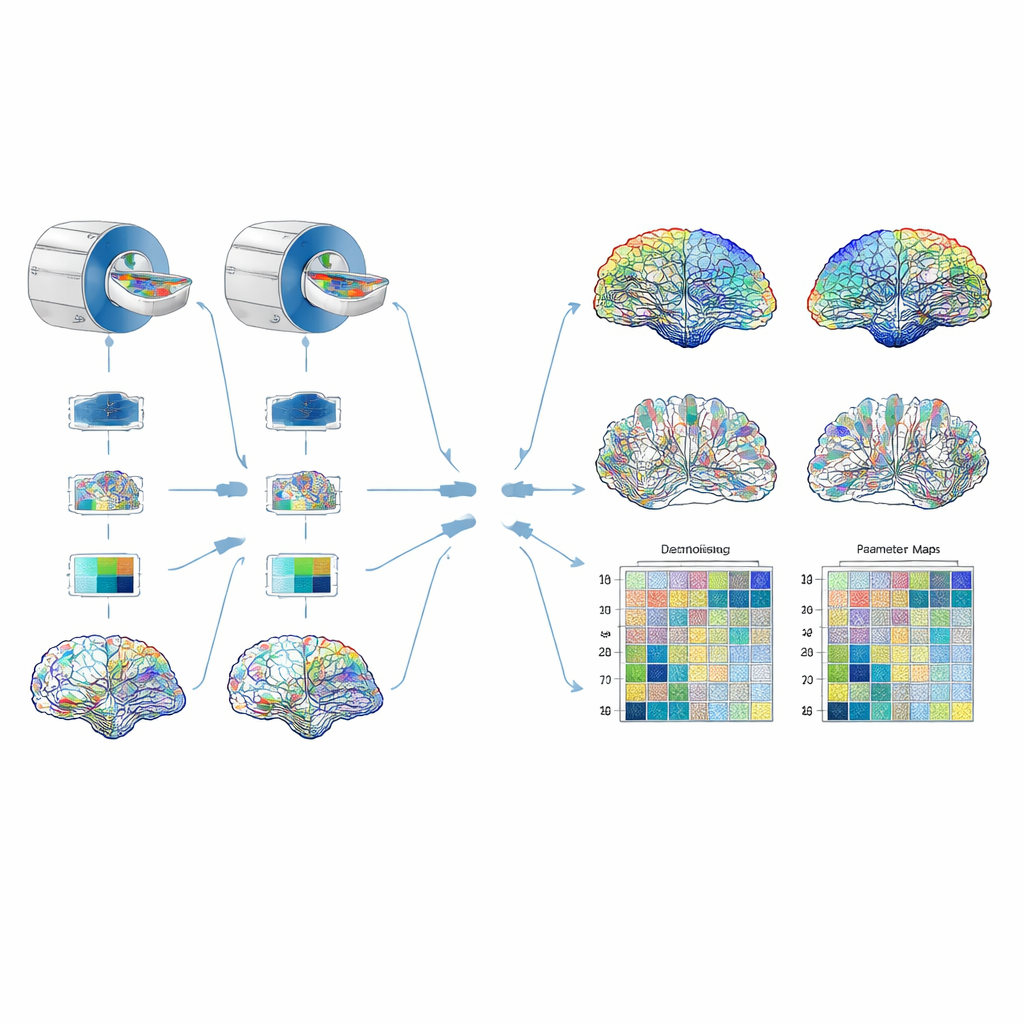
Poniendo la tubería a prueba
La fiabilidad se evaluó de tres maneras complementarias. Primero, los investigadores escanearon repetidamente un fantoma físico cuidadosamente diseñado —un enredo de fibras sintéticas en agua salina que imita características clave del tejido cerebral— para probar cuánto se mantenían estables los parámetros a corto plazo. A continuación, escanearon a cuatro voluntarios sanos en dos hospitales, usando la misma marca y modelo de escáner y los mismos ajustes, para investigar diferencias entre sitios. Finalmente, compararon el protocolo de cuatro conchas frente a un protocolo más corto y convencional de dos conchas, preguntando si ambos daban valores de parámetros similares. Para los datos cerebrales, reconstruyeron múltiples versiones del conectoma ponderadas por distintos parámetros y extrajeron medidas de grafo como la eficiencia global de la red, el grado de agrupamiento de las conexiones y la fuerza con que cada región se conecta con el resto del cerebro. Luego comprobaron cuánto variaban estas medidas de un sitio a otro y cuánto de la variación reflejaba diferencias reales entre personas en lugar de ruido de medida.
Qué resultó ser confiable
Varios parámetros clave del tejido resultaron ser notablemente consistentes. La anisotropía fraccional, la diffusividad media y las fracciones de volumen intra-neurita e intra-celular variaron menos del cinco por ciento entre escaneos repetidos, diferentes sitios y (en la mayoría de regiones) entre los protocolos de dos y cuatro conchas. En contraste, las cantidades que describen cuán dispersas están las orientaciones de las fibras —y un parámetro relacionado de “concentración”— fueron más erráticas y por ello se excluyeron de la construcción de la red. Cuando los investigadores construyeron conectomas ponderados por las medidas más estables, muchas propiedades de la red, incluida la densidad, la eficiencia global, el agrupamiento promedio y la fuerza media de las conexiones, fueron reproducibles entre sitios. Una excepción fue la modularidad, una medida de cuán claramente la red se divide en comunidades distintas; esta resultó ser notablemente más sensible a pequeños cambios en los pesos subyacentes. Los conectomas ponderados por el volumen extra-celular tuvieron el peor desempeño en general, con varias medidas de grafo mostrando pobre concordancia entre sitios.
Por qué esto importa para la salud cerebral
El estudio demuestra que no basta con contar fibras reconstruidas cuando se buscan marcadores de enfermedad en el cableado cerebral. Al seleccionar cuidadosamente parámetros microestructurales estables para ponderar cada conexión, los investigadores pueden construir redes más ricas y biológicamente fundamentadas cuyas propiedades clave sean repetibles entre escáneres y protocolos. En las condiciones probadas, los conectomas ponderados por anisotropía fraccional, diffusividad media y volumen intra-neurita parecieron lo bastante robustos como para que sus estadísticas de red básicas puedan servir como biomarcadores candidatos en trastornos que alteran la conectividad cerebral. Al mismo tiempo, el trabajo señala medidas más frágiles, como la modularidad y algunos índices microestructurales avanzados, como características que deben tratarse con cautela hasta que estudios multicéntricos más grandes confirmen su fiabilidad.
Cita: Cavallo, M., Ricchi, M., Axford, A. et al. A pilot study on protocol consistency and graph metric reproducibility in microstructure-weighted connectomes. Sci Rep 16, 8288 (2026). https://doi.org/10.1038/s41598-026-38964-z
Palabras clave: conectividad cerebral, resonancia magnética por difusión, conectoma, reproducibilidad de redes, imagen de microestructura