Clear Sky Science · es
Nueva red neuronal convolucional para la identificación bacteriana en conjuntos de datos de microscopía confocal
Por qué importa detectar gérmenes más rápido
Cuando los médicos intentan averiguar qué bacterias están causando una infección, el tiempo es crítico. Las pruebas de laboratorio tradicionales pueden tardar muchas horas o incluso días, y requieren expertos altamente cualificados que examinen las imágenes de microscopio a simple vista. Este estudio presenta un nuevo sistema de visión por ordenador, llamado CM-Net, que puede leer automáticamente imágenes microscópicas especializadas y distinguir rápidamente entre dos bacterias comunes y de importancia médica, además de reconocer si las células están vivas o muertas. El trabajo sugiere un camino hacia diagnósticos más rápidos y fiables que podrían utilizarse algún día en hospitales y laboratorios de investigación de todo el mundo.
Convertir gérmenes fluorescentes en imágenes útiles
Los investigadores partieron de una potente herramienta de imagen conocida como microscopía confocal de barrido láser. En términos sencillos, este microscopio usa un láser enfocado y tintes fluorescentes para hacer que las bacterias brillen en distintos colores según estén vivas o muertas. Las células vivas aparecen en verde, mientras que las muertas se ven en rojo. Al escanear la muestra en capas muy finas, el microscopio construye imágenes nítidas y detalladas de las bacterias sobre portaobjetos. El equipo trabajó con dos especies bien conocidas que a menudo causan infecciones hospitalarias: la forma de bastón Escherichia coli y la esférica Staphylococcus aureus. Estas imágenes de alta calidad constituyen la materia prima que CM-Net debe aprender a interpretar.
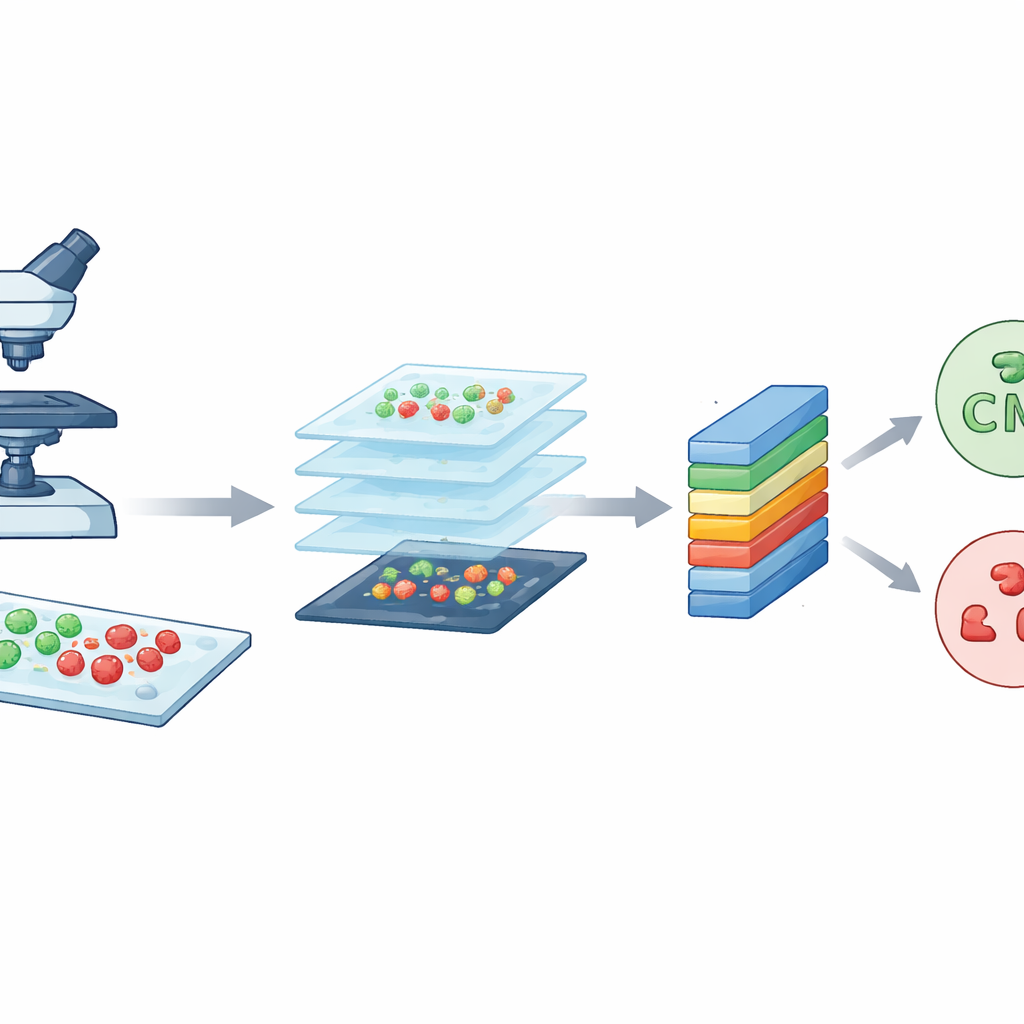
Crear muchos mosaicos pequeños a partir de imágenes grandes
Aunque cada imagen confocal está llena de detalle, también es muy grande, alrededor de 3000 por 3000 píxeles. Entrenar un modelo informático directamente con imágenes tan enormes sería lento y exigiría un poder de cálculo excesivo. Para resolver esto, el equipo cortó cada imagen grande en muchos mosaicos cuadrados más pequeños, de 224 por 224 píxeles cada uno, un tamaño estándar en análisis de imágenes. Este proceso, llamado aumento de datos, reduce la carga técnica y multiplica el número de ejemplos de entrenamiento. A partir de un conjunto original de 300 imágenes por tipo bacteriano, generaron en total 7.066 mosaicos. Estos mosaicos capturan patrones locales de formas, colores y texturas de distintas regiones de los portaobjetos, proporcionando al modelo un conjunto diverso y equilibrado de ejemplos para aprender.
Cómo el observador digital aprende a ver
CM-Net es un modelo de aprendizaje profundo cuidadosamente diseñado específicamente para la microscopía bacteriana, en lugar de ser una adaptación de colecciones generales de fotografías. Es un tipo de red neuronal convolucional, una clase de programas que sobresalen en encontrar patrones en imágenes. CM-Net procesa cada mosaico a través de una serie de etapas. Las etapas iniciales buscan señales visuales simples como bordes y puntos; las etapas más profundas combinan estos elementos en patrones más complejos que distinguen los bacilos de las esferas y las células vivas de las muertas. La red utiliza técnicas como la normalización por lotes, que mantiene sus señales internas en buen estado, y una forma recortada de su función de activación, que evita respuestas extremas que pueden desestabilizar el aprendizaje. Las capas finales condensan la información extraída y emiten una decisión final sobre el tipo bacteriano y el estado celular.
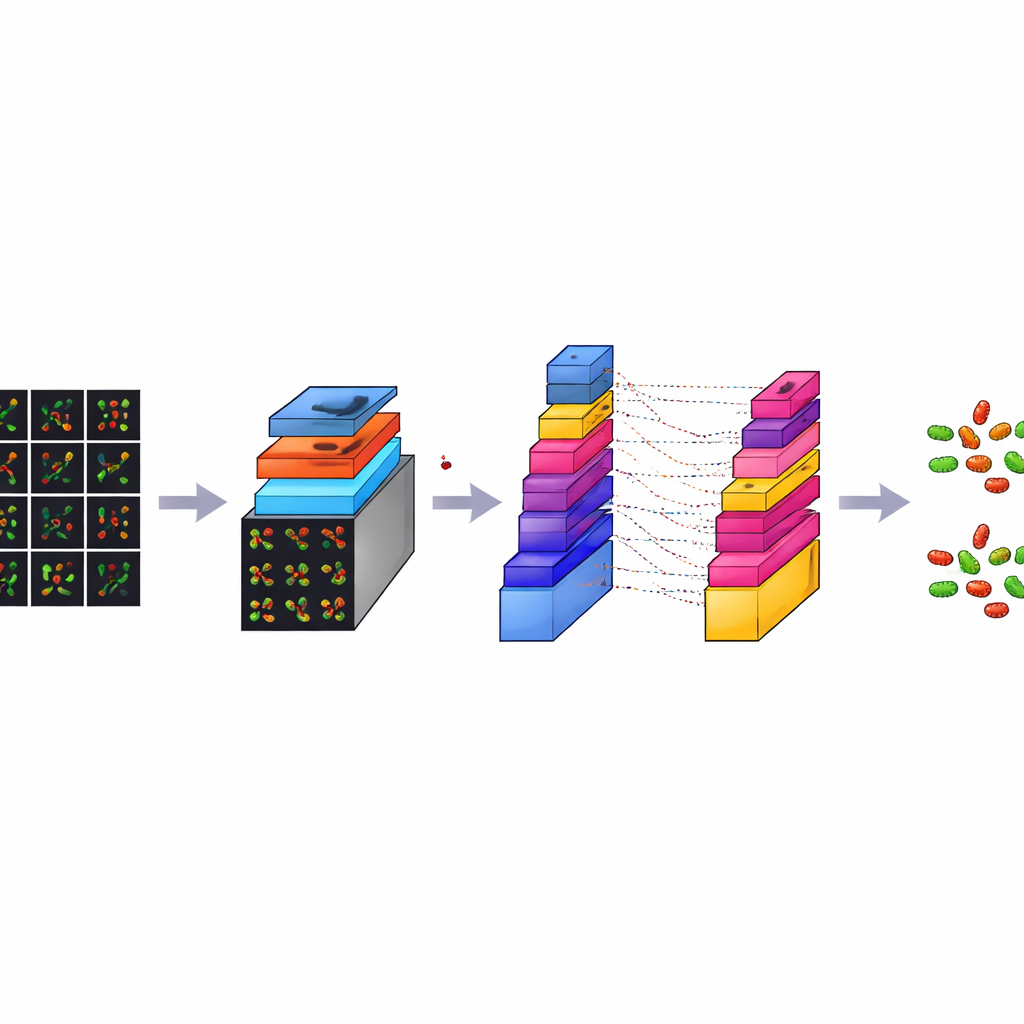
Superando a modelos populares listos para usar
Para evaluar el rendimiento de CM-Net, los autores lo entrenaron y probaron 30 veces, cada vez usando una nueva división de los datos en grupos de entrenamiento y prueba. Midieron la exactitud, la frecuencia con la que el modelo acertó en general; la sensibilidad, qué tan bien detectó cada objetivo; la especificidad, qué tan bien evitó las falsas alarmas; y varias otras métricas estándar. CM-Net alcanzó aproximadamente un 96 % de exactitud de media, con sensibilidad y especificidad también alrededor del 96 %, y un fuerte equilibrio entre las dos clases. Además, necesitó menos parámetros internos y menos memoria que varios modelos preentrenados muy usados, incluidos GoogLeNet, MobileNetV2, ResNet18 y ShuffleNet, y aun así se ejecutó más rápido. Herramientas de visualización mostraron que CM-Net centra su atención en los propios cuerpos bacterianos de las imágenes, en lugar de en características aleatorias del fondo, lo que respalda la idea de que está aprendiendo señales biológicamente relevantes.
Qué significa esto para el trabajo de laboratorio futuro
En términos cotidianos, el estudio demuestra que un sistema de aprendizaje profundo diseñado a propósito puede aprender a «leer» imágenes microscópicas complejas de bacterias con precisión, eficiencia y de una manera que se alinea con lo que valoran los expertos humanos. Por ahora, CM-Net se ha entrenado solo con dos especies bacterianas y con datos de un único tipo de microscopio, por lo que se necesita más trabajo antes de que pueda utilizarse como herramienta diagnóstica general. Los autores planean ampliarlo a más especies, diferentes estados celulares y conjuntos de datos más grandes y variados. Aun así, los resultados sugieren que sistemas como CM-Net podrían eventualmente ayudar a los laboratorios a identificar infecciones más rápidamente, orientar decisiones de tratamiento y abrir el análisis automatizado de experimentos de microbiología a usuarios sin experiencia especializada en imágenes.
Cita: Al-Jumaili, A., Al-Jumaili, S., Alyassri, S. et al. Novel convolutional neural network for bacterial identification of confocal microscopic datasets. Sci Rep 16, 8123 (2026). https://doi.org/10.1038/s41598-026-38861-5
Palabras clave: clasificación de imágenes bacterianas, microscopía confocal, aprendizaje profundo, redes neuronales convolucionales, diagnóstico médico