Clear Sky Science · es
Secuenciación del genoma de Bacillus daqingensis y Alkalicoccus luteus revela perspectivas taxonómicas y mecanismos adaptativos
Vida en lugares salinos
Desde lagos salados hasta suelos alcalinos, algunos microbios prosperan en condiciones que secarían y matarían a la mayoría de las demás formas de vida. Este estudio se adentra en el ADN de dos de esas bacterias amantes de la sal para entender cómo sobreviven en ambientes extremos y para clarificar dónde encajan realmente en el árbol de la vida. Al comparar sus genomas en detalle, los investigadores muestran que lo que se consideraba especies bacterianas distintas en realidad son el mismo tipo de organismo, y descubren los trucos moleculares que estos microbios usan para afrontar un estrés salino intenso.
Por qué importan estos amantes de la sal
Las bacterias en el centro de este trabajo fueron nombradas originalmente Bacillus daqingensis y Alkalicoccus luteus. Ambas se aislaron de ambientes salinos y alcalinos como lagos sódicos y suelos salinos, donde la mayor parte de la vida tiene dificultades. Los científicos sospechaban que Bacillus daqingensis podría pertenecer en realidad al género Alkalicoccus, pero faltaba su secuencia genómica completa, lo que dejaba su estatus oficial en suspenso. Al secuenciar y analizar los genomas completos de estos microbios y compararlos con especies relacionadas, los autores se propusieron resolver este rompecabezas taxonómico y, al mismo tiempo, aprender cómo los miembros del género Alkalicoccus pueden sobrevivir en condiciones tan duras.
Leer y comparar genomas microbianos
El equipo cultivó las bacterias en el laboratorio, extrajo su ADN y lo secuenció utilizando métodos de alto rendimiento. Luego ensamblaron los millones de pequeños fragmentos de ADN en mapas genómicos casi completos y comprobaron su calidad. Tanto Bacillus daqingensis como Alkalicoccus luteus resultaron tener genomas de tamaño similar, de alrededor de 3,4 a 3,5 millones de pares de bases, con contenido genético casi idéntico y una completitud muy alta. Un marcador genético clave, conocido como gen 16S rRNA, fue esencialmente el mismo en ambos organismos: una comparación mostró un 99,8 por ciento de identidad con mediciones previas en laboratorio y, crucialmente, las secuencias 16S de las dos cepas coincidieron al 100 por ciento entre sí.
Descifrar la supervivencia ante la sal y el estrés
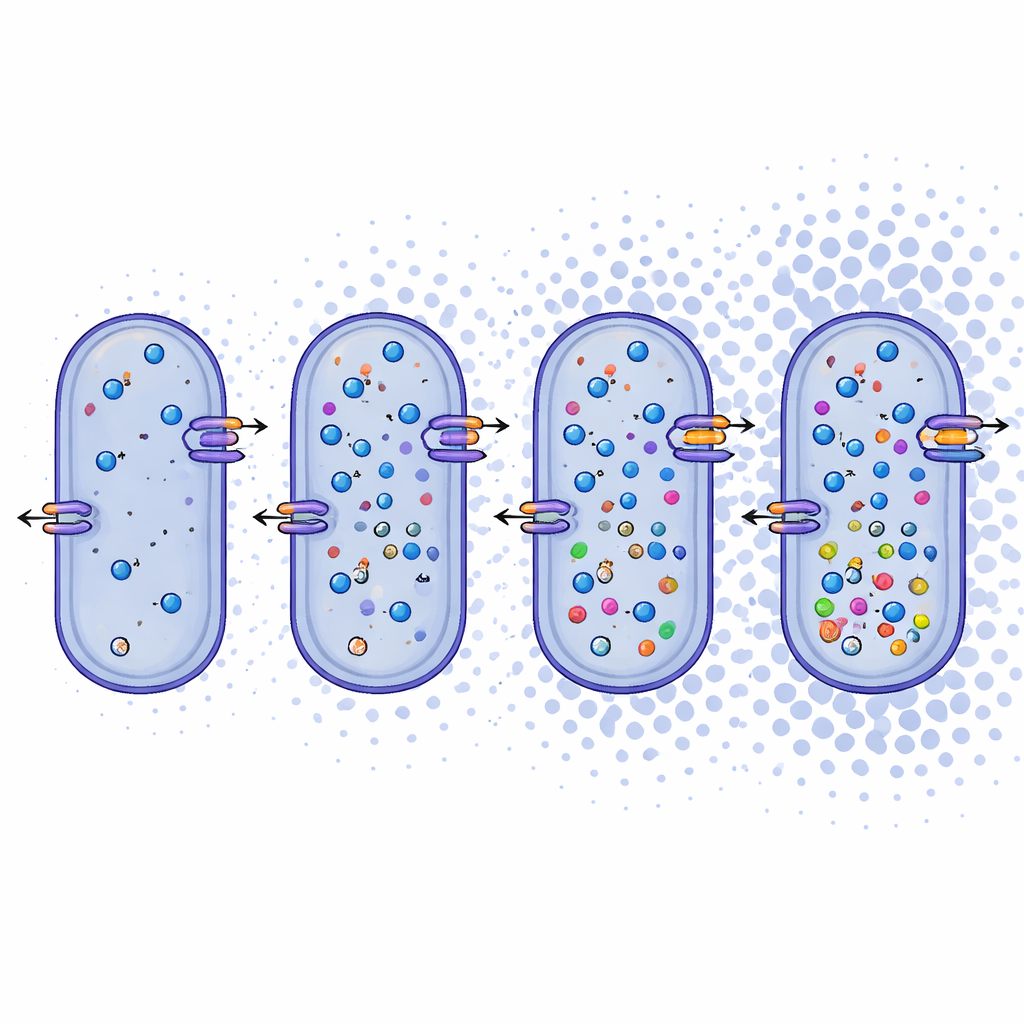
Más allá de los nombres, los investigadores examinaron lo que los genomas revelan sobre cómo estos microbios se ganan la vida. Encontraron que Bacillus daqingensis y todas las especies de Alkalicoccus analizadas comparten rutas metabólicas centrales, incluidas las vías estándar para la degradación de azúcares y un ciclo modificado llamado desvío de la glicoxilato que ayuda a conservar carbono bajo estrés. Lo más llamativo es que los genomas contienen un rico conjunto de herramientas para afrontar altas concentraciones de sal. Las bacterias parecen usar dos tácticas complementarias: sistemas de “sal-adentro” que mueven iones inorgánicos como sodio y potasio a través de la membrana celular, y sistemas de “sal-fuera” que sintetizan o importan pequeñas moléculas orgánicas, como betaína, ectoína y ciertos aminoácidos, que actúan como amortiguadores internos contra la deshidratación. Genes para transportadores iónicos, antiportadores y la biosíntesis de estos solutos compatibles están presentes en todo el género, lo que apunta a una respuesta osmótica robusta y flexible.
Probar quién es quién
Para resolver la cuestión taxonómica, los autores compararon genomas completos usando varios criterios numéricos que son ahora estándar en la sistemática microbiana. La identidad de nucleótidos promedio (ANI) mide cuán similares son las secuencias de ADN a lo largo del genoma, mientras que la identidad promedio de aminoácidos (AAI) hace lo mismo a nivel de proteínas. Entre Bacillus daqingensis y Alkalicoccus luteus, la ANI alcanzó el 98,2 por ciento y la AAI el 98,5 por ciento, muy por encima de los umbrales habituales usados para definir la misma especie e incluso el mismo género. Los árboles filogenéticos construidos a partir de muchos genes, junto con comparaciones de grupos de proteínas compartidas, mostraron que estas dos cepas se agrupan estrechamente y comparten más grupos de genes entre sí que con cualquier otra especie de Alkalicoccus. Rasgos tradicionales como la forma celular, los perfiles de ácidos grasos y las reacciones bioquímicas clave también fueron esencialmente idénticos entre ellas.
Qué significa esto para los nombres microbianos
Reuniendo todas las líneas de evidencia, el estudio concluye que Bacillus daqingensis no representa un tipo distinto de bacteria. En cambio, pertenece al género Alkalicoccus y es la misma especie que Alkalicoccus luteus, previamente conocida como Bacillus luteus. Los autores proponen formalmente la nueva combinación Alkalicoccus daqingensis y la tratan, junto con el nombre Bacillus anterior, como sinónimos posteriores de Bacillus luteus/Alkalicoccus luteus. Para los no especialistas, la conclusión es que la secuenciación genómica cuidadosa puede revelar cuándo se están usando etiquetas diferentes para microbios esencialmente iguales, ayudando a aclarar el sistema de nombres. Al mismo tiempo, el trabajo pone de manifiesto cómo estas bacterias amantes de la sal dependen de una combinación de bombas de iones y moléculas protectoras para sobrevivir en ambientes que de otro modo serían demasiado salinos para la vida.
Cita: Narsing Rao, M.P., Wang, Kk., Zhu, Ky. et al. Genome sequencing of Bacillus daqingensis and Alkalicoccus luteus reveals taxonomic insights and adaptive mechanisms. Sci Rep 16, 9720 (2026). https://doi.org/10.1038/s41598-026-38640-2
Palabras clave: bacterias halófilas, secuenciación del genoma, taxonomía microbiana, adaptación al estrés salino, Alkalicoccus luteus