Clear Sky Science · es
Edición del genoma en especies de Dictyostelia permite genética funcional comparativa de amebas sociales
Cómo se unen las células individuales
La mayor parte del tiempo, las amebas son solitarias y diminutas que se desplazan por el suelo alimentándose de bacterias. Sin embargo, algunas de ellas, llamadas amebas sociales, pueden agruparse de forma repentina para formar un cuerpo multicelular con una primitiva «cabeza» y «tallo». Este estilo de vida cambiante ofrece a los científicos una ventana poco común sobre cómo las células simples aprenden a cooperar y a especializarse, pasos clave en la evolución de la vida compleja. El nuevo estudio describe un conjunto de herramientas de edición del genoma que finalmente permite a los investigadores investigar estos comportamientos no solo en la especie favorita de laboratorio, sino en varias especies de amebas distantes.
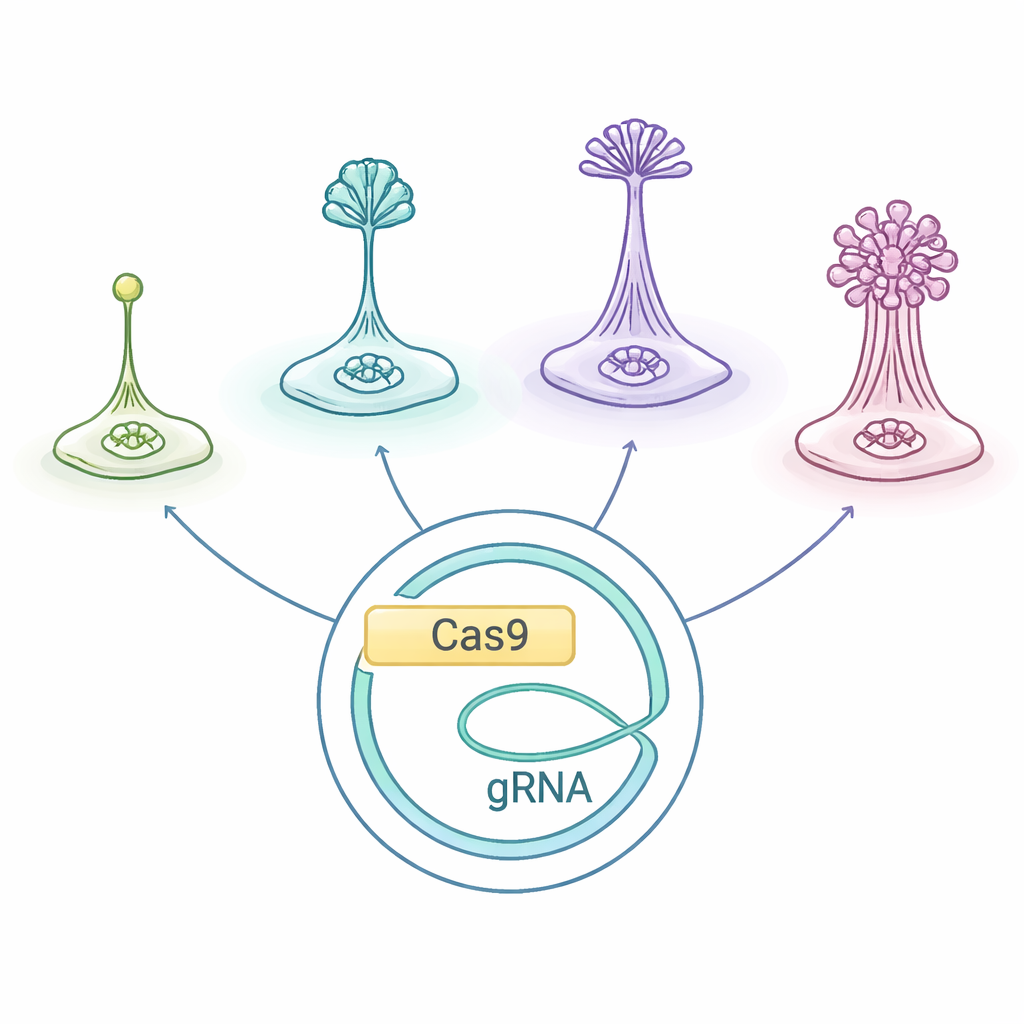
Criaturas diminutas con vidas sociales intensas
Las amebas sociales, agrupadas como Dictyostelia, viven como células individuales cuando el alimento es abundante. Cuando se quedan sin alimento, comienzan a enviar señales químicas de alarma y se desplazan unas hacia otras, reuniéndose en un montículo que construye un pequeño “cuerpo fructífero”: una columna de células de tallo sacrificadas que elevan esporas resistentes en el aire. Diferentes linajes de Dictyostelia construyen estas estructuras de maneras distintas y con conjuntos distintos de tipos celulares, lo que los convierte en un laboratorio natural para preguntar cómo evolucionan los cuerpos multicelulares y la división del trabajo.
Una especie modelo no bastaba
Hasta ahora, casi todo el trabajo molecular se centraba en una sola especie, Dictyostelium discoideum, porque sus genes son relativamente fáciles de modificar. Eso dejó a más de cien especies conocidas —algunas que representan ramas más tempranas del árbol familiar de los Dictyostelia— mayormente inexploradas. Estas especies pasadas por alto tienen historias de vida, sistemas de señalización y planes corporales distintos. Para entender cómo cambió la multicelularidad a lo largo del tiempo, los científicos necesitan manipular los mismos genes en muchas de estas especies y comparar los resultados lado a lado.
Llevando CRISPR a una familia diversa de amebas
Los investigadores adaptaron un sistema de edición de genes CRISPR/Cas9 originalmente optimizado para D. discoideum y comprobaron si funcionaba a lo largo del árbol de los Dictyostelia, incluyendo especies de ramas tempranas y otras más derivadas. Usaron un plásmido —un fragmento circular extra de ADN— que transporta las instrucciones para las “tijeras moleculares” Cas9, el ARN guía que dirige a Cas9 hacia un gen elegido y un marcador de resistencia a fármacos. Introducir este plásmido en distintas amebas permitió al equipo cortar dos genes bien estudiados, llamados stlA y pkaC, que son importantes para las señales que coordinan la agregación y la formación adecuada del cuerpo fructífero. En la ameba del suelo Polysphondylium violaceum, esta estrategia produjo de forma fiable mutantes con defectos de desarrollo claros, mostrando que el sistema adaptado puede funcionar fuera del modelo habitual.
Probando genes a través de especies
A continuación, el equipo se trasladó a especies más distantes, incluyendo Heterostelium pallidum del Grupo 2 y Cavenderia fasciculata del Grupo 1 —linajes que se separaron antes en la evolución. Usando el mismo diseño de plásmido, desactivaron el gen pkaC en ambas especies y encontraron que los mutantes no lograban agregarse ni construir cuerpos fructíferos normales, reflejando los defectos severos observados en D. discoideum. Debido a que las mutaciones CRISPR creadas por este método no dejan grandes casetes de selección, las cepas resultantes quedaron «libres de marcadores». Eso facilitó reintroducir una versión del gen procedente de D. discoideum y comprobar si podía reemplazar a la versión local. En todos los casos, el pkaC extranjero fue capaz de rescatar el paso temprano de agregación pero no el modelado posterior de un cuerpo fructífero maduro —evidencia de que el conjunto básico de señalización es compartido, mientras que el control afinado del tiempo y la posición ha evolucionado de formas específicas por especie.
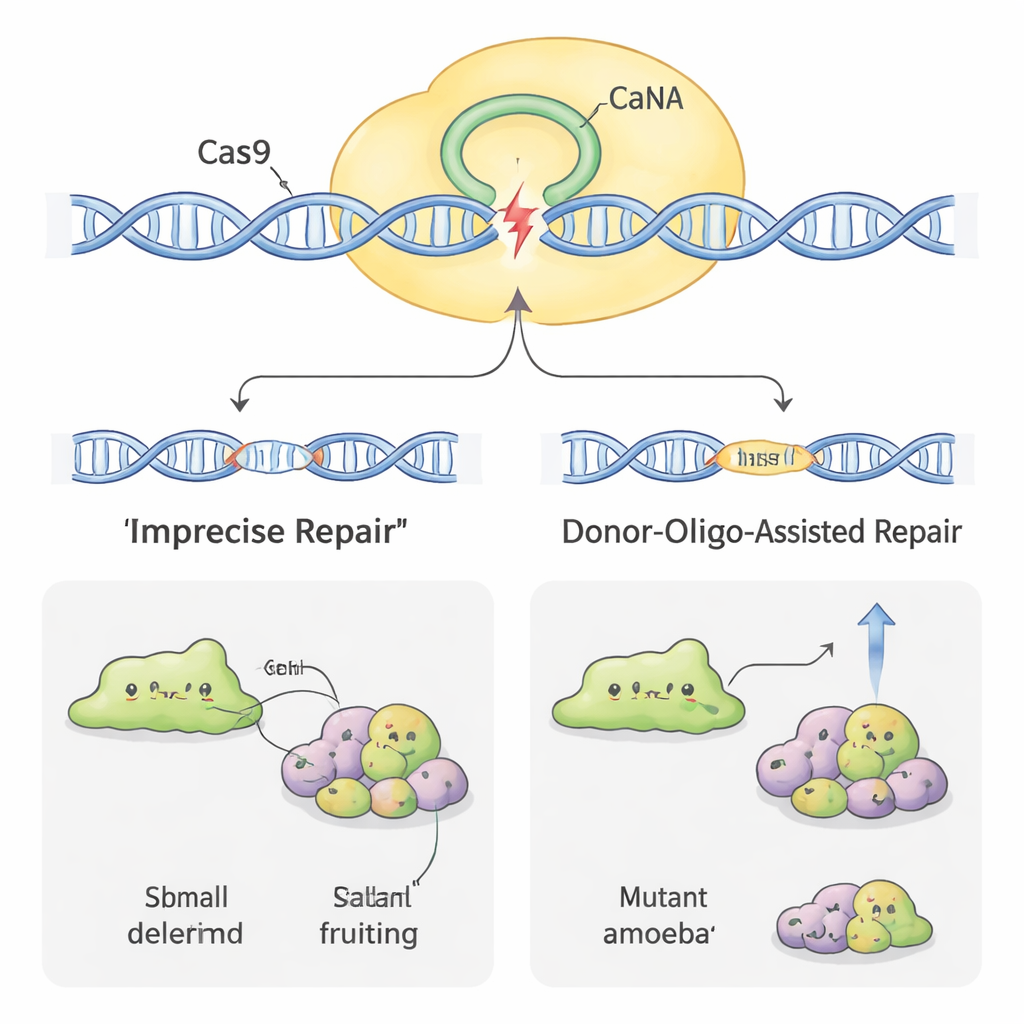
Haciendo la edición más eficiente
No todas las amebas se sometieron a la edición del genoma con la misma facilidad. En algunas especies, como H. pallidum, la tasa de éxito inicial fue muy baja. Para aumentar la eficiencia, los científicos utilizaron otro truco: añadir pequeños fragmentos de ADN “donante” junto con el plásmido CRISPR. Estos donantes llevan una pequeña etiqueta y una señal de parada flanqueada por regiones cortas coincidentes con el gen objetivo. Cuando la célula repara el corte de Cas9 usando el donante como plantilla, rompe el gen de forma reconocible. En D. discoideum, esto aumentó la proporción de clones defectuosos e incluso permitió al equipo obtener mutantes sin usar selección continua con fármacos. En la más obstinada H. pallidum, combinar ADN donante con unos días de tratamiento farmacológico incrementó las tasas de mutación casi en un orden de magnitud, transformando eventos previamente raros en algo cercano a la rutina.
Abriendo una ventana sobre los orígenes de la complejidad
Para un no especialista, los detalles de los diseños de plásmidos y las plantillas de reparación pueden sonar técnicos, pero el beneficio es amplio: un conjunto de herramientas CRISPR flexible que funciona en varias ramas del árbol familiar de las amebas sociales. Con él, los científicos pueden ahora comparar cómo el mismo gen modela el desarrollo en distintas especies y cómo cambios sutiles en la regulación génica o la estructura proteica ayudan a generar nuevos tipos celulares y planes corporales. En otras palabras, este trabajo proporciona a los investigadores las herramientas genéticas necesarias para observar, con detalle vivo, cómo la evolución modificó organismos unicelulares para construir sociedades multicelulares cooperativas.
Cita: Oishi, S., Doi, S., Sekida, T. et al. Genome editing across Dictyostelia species enables comparative functional genetics of social amoebas. Sci Rep 16, 7457 (2026). https://doi.org/10.1038/s41598-026-38605-5
Palabras clave: amebas sociales, edición genómica CRISPR, evolución de la multicelularidad, Dictyostelium, diferenciación celular