Clear Sky Science · es
Análisis integrador del transcriptoma y secuenciación unicelular combinado con validación experimental identifica biomarcadores asociados con células T y senescencia en la sepsis
Por qué esta investigación importa para pacientes con infecciones graves
La sepsis es una reacción potencialmente mortal a la infección que puede convertir una enfermedad o lesión de rutina en una urgencia, a menudo en cuestión de horas. Los médicos aún carecen de una forma simple y fiable de identificar qué pacientes están progresando hacia el fallo orgánico, y no existen fármacos diseñados específicamente para corregir el caos inmunitario que provoca la sepsis. Este estudio explora cómo ciertas células inmunitarias, llamadas células T, y el envejecimiento de estas células podrían impulsar la sepsis, e identifica un pequeño conjunto de genes que podrían ayudar a los médicos a diagnosticar la enfermedad antes y orientar el desarrollo de nuevos tratamientos.
Sepsis: cuando las defensas del cuerpo se descontrolan
En la sepsis, el sistema inmune primero estalla en una respuesta inflamatoria intensa y después a menudo deriva hacia un peligroso apagado. Las células T, que normalmente ayudan a eliminar infecciones y a recordar exposiciones previas, disminuyen en número y pierden eficacia. Al mismo tiempo, muchas células inmunitarias muestran signos de “senescencia”: una forma de envejecimiento celular en la que las células dejan de dividirse pero continúan liberando señales inflamatorias. Los autores plantearon que si podían identificar genes vinculados tanto a las células T como a la senescencia, podrían descubrir nuevos biomarcadores que revelen quién está desarrollando sepsis y por qué algunos pacientes empeoran más rápido que otros.
Analizar la sangre a nivel de células individuales
El equipo combinó varias capas de datos procedentes de muestras de sangre de personas con y sin sepsis. Primero utilizaron datos de transcriptoma a granel (un registro de qué genes están activos) para encontrar casi 10.000 genes cuya actividad cambiaba en la sepsis. Luego, mediante secuenciación de ARN unicelular, examinaron decenas de miles de células sanguíneas individuales para identificar más de 1.300 genes alterados específicamente en las células T. Al cruzar estos conjuntos con una lista curada de 866 genes conocidos por participar en el envejecimiento celular, estrecharon la selección hasta 45 candidatos que se situaban en la intersección de sepsis, células T y senescencia. 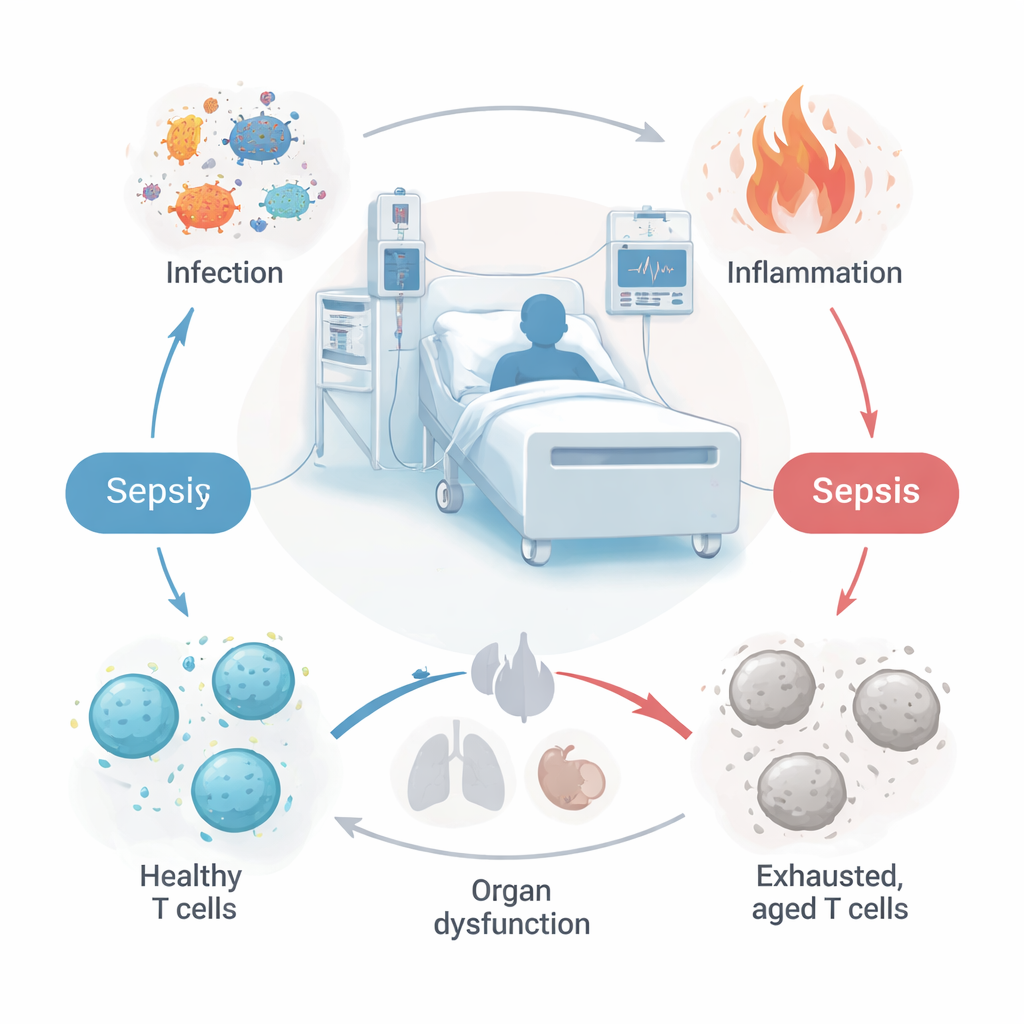
Encontrar cuatro señales genéticas clave
Para filtrar aún más esta lista, los investigadores aplicaron dos técnicas de aprendizaje automático que buscan las características más informativas en datos complejos. Estos enfoques convergieron en seis genes prometedores y, al comprobar dos conjuntos de datos de pacientes independientes, cuatro de ellos destacaron de forma consistente: PATZ1, SIN3B, BLK y MTHFD2. En datos públicos, PATZ1, SIN3B y BLK estaban reducidos en sepsis, mientras que MTHFD2 se encontraba aumentado. En un pequeño grupo de muestras clínicas evaluadas por un método sensible llamado RT-qPCR, los tres primeros genes volvieron a mostrarse claramente inferiores en la sangre de pacientes con sepsis, mientras que MTHFD2 no presentó una diferencia clara, lo que sugiere que su papel podría depender más de la función de la proteína que de su nivel de expresión.
Cómo se relacionan estos genes con el equilibrio inmunitario y fármacos potenciales
Análisis adicionales conectaron cada gen con rutas biológicas más amplias. PATZ1 se vinculó con la replicación del ADN y la señalización del receptor de células T, procesos esenciales para que las células T se multipliquen y respondan a la infección. SIN3B se asoció con un sistema de señalización lipídica que influye en la supervivencia celular y la inflamación. BLK, más conocido en enfermedades autoinmunes, se relacionó con el desarrollo de células sanguíneas y las defensas inmunitarias intestinales, incluida la producción de IgA que protege la barrera intestinal. MTHFD2 se asoció con la maquinaria de síntesis y degradación de proteínas, central para cómo las células inmunes ajustan su metabolismo bajo estrés. Cuando el equipo examinó los patrones de “infiltración” de células inmunitarias en sangre, niveles más altos de PATZ1 se correlacionaron con más células T CD8 y menos neutrófilos, un equilibrio que podría favorecer un mejor control de la infección. Usando estos cuatro genes, los investigadores construyeron una red neuronal artificial —un modelo de IA simple— que distinguió la sepsis de los casos no sépticos en dos conjuntos de datos externos con precisión casi perfecta. También emplearon una base de datos fármaco‑gen y simulaciones de acoplamiento molecular para proponer varios compuestos existentes, incluido el antibiótico latamoxef y las moléculas emetina y dihidroergotamina, como candidatos que se unen con fuerza a estos blancos. 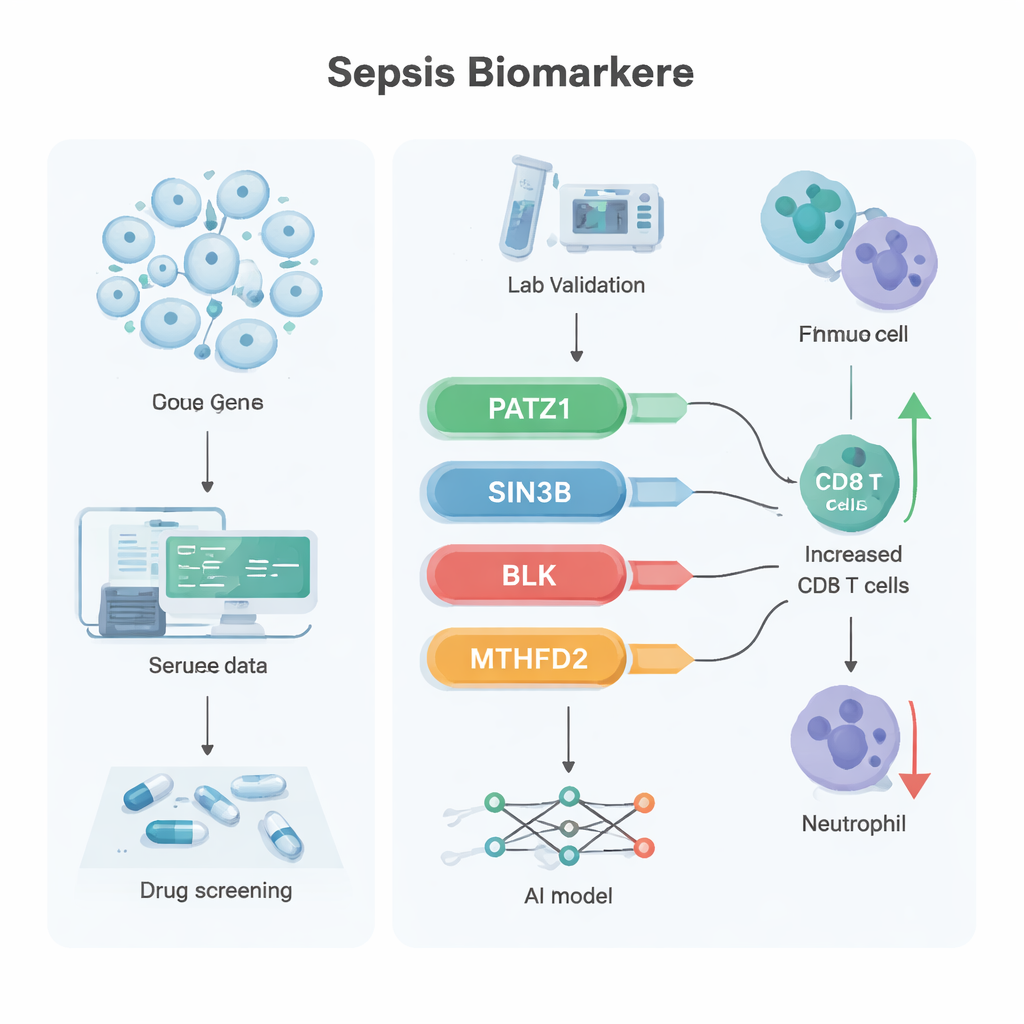
Qué podría significar esto para la atención futura
Para una persona no experta, la conclusión clave es que este estudio identifica cuatro genes que actúan como señales de alarma en células T que fallan y envejecen prematuramente durante la sepsis. En conjunto, estos genes conforman un posible panel de análisis sanguíneo que podría, en el futuro, ayudar a los médicos a diagnosticar la sepsis de forma más temprana y precisa que las herramientas actuales. También ofrecen pistas sobre cómo fallan el uso de energía y los sistemas de reparación del sistema inmune, sugiriendo nuevos enfoques para diseñar fármacos que restauren la función saludable de las células T en lugar de limitarse a reducir la inflamación. Aunque se necesitan estudios más amplios y experimentos de laboratorio antes de que cualquiera de estos hallazgos llegue a la práctica clínica, este trabajo traza un camino prometedor hacia un diagnóstico y tratamiento de la sepsis más precisos y fundamentados en la biología.
Cita: Yang, K., Hu, Y., Ma, C. et al. Integrative analysis of transcriptome and single-cell sequencing combined with experimental validation identifies biomarkers associated with T cell and senescence in sepsis. Sci Rep 16, 7109 (2026). https://doi.org/10.1038/s41598-026-38559-8
Palabras clave: biomarcadores de sepsis, células T, senescencia inmune, secuenciación unicelular, inmunometabolismo