Clear Sky Science · es
Registro no rígido automatizado y robusto de imágenes microscópicas en secciones seriadas usando PiCNoR
Ver tejidos en 3D sin perder los detalles
La biología moderna suele apoyarse en convertir finas rebanadas de tejido en vistas 3D completas de órganos y cerebros. Pero cuando cada sección microscópica se corta, tiñe e imagena, puede estirarse, rasgarse o desplazarse. Si estas secciones no se alinean correctamente, la imagen 3D resultante puede ser engañosa. Este artículo presenta un nuevo método informático llamado PiCNoR que ayuda a los científicos a alinear dichas imágenes de forma más precisa y automática, de modo que las estructuras finas en embriones y cerebros se preserven en las reconstrucciones 3D.
Por qué es tan difícil alinear las secciones
Para construir una vista 3D, los investigadores obtienen series largas de secciones ultrafinas tomadas del mismo trozo de tejido. En teoría, cada rebanada debería encajar perfectamente sobre la anterior, como cartas en una baraja bien apilada. En la realidad, cada sección puede deformarse de manera ligeramente distinta durante el corte y el teñido. Los colores pueden variar, partes pueden estirarse y las características pueden desplazarse. Los métodos tradicionales “rígidos” asumen que cada sección completa solo se traslada o rota, lo que a menudo no basta. Existen métodos más flexibles, “elásticos”, pero pueden ser lentos, requerir ajuste cuidadoso por expertos o depender fuertemente del brillo de la imagen, que puede cambiar entre secciones.
Una nueva vía: piezas locales que trabajan juntas
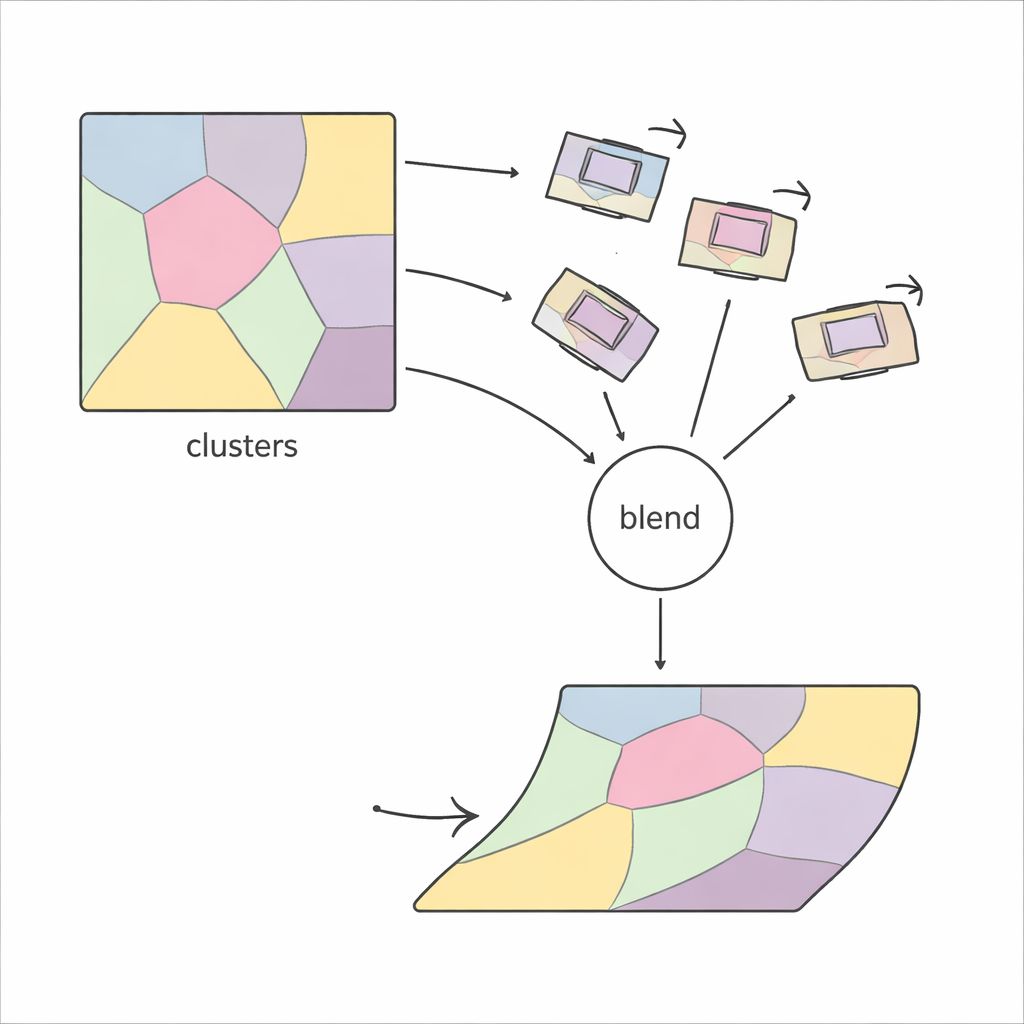
PiCNoR adopta una visión diferente, más local, del problema. En lugar de intentar deformar una imagen entera de una vez, primero divide cada sección en muchas regiones basadas en el patrón de características de la imagen. Dentro de cada región, el método encuentra puntos coincidentes entre dos secciones vecinas usando detectores de características robustos y estima cómo debe rotar y desplazarse esa región para alinearse. Estos movimientos locales se comprueban en cuanto a plausibilidad y se combinan suavemente, de modo que cada píxel de la sección recibe un movimiento que mezcla de forma continua la información de las regiones circundantes. El resultado es una alineación flexible, “no rígida”, que aun así se comporta de manera controlada y realista.
Dejar que los datos elijan la complejidad adecuada
Un desafío clave en cualquier método basado en regiones es decidir cuántas regiones usar: muy pocas y el método no puede corregir deformaciones finas; demasiadas y se vuelve inestable y lento. Los enfoques previos a menudo dependían del ensayo y error, comprobando repetidamente la calidad visual del resultado. PiCNoR evita este ajuste manual utilizando una herramienta estadística llamada criterio de información bayesiano, que equilibra automáticamente la cantidad de detalle frente al riesgo de sobreajuste. En la práctica, esto significa que el algoritmo puede decidir por sí solo cuántas regiones son necesarias para un conjunto de datos dado, sin supervisión humana, lo que ahorra tiempo y reduce sesgos.
Mantener resultados fiables y eficientes
No todo movimiento local estimado es confiable: algunos pueden verse distorsionados por ruido o por emparejamientos pobres. PiCNoR aborda esto representando cada región como un nodo en un grafo, donde las regiones vecinas se influyen entre sí. Los movimientos que parecen poco realistas en términos de rotación o desplazamiento se sustituyen por un promedio ponderado de los movimientos más fiables del entorno. Una representación matemática compacta ayuda a combinar estos movimientos de manera eficiente. Finalmente, el movimiento de cada píxel se calcula como una mezcla ponderada por probabilidad de los movimientos regionales, asegurando que las transiciones entre regiones se mantengan suaves, sin quiebres ni pliegues bruscos en el tejido.
Demostrando su eficacia con datos biológicos reales
Los investigadores probaron PiCNoR en tres conjuntos de datos muy distintos: secciones de embriones humanos de la colección de Kioto, una pila de microscopía electrónica del cordón nervioso de la mosca de la fruta y una nueva pila de microscopía óptica del hipocampo de un cerebro de rata. En estos ejemplos, PiCNoR produjo de forma consistente una mejor superposición entre secciones que los métodos rígidos estándar y que métodos no rígidos ampliamente usados. Mantuvo la continuidad de estructuras delicadas en vistas 3D y evitó las distorsiones exageradas que a veces aparecen con otras herramientas. Importante: lo hizo usando menos regiones locales que algunos competidores y con costes computacionales que siguen siendo prácticos para pilas grandes.
Qué implica esto para la microscopía 3D futura
Para los no especialistas, la conclusión es que PiCNoR ofrece una forma más fiable de convertir pilas de imágenes microscópicas 2D en reconstrucciones 3D fieles. Al elegir automáticamente cuán detallada debe ser la alineación y al protegerse contra correcciones locales erróneas, preserva las formas reales de los tejidos mientras mantiene el tiempo de procesamiento manejable. Esto facilita que biólogos y patólogos confíen en lo que ven en 3D, ya sea que estudien cómo se desarrolla un embrión o cómo se disponen las células cerebrales, y sienta las bases para análisis automáticos más precisos de conjuntos de datos microscópicos complejos.
Cita: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
Palabras clave: microscopía 3D, registro de imágenes, imagen cerebral, histología, alineación no rígida