Clear Sky Science · es
Método robusto basado en imputación para la predicción del color de ojos, cabello y piel a partir de ADN antiguo de baja cobertura
Ver los rostros detrás del ADN antiguo
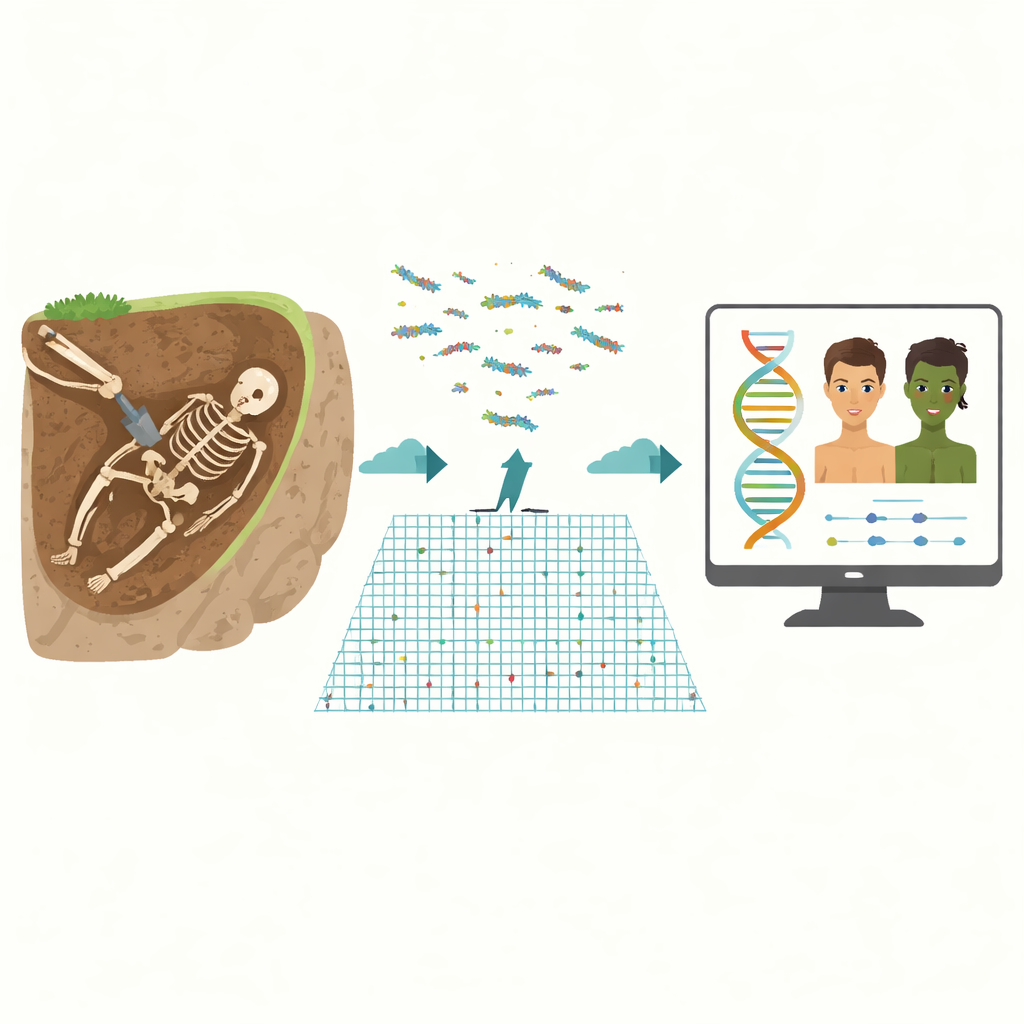
Cuando los arqueólogos desentierran huesos antiguos, rara vez saben cómo eran esas personas en vida: de qué color eran sus ojos, qué tono de piel tenían o si su cabello era negro, rubio o pelirrojo. Este estudio presenta una nueva forma de leer esos rasgos visibles a partir de ADN muy dañado, lo que permite a los científicos dibujar una imagen más humana de individuos del pasado remoto y aplicar las mismas ideas a muestras forenses degradadas hoy en día.
Por qué el ADN antiguo es tan difícil de leer
El ADN procedente de restos enterrados durante largo tiempo es un desastre biológico. El tiempo lo fragmenta en trozos diminutos e introduce daños químicos que cambian una letra genética por otra. La mayoría de los genomas antiguos se secuencian solo a "baja cobertura", lo que significa que muchas posiciones se leen una vez —o ninguna—. Herramientas forenses existentes como HIrisPlex-S, que pueden predecir el color de ojos, cabello y piel a partir de 41 marcadores clave, se diseñaron para ADN moderno y de alta calidad y esperan información fiable en ambas copias de cada marcador. Con material antiguo, esa información a menudo falta o es incierta, por lo que los métodos tradicionales fracasan o devuelven predicciones muy inestables.
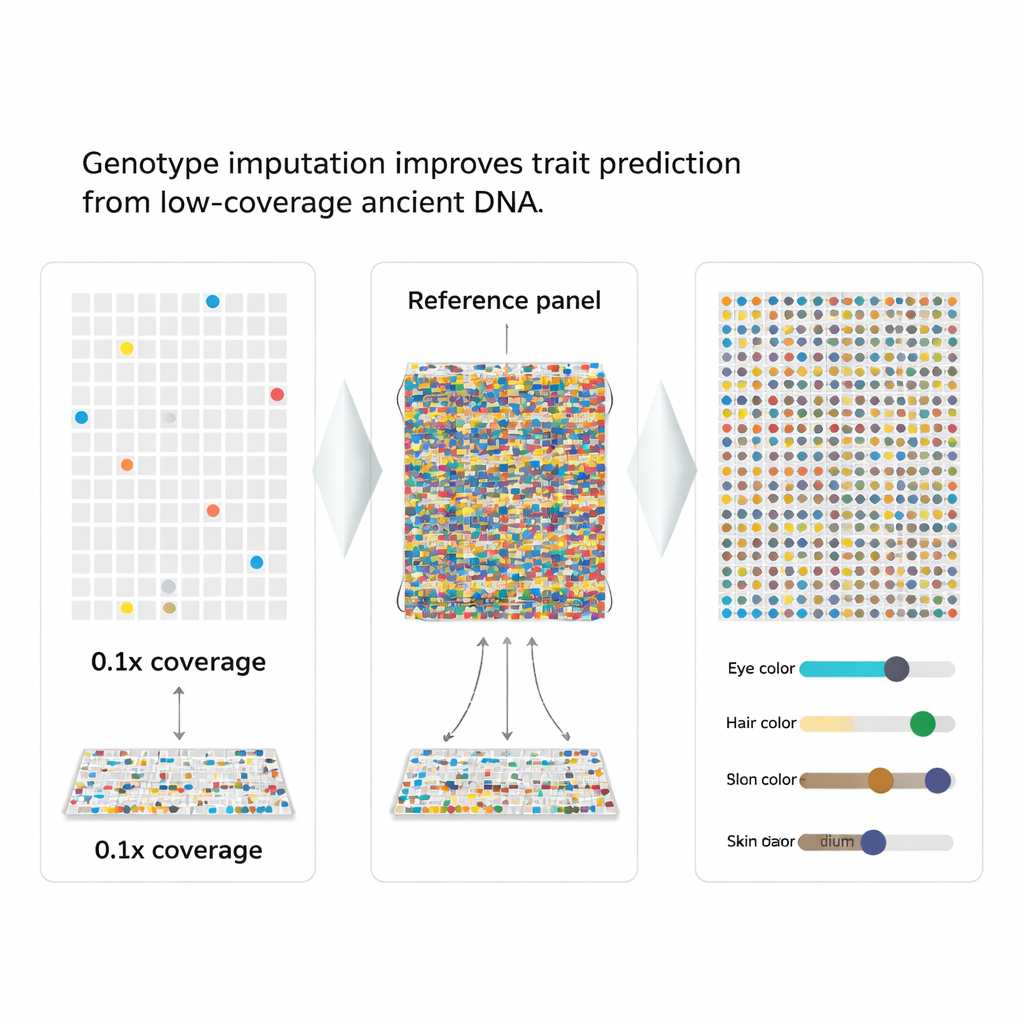
Rellenar los huecos con conjetura inteligente
Los autores recurrieron a una estrategia llamada imputación de genotipos, que utiliza patrones en un gran panel de referencia de genomas modernos para "rellenar" las piezas faltantes en uno dañado. Dado que los marcadores genéticos cercanos se heredan juntos en bloques, un patrón parcialmente observado puede indicar con fuerza las letras faltantes más probables. El equipo integró esta idea en un nuevo flujo de trabajo, aHISplex, que parte de lecturas de ADN alineadas, ejecuta software de imputación de última generación, convierte los resultados al formato exacto requerido por HIrisPlex-S y luego transforma automáticamente las probabilidades predichas en categorías claras de rasgos para ojos, cabello y piel.
Comprobando la precisión en personas modernas y antiguas
Para ver qué tan bien funciona el método, los investigadores tomaron 93 genomas modernos con rasgos conocidos y los "submuestrearon" artificialmente para imitar una cobertura muy baja, tan pobre como una décima parte de una lectura completa. Luego imputaron los marcadores faltantes y compararon los resultados con los datos reales. Incluso con solo 0,5× de cobertura, la tasa de error global para los 41 marcadores se mantuvo por debajo de aproximadamente el 2%, y los errores más graves —cambiar por completo un marcador de un estado homocigoto a su opuesto— fueron extremadamente raros. La mayoría de las predicciones de color de ojos y cabello coincidieron con los rasgos conocidos, y las predicciones de color de piel se desplazaron solo ligeramente entre categorías de tono adyacentes.
Desafíos con rasgos raros y diversidad antigua
No todos los rasgos son igualmente fáciles de recuperar. El pelo rojo, causado en gran medida por variantes raras en el gen MC1R, resultó más difícil: el método casi nunca inventó pelo rojo donde no existía, pero a veces pasó por alto a individuos pelirrojos reales, asignándoles rubio o rubio oscuro en su lugar. El equipo también aplicó su flujo de trabajo a 31 individuos genuinamente antiguos con genomas de alta calidad y luego simuló baja cobertura e imputó de nuevo. De nuevo, la precisión global fue alta, con alrededor del 95% de los marcadores clave imputados correctamente a 0,5× de cobertura. Sin embargo, un pequeño conjunto de combinaciones marcador–muestra, especialmente en individuos cuyos antecedentes genéticos están poco representados en los paneles de referencia modernos, mostró un error sistemáticamente mayor. Este "sesgo de referencia" podría, por ejemplo, transformar un genotipo de ojos azules en una predicción de ojos marrones en una fracción de las ejecuciones.
Enfocar con más nitidez a las personas antiguas
A pesar de estas advertencias, el estudio demuestra que ahora es práctico predecir el color de ojos, cabello y piel de muchos individuos antiguos incluso cuando su ADN es extremadamente escaso, con solo 0,1–0,5× de cobertura. La nueva canalización aHISplex automatiza los pasos complejos entre los archivos de secuenciación crudos y llamadas de rasgos accesibles, haciéndola apta para laboratorios de arqueogenética y potencialmente para equipos forenses que manejan muestras degradadas. A medida que los paneles de referencia se amplíen para incluir genomas más diversos y antiguos, y a medida que los científicos descubran marcadores adicionales vinculados a rasgos, este enfoque debería volverse aún más preciso —ayudándonos a pasar de huesos y secuencias de ADN anónimos a retratos vivos y éticamente considerados de personas que vivieron hace mucho tiempo.
Cita: Maróti, Z., Nyerki, E., Török, T. et al. Robust imputation-based method for eye, hair, and skin colour prediction from low-coverage ancient DNA. Sci Rep 16, 7371 (2026). https://doi.org/10.1038/s41598-026-38372-3
Palabras clave: ADN antiguo, fenotipado forense, ojos cabello piel, imputación de genotipos, arqueogenética