Clear Sky Science · es
Perfiles de microbiota intestinal y resistoma de expatriados suizos en África revelados por metagenómica Nanopore
Por qué cambian tus microbios intestinales cuando vives en el extranjero
Mucha gente pasa meses o años viviendo fuera de su país, con frecuencia en lugares donde las bacterias resistentes a antibióticos son comunes. Este estudio plantea una pregunta sencilla pero importante: cuando expatriados suizos residen en países africanos con alta carga de infecciones multirresistentes, ¿cambia la comunidad de microbios y los genes de resistencia en su intestino de maneras que puedan afectar su salud y la propagación más amplia de la resistencia antimicrobiana?
La comunidad invisible dentro de nosotros
Nuestros intestinos albergan billones de microbios, en su mayoría bacterias, que ayudan a digerir los alimentos, entrenan al sistema inmunitario y mantienen a raya a los gérmenes dañinos. Junto a estos microbios útiles está el «resistoma», la colección de genes que confieren resistencia a los antibióticos. Incluso las personas sanas portan muchos de esos genes. Cuando individuos se mudan o viajan por regiones donde las bacterias multirresistentes son frecuentes, pueden adquirir silenciosamente nuevos genes de resistencia y los elementos de ADN móviles, llamados plásmidos, que los diseminan. Entender cómo ocurre esto es vital para controlar la resistencia antibiótica a nivel global.
Comparando expatriados en Europa y en África
Los investigadores analizaron muestras de heces de 72 expatriados suizos sanos que regresaban a Suiza: 39 habían vivido en países africanos y 33 en otros países europeos. En lugar de cultivar bacterias en el laboratorio, emplearon una tecnología de secuenciación de lecturas largas denominada metagenómica shotgun Nanopore, que lee todo el material genético de una muestra de una sola vez. Esto les permitió mapear qué bacterias estaban presentes (la microbiota) y qué genes de resistencia y plásmidos portaban (el resistoma y el plasmidoma). Cada muestra se secuenció dos veces para mayor fiabilidad y se usó software avanzado para identificar grupos bacterianos y genes de resistencia y ensamblar fragmentos genómicos más largos a partir del ADN mixto.
Sorprendente estabilidad de los microbios intestinales
A pesar de que más personas del grupo africano estaban colonizadas con bacterias intestinales multirresistentes en pruebas previas basadas en cultivos, la composición global de su microbiota intestinal era notablemente similar a la de los expatriados que habían vivido en Europa. Las medidas de diversidad —cuántos tipos distintos de bacterias estaban presentes y cuán equilibrada era su representación— no difirieron por continente, y los análisis estadísticos no mostraron una agrupación clara de muestras de África frente a Europa. En ambos grupos dominaron residentes intestinales habituales como Blautia, Faecalibacterium y Bacteroides, lo que sugiere que la residencia prolongada en el extranjero no necesariamente rehace la comunidad bacteriana core en adultos sanos.
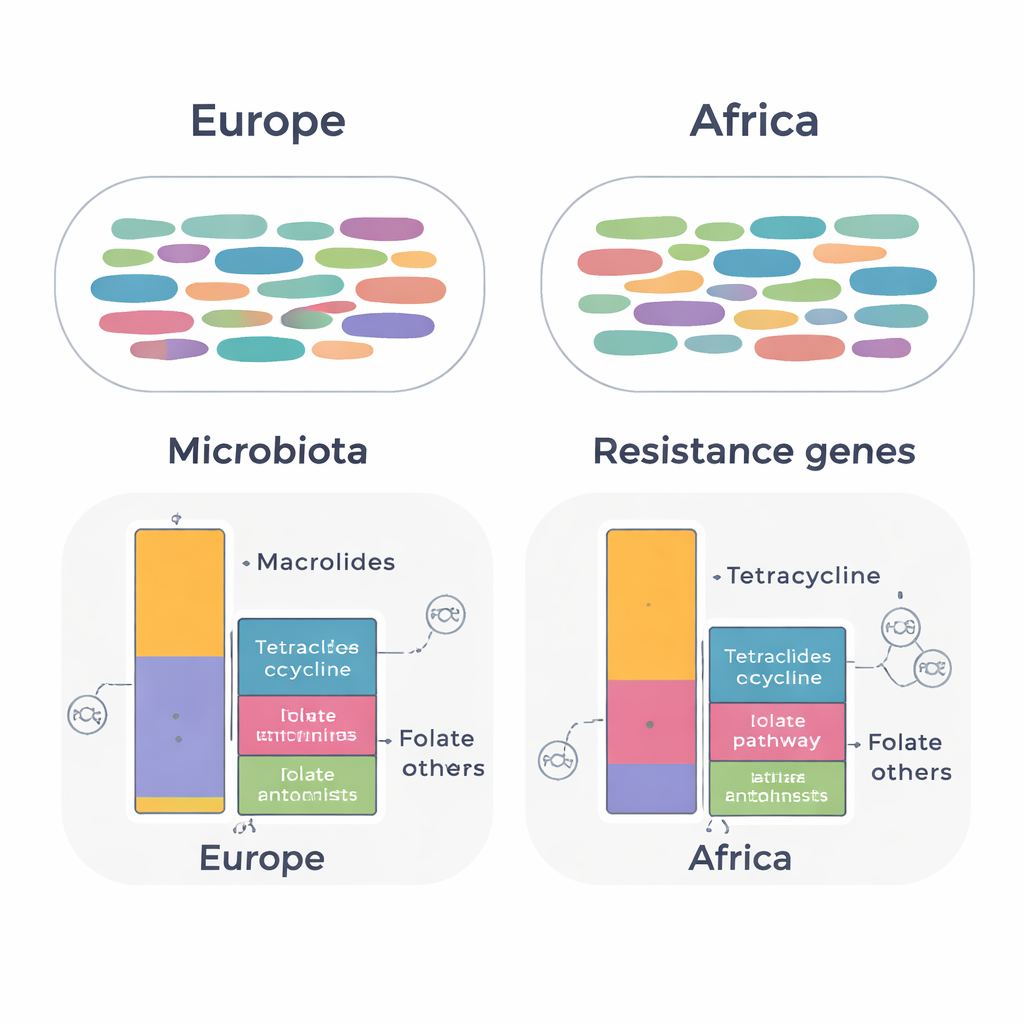
Los genes de resistencia y el ADN móvil cuentan otra historia
Cuando el equipo se centró en los genes de resistencia, emergieron diferencias más sutiles pero significativas. En todas las muestras detectaron 134 genes de resistencia distintos pertenecientes a 14 clases de antibióticos. El patrón global de genes fue en general similar entre continentes, pero los expatriados que habían vivido en África llevaban niveles más altos de genes que protegen a las bacterias frente a las tetraciclinas y frente a fármacos que actúan sobre la vía del folato (como trimetoprim‑sulfametoxazol). En contraste, los expatriados de países europeos mostraron niveles más altos de genes que confieren resistencia a macrólidos. Muchos de estos genes estaban ligados a bacterias intestinales comunes, incluidos Ruminococcoides, Bifidobacterium y Bacteroides. Se detectaron genes clínicamente importantes, como blaCTX-M-15, que pueden inactivar cefalosporinas avanzadas, en Escherichia coli de ambos grupos.
Plásmidos como vehículos globales de la resistencia
El estudio también rastreó plásmidos: pequeños círculos de ADN a menudo transferibles que transportan genes de resistencia entre bacterias y a través de distintos entornos. Gracias a las lecturas largas de ADN, los investigadores pudieron en ocasiones ver genes de resistencia y marcadores de «replicón» plasmídico en el mismo fragmento de ADN ensamblado, confirmando que viajaban juntos. Identificaron 46 tipos de plásmidos diferentes, algunos únicos de cada continente y otros compartidos. Cabe destacar que ciertos plásmidos portaban múltiples genes de resistencia y se asemejaban a plásmidos conocidos procedentes de humanos, animales, alimentos y aguas residuales en distintas partes del mundo. Un tipo de plásmido comúnmente asociado a Enterococcus y hallado en pollo y aguas residuales fue más frecuente en heces de expatriados en África, subrayando cómo la comida, los animales y el entorno pueden contribuir a lo que acaba en nuestro intestino.
Qué significa esto para la vida cotidiana y la salud pública
Para un lector general, el mensaje clave es que simplemente vivir en una región de alto riesgo no parece cambiar radicalmente qué bacterias intestinales albergas, pero sí puede ajustar la mezcla de genes de resistencia a antibióticos y de los elementos de ADN móviles que los diseminan. Estos cambios ocultos, moldeados en parte por los patrones locales de uso de antibióticos, pueden ser relevantes para infecciones futuras y para cómo los rasgos de resistencia se mueven entre personas, animales y el medio ambiente. El trabajo también demuestra que la secuenciación portátil de lecturas largas puede actuar como una herramienta de aviso temprano, revelando cómo circulan genes de resistencia y plásmidos en viajeros y expatriados sanos antes de que causen enfermedad.
Cita: Campos-Madueno, E.I., Aldeia, C. & Endimiani, A. Gut microbiota and resistome profiles of Swiss expatriates in Africa revealed by Nanopore metagenomics. Sci Rep 16, 7016 (2026). https://doi.org/10.1038/s41598-026-38302-3
Palabras clave: microbioma intestinal, resistencia a antibióticos, extranjeros, plásmidos, metagenómica