Clear Sky Science · es
Resistencia antimicrobiana de Escherichia coli en ratas silvestres húngaras y caracterización de un plásmido ESBL tipo CTX-M-1
Por qué las ratas de la ciudad importan para nuestros medicamentos
La resistencia a los antibióticos suele presentarse como un problema de hospitales y granjas, pero la historia no termina ahí. Las ratas pardas que viven en nuestras ciudades y alrededor del ganado comparten silenciosamente nuestros espacios, correteando por alcantarillas, parques y establos. Este estudio desde Hungría plantea una pregunta sencilla pero importante: ¿están estos roedores cotidianos ayudando a difundir bacterias que ya no responden a fármacos importantes, y en caso afirmativo, cuán estrechamente emparentados están esos microbios con las cepas que preocupan a médicos y veterinarios?
Siguiendo pasajeros invisibles en los intestinos de las ratas
Los investigadores capturaron ratas pardas y negras en espacios públicos, industriales y granjas a lo largo de Hungría y examinaron las bacterias que habitan en su intestino grueso. En lugar de probar solo una cepa bacteriana por animal, muestrearon múltiples colonias de Escherichia coli de cada rata para captar la diversidad oculta dentro de un solo intestino. Luego expusieron estas bacterias a un panel de antibióticos de uso común para ver cuáles sobrevivían, centrándose en fármacos cuya resistencia suele estar transportada por fragmentos de ADN pequeños y móviles que pueden saltar entre microbios.
Qué bacterias resistentes llevaban las ratas
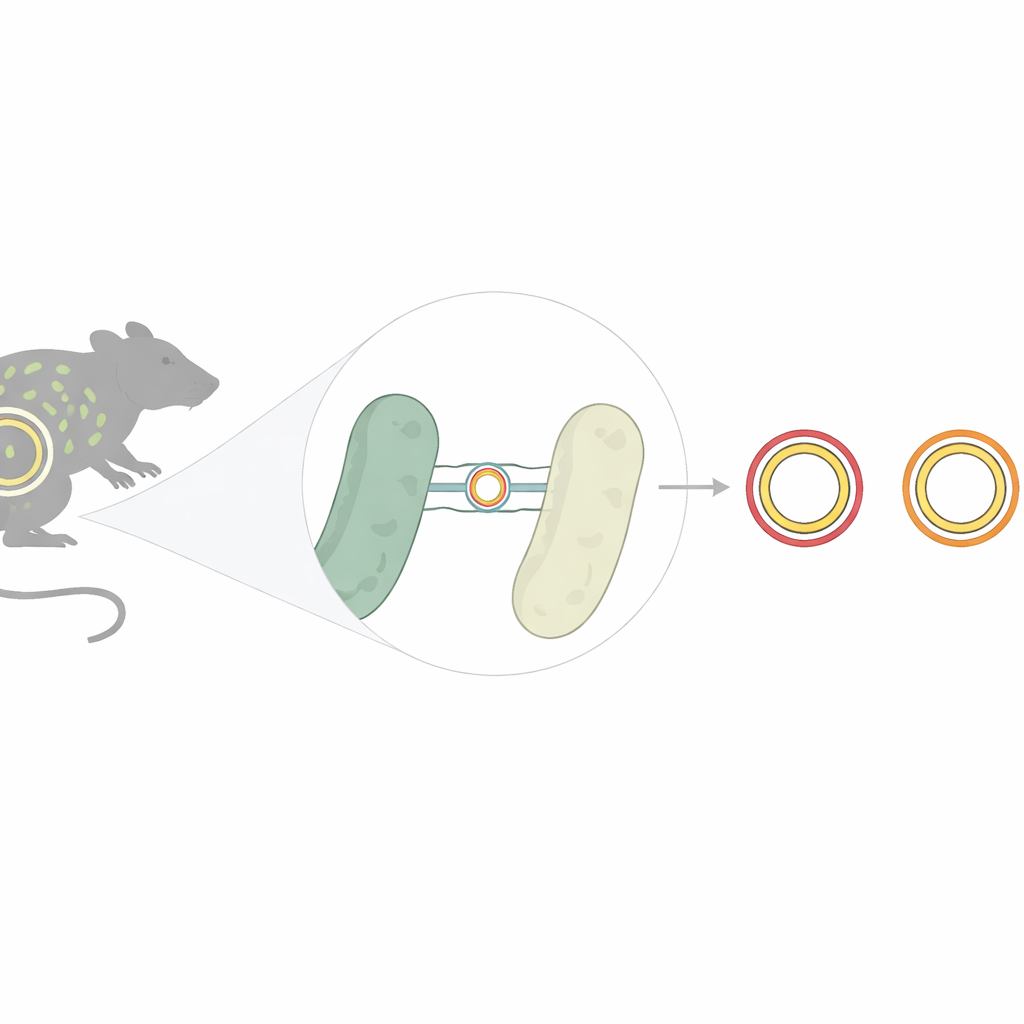
Aproximadamente una cuarta parte de las 90 ratas estudiadas portaban E. coli capaz de resistir al menos un antibiótico, y casi una de cada once albergaba cepas resistentes a varias familias de fármacos a la vez. Todas esas bacterias resistentes provenían de ratas pardas; no se encontraron en la muestra más pequeña de ratas negras. El patrón más frecuente fue la resistencia combinada a ampicilina, un fármaco parecido a la penicilina, y tetraciclina, un pilar de larga data en medicina humana y veterinaria. Las pruebas genéticas mostraron que estas resistencias solían estar vinculadas a genes conocidos que viajan en plásmidos—moléculas circulares de ADN que las bacterias comparten entre sí como diminutos pendrives, permitiendo que la resistencia se propague rápidamente en las condiciones adecuadas.
Una resistencia de alto nivel, rara pero preocupante
En una rata parda urbana, el equipo encontró algo más inquietante: una cepa de E. coli capaz de inactivar potentes cefalosporinas de tercera generación, fármacos a menudo reservados para infecciones graves. Esta capacidad procedía de un gen conocido como CTX-M-1, miembro de una familia extendida de enzimas que inactivan muchos antibióticos modernos. Mediante la combinación de secuenciación de lecturas cortas y largas, los científicos reconstruyeron el plásmido completo—de unas 92 mil bases—que portaba este gen. Al comparar su secuencia con plásmidos de E. coli y Salmonella aislados de enfermedades humanas, encontraron que era casi idéntico, difiriendo solo en unos pocos detalles menores. Esto sugiere que esencialmente el mismo elemento de resistencia circula entre animales, personas y el medio ambiente.
Cómo se relacionan las bacterias de las ratas con las cepas humanas globales
Para situar a esta E. coli procedente de una rata en el árbol genealógico más amplio, los investigadores compararon su genoma con cientos de cepas productoras de CTX-M aisladas de pacientes humanos en 50 países. La cepa de rata representó una línea previamente no descrita, pero se ubicó en el centro de varias ramas humanas importantes, bien conocidas por causar infecciones difíciles de tratar en todo el mundo. Aunque esta cepa en particular no portaba los genes de virulencia adicionales vinculados a enfermedades graves, su estrecha relación con linajes epidémicos humanos muestra que las fronteras entre fauna silvestre, animales de granja y personas son porosas cuando se trata de la evolución bacteriana.
Qué significa esto para la salud y el medio ambiente
Este trabajo dibuja un panorama matizado. Por un lado, la mayoría de las ratas húngaras no portaban las formas de resistencia más alarmantes, y la amenaza global que suponen parece similar a la reportada en otros países. Por otro lado, el hallazgo de una cepa de E. coli en rata con un plásmido CTX-M-1 similar al humano y un fondo genético nuevo subraya cómo la fauna urbana puede actuar como reservorio y escalón para genes de resistencia. Para el público general, la conclusión es que la resistencia a los antibióticos es un asunto compartido, de “One Health”: lo que ocurre en hospitales, granjas y alcantarillas urbanas está entrelazado. Mantener a las ratas y otros animales urbanos bajo vigilancia mediante un seguimiento continuo ayudará a los científicos a detectar temprano cepas resistentes emergentes y a entender mejor cómo frenar la propagación de estos genes problemáticos entre especies y ecosistemas.
Cita: Szmolka, A., Locsmándi, G., Makó, A. et al. Antimicrobial resistance of Escherichia coli in Hungarian wild rats and characterization of a CTX-M-1 type ESBL plasmid. Sci Rep 16, 8583 (2026). https://doi.org/10.1038/s41598-026-38191-6
Palabras clave: resistencia a los antibióticos, Escherichia coli, ratas urbanas, plásmidos, one health