Clear Sky Science · es
Un genoma antiguo de Erysipelothrix rhusiopathiae recuperado de restos humanos de 1.400 años en el Cáucaso septentrional
Pistas antiguas en los huesos de una niña
En un cementerio de montaña del Cáucaso septentrional, el esqueleto de una niña de 10–11 años que murió hace unos 1.400 años ha aportado una historia inesperada. Su columna dañada parecía, a primera vista, tuberculosis clásica. Pero al leer trazas microscópicas de ADN conservadas dentro de sus dientes, los científicos descubrieron otro culpable: una bacteria zoonótica poco conocida que aún infecta a personas y ganado hoy en día. Este trabajo muestra cómo el ADN antiguo puede reescribir diagnósticos del pasado lejano e iluminar la larga historia de las enfermedades modernas.
Vida y muerte en una comunidad pastoril de la Alta Edad Media
La niña, conocida por los arqueólogos como Sk213, fue enterrada en una tumba sencilla cerca de la actual localidad de Zayukovo, en el Cáucaso norte. Su pueblo, los alanos, eran comunidades agrícolas y pastoriles que criaban ganado vacuno, ovejas, cabras, caballos y cerdos. La datación por radiocarbono sitúa su muerte entre 574 y 668 d. C. Los ajuares eran escasos: solo un pendiente de bronce. Eso, junto con la tumba en un foso rudimentario, sugiere que procedía de una clase social baja, probablemente implicada en tareas cotidianas que la ponían en contacto estrecho con animales y sus productos.
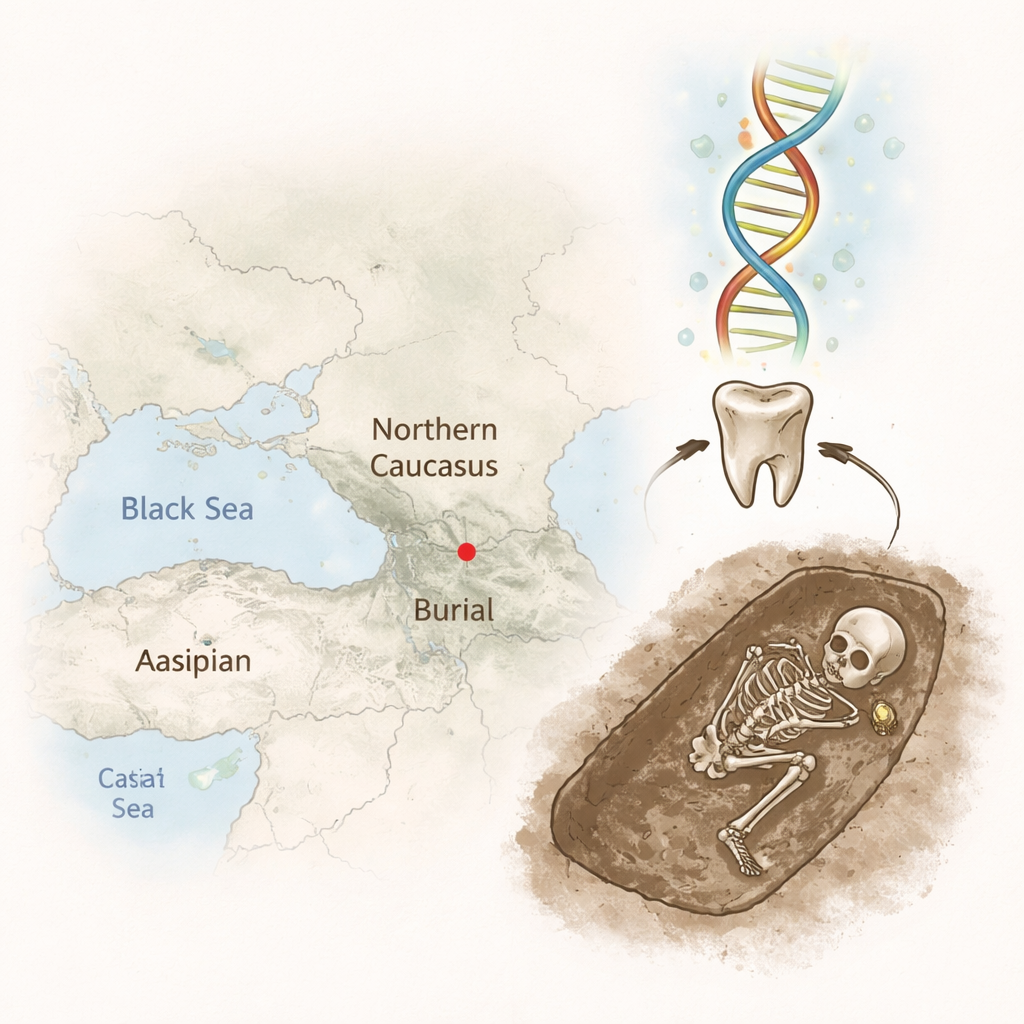
Huesos que parecían tuberculosis
El estudio detallado del esqueleto de Sk213 reveló una enfermedad dramática en la zona media de la columna y en costillas cercanas. Varias vértebras torácicas mostraban áreas donde el hueso había sido consumido, otras estaban deformadas o parcialmente destruidas, y finas capas de hueso nuevo recubrían el interior de varias costillas. Para los especialistas, este patrón se asemeja fuertemente a la tuberculosis vertebral, una infección crónica que erosiona lentamente el hueso y que puede acabar dejando invalidez o provocar la muerte. Con base en ello, un diagnóstico paleopatológico inicial apuntó hacia la tuberculosis, un azote bien conocido de las poblaciones antiguas.
Sorpresas de ADN dentro de dientes antiguos
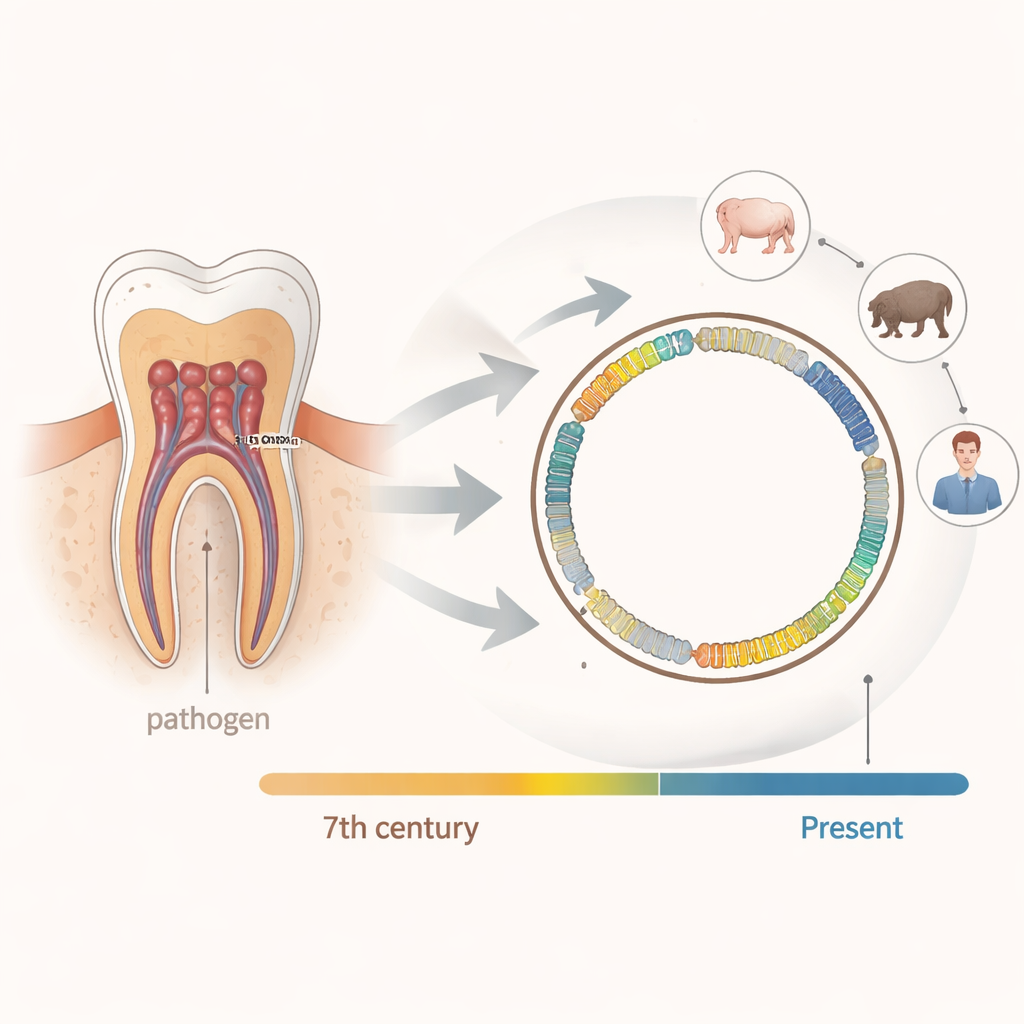
Para comprobar ese diagnóstico, el equipo taladró dos de los dientes de la niña y extrajo polvo de la pulpa interior, un tejido muy vascularizado en vida y excelente trampa para microbios presentes en la sangre. Usando secuenciación masiva, catalogaron todos los fragmentos de ADN presentes y los compararon con bases de datos modernas. Sorprendentemente, hallaron prácticamente ninguna huella genética de las bacterias de la tuberculosis. En su lugar, un gran número de secuencias coincidieron con Erysipelothrix rhusiopathiae, una bacteria que hoy causa una enfermedad llamada erisipeloide en humanos y erisipela porcina en cerdos y jabalíes.
Pruebas adicionales confirmaron que el ADN bacteriano era realmente antiguo: los fragmentos eran muy cortos y mostraban patrones de daño químico típicos de material centenario. La misma cepa apareció de forma independiente en ambos dientes, lo que indica que este microbio circuló por el torrente sanguíneo de la niña mientras estaba viva, en lugar de ser un contaminante posterior del suelo. En pacientes modernos, encontrar esta bacteria en la sangre se asocia con una infección sistémica grave, a veces letal.
Una línea de larga duración que une humanos y cerdos
Utilizando los fragmentos de ADN antiguo, los investigadores reconstruyeron un genoma bacteriano casi completo, al que denominaron ERA_01. Luego compararon ERA_01 con más de 500 genomas modernos del mismo grupo bacteriano, muchos aislados de cerdos y jabalíes de todo el mundo. ERA_01 se situó claramente dentro de una rama principal que hoy domina en Europa y Asia. Sus parientes más cercanos conocidos son cepas recientes de jabalíes en Suecia y de cerdos de granja en Europa, lo que sugiere que esta línea patógena ha circulado en animales —y ocasionalmente ha saltado a humanos— durante al menos 1.400 años.
Genéticamente, ERA_01 portaba la mayoría de los mismos genes que hacen virulentas a las cepas modernas, incluido un importante proteína de superficie que ayuda a la bacteria a adherirse a los tejidos del huésped y a evitar ser fagocitada por las células inmunitarias. También mostraba indicios genéticos de resistencia a la vancomicina, un antibiótico potente, lo que demuestra que este rasgo precede con mucho al uso moderno de fármacos. Diferencias en un grupo de genes que definen los “serotipos” sugieren que la cepa antigua pudo haber sido típica de animales silvestres, coherente con una infección por contacto con jabalíes o cerdos cazados o pastoreados.
Replantear enfermedades antiguas con herramientas nuevas
La columna dañada de Sk213 probablemente refleja aún una infección grave y prolongada, y la tuberculosis u otras bacterias relacionadas también pudieron estar presentes. Pero la abundancia de ADN de E. rhusiopathiae en sus dientes, combinada con informes clínicos modernos de esta bacteria atacando huesos y vértebras, hace probable que el erisipeloide —en solitario o en combinación con otras infecciones— desempeñara un papel importante en su enfermedad y muerte prematura. En términos más generales, este estudio demuestra cómo el ADN antiguo puede revelar actores ocultos en las enfermedades del pasado y muestra que algunos patógenos zoonóticos que afectan hoy a agricultores y trabajadores de mataderos han acompañado a las sociedades pastoriles humanas al menos desde los primeros siglos de la Edad Media.
Cita: Kritsky, A.A., Berezina, N.Y., Ivanova, A.O. et al. An ancient Erysipelothrix rhusiopathiae genome recovered from 1400-year-old human remains in the Northern Caucasus. Sci Rep 16, 7097 (2026). https://doi.org/10.1038/s41598-026-37742-1
Palabras clave: ADN antiguo, enfermedad zoonótica, erisipeloide, paleopatología, Cáucaso medieval