Clear Sky Science · es
Un marco adaptable a la estructura genómica para la estimación de endogamia basada en ROH en Penaeus vannamei
Por qué los árboles genealógicos de los camarones importan para tu plato
Las granjas modernas de camarón suministran gran parte de los mariscos del mundo, pero reproducir sistemáticamente las mismas líneas familiares puede erosionar silenciosamente su salud. Cuando emparentados cercanos se cruzan, genes perjudiciales ocultos pueden emparejarse, reduciendo el crecimiento, la supervivencia y la resistencia a enfermedades. Este estudio plantea una pregunta aparentemente simple con grandes implicaciones para la acuicultura global: ¿cómo podemos medir la endogamia en camarones de granja con suficiente precisión para mantener los lotes sanos y productivos?
Huellas genéticas ocultas de la endogamia
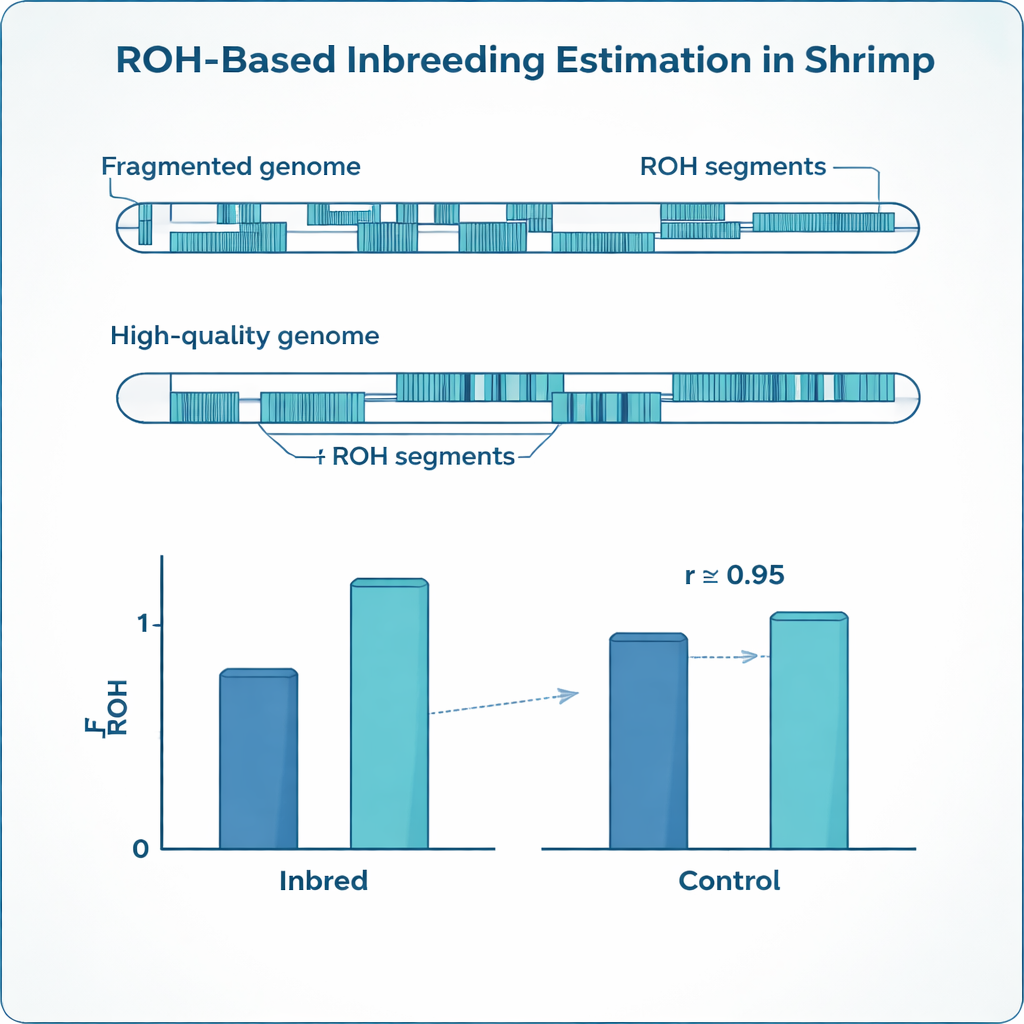
La endogamia deja huellas distintivas en el ADN. En lugar de portar dos versiones ligeramente distintas de muchos genes, los animales endogámicos tienden a tener tramos largos donde ambas copias son idénticas. Los genetistas llaman a estos tramos “corridos de homocigosidad” u ROH. Sumando cuánto del genoma de un animal cae en estos corridos, los investigadores pueden estimar su nivel de endogamia con mayor precisión que con los árboles genealógicos en papel, que a menudo están incompletos o contienen errores. Esta medida basada en ROH, conocida como FROH, se ha convertido en estándar en ganado vacuno, porcino y otros animales de producción, pero los genomas de los camarones plantean desafíos especiales que hacen que los métodos estándar sean poco fiables.
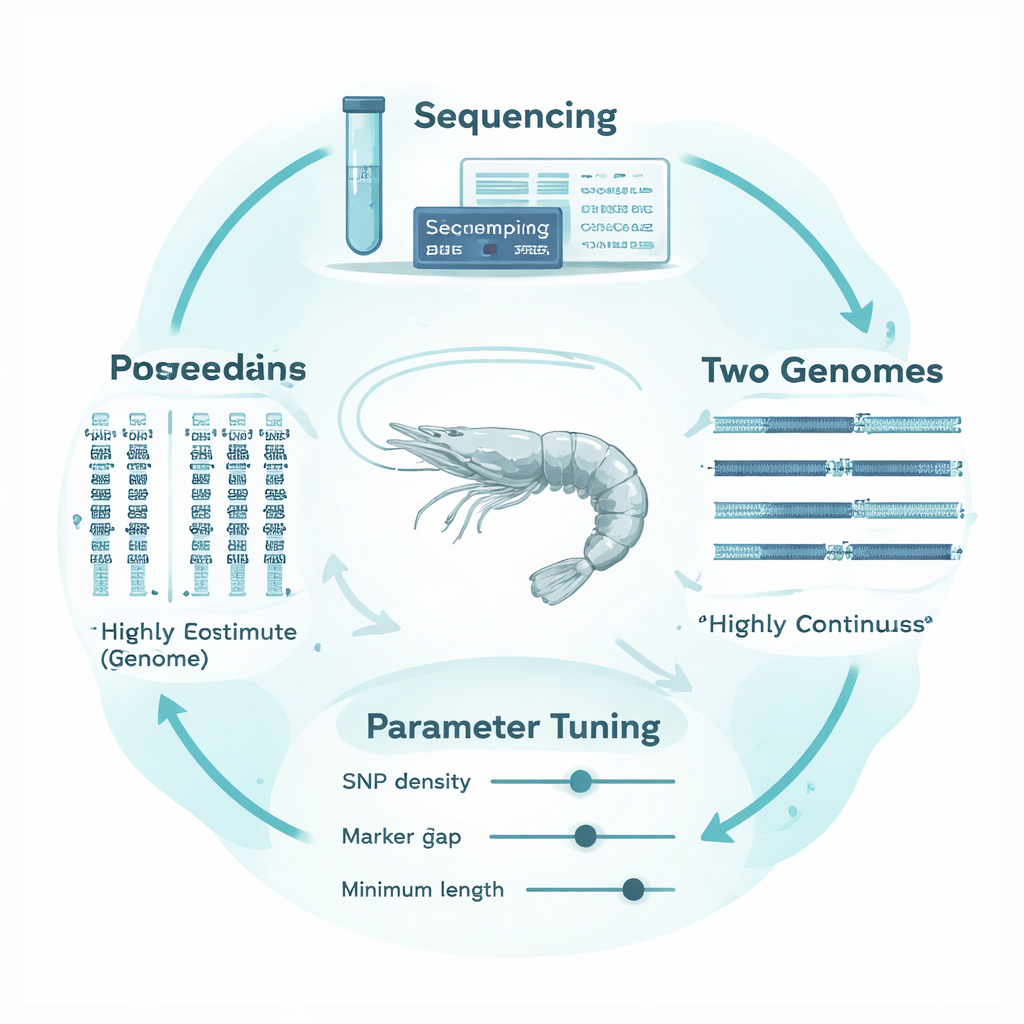
Por qué los genomas de los camarones son especialmente complicados
El camarón blanco (Penaeus vannamei), el más cultivado del mundo, tiene genomas altamente fragmentados y complejos. En lugar de largas secuencias cromosómicas continuas, muchos mapas genómicos disponibles están rotos en miles de fragmentos más pequeños, separados por huecos y regiones repetitivas. Los marcadores genéticos están distribuidos de forma desigual a lo largo de este mosaico, y la especie presenta una diversidad genética muy alta. Los métodos y ajustes de software originalmente diseñados para genomas de mamíferos bien mapeados pueden, por tanto, confundir huecos técnicos con rupturas reales de ROH, o tomar similitudes cortas y de fondo por verdaderas señales de endogamia. El resultado es un alto riesgo de estimar erróneamente cuán endogámico es realmente un camarón.
Construyendo una regla de medida que conozca el genoma
Para resolver esto, los autores diseñaron un marco “adaptable a la estructura genómica” que ajusta el análisis de ROH a las peculiaridades del ADN de los camarones. Crearon trece familias de camarones altamente endogámicas mediante apareamientos controlados, y luego secuenciaron en profundidad los genomas de cinco de estas familias más sus progenitores. De forma crucial, alinearon los mismos datos de secuenciación frente a dos genomas de referencia muy distintos: uno antiguo y fragmentado y otro más nuevo y altamente continuo. Usando la herramienta de análisis común PLINK, probaron sistemáticamente cómo ocho parámetros clave afectaban las llamadas de ROH, centrándose en tres que eran especialmente sensibles a la estructura del genoma: cuán densamente deben estar empaquetados los marcadores, cuánto espacio entre marcadores se permite dentro de un corrido y cuán largo debe ser un corrido para contarlo. Construyeron ventanas genómicas empíricas y no solapadas para rastrear el espaciado local de marcadores y los datos faltantes, y utilizaron la “cobertura genómica” de estas ventanas, junto con la estabilidad de FROH y las longitudes de ROH, como guías objetivas para elegir umbrales sensatos.
Diferentes ajustes, misma imagen de endogamia
Los ajustes optimizados resultaron ser muy distintos para los dos genomas de referencia. El genoma fragmentado requirió marcadores mucho más densos, huecos permitidos más cortos y longitudes mínimas de corrido más pequeñas que el genoma de alta calidad para evitar fragmentar los ROH verdaderos en muchos trozos pequeños. Sin embargo, tras afinar estos controles por separado, las estimaciones de endogamia de ambos referentes convergieron: la FROH media en los camarones endogámicos fue de aproximadamente 0,24 en ambos casos, coincidiendo estrechamente con el valor esperado de los cruces planificados y mostrando una fuerte concordancia entre sí. Al mismo tiempo, el genoma más continuo reveló menos segmentos de ROH pero mucho más largos, mientras que el mapa fragmentado los dividía en tramos cortos. El estudio también expuso diferencias llamativas entre hermanos de camada: incluso dentro de la misma familia, los niveles de endogamia variaron ampliamente, algo que los registros genealógicos simples no pueden captar.
Herramientas más precisas para lotes de camarón más sanos
Para los no especialistas, la conclusión es directa: medir la endogamia a partir del ADN puede ser muy preciso en camarones de cultivo, pero solo si el método respeta la estructura subyacente del genoma. Al ofrecer una receta práctica para ajustar el análisis de ROH a genomas de crustáceos fragmentados, este trabajo permite a los criadores monitorizar la endogamia animal por animal, en lugar de confiar en árboles familiares imperfectos. Eso, a su vez, puede ayudar a diseñar planes de apareamiento que mantengan la diversidad genética mientras mejoran el crecimiento y la resiliencia, apoyando una acuicultura de camarón más sostenible y ofreciendo un modelo para otras especies acuícolas que enfrentan obstáculos genómicos similares.
Cita: Zou, X., Zhou, H., Liu, M. et al. A genome-structure adaptive framework for ROH-based inbreeding estimation in Penaeus vannamei. Sci Rep 16, 6769 (2026). https://doi.org/10.1038/s41598-026-37622-8
Palabras clave: crianza de camarones, endogamia, selección genómica, corridos de homocigosidad, genética de la acuicultura