Clear Sky Science · es
Conjugación de ADN en superficies plásticas funcionalizadas para la secuenciación de moléculas individuales secuencial e iterativa
Almacenando los datos del mañana en hebras minúsculas
Imagínese hacer una copia de seguridad de sus fotos, libros o registros científicos en una forma que podría durar siglos y caber en una mota más pequeña que un grano de arena. El ADN —la misma molécula que porta nuestros genes— surge como un candidato potente para un almacenamiento de datos ultra denso y de larga duración. Este artículo explora una nueva manera de “aparcar” datos en ADN de forma segura en el interior de tubos de plástico de laboratorio comunes y volver a leerlos una y otra vez sin destruir las moléculas originales.
Un nuevo tipo de «pendrive» de datos
Los discos duros y la memoria flash actuales se desgastan, y almacenan mucha menos información por gramo de la que potencialmente puede ofrecer el ADN. Investigadores ya han mostrado cómo traducir archivos digitales a secuencias de “letras” de ADN. Pero cada vez que esas hebras se copian o secuencian, parte del material original se consume, como la tinta que se desvanece cuando fotocopias una página demasiadas veces. En este estudio, los autores transformaron el humilde tubo PCR de plástico —ya estándar en laboratorios de biología— en un dispositivo físico de almacenamiento reutilizable. Unieron químicamente hebras de ADN que portaban datos codificados a la superficie interna del tubo, de modo que el ADN queda fijado en su lugar mientras se hacen y leen repetidamente copias. 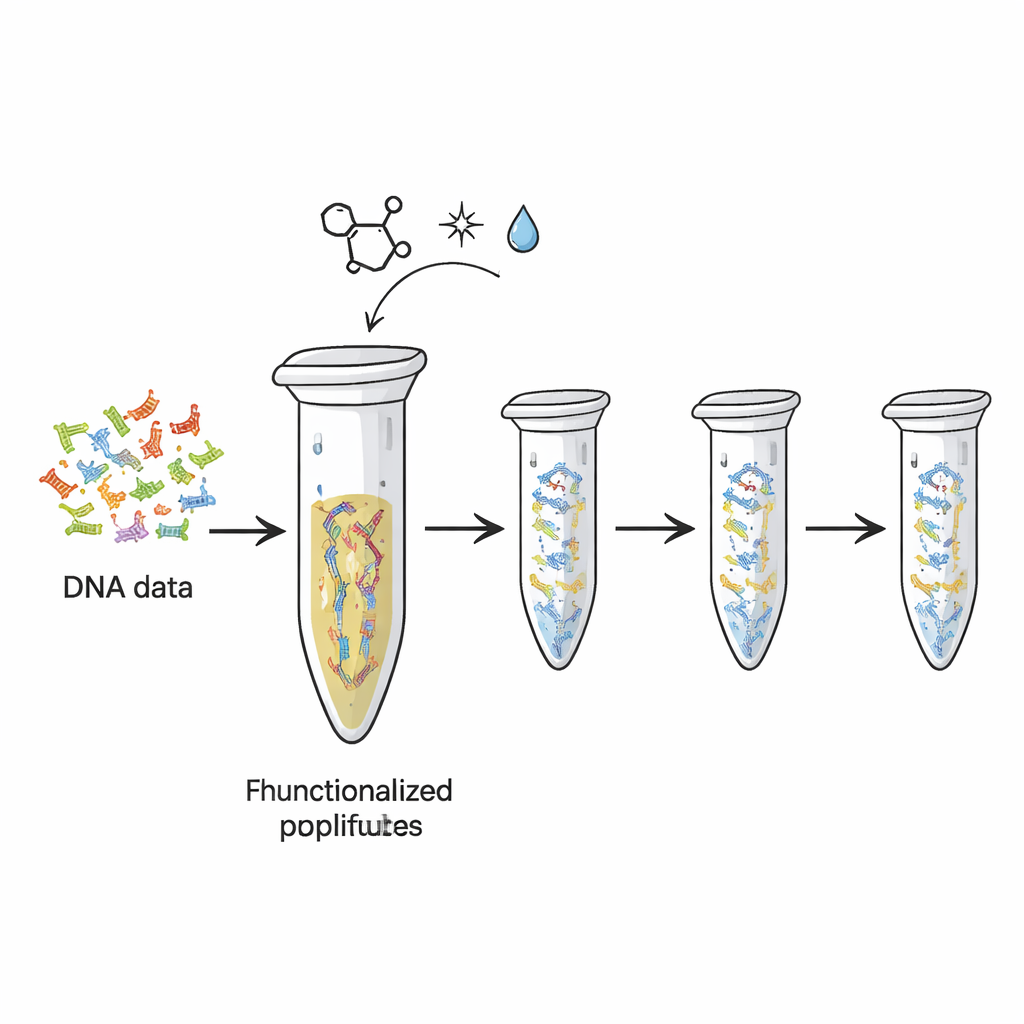
Clavando ADN en plástico con química click
El equipo se basó en un tipo de ‘química click’ altamente específica —un conjunto de reacciones valoradas por ser rápidas, fiables y suaves. Primero añadieron colas químicas especiales a los extremos de las hebras de ADN que representan distintos “archivos” de datos. Estas colas, basadas en una molécula llamada TCO, están diseñadas para unirse a grupos complementarios (MTz) que se han injertado en la superficie plástica del tubo. Cuando ambas se encuentran, forman un enlace covalente estable, pegando efectivamente el ADN al plástico. Pruebas con un fragmento de ADN de control mostraron que tras la incubación casi todo el ADN había desaparecido de la solución, lo que indica que ahora estaba inmovilizado en la pared del tubo. La plataforma podía contener del orden de cientos de femtomoles de ADN, lo que sugiere una capacidad suficiente para conjuntos de datos prácticos.
Recuperando «archivos» digitales bajo demanda
Para comprobar si ese ADN fijado en la superficie seguía comportándose como un archivo viable, los investigadores codificaron texto y otros datos en una mezcla de aproximadamente 15.000 hebras cortas de ADN, agrupadas en 18 “grupos de archivos”. Cada grupo podía copiarse selectivamente usando su propio par de cebadores —secuencias cortas de inicio que dirigen la maquinaria de copia hacia los objetivos correctos. El equipo realizó repetidamente reacciones PCR estándar en el mismo tubo, eligiendo cada vez un grupo de archivos distinto para amplificar. Tras cada ciclo, retiraban el ADN copiado, limpiaban el tubo con enzimas que digieren los productos residuales en solución y pasaban al siguiente archivo. La secuenciación por nanoporo del material copiado mostró que la mayoría de los grupos de archivos se recuperaron con alta precisión, y la contaminación cruzada de corridas anteriores se mantuvo extremadamente baja, típicamente alrededor del 1 por ciento o menos.
Buscando una forma más suave de leer
Sin embargo, había un problema: al repetir PCR en el mismo tubo hasta 18 veces, la cantidad de ADN recuperado disminuía de forma sostenida. La PCR depende de ciclos rápidos de calentamiento y enfriamiento, y los autores dedujeron que las repetidas temperaturas elevadas estaban dañando el ADN inmovilizado o su unión al plástico, aunque las pruebas de control sugerían que el ADN no se estaba simplemente lavando a la solución. Para resolver esto, recurrieron a la amplificación por recombinasa-polimerasa (RPA), un método más reciente que funciona a una única temperatura comparativamente baja, cercana a la temperatura corporal. Usando RPA en tubos nuevos recubiertos de ADN, volvieron a consultar los 18 grupos de archivos en secuencia. Esta vez, los rendimientos fueron altos —alrededor de 60 ng/µL— y no mostraron la misma tendencia a la baja. El patrón de qué hebras eran favorecidas o desfavorecidas durante la copia también coincidió estrechamente con lo observado cuando el ADN estaba libre en solución. 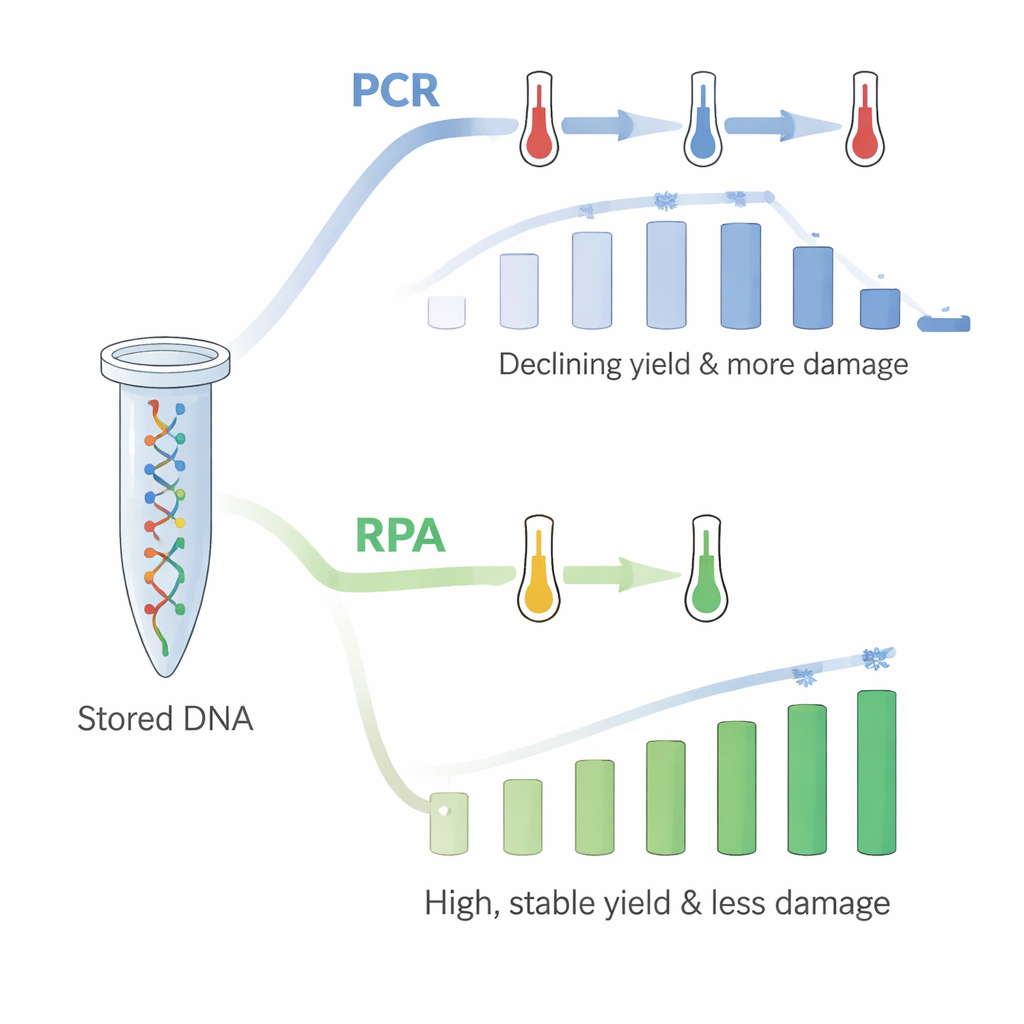
Hacia una memoria de ADN portátil y duradera
Al combinar química click robusta con copiado de ADN a baja temperatura, este trabajo apunta a una manera práctica de convertir simples tubos de plástico en cartuchos reutilizables de datos en ADN. El ADN permanece físicamente bloqueado al tubo, donde puede ser consultado repetidamente para archivos específicos sin consumir las moléculas originales, especialmente al usar el método más suave RPA. Para los no especialistas, el mensaje clave es que el ADN no es solo el código de la vida: también puede actuar como un medio de almacenamiento digital compacto y duradero. Métodos como este nos acercan a un futuro en el que sus copias de seguridad a largo plazo podrían residir no en discos giratorios, sino en moléculas cuidadosamente diseñadas reposando tranquilamente en una estantería de laboratorio.
Cita: Roy, S., Ji, H.P. & Lau, B.T. DNA conjugation on functionalized plastic surfaces for sequential, iterative single molecule sequencing. Sci Rep 16, 6467 (2026). https://doi.org/10.1038/s41598-026-37575-y
Palabras clave: almacenamiento de datos en ADN, química click, conjugación en superficies plásticas, amplificación por recombinasa-polimerasa, secuenciación por nanoporo