Clear Sky Science · es
Cuantificación y seguimiento rápidos de organoides sin aprendizaje automático con OrganoSeg2
Por qué importan los tejidos diminutos cultivados en el laboratorio
En laboratorios de todo el mundo, los científicos cultivan ahora versiones en miniatura de tejidos humanos llamadas organoides. Estos pequeños agregados celulares tridimensionales pueden imitar el comportamiento de órganos o tumores reales, lo que los convierte en herramientas potentes para estudiar enfermedades y probar tratamientos. Pero existe un cuello de botella: los investigadores pueden recopilar miles de imágenes de microscopía a baja magnificación de organoides y, aun así, tener dificultades para medir cómo crece cada uno, cómo cambia de forma o cuándo muere a lo largo del tiempo. Este artículo presenta OrganoSeg2, una versión rediseñada del software que convierte esas imágenes grises y simples en mediciones ricas y fiables de cada organoide individual, sin necesidad de entrenar inteligencia artificial ni de equipos de imagen costosos.
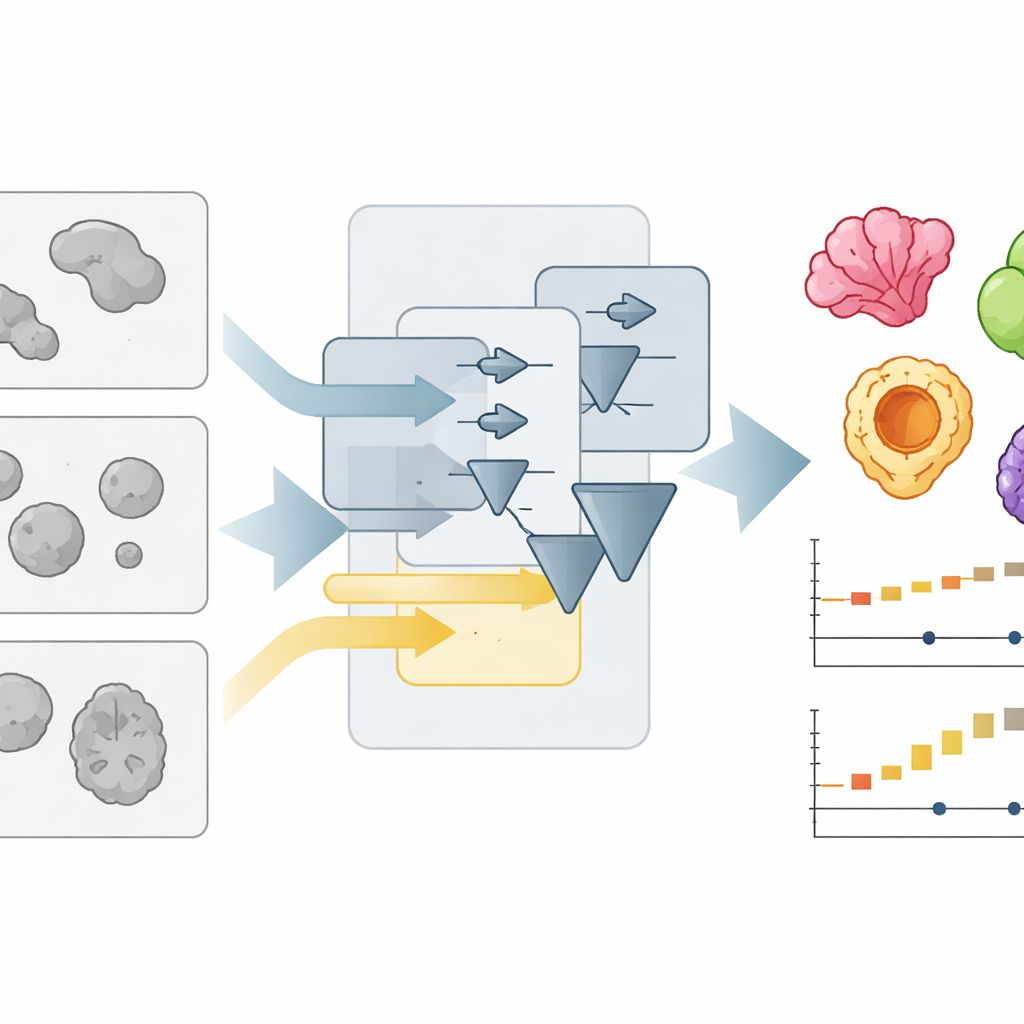
Una nueva forma de interpretar imágenes microscópicas abarrotadas
Los organoides suelen capturarse con microscopía de campo claro, que los muestra como manchas tenues y superpuestas. Delinear automáticamente cada mancha —“segmentar” la imagen— es mucho más difícil de lo que parece, sobre todo cuando los laboratorios usan diferentes formatos de cultivo, iluminación o lentes. Los autores crearon anteriormente OrganoSeg, un programa capaz de manejar segmentaciones básicas pero que se ralentizaba y volvía engorroso cuando las colecciones de imágenes crecían hasta cientos. Con OrganoSeg2, reconstruyeron el software desde cero en una interfaz moderna, racionalizaron el código interno y expusieron varios ajustes ocultos para que los usuarios puedan afinar cómo el programa separa los organoides del fondo, divide los vecinos que se tocan e ignora artefactos en los bordes de la imagen. La aplicación ahora guarda estas elecciones como metadatos para que los análisis sean reproducibles y compartibles.
Acelerar el trabajo sin sacrificar el detalle
Más allá de la flexibilidad, el equipo se centró intensamente en la velocidad y en la experiencia del usuario. En versiones anteriores, el software calculaba automáticamente todas las medidas posibles para cada organoide, incluso cuando solo se necesitaban unas pocas. OrganoSeg2, en cambio, calcula únicamente lo que el usuario selecciona y reorganiza los cálculos relacionados para reutilizar de forma eficiente los pasos que consumen tiempo. También reduce la cantidad de información dibujada en pantalla, muestra etiquetas solo cuando es necesario y añade atajos de teclado y herramientas interactivas para eliminar rápidamente residuos u objetos que no son organoides. Estas decisiones de diseño reducen las operaciones comunes —como segmentar imágenes, mostrar contornos y exportar datos— aproximadamente diez veces, lo que hace práctico manejar imágenes grandes en mosaico y experimentos de lapso temporal prolongado en un ordenador corriente.
Superando a rivales de alta tecnología con datos reales
Para probar el rendimiento de OrganoSeg2, los autores lo compararon con varias otras herramientas de segmentación, incluidos sistemas de aprendizaje profundo que requieren entrenamiento con ejemplos etiquetados manualmente. Reunieron conjuntos de imágenes de seis orígenes diferentes —como organoides de colon, pulmón, páncreas, cerebro y mama, además de cuerpos embrioides— donde expertos humanos ya habían trazado las fronteras de los organoides. Usando una puntuación de precisión estándar que mide cuánto se solapan los contornos automatizados con los manuales, OrganoSeg2 igualó o superó a herramientas especializadas en la mayoría de los conjuntos de datos y lideró claramente en las imágenes desafiantes de cáncer de mama repletas de material suelto y organoides de forma extraña. Es notable que OrganoSeg2 logró este rendimiento sin necesitar decenas de miles de ejemplos de entrenamiento y que funcionó al menos tan rápido como sus competidores, incluso aquellos basados en inteligencia artificial.
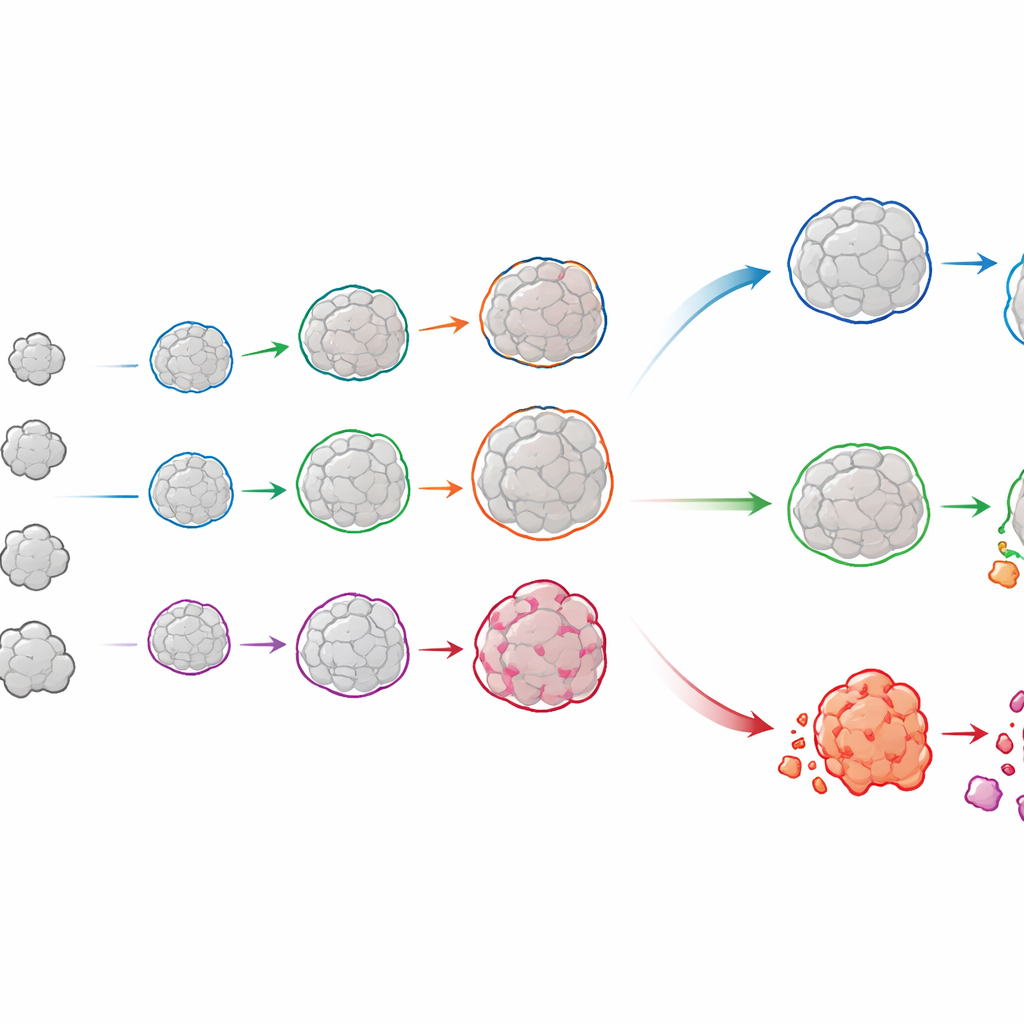
Siguiendo la historia vital de cada organoide
OrganoSeg2 hace más que delinear organoides en instantáneas individuales. Puede alinear imágenes tomadas en días distintos y vincular el mismo organoide a lo largo del tiempo, construyendo así un historial de crecimiento para cada uno. Cuando los autores aplicaron esto a organoides cultivados directamente a partir de tumores luminales de mama de pacientes, observaron que los organoides individuales rara vez crecían de forma uniforme; en cambio, muchos ralentizaban o alcanzaban mesetas, reflejando cómo los tumores reales contienen una mezcla de regiones de crecimiento rápido y lento. Al ajustar estas trayectorias a un modelo de crecimiento simple, el equipo pudo cuantificar tanto la rapidez con la que se expandía cada organoide como el tamaño que probablemente alcanzaría. Comparar estos patrones entre pacientes reveló que tumores con un crecimiento global similar pueden ocultar mezclas muy distintas de comportamientos subyacentes, diferencias que podrían ser relevantes para predecir la respuesta a tratamientos.
Observar cómo las células cancerosas viven y mueren tras la radiación
El software también vincula imágenes de campo claro con tintes fluorescentes que informan sobre la salud celular. En experimentos nuevos, los autores expusieron organoides de cáncer de mama a dosis de radiación similares a las usadas en la clínica y los tiñeron con un marcador de células vivas que se ilumina durante la muerte programada, junto con un segundo tinte que revela las células muertas en el punto final. OrganoSeg2 empleó la imagen de campo claro para definir la forma del organoide y luego midió las señales fluorescentes dentro de cada uno durante varios días. Esto permitió al equipo seguir, organoide por organoide, cuándo la radiación desencadenó la muerte y con qué intensidad. Los organoides de algunos pacientes apenas respondieron, mientras que otros mostraron alta sensibilidad incluso a dosis más bajas, subrayando lo variable que puede ser la respuesta tumoral.
Qué significa esto para la investigación y la atención futura
En conjunto, el trabajo demuestra que un procesamiento de imágenes cuidadoso y ajustable puede igualar o superar métodos complejos de aprendizaje profundo para una amplia gama de imágenes de organoides, a la vez que permanece transparente y fácil de ajustar. OrganoSeg2 transforma películas simples de baja magnificación de organoides en registros detallados de cómo cada pequeño tejido crece y sobrevive bajo distintas condiciones. Para los investigadores básicos, ofrece una vía sólida para diseccionar la diversidad oculta dentro de los cultivos de organoides. En estudios sobre cáncer en particular, abre la puerta a utilizar organoides derivados de pacientes no solo para cribados binarios de fármacos, sino para mediciones ricas y temporales del crecimiento y la muerte celular que algún día podrían ayudar a personalizar los tratamientos con mayor precisión.
Cita: Wells, C.J., Labban, N., Showalter, S.L. et al. Fast learning-free organoid quantification and tracking with OrganoSeg2. Sci Rep 16, 7928 (2026). https://doi.org/10.1038/s41598-026-37526-7
Palabras clave: organoides, análisis de imágenes, investigación del cáncer, microscopía, respuesta a la radiación