Clear Sky Science · es
Un marco tri-ómico y de aprendizaje automático identifica biomarcadores pronósticos y firmas metabólicas en la sepsis
Por qué esto importa para las personas con infecciones graves
La sepsis es una reacción potencialmente mortal ante una infección que puede sobreactivar el sistema inmunitario y provocar fallo orgánico. Los médicos saben que detectar la sepsis pronto y adaptar el tratamiento a cada paciente puede salvar vidas, pero las pruebas de sangre actuales son herramientas poco precisas: a menudo dicen poco sobre quién mejorará y quién tiene mayor riesgo. Este estudio emplea una potente combinación de tres tipos de mediciones moleculares y el aprendizaje automático moderno para buscar señales de aviso más precisas en la sangre de pacientes con sepsis.
Mirar la sangre a través de tres lentes distintas
En lugar de centrarse en un solo tipo de molécula, los investigadores perfilaron a los mismos pacientes de tres maneras a la vez. Midieron qué genes estaban activados o desactivados (transcriptómica), qué proteínas estaban presentes y activas (proteómica) y qué pequeñas moléculas metabólicas circulaban (metabolómica). Recolectaron sangre de 21 pacientes con sepsis y 10 voluntarios sanos y usaron estadísticas avanzadas para ver cómo cambiaban estas tres capas juntas en la enfermedad. Esta visión "tri-ómica" ayuda a superar un problema clave: en la sepsis, la actividad génica y los niveles proteicos pueden desacoplarse, por lo que observar solo una capa puede resultar engañoso.
Enseñar a los algoritmos a detectar patrones de alto riesgo
A partir de miles de genes y proteínas, el equipo usó primero un método de redes para encontrar grupos que se movían en conjunto en la sepsis. Luego contrastaron esos grupos con proteínas que diferían claramente entre pacientes y controles sanos, quedándose con 32 candidatos sólidos. Para reducir aún más esta lista, recurrieron al aprendizaje automático, empleando dos algoritmos complementarios para eliminar señales más débiles y conservar solo las más informativas. Al probar cómo se relacionaban los genes restantes con la supervivencia en un gran conjunto de datos públicos de sepsis, surgieron dos genes destacados: TPR y ERN1. Los pacientes con niveles más altos de TPR tendieron a sobrevivir más tiempo, mientras que niveles superiores de ERN1 se vincularon con peores resultados.
Vinculando células inmunes y metabolismo alterado
El estudio no se limitó a genes y proteínas. Al analizar miles de metabolitos en la sangre de los pacientes, los investigadores encontraron 136 pequeñas moléculas que seguían de cerca a TPR y ERN1. Muchas pertenecían a vías que manejan lípidos de membrana y ácidos grasos, que son clave para cómo las células inmunes envían señales y cómo se propaga la inflamación. Al mismo tiempo, un análisis de una sola célula —que examina células inmunes individuales en sangre en lugar de mezclarlas— mostró que TPR y ERN1 están especialmente activos en monocitos, macrófagos y células asesinas naturales. En conjunto, estos resultados sugieren que los dos marcadores se sitúan en la intersección entre las células que combaten la infección y la forma en que esas células usan y remodelan los lípidos y la energía durante la sepsis.
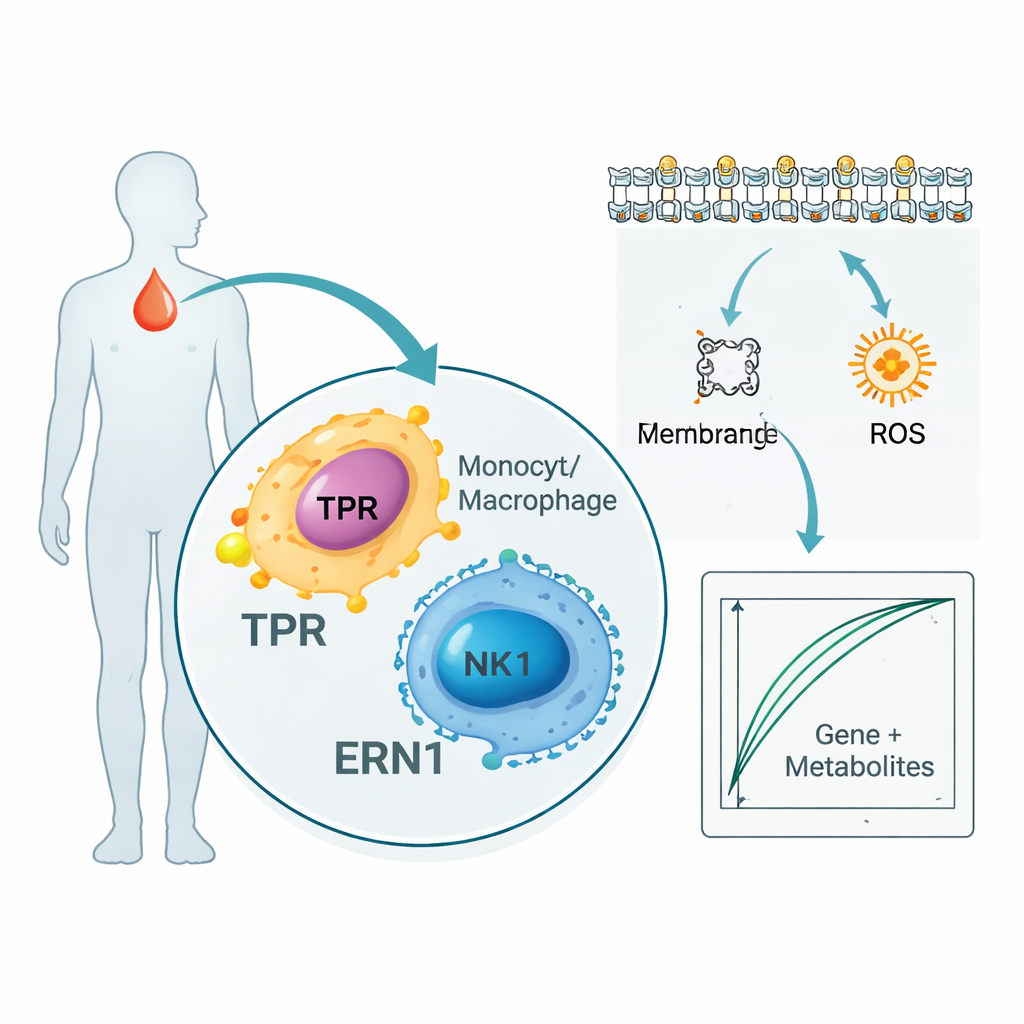
Construyendo una prueba de sangre a modo de prueba de concepto
Para explorar cómo podrían traducirse estos hallazgos en la práctica, los autores combinaron los dos genes con cinco de los metabolitos más informativos para entrenar modelos informáticos simples que separaran a los pacientes con sepsis de las personas sanas. En su pequeño conjunto de datos interno, estas firmas combinadas de "gen más metabolito" pudieron casi perfectamente distinguir quién tenía sepsis. Los investigadores también consultaron grandes bases de datos públicas que vinculan proteínas sanguíneas con riesgo de enfermedad en decenas de miles de personas y encontraron que los niveles proteicos de TPR y ERN1 se asociaban de forma consistente con condiciones relacionadas con la sepsis, agregando otra capa de soporte. Aun así, los autores señalan que estos modelos son herramientas en etapa temprana diseñadas para generar hipótesis, no pruebas listas para usar en la cabecera del paciente.
Compuestos vegetales como pistas tempranas, no como curas
En un paso final, el equipo indagó si alguna molécula natural podría influir en TPR o ERN1. Buscaron en una base de datos especializada de casi 500 compuestos purificados de medicinas tradicionales chinas, cada uno con su propio perfil de actividad génica. Varios compuestos parecieron influir fuertemente en la expresión de estos dos genes en células cultivadas en laboratorio, lo que sugiere que podrían algún día ayudar a los investigadores a sondear la biología de la sepsis o a diseñar nuevos fármacos. Sin embargo, estos hallazgos provienen únicamente de emparejamientos computacionales: no demuestran que cualquiera de estas sustancias sea segura o eficaz para personas con sepsis.
Qué nos dice realmente este trabajo
Este estudio ofrece un mapa detallado más que una solución terminada. Al entrelazar tres capas moleculares, datos de una sola célula y aprendizaje automático, los autores destacan a TPR y ERN1 —y los cambios metabólicos asociados— como indicadores prometedores de cómo el sistema inmunitario y el metabolismo se desequilibran en la sepsis. Para un lector no especializado, el mensaje clave es que la sepsis no es una enfermedad única sino un patrón cambiante de estados inmunitarios y metabólicos, y que pruebas de sangre más inteligentes podrían algún día ayudar a los médicos a ver en qué estado se encuentra un paciente y ajustar el tratamiento en consecuencia. Antes de que eso ocurra, estas señales tempranas deben probarse y confirmarse en grupos de pacientes mucho más numerosos y diversos y en experimentos de laboratorio que puedan demostrar causa y efecto.
Cita: Li, X., Ke, G., Hu, Y. et al. A tri-omics and machine learning framework identifies prognostic biomarkers and metabolic signatures in sepsis. Sci Rep 16, 6648 (2026). https://doi.org/10.1038/s41598-026-37342-z
Palabras clave: biomarcadores de sepsis, multi-ómica, aprendizaje automático en medicina, metabolismo inmune, diagnósticos de precisión