Clear Sky Science · es
Análisis comparativo del cariotipo de once especies de Lilium de China mediante FISH con sondas oligo de ADN ribosomal
Por qué importan los cromosomas de los lirios más allá del laboratorio
Los lirios de jardín son más que flores bellas y remedios tradicionales: también son modelos genéticos que ayudan a los científicos a entender cómo surgen nuevas especies vegetales y cómo clasificarlas correctamente. Este estudio examina el interior de las células de once especies de lirio chinas, muchas utilizadas como alimento o medicina, para observar cómo están dispuestos y señalados sus cromosomas. Al comparar estas estructuras ocultas, los autores aclaran qué lirios son realmente parientes cercanos y aportan pruebas para resolver debates de larga data sobre los árboles genealógicos de los lirios.
Desenredando un confuso árbol genealógico de lirios
El género Lilium contiene unas 125 especies repartidas por el Hemisferio Norte, siendo China uno de sus principales centros de diversidad. Durante más de un siglo, los botánicos han intentado agrupar estas especies en secciones naturales basándose en gran medida en rasgos visibles como la forma de la flor. Pero flores similares no siempre implican parentesco cercano, y los estudios genéticos del cloroplasto y del núcleo a veces han dado respuestas contradictorias sobre cómo se relacionan los lirios. En particular, un grupo llamado Leucolirion y sus dos subsecciones (6a y 6b), además de varias especies del suroeste y centro de China, han sido difíciles de situar con confianza.
Leyendo códigos de barras en los cromosomas
Para abordar este problema, los autores recurrieron a la citogenética, el estudio de los cromosomas. Las once especies examinadas comparten el mismo conjunto básico de doce cromosomas, normalmente presentes como 24 en los diploides; dos poblaciones de Lilium lancifolium eran triploides con 36 cromosomas. Al microscopio, cada especie muestra dos cromosomas más grandes y diez más pequeños, pero las diferencias sutiles en forma y longitud pueden ser difíciles de ver a simple vista. El equipo por tanto midió con precisión el tamaño de los cromosomas y usó una técnica llamada hibridación fluorescente in situ (FISH) para fijar etiquetas de ADN fluorescentes en regiones específicas del ADN ribosomal (ADNr), que actúan como códigos de barras brillantes a lo largo de cada cromosoma.
Encontrando patrones en los genomas de los lirios
Los investigadores cartografiaron dos tipos de ADNr —5S y 35S— en los cromosomas de cada especie. La mayoría de los lirios presentaron un sitio 5S y entre dos y seis sitios 35S, con frecuencia en posiciones características. Por ejemplo, cuatro especies tradicionalmente situadas en la subsección Leucolirion 6a (L. leucanthum, L. sargentiae, L. sulphureum y L. regale) compartieron patrones muy similares de marcas de ADNr en los mismos pares cromosómicos, lo que apunta a una relación cercana, aunque L. regale mostró algunos cambios adicionales. En contraste, las especies de la subsección hermana 6b y algunos lirios Sinomartagon presentaron disposiciones de ADNr claramente diferentes, subrayando una separación real entre estos dos grupos. Fuera de Leucolirion, patrones fuertemente compartidos vincularon al ampliamente cultivado L. lancifolium con L. pumilum y L. davidii, coincidiendo con estudios previos de secuencias de ADN que los habían agrupado juntos.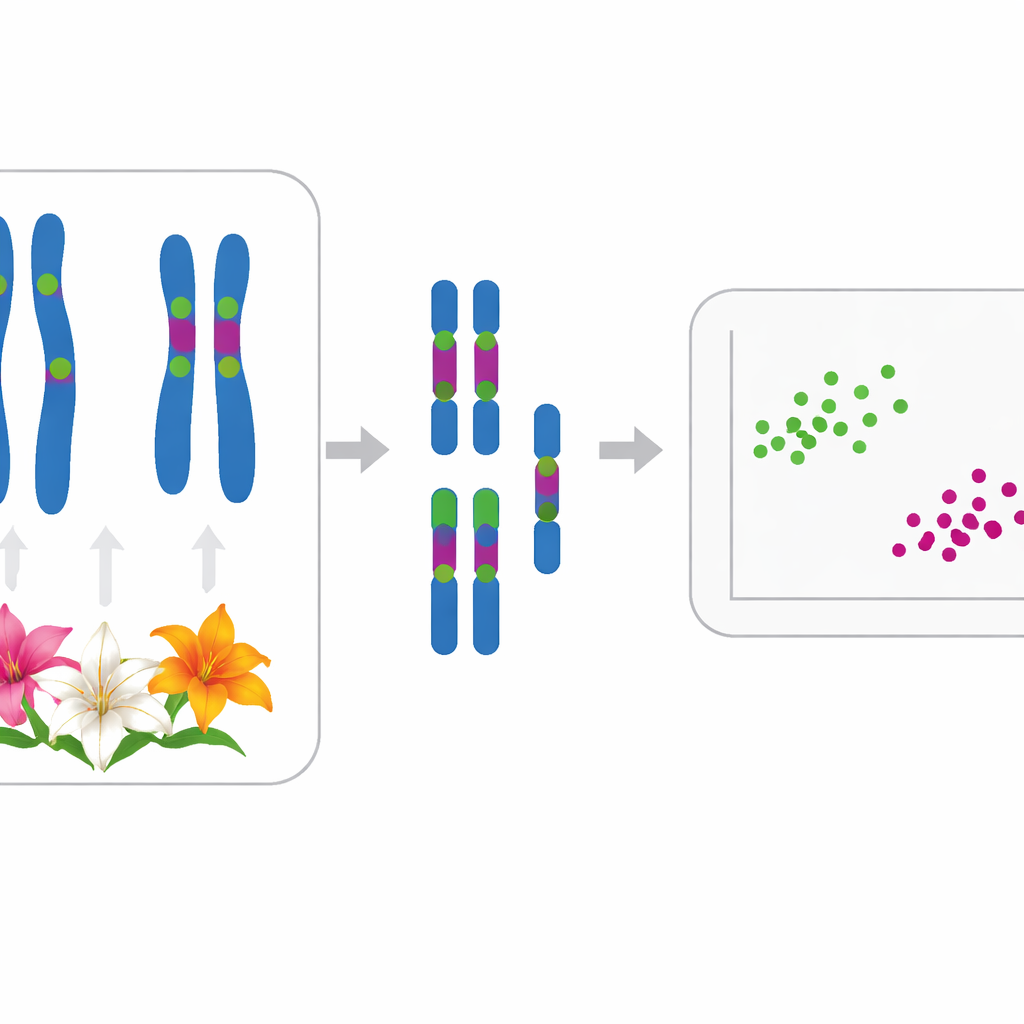
Convertir mediciones en un mapa de relaciones
Más allá de las posiciones de los códigos de barras, el equipo cuantificó cuán desigual era cada cariotipo —tanto en las posiciones de los centrómeros (la “cintura” del cromosoma) como en las longitudes cromosómicas. Utilizaron dos índices estadísticos, MCA y CVCL, para capturar estas características y representaron las once especies en un gráfico bidimensional. Cada especie ocupó su propio lugar distintivo, mostrando que incluso cariotipos aparentemente similares se pueden distinguir cuando se miden con cuidado. Un análisis estadístico más amplio (análisis de coordenadas principales) agrupó luego los lirios en dos clústeres principales que se corresponden bien con su historia evolutiva inferida. Un clúster contenía a L. pumilum, L. jinfushanense, L. brownii var. viridulum, L. regale y las formas de L. lancifolium y L. davidii; el otro agrupó a L. leucanthum, L. sargentiae, L. sulphureum, L. henryi y L. rosthornii.
Qué significa esto para la nomenclatura y el uso de los lirios
Al combinar mediciones cromosómicas detalladas con mapas de códigos de barras de ADNr, este estudio demuestra que las especies de lirio difieren más en sus cariotipos de lo que se pensaba y que estas diferencias llevan una señal evolutiva clara. En términos prácticos, el trabajo respalda tratar la subsección Leucolirion 6a como un grupo natural y bien definido dentro del género Lilium, en línea con propuestas de clasificación recientes. Para cultivadores, herboristas y planificadores de conservación, contar con una imagen más precisa de quién está emparentado con quién entre los lirios puede guiar los cruces, salvaguardar la diversidad genética y garantizar que las variedades medicinales y alimentarias se identifiquen y utilicen correctamente.
Cita: Yang, YD., Jiang, XH., Zhang, BY. et al. Comparative karyotype analysis of eleven species of Lilium from China using FISH with rDNA oligo-probes. Sci Rep 16, 9446 (2026). https://doi.org/10.1038/s41598-026-37297-1
Palabras clave: Lilium, cromosomas, hibridación fluorescente in situ, evolución vegetal, citotaxonomía