Clear Sky Science · es
Investigación del mecanismo de unión del corrolato de fósforo(V) con hemoglobina mediante enfoques fotofísicos y computacionales
Medicamentos activados por luz circulando en tu sangre
Muchos tratamientos oncológicos de próxima generación dependen de tintes especiales que se iluminan o se vuelven tóxicos solo cuando se exponen a un color específico de luz. Una de estas familias de tintes, llamadas corroles, muestra potencial para eliminar células tumorales con menos efectos secundarios. Pero antes de que un agente así pueda usarse de forma segura en humanos, los científicos deben saber cómo viaja por el cuerpo, en particular cómo interactúa con la principal proteína transportadora de oxígeno en nuestra sangre: la hemoglobina. Este estudio explora exactamente cómo un nuevo corrolato a base de fósforo se une a la hemoglobina humana y qué implica eso para convertir las proteínas sanguíneas en transportadores naturales de fármacos. 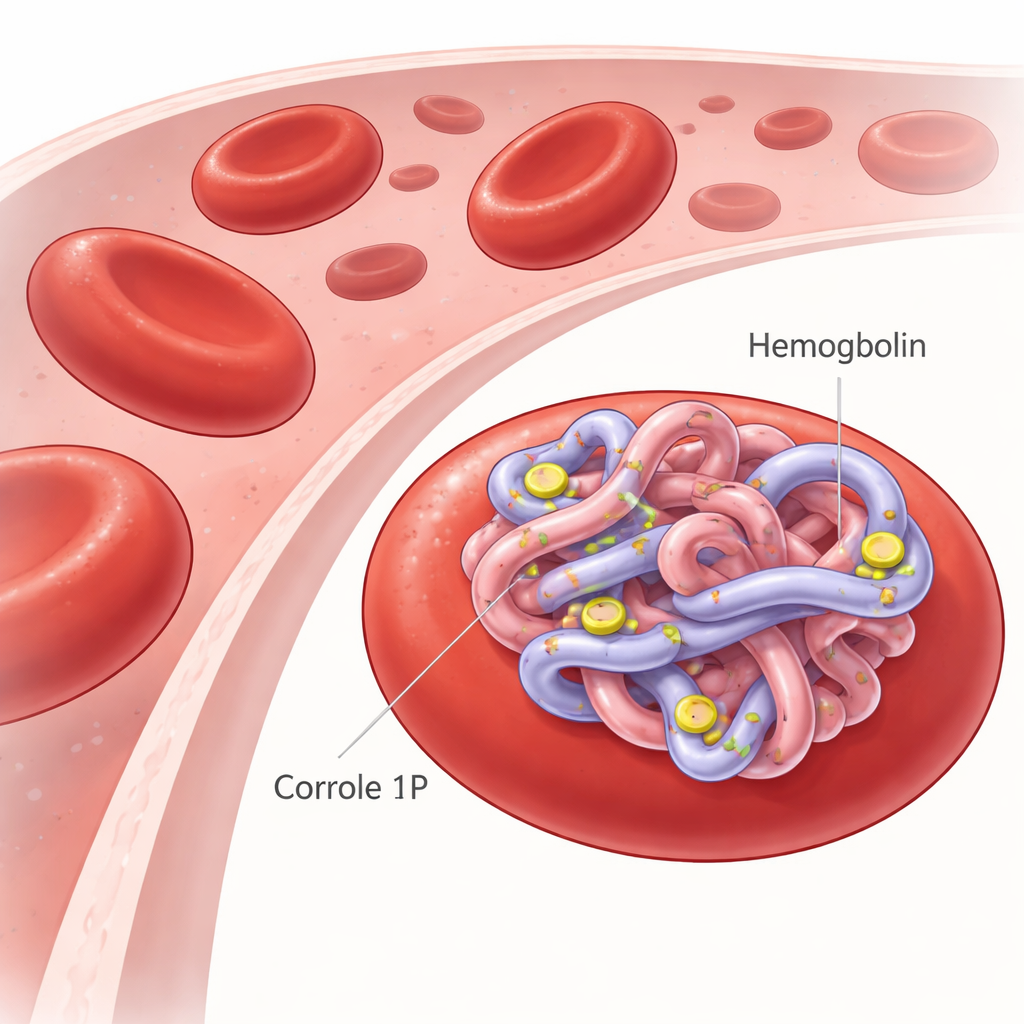
Un nuevo compañero para el transportador de oxígeno de la sangre
La hemoglobina, contenida dentro de los glóbulos rojos, transporta oxígeno desde los pulmones a cada órgano y devuelve dióxido de carbono para su eliminación. Debido a que es abundante y posee múltiples huecos y superficies donde pequeñas moléculas pueden alojarse, la hemoglobina también puede unirse a fármacos e influir en el tiempo que estos circulan. Los corroles son moléculas pigmentarias en forma de anillo relacionadas con el grupo hemo presente en la hemoglobina, pero pueden modificarse químicamente para tareas médicas como imagenología, combatir infecciones o destruir células cancerosas mediante luz. Los investigadores se centraron en un corrolato de fósforo(V) especialmente diseñado, denominado 1P, elegido por su estabilidad, fuerte absorción de luz y capacidad para generar especies reactivas de oxígeno empleadas en terapia fotodinámica.
Observar cómo las moléculas se comunican con luz
Para comprobar si 1P realmente se une a la hemoglobina, el equipo empleó primero técnicas basadas en luz. Iluminando con luz ultravioleta y visible soluciones de hemoglobina con cantidades crecientes de 1P, siguieron sutiles desplazamientos en los picos de absorción característicos de la proteína. Estos cambios revelaron que 1P y la hemoglobina forman un complejo estable en su estado fundamental, en lugar de limitarse a colisiones pasajeras. Experimentos de fluorescencia, que miden el resplandor natural de determinados aminoácidos en la hemoglobina, mostraron que ese brillo se atenúa de un modo que se explica mejor porque 1P forma un complejo compacto cerca de esos residuos emisores. A partir del grado de atenuación a distintas temperaturas, los científicos calcularon una fuerza de unión considerable y una energía libre de Gibbs negativa, lo que significa que la interacción ocurre de forma espontánea y es energéticamente favorable en condiciones semejantes a las del organismo.
Cómo la unión moldea sutilmente la proteína
Como la unión de un fármaco puede remodelar suavemente una proteína, los investigadores examinaron a continuación la estructura de la hemoglobina mediante dicroísmo circular, un método que detecta cómo las hélices y bobinas proteicas absorben luz polarizada. Añadir más 1P redujo ligeramente la señal asociada al contenido helicoidal de la hemoglobina, lo que indica un aflojamiento moderado de su estructura local en vez de un colapso total. Cuando calentaron la hemoglobina con y sin 1P, el complejo comenzó a desplegarse unos grados antes, lo que apunta de nuevo a una leve desestabilización. Estos resultados sugieren que 1P se sitúa cerca de regiones estructurales clave—lo suficiente para modificar la estabilidad de la proteína y el entorno alrededor de los grupos hemo, pero no lo bastante como para destruir la arquitectura o la función global de la hemoglobina. 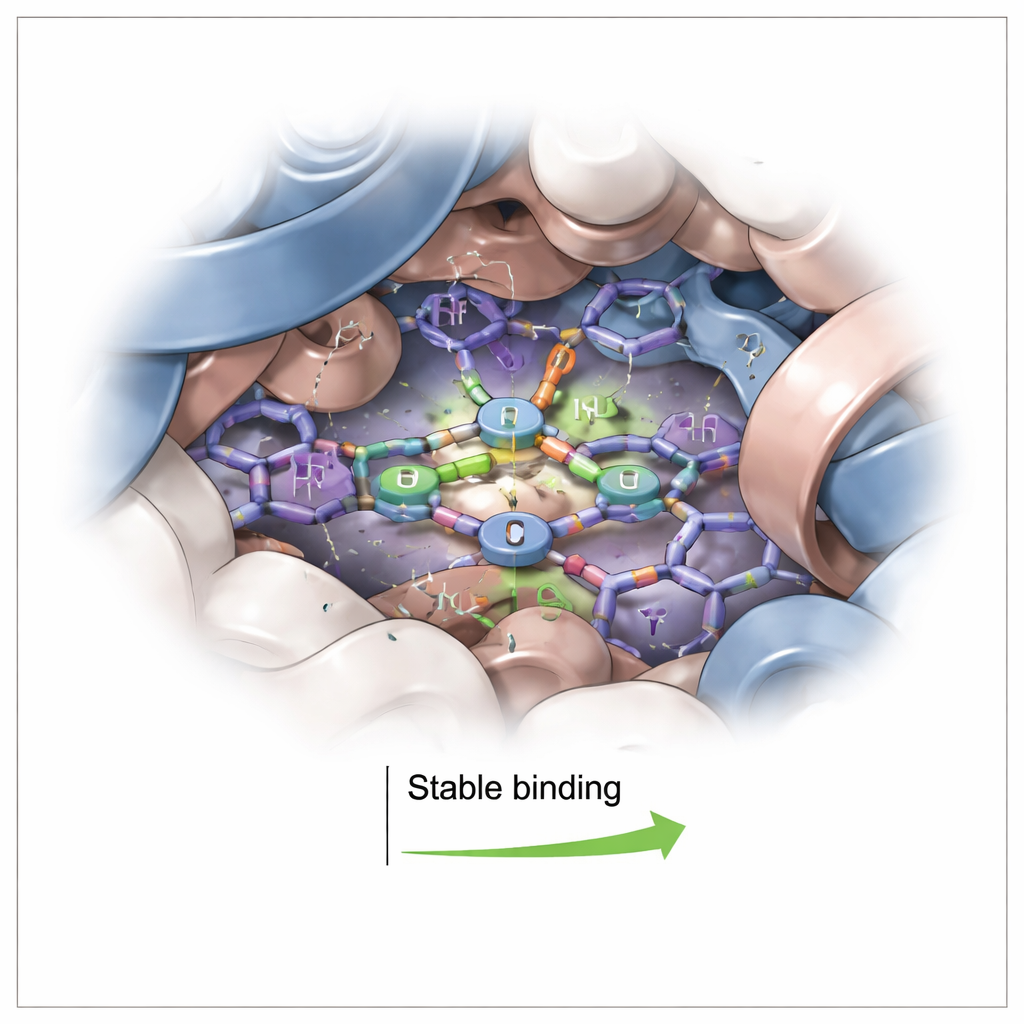
Simulaciones por ordenador revelan el plano de asiento
Para visualizar exactamente dónde se coloca 1P, el equipo recurrió a modelado computacional. Acoplaron 1P sobre una estructura de alta resolución de la hemoglobina humana y luego simularon el complejo en agua durante 100 mil millones de segundos de nanosegundos (100 ns). Las simulaciones mostraron que 1P se instala en un bolsillo aromático a unos pocos nanómetros (orden de 10⁻⁹ m) del hemo, pero sin unirse directamente al centro férrico. En lugar de ello, la superficie plana y anular del corrolato se apila contra aminoácidos aromáticos cercanos, sostenida por enlaces de hidrógeno ocasionales. A lo largo de la simulación, tanto la forma general de la hemoglobina como la posición de 1P permanecieron notablemente estables. Cálculos de energía confirmaron que la unión está fuertemente favorecida, impulsada principalmente por un empaquetamiento cercano y contactos “aceitosos” (hidrofóbicos) más que por una fuerte atracción eléctrica por sí sola.
Qué implica esto para los fármacos impulsados por luz
En conjunto, estos experimentos y simulaciones muestran que el corrolato de fósforo(V) 1P se une de forma firme y específica a la hemoglobina humana, formando un complejo estable que altera solo modestamente la estructura de la proteína. En términos sencillos, 1P encuentra un asiento cómodo en la hemoglobina sin desplazar su grupo hemo vital. Esto convierte a la hemoglobina en un prometedor vehículo natural para la entrega de fármacos basados en corroles a través del torrente sanguíneo, lo que podría mejorar el tiempo de circulación y la eficacia con la que alcanzan los tejidos enfermos. Al aclarar dónde y cómo se une 1P, este trabajo sienta las bases para diseñar medicamentos activados por luz más seguros que aprovechen nuestras propias proteínas sanguíneas como transportadores integrados.
Cita: Kritika, Kubba, R., Kumar, L. et al. Probing into the binding mechanism of phosphorus(V)-corrole with hemoglobin using photophysical and computational approach. Sci Rep 16, 6097 (2026). https://doi.org/10.1038/s41598-026-37177-8
Palabras clave: transporte de fármacos por hemoglobina, terapia fotodinámica, fotosensibilizador corrolato, unión ligando-proteína, acoplamiento molecular