Clear Sky Science · es
Predicción de la supervivencia del injerto renal mediante un modelo de aprendizaje automático basado en transcriptómica de biopsias por indicación
Por qué esto importa para los pacientes con trasplante
Para las personas con insuficiencia renal, un trasplante puede suponer la diferencia entre depender de una máquina de diálisis y volver a las actividades cotidianas. Sin embargo, muchos riñones trasplantados siguen fallando años después de la cirugía, a menudo porque el sistema inmunitario del cuerpo ataca de forma progresiva el nuevo órgano. Este estudio explora si los patrones de actividad génica obtenidos de biopsias renales de rutina pueden combinarse con técnicas modernas de aprendizaje automático para identificar qué injertos están realmente en peligro mucho antes de que las pruebas estándar muestren problemas.
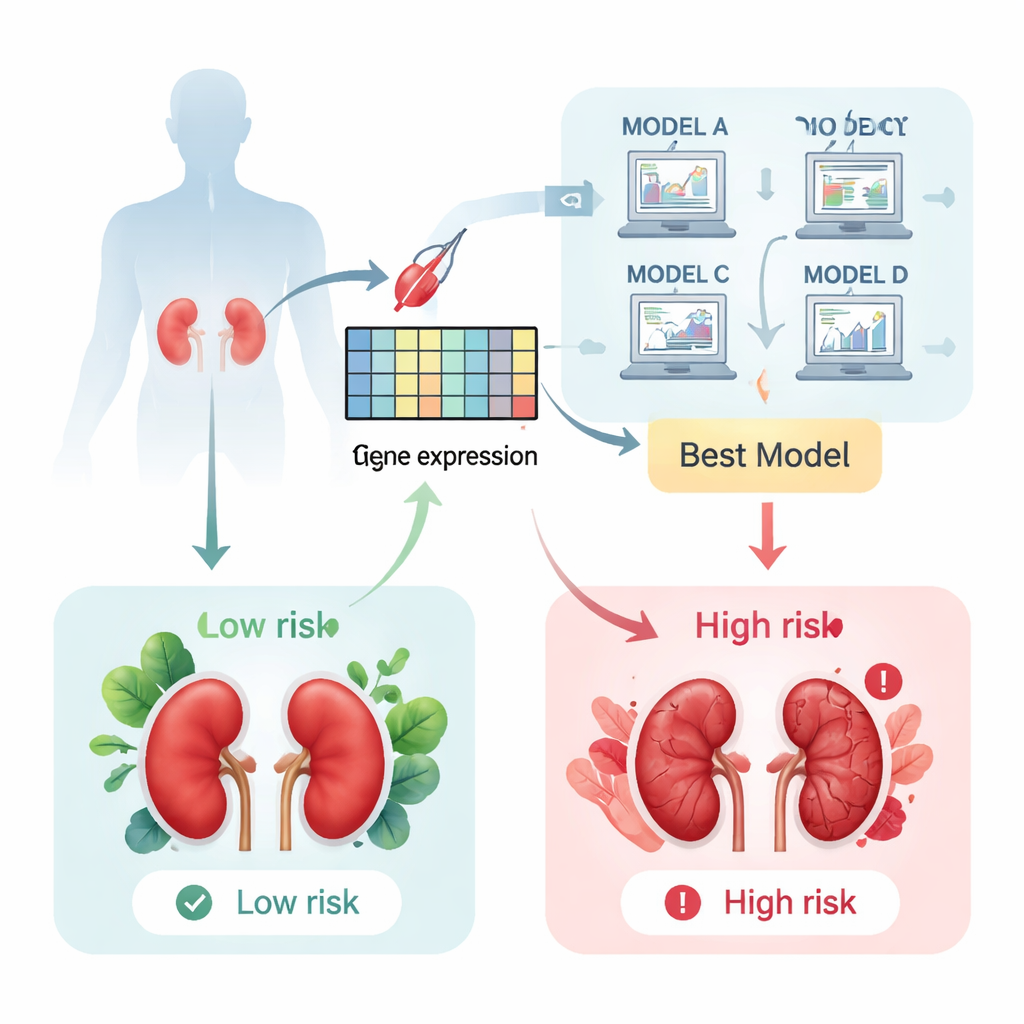
Mirando dentro del trasplante a nivel molecular
Tras un trasplante renal, los médicos a veces realizan una biopsia “por indicación” cuando análisis de sangre o de orina sugieren que el órgano podría estar bajo estrés. Tradicionalmente, los patólogos examinan estas muestras al microscopio para valorar el grado de daño. Los autores de este artículo plantearon una pregunta distinta: ¿podrían los genes activados en esas muestras de biopsia revelar una señal de aviso más clara y temprana de una futura pérdida del injerto? Para comprobarlo, reunieron datos de actividad génica de más de 1.200 biopsias procedentes de seis colecciones internacionales de investigación y se centraron en pacientes cuyos injertos o bien sobrevivieron o bien fracasaron posteriormente.
Identificación de una señal de advertencia de 11 genes
Los investigadores compararon primero las muestras de biopsia de pacientes que finalmente perdieron su riñón trasplantado con las de aquellos que mantuvieron una buena función. Buscaron entre miles de genes e identificaron un grupo pequeño de 11 que estaban consistentemente más activos en los injertos en fallo. Estos genes se asociaban fuertemente con la activación inmune y la inflamación, incluidas señales que reclutan glóbulos blancos al riñón y facilitan el ataque al tejido. En otras palabras, las biopsias de riñones que más tarde fracasarían ya estaban «encendidas» con una firma inmune agresiva, incluso cuando las medidas tradicionales podían seguir pareciendo aceptables.
Entrenando máquinas para predecir la supervivencia del injerto
A continuación, el equipo alimentó los niveles de actividad de estos 11 genes a una amplia gama de enfoques de aprendizaje automático diseñados para predecir cuánto tiempo seguiría funcionando un riñón trasplantado. Probaron 117 configuraciones de modelos diferentes y las evaluaron según la precisión con la que podían ordenar a los pacientes del mayor al menor riesgo de pérdida del injerto. Un tipo de algoritmo llamado Gradient Boosting Machine resultó ser el claro vencedor, ordenando correctamente a los pacientes con un alto grado de precisión. Cuando el modelo asignaba una puntuación de alto riesgo, esos pacientes eran mucho más propensos a perder su injerto en los años siguientes que los pacientes con puntuaciones bajas, como muestran curvas de supervivencia que se separan de forma marcada con el tiempo.
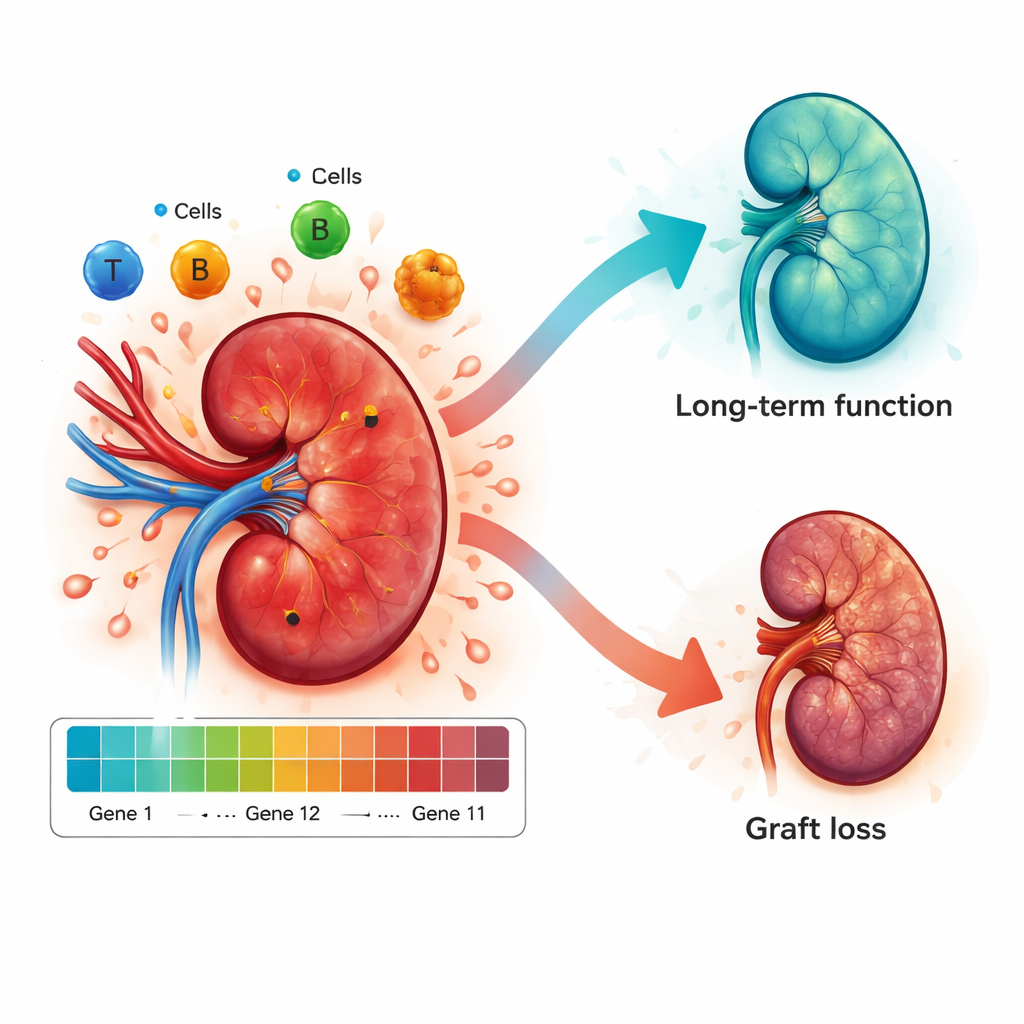
Comprobación del rendimiento en nuevos grupos de pacientes
Para ser útil en la clínica, una herramienta de riesgo debe funcionar más allá de los datos con los que se construyó. Por ello, los autores aplicaron su modelo de 11 genes a cuatro colecciones de biopsias completamente independientes de otros centros. En estos grupos, los tiempos de supervivencia detallados no siempre estaban disponibles, pero los expertos habían etiquetado cada biopsia como con rechazo o sin rechazo. La misma puntuación basada en genes hizo un buen trabajo distinguiendo el rechazo de los injertos estables, con medidas de precisión comparables a muchas pruebas médicas usadas en la práctica. En un estudio separado en el que los pacientes tenían biopsias programadas a los 0, 6 y 24 meses tras el trasplante, aquellos que más tarde desarrollaron daño crónico ya mostraban puntuaciones de riesgo más altas meses antes de que el daño fuera evidente al microscopio.
Lo que el modelo revela sobre la batalla inmune
Más allá de la predicción, los investigadores utilizaron los patrones génicos para asomarse al paisaje inmunitario dentro del riñón. Las biopsias con puntuaciones de alto riesgo mostraron tipos de células inmunitarias más agresivas, como ciertos macrófagos y células T, y más señales químicas que facilitan su infiltración en el órgano. Por el contrario, las biopsias de bajo riesgo eran más ricas en tipos celulares asociados con la calma de la inflamación y la promoción de la reparación tisular. Esto sugiere que el modelo no es simplemente una caja negra: su puntuación de riesgo refleja procesos biológicos reales que empujan al riñón hacia el rechazo o favorecen la convivencia a largo plazo entre el órgano y el sistema inmunitario del receptor.
Cómo esto podría cambiar la atención en trasplantes
El estudio concluye que una puntuación basada en 11 genes y en aprendizaje automático, derivada de biopsias renales de rutina, puede predecir con fiabilidad qué injertos tienen más probabilidades de fallar y puede detectar problemas antes que los métodos estándar. Para pacientes y clínicos, una herramienta así podría en el futuro guiar una atención personalizada: los individuos de alto riesgo podrían recibir seguimiento más estrecho o ajustes de medicación a medida, mientras que los pacientes de bajo riesgo podrían evitar procedimientos innecesarios. Dado que la firma utiliza solo un conjunto pequeño de genes, podría traducirse en pruebas de laboratorio prácticas con la tecnología existente. Aunque hacen falta más ensayos prospectivos antes de que forme parte de la práctica cotidiana, este trabajo apunta hacia un futuro en el que las lecturas moleculares y la inteligencia artificial ayuden a proteger los riñones trasplantados a largo plazo.
Cita: Filho, V.O.C., Passos, P.R.C., de Andrade, L.G.M. et al. Predicting kidney graft survival with a machine learning model based on for-cause biopsy transcriptomics. Sci Rep 16, 6157 (2026). https://doi.org/10.1038/s41598-026-37038-4
Palabras clave: trasplante renal, supervivencia del injerto, aprendizaje automático, expresión génica en biopsia, rechazo inmunitario