Clear Sky Science · es
Portación fecal y caracterización molecular de Enterobacteriaceae productoras de BLEE entre agricultores en el centro-oeste de Uganda
Por qué los gérmenes en el intestino de los agricultores nos importan a todos
Las bacterias resistentes a los antibióticos suelen considerarse un problema limitado a los hospitales, pero este estudio muestra que se están propagando silenciosamente en la vida cotidiana, también en pequeñas explotaciones agrícolas de la Uganda rural. Los investigadores analizaron las bacterias que habitan el intestino de agricultores y se plantearon: ¿qué tan frecuentes son las cepas altamente resistentes, qué las hace resistentes y qué condiciones cotidianas facilitan su diseminación? Sus hallazgos arrojan luz sobre cómo la resistencia puede moverse entre personas, animales y el medio ambiente—y por qué eso importa para cualquiera que pueda necesitar que los antibióticos sigan siendo eficaces.
Comprobando la salud de las bacterias intestinales en pequeñas granjas
El equipo trabajó en la parroquia de Kibimba, una zona mayoritariamente agrícola en el centro-oeste de Uganda donde muchas familias crían ganado y aves. Reclutaron a 250 agricultores adultos que donaron una pequeña muestra de heces. En el laboratorio, los científicos cultivaron bacterias a partir de esas muestras y se centraron en una familia de microbios llamada Enterobacteriaceae, que incluye especies conocidas como Escherichia coli. Utilizando métodos de cultivo estándar y pruebas bioquímicas, identificaron las especies presentes. Después evaluaron cómo respondían esas bacterias a un panel de antibióticos de uso común y emplearon un método específico para detectar aquellas capaces de descarboxilar (inactivar) fármacos potentes conocidos como cefalosporinas de tercera generación.
Buscando genes de resistencia dentro de los microbios
Para entender qué hacía que algunas bacterias fueran tan difíciles de tratar, los investigadores buscaron tres genes de resistencia bien conocidos: blaCTX-M, blaTEM y blaSHV. Estos genes codifican enzimas denominadas betalactamasas de espectro extendido (BLEE), que permiten a las bacterias inactivar muchos antibióticos importantes. Mediante una técnica llamada PCR comprobaron si estos genes estaban presentes en las cepas positivas para BLEE. También examinaron si una misma bacteria portaba más de un gen de resistencia simultáneamente, lo que sugeriría que la resistencia puede compartirse y acumularse a través de elementos genéticos móviles que se trasladan entre microbios.
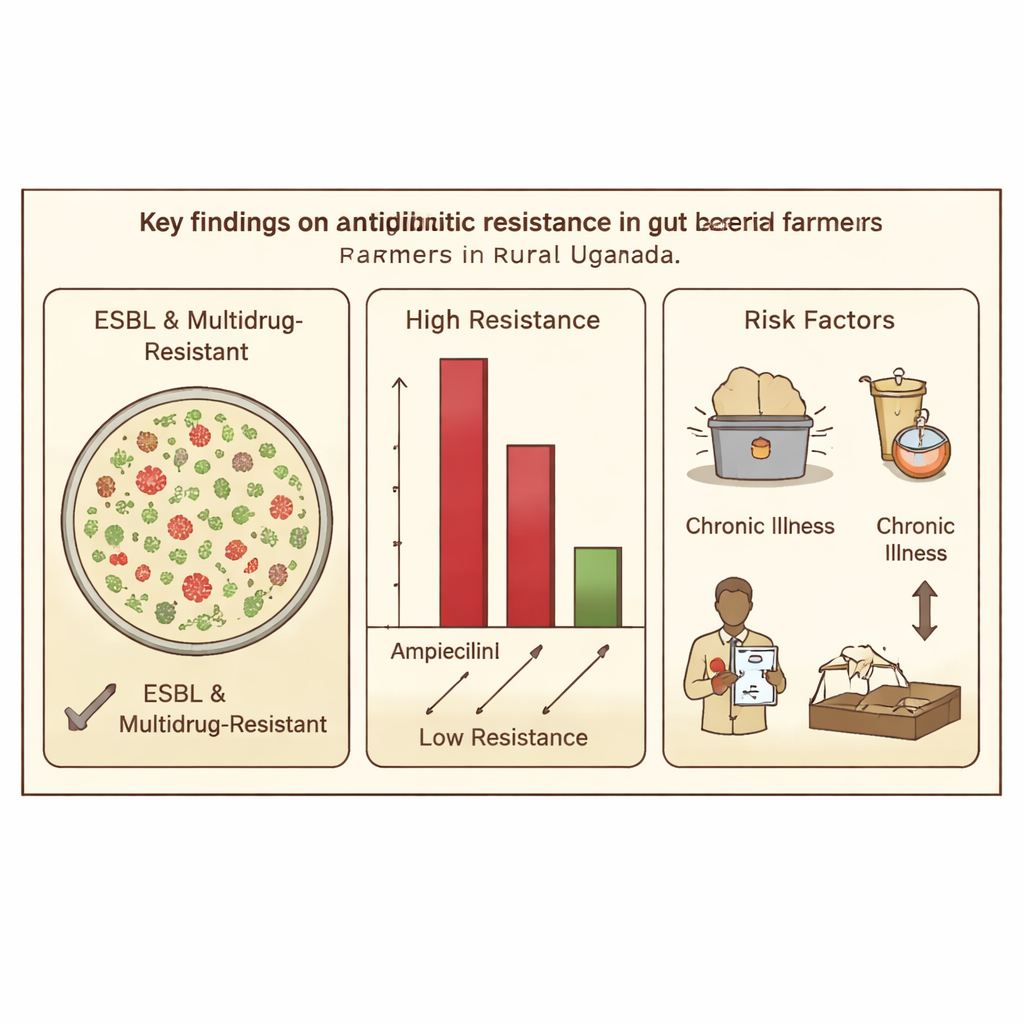
Qué encontraron los científicos en las heces de los agricultores
De los 250 agricultores, más de uno de cada tres (36,4 %) portaba bacterias productoras de BLEE en su intestino, lo que muestra que estos microbios difíciles de tratar son comunes incluso en personas que no están hospitalizadas. De 312 aislamientos bacterianos cultivados a partir de las muestras, Escherichia coli predominó, constituyendo alrededor del 70 % de todas las cepas y de los productores de BLEE en particular. Muchos aislamientos eran resistentes a varias clases de fármacos a la vez, un patrón conocido como multirresistencia. La resistencia fue especialmente alta frente a antibióticos antiguos y de uso común, como ampicilina y piperacilina, mientras que un fármaco de último recurso, imipenem, permaneció mayormente eficaz, probablemente porque es caro y se utiliza con menos frecuencia en entornos rurales.
Genes que impulsan la resistencia y el papel de la vida cotidiana
Entre las bacterias confirmadas como productoras de BLEE, aproximadamente cuatro de cada cinco portaban al menos uno de los tres genes clave de resistencia. El más común fue blaCTX-M, seguido de blaTEM y blaSHV. Muchas bacterias llevaban más de un gen a la vez, y algunas albergaban los tres, lo que indica que estos microbios han acumulado múltiples herramientas para vencer a los antibióticos. Los investigadores también relacionaron la portación bacteriana con condiciones cotidianas. Los agricultores que dependían de pozos poco profundos tenían mayor probabilidad de portar bacterias productoras de BLEE, lo que sugiere que el agua no tratada puede actuar como reservorio. Tener enfermedades crónicas como hipertensión o VIH/SIDA también se asoció con mayor probabilidad de portar cepas resistentes, posiblemente debido a un contacto más frecuente con el sistema sanitario y con antibióticos. De forma interesante, la cría de cabras pareció vincularse con un menor riesgo, lo que insinúa que distintos animales y estilos de manejo pueden influir en cómo circula la resistencia.
Qué significa esto para los agricultores y el mundo en general
En conjunto, el estudio dibuja una imagen clara: en esta comunidad rural de Uganda, muchos agricultores portan silenciosamente bacterias intestinales capaces de resistir múltiples antibióticos, impulsadas por potentes genes de resistencia. Para el público general, esto significa que infecciones que antes se curaban con facilidad podrían volverse mucho más difíciles de tratar, incluso lejos de los grandes hospitales urbanos. Los hallazgos respaldan una perspectiva “One Health”, en la que la salud humana está ligada a la de los animales y al medio ambiente. Mejorar el acceso a agua segura, fomentar una mejor higiene, usar antibióticos con más prudencia tanto en personas como en ganado, y ampliar pruebas de laboratorio sencillas en clínicas rurales podrían ayudar a frenar la propagación de estos microbios peligrosos antes de que se arraiguen aún más.
Cita: Wilson, G., Micheal, K., Catherine, A. et al. Fecal carriage and molecular characterization of ESBL-producing Enterobacteriaceae among farmers in Mid-Western Uganda. Sci Rep 16, 6249 (2026). https://doi.org/10.1038/s41598-026-36817-3
Palabras clave: resistencia a los antibióticos, bacterias BLEE, agricultura rural, One Health, Uganda