Clear Sky Science · es
Identificador integrado de bacterias en chip para BSI usando emparejamiento aproximado de k-mers
Por qué importa detectar gérmenes más rápido
Para los pacientes que reciben trasplantes de células madre que les salvan la vida, las infecciones en el torrente sanguíneo pueden convertir la recuperación en una urgencia médica en cuestión de horas. Los médicos saben que cada minuto cuenta, pero las herramientas de laboratorio actuales para encontrar a la bacteria culpable pueden ser lentas o exigir equipos informáticos potentes. Este estudio presenta un chip informático diminuto y eficiente en energía —llamado PC-CAM— que puede escanear rápidamente el ADN de muestras de pacientes y señalar bacterias peligrosas en tiempo real, potencialmente junto a la cama del hospital.
El riesgo de infección tras un tratamiento que salva el intestino
Algunos pacientes trasplantados desarrollan una complicación grave en la que las células inmunitarias donadas atacan el intestino del paciente. Un tratamiento prometedor es el trasplante de microbiota fecal, en el que se introducen microbios intestinales sanos de un donante en el paciente. Aunque esto puede rescatar el intestino, a veces conlleva un peligro añadido: bacterias perjudiciales del intestino pueden escapar al torrente sanguíneo y provocar infecciones que ponen en riesgo la vida. Para tratar estas infecciones de forma eficaz, los médicos deben identificar rápidamente qué especies bacterianas están presentes, pero las pruebas tradicionales pueden tardar horas o días y pueden pasar por alto cepas poco conocidas.
De ensamblar genomas lentamente a buscar fragmentos de ADN rápido
Los secuenciadores de ADN modernos pueden leer material genético directamente de muestras de sangre o heces casi en tiempo real. El cuello de botella ya no es leer el ADN, sino interpretarlo. Los métodos convencionales intentan primero reconstruir genomas completos a partir de millones de fragmentos cortos de ADN y luego emparejar esos genomas ensamblados con una biblioteca de referencia, un proceso intensivo en cálculo. Los autores lo sustituyen por una estrategia más simple: dividir el ADN en piezas cortas de longitud fija, llamadas k-mers, y buscar esos fragmentos directamente en una base de datos de secuencias bacterianas conocidas. En lugar de exigir una coincidencia perfecta letra por letra, su sistema tolera un cierto número de diferencias, lo que le permite manejar los errores inevitables de la secuenciación y las mutaciones naturales. 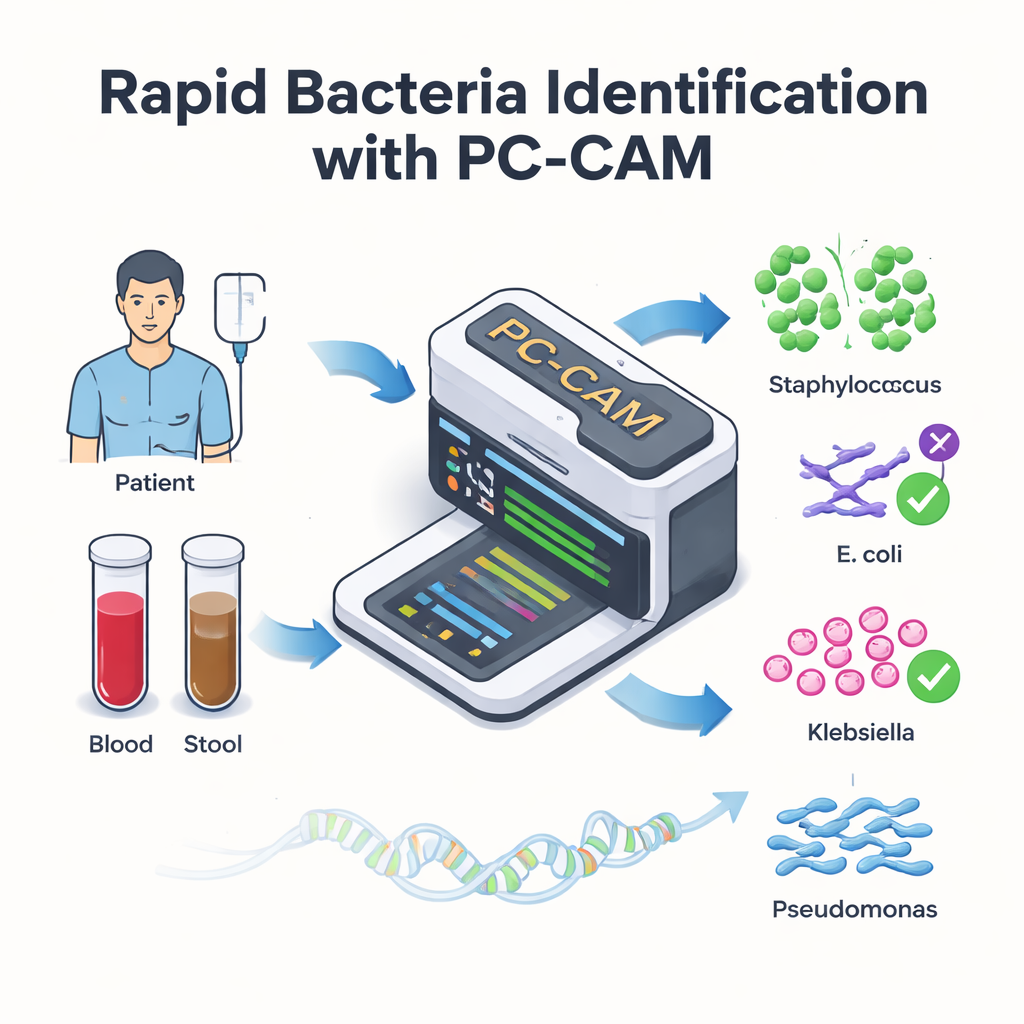
Un chip de memoria inteligente diseñado para buscar ADN
En el núcleo de PC-CAM hay un tipo especializado de memoria llamada memoria asociativa por contenido (content-addressable memory), que puede comparar datos entrantes con todo lo que almacena a la vez. Los investigadores diseñaron una versión de esta memoria para "búsqueda aproximada" (ACAM) que puede ajustarse para aceptar coincidencias próximas en lugar de exactas. Cada fragmento corto de ADN se codifica y almacena como una fila en esta memoria. Cuando llega un nuevo fragmento de una muestra de paciente, el chip activa una línea de búsqueda a través de todas las filas simultáneamente y mide qué tan rápido se descargan pequeñas señales eléctricas. Al ajustar dos tensiones de control, el sistema fija un umbral sobre cuántas discordancias tolerará, calibrando en la práctica cuán permisiva debe ser la coincidencia. Esta comparación a nivel de hardware permite al chip tamizar patrones mucho más rápido y con menos energía que un ordenador de propósito general.
Qué tan bien encuentra bacterias reales el chip
El equipo probó PC-CAM con conjuntos de datos del mundo real de pacientes que habían recibido trasplante de microbiota fecal, comparando las bacterias detectadas en su sangre y heces con los resultados de un análisis genómico completo basado en software. Incluso cuando el chip almacenaba solo un subconjunto pequeño y cuidadosamente seleccionado de fragmentos de ADN de cada genoma bacteriano, coincidió en gran medida con el método más costoso en cálculo, identificando correctamente patógenos clave en varios pacientes. En experimentos ampliados usando lecturas de ADN simuladas de diversas bacterias y distintos niveles de error, la sensibilidad del chip (su capacidad para capturar coincidencias verdaderas) aumentó a medida que se le permitía tolerar más diferencias, mientras que la especificidad (su capacidad para evitar falsas alarmas) disminuyó en niveles de tolerancia muy altos. Los autores muestran que pasos sencillos de posprocesado —como exigir múltiples fragmentos concordantes o descartar coincidencias débiles— pueden reducir estos falsos positivos. 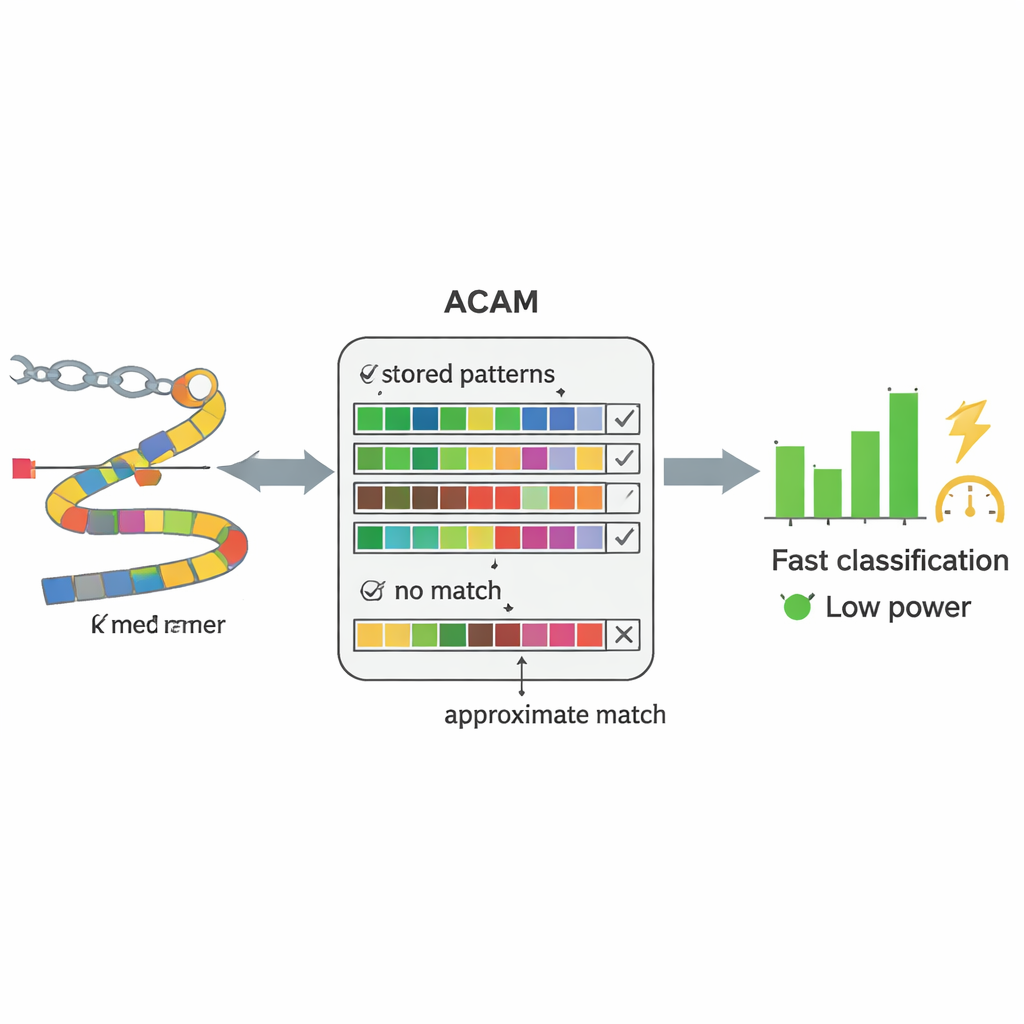
Hardware diminuto con gran velocidad y bajo consumo
PC-CAM integra la memoria ACAM con un pequeño procesador RISC-V en un chip de apenas unos milímetros cuadrados, fabricado en una tecnología estándar de 65 nanómetros. Medidas en hardware real muestran que puede clasificar alrededor de 960.000 lecturas cortas de ADN por segundo mientras consume aproximadamente 1,27 miliwatios de potencia —menos que muchos relojes digitales de pulsera. En comparación con una herramienta de software líder ejecutándose en un procesador de sobremesa de alta gama, el chip fue aproximadamente 1.900 veces más rápido para este tipo de tarea de clasificación. Aunque su precisión se reduce modestamente al almacenar una versión diluida de cada genoma, los autores sostienen que este compromiso es aceptable cuando la velocidad y el consumo son las principales limitaciones, como en atención de emergencia o dispositivos portátiles.
Qué significa esto para los pacientes y más allá
En términos sencillos, el estudio demuestra que un chip diminuto y de bajo consumo puede actuar como un motor de búsqueda especializado para ADN bacteriano, detectando gérmenes peligrosos en muestras de sangre o heces casi al instante. Si bien no reemplaza el análisis genético completo de un laboratorio importante, puede proporcionar orientación rápida y en el lugar sobre qué bacterias están presentes, ayudando a los médicos a elegir antibióticos antes y con mayor precisión. El mismo enfoque podría ampliarse para monitorear resistencia a antibióticos, comprobar alimentos y agua en busca de contaminación o vigilar cultivos ante enfermedades—todo ello usando hardware compacto que traslada el análisis sofisticado de ADN fuera del centro de datos y más cerca del lugar donde deben tomarse las decisiones.
Cita: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
Palabras clave: infección del torrente sanguíneo, detección rápida de patógenos, secuenciación de ADN, laboratorio en un chip, microbioma