Clear Sky Science · es
Ensamblado del transcriptoma de longitud completa y desarrollo de marcadores SSR para Spinibarbus hollandi mediante secuenciación PacBio SMRT
Por qué importa un modesto pez de río
A lo largo de los ríos del sur de China nada Spinibarbus hollandi, un pez parecido a la carpa apreciado tanto en la mesa como como especie ornamental. Los criadores desean cultivarlo de forma más eficiente, pero el pez crece despacio, madura tarde y produce relativamente pocos huevos. El estudio descrito aquí utiliza herramientas avanzadas de secuenciación de ADN y ARN para construir una lista detallada de “componentes” genéticos de esta especie. Esa información genética puede, en última instancia, ayudar a los criadores a seleccionar peces más resistentes y de crecimiento más rápido, y apoyar la conservación de las poblaciones silvestres.
Convertir muchos tejidos en un mapa genético
Para capturar la mayor cantidad de información genética posible, los investigadores recogieron seis tejidos diferentes —corazón, branquia, cerebro, aleta, hígado y gónada— de seis adultos machos y hembras. De estos tejidos extrajeron ARN, la molécula que transporta copias de los genes activos dentro de las células. Usando una tecnología llamada PacBio SMRT, que lee tramos muy largos de las copias de ARN, ensamblaron el primer transcriptoma de longitud completa de S. hollandi. En términos sencillos, construyeron un catálogo de alta resolución con 15.197 genes distintos y 23.403 secuencias de transcritos, la mayoría mucho más largas y completas que las que podían producir los métodos anteriores de lecturas cortas.
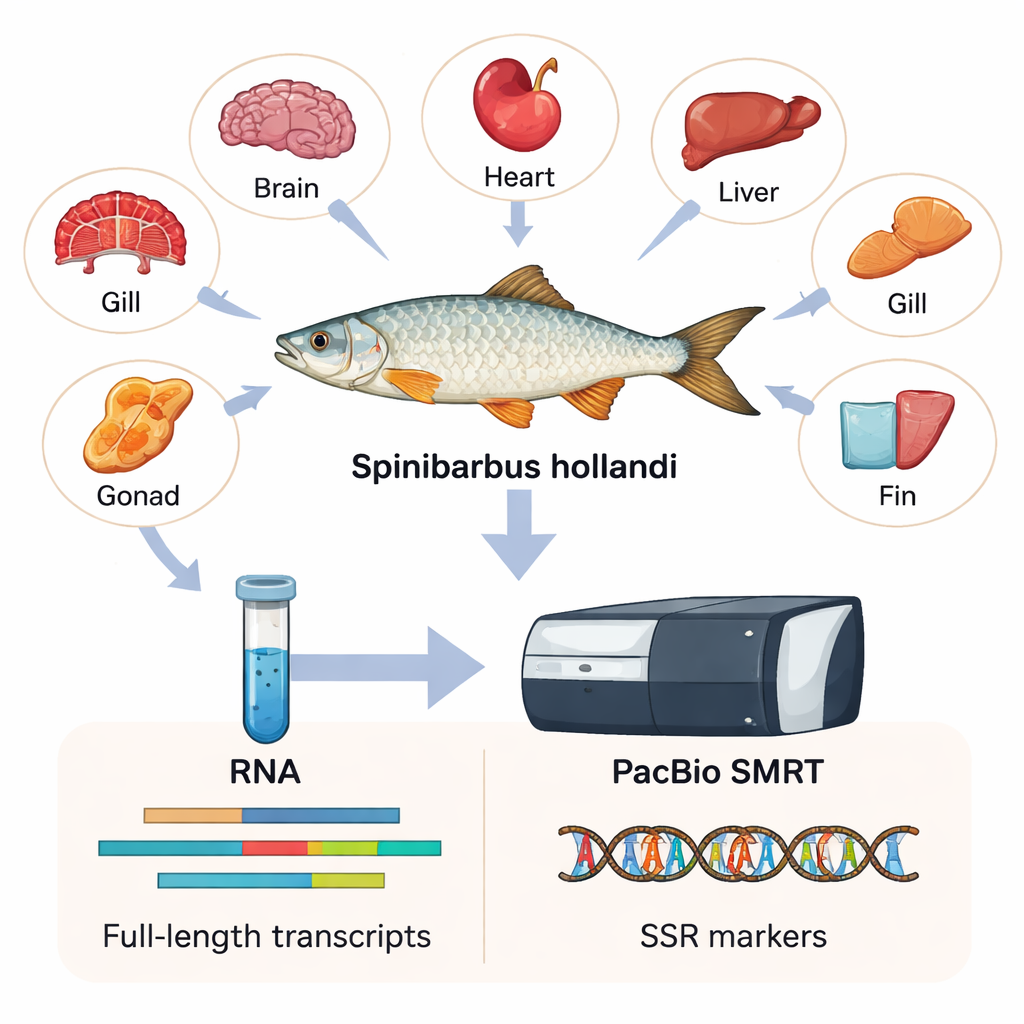
Lo que los genes revelan sobre el pez
A continuación, el equipo preguntó qué hacen en realidad esos genes. Compararon cada secuencia con grandes bases de datos públicas que agrupan genes por función. Más del 95% de los genes pudieron emparejarse con entradas conocidas, una tasa de éxito muy alta que indica buena calidad de los datos. Muchos genes se agruparon en categorías relacionadas con actividades celulares básicas como el metabolismo, la transmisión de señales y el desarrollo, y la mayoría se parecían más a genes de otros peces de la familia de las carpas. Esto confirma que el nuevo transcriptoma es biológicamente sólido y proporciona una base para encontrar genes vinculados a rasgos como la tasa de crecimiento, la tolerancia al estrés y la reproducción en S. hollandi.
Capas ocultas de control en el ARN
Más allá de identificar genes, los científicos también examinaron cómo se controlan esos genes. Encontraron 373 casos de empalme alternativo, donde el mismo gen se recorta y pega de diferentes maneras para generar mensajes de ARN distintos. El patrón más común mantuvo fragmentos de ARN que a menudo se eliminan en otras especies, lo que sugiere una forma particular en que este pez ajusta finamente sus proteínas. También descubrieron 2.397 ARN largos no codificantes —moléculas de ARN que no producen proteínas pero que pueden regular cuándo y dónde se activan otros genes. En conjunto, estos hallazgos muestran que S. hollandi utiliza un conjunto rico de controles a nivel de ARN que pueden influir en el crecimiento, la maduración sexual y la adaptación a los entornos locales.
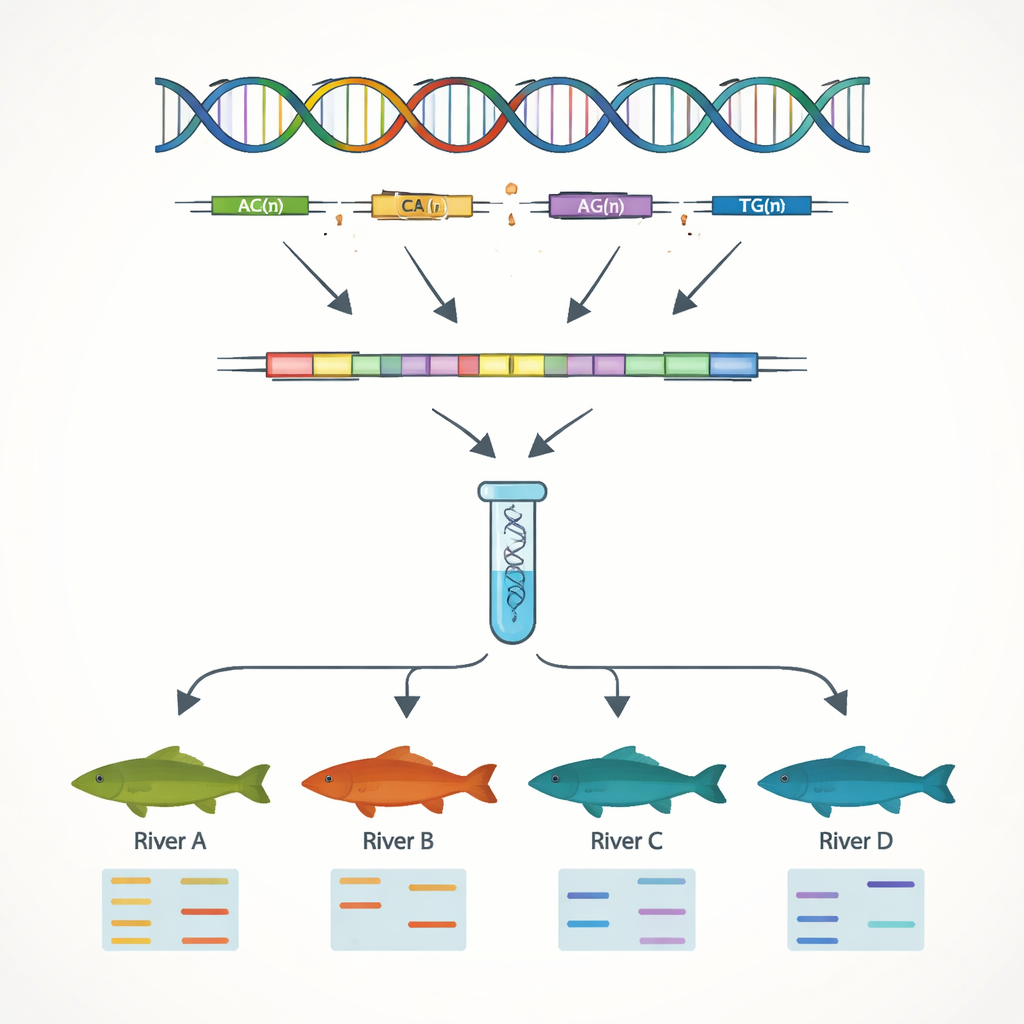
Construir hitos de ADN para la cría y la conservación
Un objetivo principal del trabajo fue desarrollar marcadores de ADN simples que permitan distinguir individuos y poblaciones. Centrándose en las secuencias génicas, los autores buscaron repeticiones de secuencias simples, o SSR —motivos cortos de ADN como “AC” o “AAT” repetidos muchas veces seguidas. Estos tramos tienden a variar entre individuos, por lo que son útiles como códigos genéticos. Descubrieron 7.449 sitios SSR y diseñaron docenas de primers cortos de ADN para amplificarlos en el laboratorio. Trece de estos marcadores resultaron ser altamente variables y fiables cuando se probaron en 51 peces de cuatro sistemas fluviales. Usando solo estos 13 marcadores, el equipo pudo detectar claramente diferencias genéticas entre poblaciones del río Yangtsé y las del río de la Perla, lo que refleja las cordilleras que limitan la mezcla natural entre cuencas.
Qué significa esto para los criadores y los ríos
Para el público general, la conclusión clave es que los autores han creado una referencia genética detallada y de alta calidad para S. hollandi y un conjunto de marcadores de ADN prácticos. Este conjunto de herramientas ayudará a los investigadores a identificar los genes responsables del crecimiento lento o de la baja fertilidad, asistirá a los criadores en la selección de reproductores con rasgos deseables y permitirá a los conservacionistas rastrear la diversidad genética entre sistemas fluviales. Aunque se necesita más trabajo para vincular genes específicos con el rendimiento en estanques o en la naturaleza, este estudio sienta las bases moleculares para transformar un pez tradicional de río en una especie de acuicultura moderna y gestionada de forma sostenible.
Cita: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
Palabras clave: Spinibarbus hollandi, transcriptoma de peces, secuenciación PacBio, marcadores de microsatélites, genética de la acuicultura