Clear Sky Science · es
Identificación de genes bacterianos clave y dianas terapéuticas en pacientes hipertensos con diabetes tipo 2 mediante análisis bioinformático
Por qué tu intestino importa para la presión arterial y el azúcar en sangre
La hipertensión y la diabetes tipo 2 suelen aparecer juntas, aumentando el riesgo de infartos, ictus y enfermedad renal. Durante mucho tiempo los médicos han tratado estas afecciones por separado, centrándose en fármacos que actúan sobre el corazón, los vasos sanguíneos o la insulina. Este estudio plantea una pregunta distinta: ¿podrían los diminutos microbios que viven en nuestros intestinos —y los genes que llevan— contribuir a ambos problemas a la vez, y revelar nuevas opciones terapéuticas?
El mundo oculto dentro del intestino
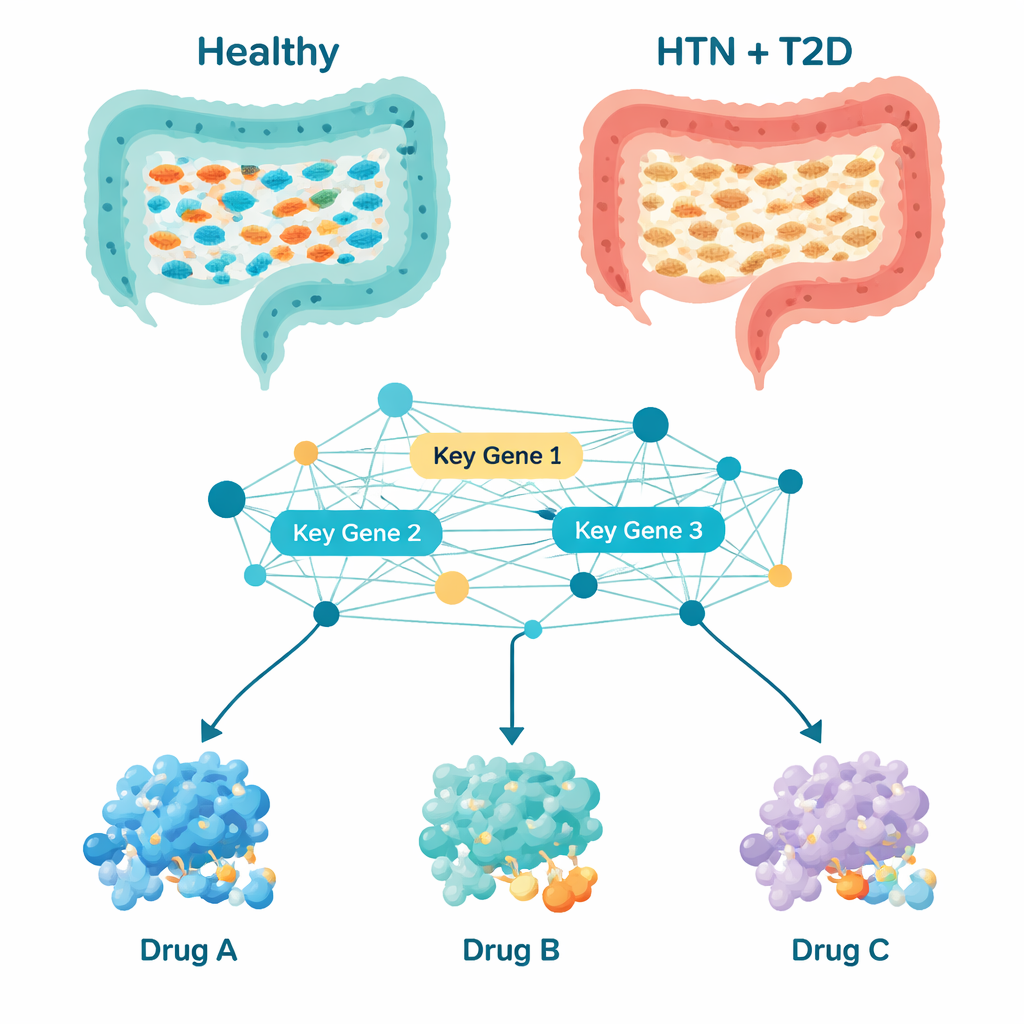
Los investigadores analizaron muestras de heces de 124 adultos, comparando a 29 personas con hipertensión y diabetes tipo 2 con 95 voluntarios sanos. Mediante secuenciación genética de marcadores bacterianos, construyeron un retrato detallado de qué microbios estaban presentes y de la diversidad de la comunidad intestinal de cada persona. Las personas con ambas afecciones presentaron comunidades bacterianas más ricas y más equitativamente distribuidas que se agruparon por separado de las de los individuos sanos, lo que indica que sus ecosistemas intestinales estaban claramente reorganizados y no simplemente ligeramente alterados.
Un cambio microbiano de lo beneficioso a lo perjudicial
Al centrarse en qué tipos de bacterias eran más abundantes, el equipo observó un patrón claro. En las personas sanas eran comunes bacterias que ayudan a producir ácidos grasos de cadena corta —compuestos conocidos por mantener la salud del revestimiento intestinal y por ayudar a controlar la inflamación y el metabolismo—. Entre ellas figuraban grupos como Bacteroides, Prevotella, Roseburia y Akkermansia. En las personas con hipertensión y diabetes, muchas de estas bacterias beneficiosas estaban disminuidas. Al mismo tiempo, aumentaron bacterias que en otros estudios se han vinculado con inflamación y desequilibrios metabólicos, como Megasphaera, Lactobacillus, Streptococcus y Veillonella. Diecinueve grupos bacterianos fueron consistentemente diferentes entre pacientes y controles sanos, lo que sugiere un cambio coordinado hacia un entorno intestinal que podría favorecer la inflamación de bajo grado y el estrés metabólico.
De microbios a «mandos de control» moleculares
Contar microbios por sí solo no explica cómo influyen en el organismo, por lo que los científicos usaron herramientas computacionales para inferir qué están probablemente haciendo las bacterias intestinales. Predijeron qué vías metabólicas —cadenas de reacciones químicas— estaban más o menos activas en los pacientes. De más de mil vías, 195 destacaron como alteradas. Muchas estaban relacionadas con cómo las bacterias fabrican proteínas, procesan energía y manejan bloques básicos como nucleótidos y aminoácidos. Al construir una red de interacción de las proteínas bacterianas correspondientes, el equipo identificó diez genes “hub” que ocupaban puestos clave en esa red. Estos genes, con nombres como gltB, gyrB, fusA y mdh, actúan como mandos de control para funciones bacterianas esenciales como la producción de energía, la replicación del ADN, la síntesis proteica y el metabolismo de ácidos grasos y nucleótidos. Dado que estas actividades están estrechamente ligadas a la inflamación, la salud vascular y el control de la glucosa, los cambios en estos genes microbianos podrían propagarse hacia fuera y afectar la presión arterial y el azúcar en sangre.
Búsqueda de nuevos usos para fármacos existentes
Con esa lista de genes bacterianos de control, los investigadores recurrieron a cribado computacional de fármacos. Reunieron 189 fármacos ya estudiados para hipertensión, diabetes tipo 2 o problemas metabólicos relacionados, y usaron acoplamiento molecular —esencialmente un rompecabezas 3D— para ver qué compuestos podrían unirse con mayor afinidad a las proteínas producidas por los diez genes bacterianos clave. Tres candidatos destacaron: Naringina y Neohesperidina, compuestos vegetales presentes en cítricos, y Bromocriptina, un fármaco ya aprobado para la diabetes tipo 2. Simulaciones detalladas durante 100 billonésimas de segundo sugirieron que los complejos que incluían Neohesperidina y Bromocriptina eran especialmente estables, lo que significa que estos fármacos podrían unirse y afectar de forma fiable a las proteínas bacterianas objetivo en la práctica. Comprobaciones adicionales sobre las propiedades tipo fármaco de estos compuestos y sobre cómo podrían ser absorbidos, distribuidos y eliminados por el organismo señalaron a la Bromocriptina como la candidata más práctica a corto plazo, aunque los tres requerirán estudios cuidadosos de seguridad y dosificación.
Qué significa esto para la atención futura
En términos sencillos, este trabajo traza una cadena de tres pasos: las personas con hipertensión y diabetes tipo 2 tienden a tener un microbioma intestinal distinto; ese microbioma contiene un conjunto de genes bacterianos que pueden empujar el metabolismo y los vasos sanguíneos en direcciones perjudiciales; y algunos fármacos existentes parecen capaces de dirigirse a esos genes bacterianos. El estudio no demuestra que cambiar estos microbios o sus genes cure la enfermedad, ni prueba tratamientos en pacientes. Pero establece un plano para diagnósticos y terapias basados en el microbioma, donde algún día los médicos podrían modificar las bacterias intestinales o usar fármacos a medida para aliviar la carga combinada de hipertensión y diabetes.
Cita: Rahat, M.T.I., Sumi, M.S.A., Nurejannath, M. et al. Identification of bacterial key genes and therapeutic targets in hypertensive patients with type 2 diabetes through bioinformatics analysis. Sci Rep 16, 6431 (2026). https://doi.org/10.1038/s41598-026-36467-5
Palabras clave: microbioma intestinal, hipertensión, diabetes tipo 2, genes bacterianos, reposicionamiento de fármacos