Clear Sky Science · es
ONCOPLEX: un modelo de hipergráfica inspirado en la oncología que integra diversos conocimientos biológicos para la predicción de genes conductores del cáncer
Por qué importa esta investigación
El cáncer está impulsado por un pequeño número de cambios genéticos potentes ocultos entre miles de alteraciones inocuas. Encontrar esos genes “conductores” verdaderamente peligrosos es esencial para mejorar el diagnóstico y los tratamientos dirigidos, pero es como detectar a unos pocos instigadores en una multitud vasta y ruidosa. Este estudio presenta ONCOPLEX, un nuevo marco de inteligencia artificial que observa los genes no de uno en uno, sino en el contexto de las vías biológicas en las que actúan conjuntamente, ofreciendo una forma más nítida de identificar los genes que realmente alimentan los tumores.
Ver los genes del cáncer en sus vecindarios biológicos
La mayoría de los métodos actuales examinan los genomas de cáncer en busca de mutaciones que aparezcan con frecuencia inusual o que destaquen en redes génicas simples. Estos enfoques ayudan, pero la biología rara vez es tan simple. Los genes suelen actuar en grupos dentro de vías que controlan el crecimiento celular, la reparación del ADN y muchos otros procesos. ONCOPLEX asume esta complejidad representando los genes como puntos y las vías como grupos superpuestos más grandes que pueden contener muchos genes a la vez. Este tipo de estructura, conocida como hipergráfica, permite al modelo considerar relaciones multi-génicas directamente en lugar de descomponerlas en muchos pares separados.
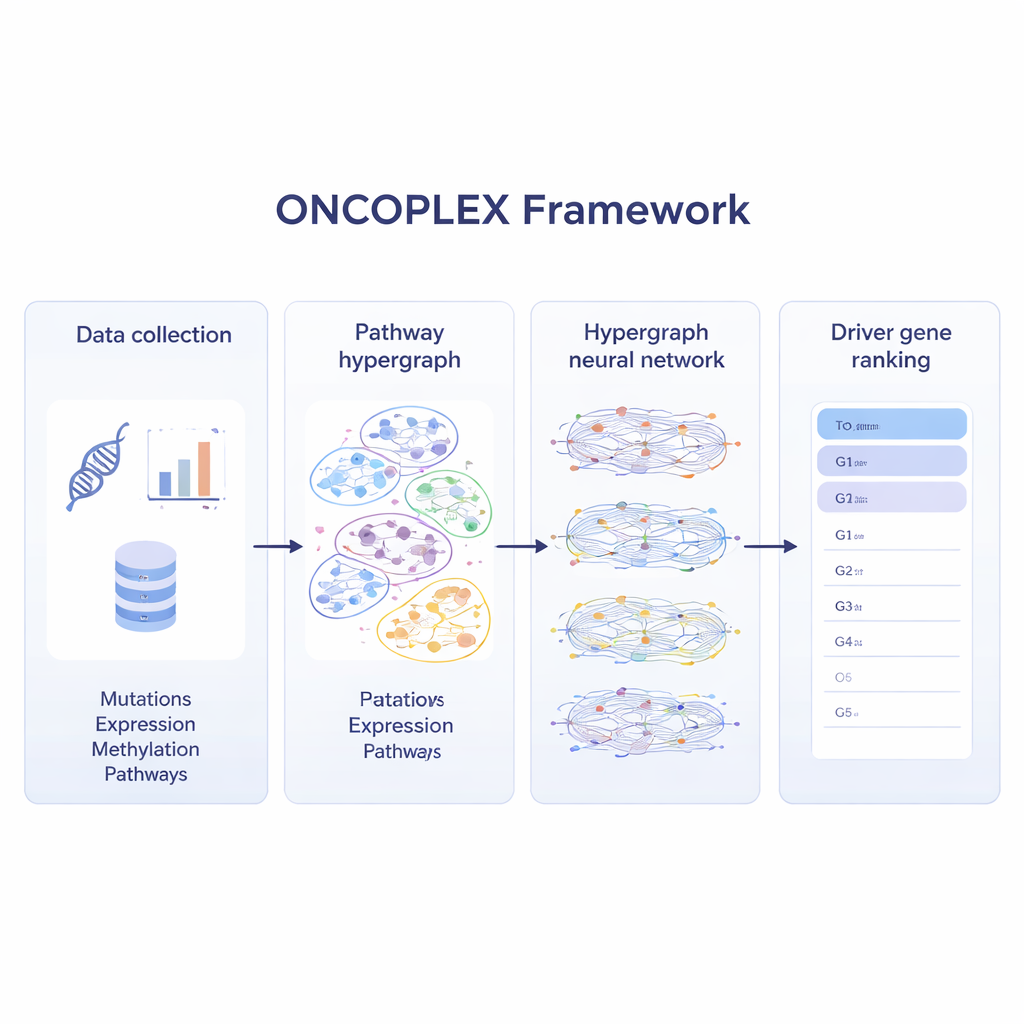
Combinando muchas capas de datos sobre el cáncer
Para aprovechar al máximo los conjuntos de datos modernos sobre cáncer, ONCOPLEX integra varios tipos de información sobre cada gen. Utiliza frecuencias de mutación, cambios en la actividad génica, marcas químicas sobre el ADN (metilación) y un conjunto amplio de características biológicas como la conservación evolutiva y anotaciones funcionales. Estas características se asignan a cada gen en la hipergráfica. Una red neuronal especializada luego transmite información a través de las vías, permitiendo que la representación de cada gen se forme tanto por sus propios datos como por el comportamiento de los genes con los que coopera. El modelo se entrena usando genes ya conocidos como conductores del cáncer, mientras también aprende de muchos genes no etiquetados que podrían ser importantes pero aún no reconocidos.
Superando herramientas existentes en muchos cánceres
Los investigadores probaron ONCOPLEX con datos de The Cancer Genome Atlas, tanto agrupando muchos tipos tumorales como examinando 11 cánceres individuales, incluidos mama, pulmón, hígado, vejiga y cabeza y cuello. Lo compararon con varios métodos líderes basados en grafos e hipergráficas. En general, ONCOPLEX fue mejor distinguiendo genes conductores conocidos de los no conductores mucho más comunes y en situar los posibles conductores en los primeros puestos de sus listados. Su ventaja fue especialmente evidente al observar los genes mejor clasificados, donde la identificación precisa es más valiosa para experimentos posteriores y la traducción clínica.
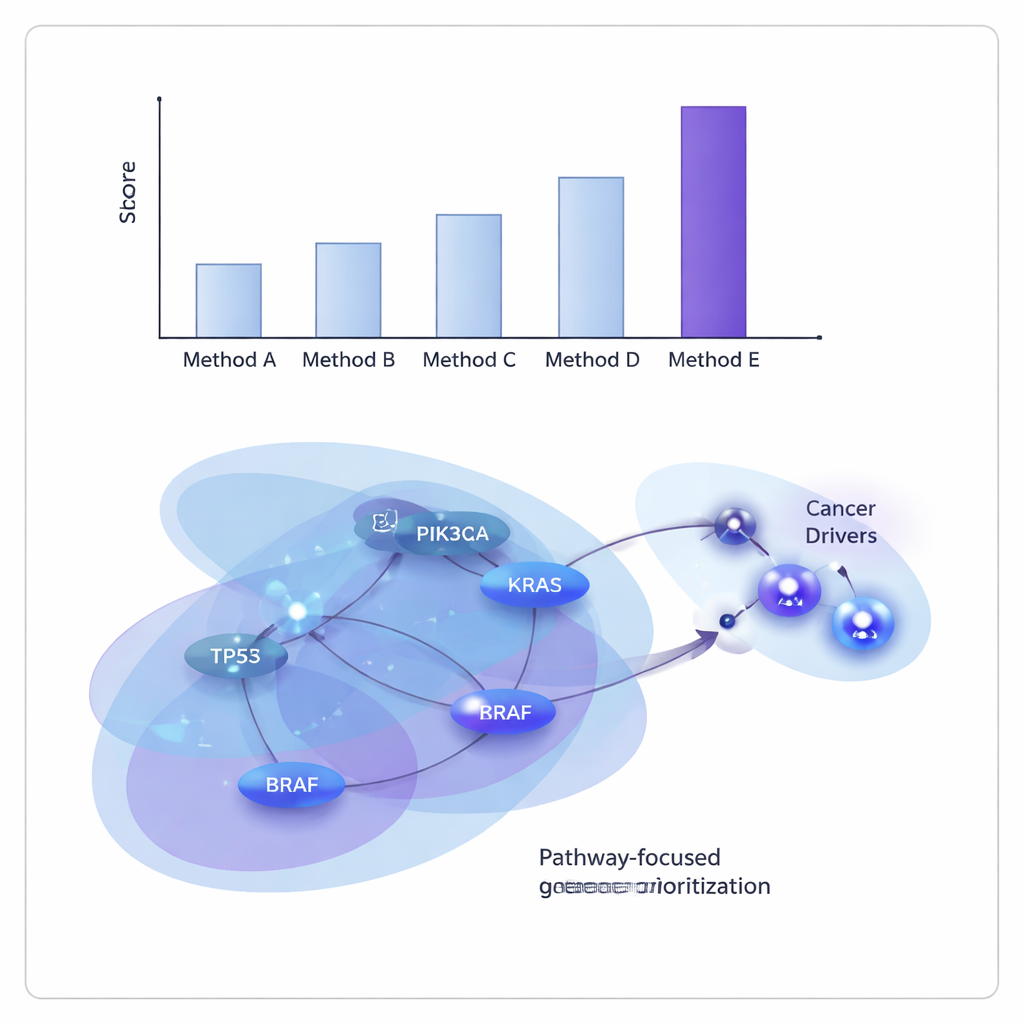
Revelando culpables compartidos y específicos de cada cáncer
Más allá de los números de rendimiento bruto, las listas ordenadas de genes de ONCOPLEX recuperaron muchos genes de cáncer conocidos, como KRAS, BRAF y miembros de la vía de señalización PI3K–AKT, confirmando que el modelo captura biología bien establecida. También señaló candidatos prometedores que aún no están firmemente reconocidos como conductores en ciertos tipos de cáncer, incluidos genes como GRB2 y MAPK3 en cáncer de mama y SHC1 en cáncer de estómago. Cuando el equipo examinó los genes mejor clasificados mediante análisis de enriquecimiento de vías, encontró firmas claras de vías de cáncer bien conocidas, incluidas la señalización ErbB y PI3K–AKT–mTOR, así como vías relacionadas con el sistema inmunitario, lo que sugiere que ONCOPLEX está enfocándose en redes que tienen relevancia clínica.
Fortalezas, límites y próximos pasos
Al mostrar que características biológicas más ricas mejoran de forma constante sus predicciones, ONCOPLEX demuestra el valor de fusionar múltiples fuentes de datos dentro de un marco centrado en las vías. Al mismo tiempo, el estudio descubre una limitación: dado que muchos cánceres comparten un gran número de vías, el modelo a veces favorece genes de acción amplia “pan-cáncer” por encima de aquellos que son verdaderamente específicos de un tipo tumoral. Los autores sugieren que trabajos futuros deberían refinar cómo se utiliza la información de vías para que las señales comunes y las específicas del cáncer puedan separarse con mayor claridad.
Qué significa esto para pacientes y clínicos
Para el público no especializado, la conclusión clave es que ONCOPLEX ofrece una forma más biológicamente realista de buscar los genes que impulsan el cáncer. Al observar los genes en la compañía que mantienen —dentro de vías en lugar de aisladamente—, mejora nuestra capacidad de detectar tanto conductores bien conocidos como previamente pasados por alto, incluso en cánceres sobre los que actualmente se sabe poco. Este tipo de herramienta puede ayudar a los investigadores a priorizar qué genes estudiar en el laboratorio, guiar la búsqueda de nuevos objetivos farmacológicos y, en última instancia, apoyar estrategias de tratamiento más precisas y conscientes de las vías en oncología.
Cita: Alotaibi, E.M., Alkhnbashi, O.S. & Tran, V.D. ONCOPLEX: an oncology-inspired hypergraph model integrating diverse biological knowledge for cancer driver gene prediction. Sci Rep 16, 5164 (2026). https://doi.org/10.1038/s41598-026-36127-8
Palabras clave: genes conductores del cáncer, redes neuronales en hipergráficas, integración multi-ómica, análisis de vías, oncología de precisión