Clear Sky Science · es
Diversidad genética y dinámica de transmisión del SARS-CoV-2 en África Oriental
Por qué importa esta historia de viajes virales
Cuando el COVID-19 se extendió por el mundo, no lo hizo al azar. Siguió a las personas por carreteras, rutas comerciales y trayectos aéreos. Este estudio examina de cerca cómo el coronavirus se propagó y evolucionó en África Oriental entre 2020 y 2022, usando pistas genéticas del propio virus. Al reconstruir el recorrido del virus por países como Kenia, Uganda, Ruanda, Burundi, Sudán del Sur y la República Democrática del Congo (RDC), los investigadores muestran cómo los desplazamientos cotidianos de conductores de camiones, comerciantes y refugiados ayudaron a dar forma a la pandemia y qué significa eso para proteger la región frente a futuros brotes.
Siguiendo al virus a través de sus huellas genéticas
Copia tras copia, el coronavirus lleva un código genético que cambia ligeramente a medida que se transmite de persona a persona. Al recopilar y comparar más de 11.000 genomas virales de alta calidad de África Oriental, el equipo pudo determinar qué versiones del virus aparecieron dónde y cuándo. La mayoría de las secuencias procedían de Kenia y la RDC, con Uganda también bien representada; Ruanda, Burundi y Sudán del Sur presentaron muchas menos muestras, lo que refleja una menor capacidad de pruebas y secuenciación. Aun así, los datos combinados ofrecieron una instantánea poderosa de cómo se desarrolló la pandemia en la región y de cómo los movimientos internacionales alimentaron brotes locales.
Olas de nuevas variantes en la región
Con estas secuencias, los investigadores trazaron cómo distintas variantes de COVID-19 surgieron y decrecieron a lo largo del tiempo. Las formas tempranas del virus fueron pronto reemplazadas por versiones mejor adaptadas como Beta, Delta y, más tarde, Ómicron, reflejando las tendencias globales. Kenia registró de forma constante el mayor número y la mayor mezcla de variantes, con picos claros durante la ola Delta en 2021 y el aumento de Ómicron en 2022. Uganda y la RDC mostraron olas notables pero más pequeñas, mientras que Ruanda, Burundi y Sudán del Sur reportaron solo una diversidad limitada de variantes —probablemente una combinación de menos infecciones detectadas y menos muestras secuenciadas. En conjunto, la región experimentó olas ampliamente sincronizadas, lo que sugiere que cuando una nueva variante llegaba a un país no permanecía mucho tiempo aislada allí.
Un árbol familiar enredado que ignora las fronteras
Para entender cómo se relacionaban estas variantes, el equipo construyó un gran “árbol familiar” de los genomas virales. En vez de encontrar agrupaciones ordenadas limitadas a un solo país, hallaron ramas donde las secuencias de Kenia, Uganda, Ruanda, Burundi, Sudán del Sur y la RDC estaban completamente mezcladas. Cinco grandes conglomerados genéticos contenían muestras de varios países, lo que apunta a introducciones repetidas y a una propagación transfronteriza en lugar de epidemias nacionales aisladas. Kenia y Uganda, que aportaron la mayor cantidad de secuencias, aparecían a lo largo de todo el árbol, mientras que los países más pequeños aparecían en menos lugares pero aun así compartían linajes con sus vecinos. La imagen que emerge es la de una epidemia regional entrelazada por los desplazamientos a lo largo de carreteras y por ciudades fronterizas, no de brotes separados y sellados.
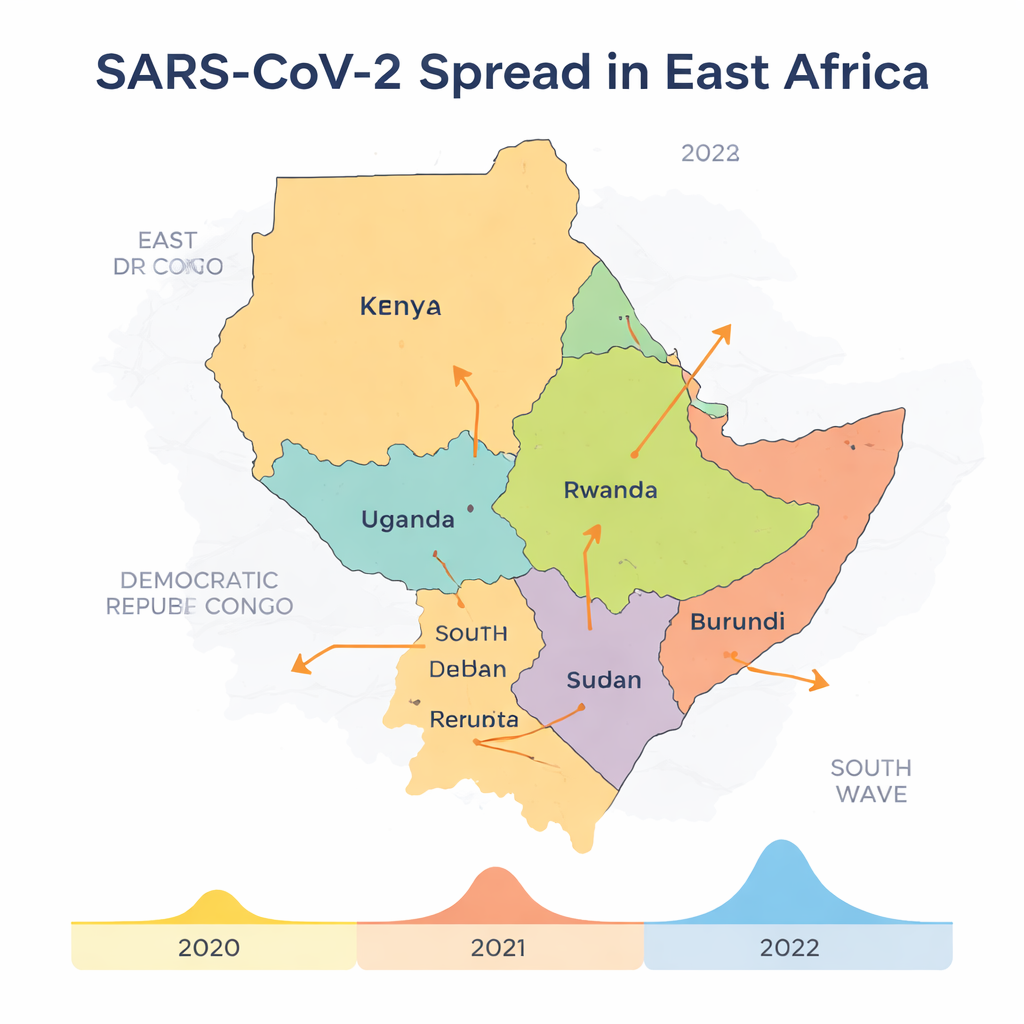
Carreteras, camiones y refugiados como autopistas ocultas
Combinando este árbol genético con mapas y cronologías, los investigadores trazaron las direcciones probables de propagación. Kenia surgió como una fuente clave de infecciones para la RDC, Uganda y Sudán del Sur, con movimientos virales adicionales entre la RDC y Uganda y desde Ruanda hacia Sudán del Sur. Este patrón encaja con el papel de Kenia como principal centro de comercio y transporte de África Oriental, con carreteras, puertos y aeropuertos muy activos que permanecieron al menos parcialmente operativos incluso durante los confinamientos. Los conductores de camiones de larga distancia y los manipuladores de carga, que a menudo estaban exentos de las prohibiciones estrictas de viaje, se convirtieron en portadores involuntarios del virus a través de las fronteras. Al mismo tiempo, las fronteras terrestres porosas, los puntos de cruce informales y los movimientos de refugiados —especialmente entre la RDC, Uganda, Ruanda y Sudán del Sur— crearon muchas oportunidades para que el virus sorteara los controles oficiales y los filtros sanitarios.
Lecciones para la próxima pandemia
Para el público general, el mensaje clave es simple pero contundente: los virus prestan mucha atención a cómo nos movemos. En África Oriental, el COVID-19 no se detuvo en los puestos fronterizos; fluyó por los corredores comerciales y las rutas migratorias, con Kenia actuando como una estación de relevo importante. El estudio muestra que el seguimiento de los cambios genéticos del virus puede revelar estas rutas ocultas de propagación y señalar dónde es necesaria una cooperación más estrecha. Los autores sostienen que la preparación frente a pandemias futuras en la región debe centrarse en sistemas de salud fronterizos compartidos, mejor intercambio de datos y mayor acceso a pruebas genómicas, de modo que los países puedan detectar pronto nuevas amenazas y actuar de forma conjunta. En un mundo donde una infección puede cruzar un continente en días, la seguridad sanitaria de un país no puede separarse de la de sus vecinos.
Cita: Nabisubi, P., Kanyerezi, S., Agasi, H. et al. Genetic diversity and transmission dynamics of SARS-CoV-2 in East Africa. Sci Rep 16, 5235 (2026). https://doi.org/10.1038/s41598-026-36094-0
Palabras clave: COVID-19, variantes de SARS-CoV-2, África Oriental, vigilancia genómica, transmisión transfronteriza