Clear Sky Science · es
Análisis a nivel de haplotipos de metabarcoding de ADN ambiental reveló la biogeografía y filogeografía de peces de agua dulce en la Península de Corea
Leer los ríos a través de pistas invisibles
Los ríos y arroyos pueden parecer limpios a simple vista, pero están llenos de rastros microscópicos de vida. Este estudio muestra cómo los científicos pueden leer esa “tinta” genética invisible en el agua para descubrir qué peces viven en cada lugar, cómo se relacionan sus poblaciones a lo largo de la Península de Corea e incluso si algunos peces han sido trasladados por personas de una región a otra. El trabajo ofrece una visión de cómo los conservacionistas pronto podrán monitorear la biodiversidad y proteger especies raras sin lanzar una sola red.
Pescar con ADN, no con redes
En lugar de capturar peces, los investigadores recolectaron botellas de agua de un litro de tres arroyos pequeños —Seom, Gilan y Oshipcheon—, cada uno situado en una región biogeográfica distinta de Corea del Sur. En estas muestras buscaron ADN ambiental (eDNA): diminutos fragmentos de material genético que los peces liberan a través de la piel, los desechos y el moco. Usando una técnica llamada metabarcoding, amplificaron y secuenciaron un fragmento corto de ADN de peces y luego compararon millones de lecturas con bases de datos de referencia para identificar qué especies —e incluso qué variantes genéticas, o haplotipos— estaban presentes en cada arroyo.
¿Quién vive dónde en los arroyos de Corea?
A partir de solo 54 muestras de agua tomadas en nueve sitios, el equipo detectó 107 variantes de ADN distintas que representan 76 especies de peces —alrededor de un tercio de todos los peces de agua dulce conocidos en Corea. El arroyo Seom, un río de menor altitud vinculado al Mar Amarillo, albergó la comunidad ictiológica más rica, con 49 especies. Gilan y Oshipcheon, afluentes más altos y empinados que fluyen hacia costas diferentes, albergaban cada uno 28 especies. Muchos peces se compartían entre arroyos, pero casi 30 especies resultaron ser endémicas de los hábitats de agua dulce de Corea, y cada arroyo también presentó su propio conjunto único de especies. En general, los patrones coincidieron con el conocimiento de larga data de que la vida de agua dulce de Corea está dividida en tres regiones principales por las cadenas montañosas y la historia geológica.
Huellas genéticas y traslados ocultos
Porque los científicos trabajaron a nivel de haplotipo —las “variantes” finas del ADN dentro de una especie— pudieron hacer más que listar especies; pudieron comparar poblaciones. Varios peces nativos comunes mostraron claras diferencias genéticas entre regiones, lo que indica separación de larga data y mezcla natural limitada a lo largo de la península. Al mismo tiempo, los datos de ADN revelaron probables casos de movimiento asistido por humanos. Para especies como Pungtungia herzi, Coreoleuciscus splendidus y Nipponocypris koreanus, los patrones de haplotipos en el arroyo oriental Oshipcheon coincidían estrechamente con los de ríos occidentales o meridionales, lo que apunta a repoblaciones o traslados pasados. Al reconstruir virtualmente “árboles genealógicos” de estas variantes de ADN, el equipo pudo inferir las regiones probables de origen de los peces trasladados —ofreciendo una especie de forense genética para la gestión fluvial.
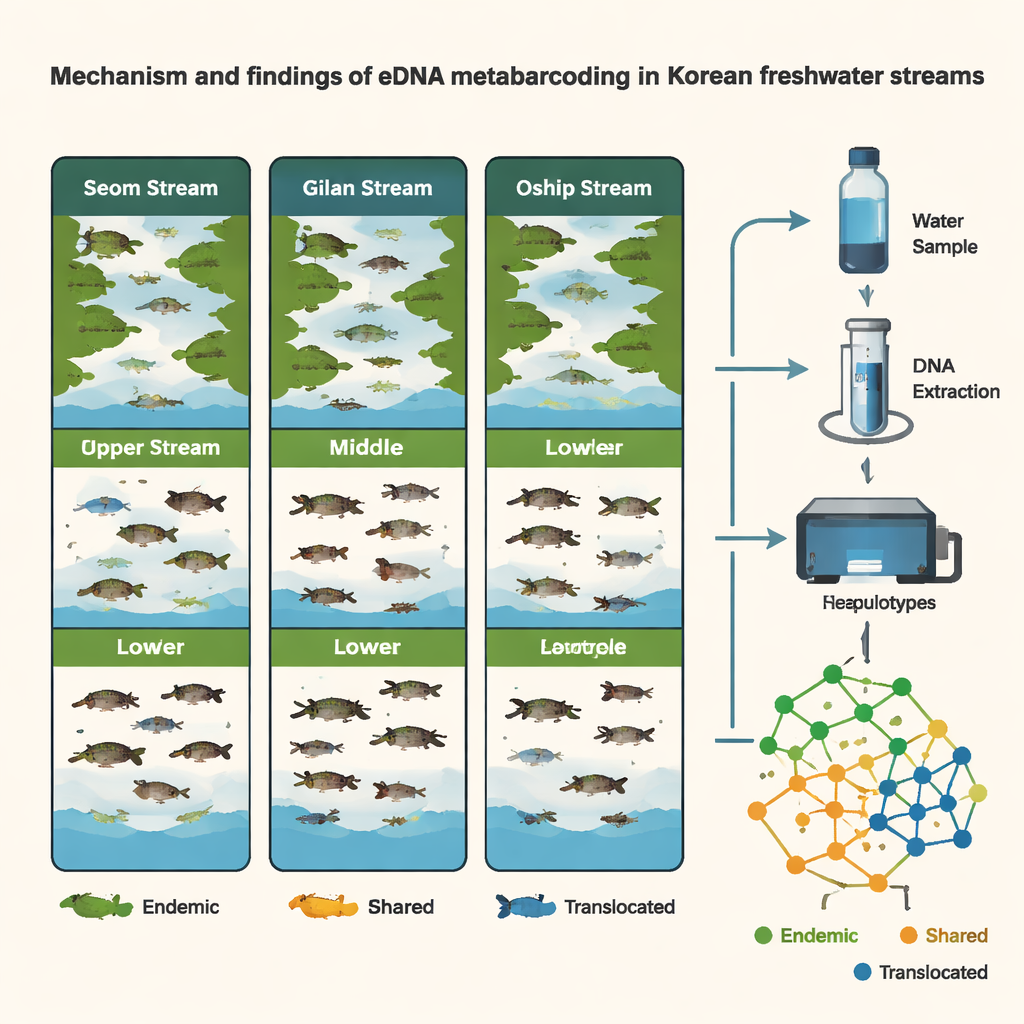
Estaciones, hábitats y objetivos en movimiento
El estudio también siguió cómo cambiaban las comunidades de peces en el tiempo y el espacio. Comparando muestras recogidas a finales del invierno (marzo) y en verano (agosto), los investigadores hallaron una mayor riqueza de especies en verano y claros cambios estacionales, especialmente en el arroyo Seom. En Oshipcheon, el eDNA de especies migratorias —como salmones y otros peces que se mueven entre río y mar— apareció y desapareció de formas que coincidían con sus ciclos de vida conocidos. Sorprendentemente, dentro de cada sitio, rápidos, tramos de corriente y pozas no mostraron diferencias marcadas en el ADN de peces, probablemente porque el flujo de agua mezcla lateralmente el eDNA a través de estos pequeños canales. En cambio, los contrastes principales se encontraron entre diferentes secciones del arroyo (superior, medio, inferior) y entre los tres arroyos, subrayando la importancia del punto a lo largo del río donde se toman las muestras.
Qué significa esto para la protección de la vida de agua dulce
En términos sencillos, esta investigación demuestra que una botella de agua de río puede revelar una instantánea detallada de quién vive en el arroyo, cómo las poblaciones locales de peces están relacionadas a través de grandes regiones y si las personas han alterado esos patrones al mover peces. Para la conservación, eso significa que los gestores pueden monitorear rápidamente especies raras y endémicas, detectar peces invasores y trasladados y seguir cambios estacionales en poblaciones migratorias sin trabajo de campo intensivo ni daño a los animales. Aunque el eDNA aún no puede reemplazar por completo los estudios genéticos tradicionales, ofrece una herramienta poderosa y de bajo impacto para vigilar la biodiversidad de agua dulce en un mundo que se calienta y está fuertemente gestionado —y para asegurar que los peces fluviales únicos de Corea continúen prosperando en sus hogares nativos.
Cita: Amin, M.H.F., Kim, A.R., Jang, J.E. et al. Haplotype-level analysis of environmental DNA metabarcoding revealed the biogeography and phylogeography of freshwater fishes in Korean Peninsula. Sci Rep 16, 6955 (2026). https://doi.org/10.1038/s41598-026-36043-x
Palabras clave: ADN ambiental, peces de agua dulce, biodiversidad, ríos coreanos, genética de la conservación