Clear Sky Science · es
IL2Pepscan: Un marco de aprendizaje automático para predecir péptidos que inducen IL-2 y su identificación en proteomas virales globales
Enseñar al sistema inmunitario con diminutos fragmentos proteicos
Las vacunas modernas y las terapias contra el cáncer dependen cada vez más de orientar con precisión al sistema inmunitario en lugar de atacar la enfermedad con fármacos de forma indiscriminada. Este estudio explora cómo se pueden seleccionar pequeños fragmentos de proteínas, llamados péptidos, para activar un mensajero inmunitario potente: la interleucina‑2 (IL‑2). Mediante modelos informáticos avanzados, los autores rastrean tanto datos inmunológicos conocidos como los catálogos proteicos de miles de virus para encontrar “agujas” peptídicas en un pajar molecular que podrían ayudar a diseñar mejores vacunas e inmunoterapias.
Por qué la IL-2 importa para la salud y la enfermedad
La IL‑2 es una pequeña molécula de señalización que actúa como factor de crecimiento para células inmunitarias clave conocidas como linfocitos T. Cuando estas células encuentran por primera vez una amenaza —como un virus o una célula cancerosa— pueden liberar IL‑2, que a su vez fomenta la multiplicación de los linfocitos T, su especialización y la formación de memoria frente al invasor. La IL‑2 también contribuye a mantener las células T reguladoras que impiden que el sistema inmunitario ataque los propios tejidos del organismo. Por este doble papel, la IL‑2 se ha utilizado como fármaco para tratar cánceres como el melanoma y se investiga en enfermedades autoinmunes. Sin embargo, administrar IL‑2 directamente puede resultar duro para los pacientes, por lo que hay un interés creciente en diseñar péptidos seguros que induzcan la producción de IL‑2 de forma más controlada y dirigida.
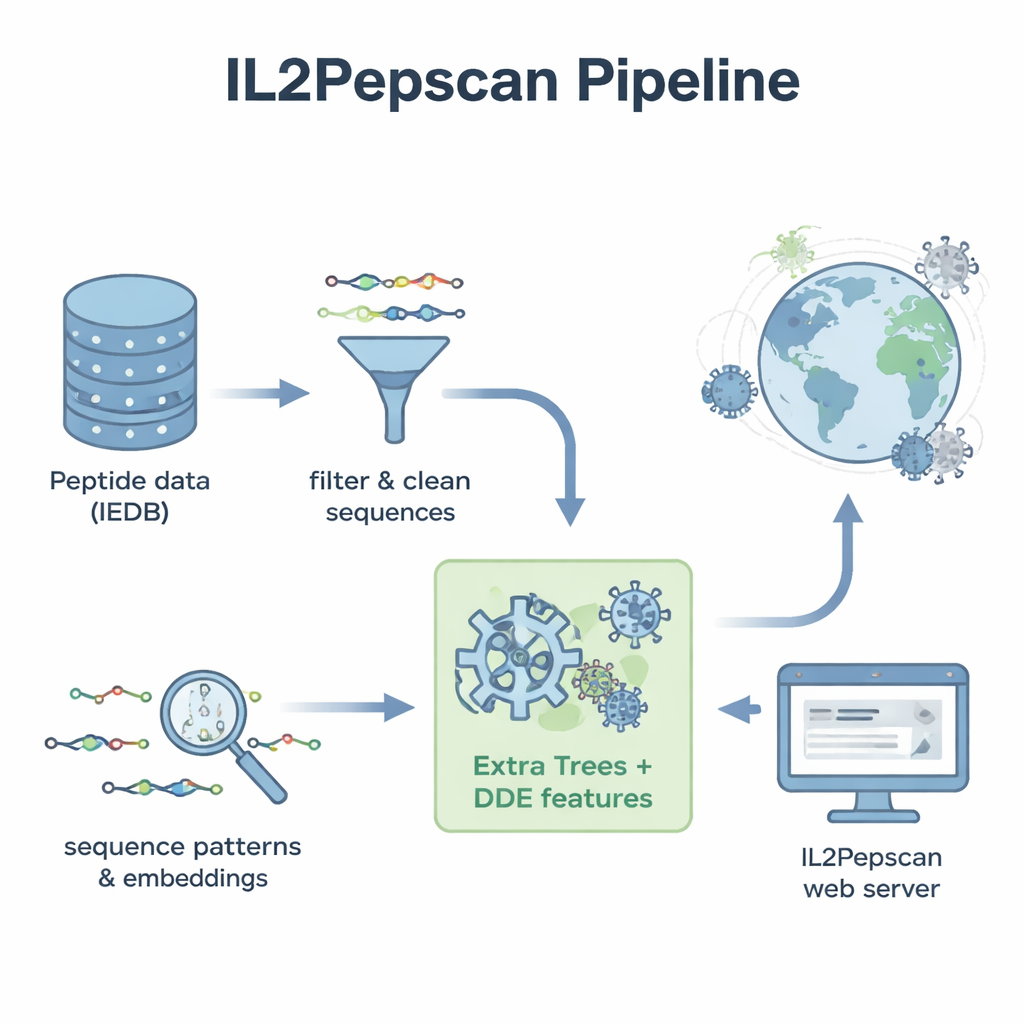
Aprender el “sabor” de los péptidos que inducen IL-2
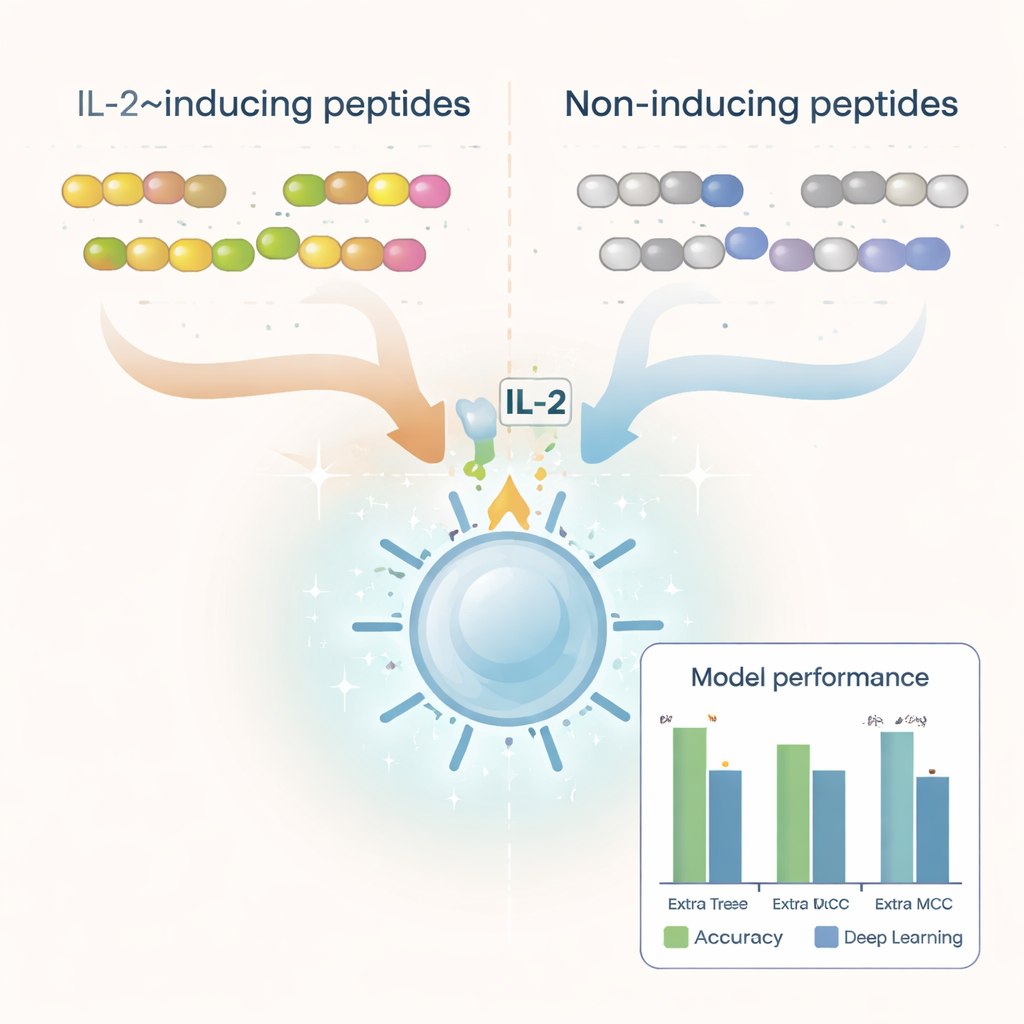
Los investigadores partieron de miles de secuencias peptídicas ya evaluadas en experimentos de laboratorio y etiquetadas como inductoras de IL‑2 o no inductoras. Limpiaron este conjunto de datos para eliminar duplicados, bloques constructores inusuales y péptidos demasiado cortos o largos, obteniendo más de 6.000 ejemplos bien caracterizados. Al examinar los bloques constructores (aminoácidos) que componen estos péptidos, descubrieron diferencias claras entre ambos grupos. Los péptidos inductores de IL‑2 tendían a ser más ricos en aminoácidos hidrofóbicos, o que repelen el agua, como la leucina y la alanina, mientras que los no inductores se inclinaban hacia residuos más polares y cargados. Ciertos patrones cortos, o motivos, como “LEGS” y “ALEG”, aparecían solo en péptidos inductores de IL‑2, lo que sugiere firmas estructurales que pueden favorecer la activación inmunitaria.
Entrenar máquinas para detectar patrones que refuerzan la inmunidad
Para convertir estos patrones en una herramienta de predicción práctica, el equipo transformó cada péptido en descripciones numéricas que capturan su composición y el orden de sus aminoácidos. Probaron una variedad de métodos de aprendizaje automático —incluidos algoritmos populares como bosques aleatorios, máquinas de vectores de soporte y árboles potenciados— junto con arquitecturas de aprendizaje profundo que se usan a menudo en tareas de lenguaje e imagen. También aprovecharon un gran «modelo de lenguaje» para proteínas llamado ProtBERT, entrenado originalmente con cientos de millones de secuencias proteicas, y lo ajustaron para reconocer mejor señales relacionadas con IL‑2. Tras pruebas extensas con validación cruzada y un conjunto de prueba independiente, el mejor rendimiento lo obtuvo un modelo llamado Extra Trees combinado con un conjunto de características conocido como desviación de dipeptido respecto a la media esperada (DDE). Este modelo alcanzó casi un 80% de precisión y una sólida puntuación de correlación, superando a múltiples enfoques de aprendizaje profundo.
Rastreando el mundo viral en busca de desencadenantes inmunitarios ocultos
Con su mejor modelo, los autores ampliaron considerablemente la búsqueda. Reunieron secuencias proteicas de referencia de más de 14.000 virus, dividieron estas proteínas en unos 156 millones de péptidos superpuestos y pidieron al modelo que predijera cuáles podrían inducir IL‑2. Entre los candidatos con mayor puntuación se encontraban péptidos de familias virales bien conocidas, como flavivirus —virus del Nilo Occidental, Zika, fiebre amarilla y hepatitis C— así como de influenza y SARS‑CoV‑2. Muchos péptidos prometedores procedían de proteínas de envoltura o de la nucleocápside viral, los mismos tipos de proteínas que otros estudios han mostrado que pueden provocar respuestas de IL‑2 en animales. El modelo también señaló péptidos potencialmente inductores de IL‑2 codificados por bacteriófagos, virus que infectan bacterias, lo que apunta a un paisaje aún más amplio de secuencias relevantes para la inmunidad.
Del algoritmo a una herramienta accesible
Para que su trabajo fuera útil más allá del laboratorio informático, los autores construyeron un servidor web público llamado IL2Pepscan. Los investigadores pueden pegar secuencias de péptidos o proteínas en el sitio para estimar su potencial de inducir IL‑2, diseñar nuevas variantes mediante mutaciones en posiciones concretas, escanear proteínas completas en busca de puntos calientes o buscar motivos vinculados a IL‑2 ya conocidos. Aunque el estudio aún no confirma experimentalmente cada péptido predicho, la concordancia con hallazgos de laboratorio existentes sugiere que IL2Pepscan puede reducir de forma fiable la lista de candidatos para pruebas posteriores. Para los no especialistas, la conclusión es que algoritmos cuidadosamente entrenados pueden cribar enormes conjuntos de datos biológicos para identificar pequeños fragmentos proteicos que algún día podrían ayudar a que las vacunas y las inmunoterapias induzcan una respuesta inmunitaria más potente —y más precisa—.
Cita: Arora, P., Abhigyan, R., Periwal, N. et al. IL2Pepscan: A machine learning framework for predicting IL-2 inducing peptides and their identification across global viral proteomes. Sci Rep 16, 6701 (2026). https://doi.org/10.1038/s41598-026-35977-6
Palabras clave: interleucina-2, vacunas peptídicas, aprendizaje automático, proteoma viral, inmunoterapia