Clear Sky Science · es
Análisis estructural de la unión de OCT4 a nucleosomas humanos de LIN28B
Cómo las células acceden a instrucciones genéticas ocultas
Cada célula de tu cuerpo contiene el mismo ADN, sin embargo solo una fracción de esas instrucciones genéticas se utiliza en un tipo celular dado. Gran parte de este control proviene de cómo el ADN se empaqueta de forma compacta alrededor de proteínas llamadas histonas, formando estructuras conocidas como nucleosomas. Este empaquetamiento puede ocultar tramos clave de ADN frente a la maquinaria celular que lee los genes. El estudio descrito aquí examina cómo una proteína especial, OCT4, consigue encontrar y unirse a su ADN diana incluso cuando ese ADN está enrollado y en parte oculto dentro de nucleosomas, un proceso central para la identidad de las células madre y la reprogramación celular.
Por qué importan los factores pioneros en las células madre
OCT4 pertenece a un grupo pequeño pero potente de proteínas llamadas factores de transcripción pioneros. A diferencia de la mayoría de las proteínas que se unen al ADN, los pioneros pueden acceder a regiones compactadas y “apagadas” del genoma y ayudar a activar genes, desempeñando un papel crucial en la configuración de la identidad celular y en la reprogramación de células adultas hacia estados parecidos a células madre. OCT4 actúa junto con socios como SOX2, KLF4 y c-MYC para inducir la pluripotencia, la propiedad que permite a las células madre convertirse en casi cualquier tipo celular. Comprender exactamente cómo OCT4 se agarra al ADN enrollado en nucleosomas es esencial para descifrar cómo las células cambian de destino y para diseñar formas más precisas de manipular la identidad celular en investigación y medicina.
Comprobar si las diferencias entre especies importan
La mayoría de los estudios estructurales de nucleosomas usan histonas de ranas (Xenopus laevis) o humanas, porque estas proteínas son muy similares pero no idénticas. Pequeñas diferencias en sus secuencias de aminoácidos podrían, en principio, alterar cómo se enrolla el ADN o cómo se unen proteínas regulatorias como OCT4. En trabajos anteriores, los autores mostraron que OCT4 se une a una secuencia reguladora específica del gen humano LIN28B cuando ese ADN está enrollado en nucleosomas hechos con histonas de rana. En el nuevo estudio se plantearon una pregunta simple pero importante: ¿se comporta OCT4 de la misma manera cuando los nucleosomas están formados por histonas humanas en lugar de histonas de rana?
Ensamblar y sondear nucleosomas de LIN28B
Para responder a esto, los investigadores reconstituyeron nucleosomas en el laboratorio usando un segmento de 182 pares de bases del ADN de LIN28B y histonas humanas o de rana, ensambladas mediante un cuidadoso método de “diálisis lenta” que imita condiciones celulares. Ensayos en gel confirmaron que ambos tipos de octámeros de histonas formaron nucleosomas de manera eficiente. A continuación examinaron cómo se posicionaban estos nucleosomas sobre el ADN de LIN28B. Tanto experimentos en gel como el corte de ADN seguido de secuenciación (MNase-seq) mostraron que el ADN de LIN28B puede adoptar múltiples posiciones sobre el núcleo de histonas, y este comportamiento no cambió si los nucleosomas se calentaban a temperatura corporal. Crucialmente, que las histonas provinieran de ranas o de humanos no produjo diferencias apreciables en cómo se posicionaba el ADN ni en la afinidad con la que OCT4 se unía.
Visualizar OCT4 sobre el nucleosoma
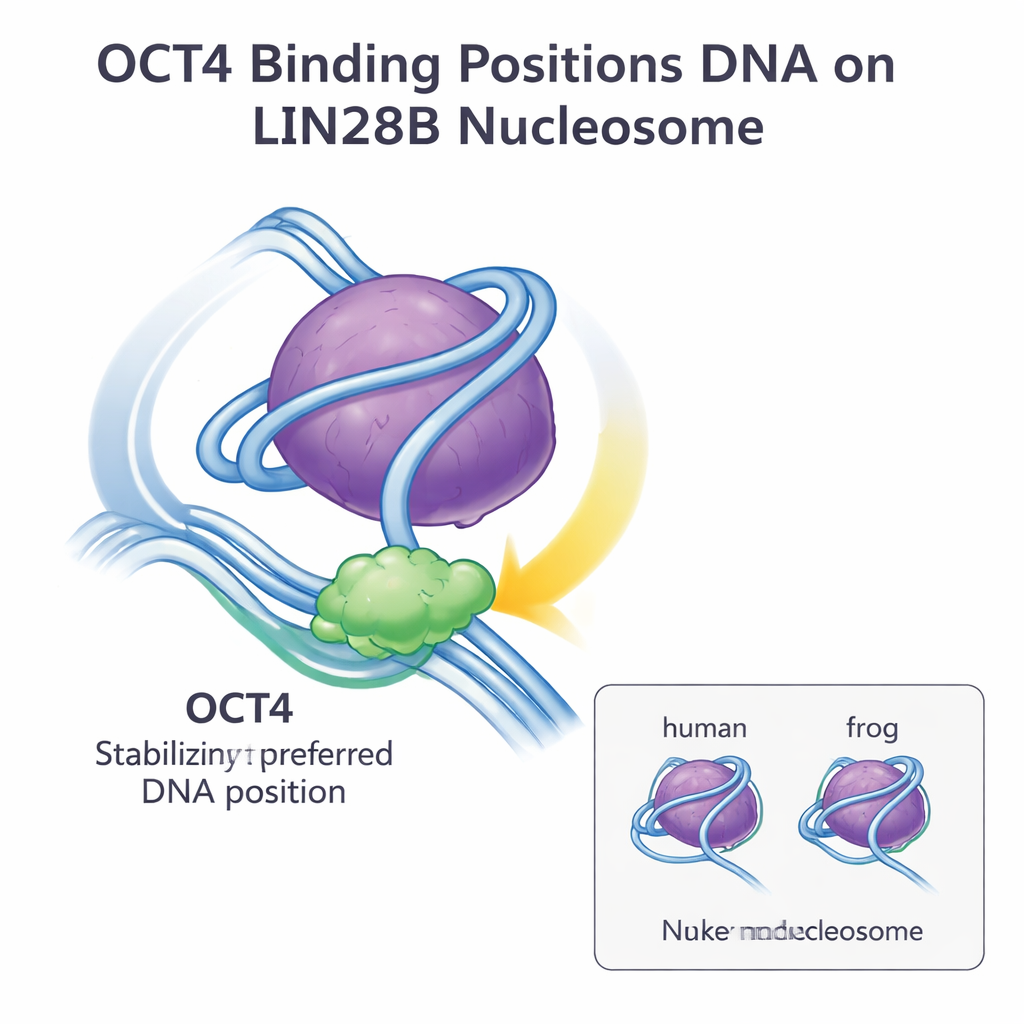
El equipo usó a continuación microscopía crioelectrónica (cryo-EM) para visualizar la estructura de OCT4 unido a nucleosomas de LIN28B que contenían histonas humanas. A partir de unas 15.000 partículas, reconstruyeron un mapa tridimensional a aproximadamente 6 angstroms de resolución. Las imágenes revelaron que ambas regiones de unión al ADN de OCT4 contactan el mismo tramo expuesto de ADN cerca del punto de entrada y salida del nucleosoma, la llamada región de enlace (linker). Este es exactamente el sitio y la orientación previamente observados cuando OCT4 estaba unido a nucleosomas hechos con histonas de rana. Al ajustar el modelo anterior en el nuevo mapa de cryo-EM, la concordancia fue excelente, lo que indica que la arquitectura general del complejo OCT4–nucleosoma LIN28B es esencialmente idéntica en ambas especies.
Una estrategia general para abrir la cromatina
En conjunto, estos hallazgos muestran que pequeñas diferencias en la secuencia entre histonas de rana y humanas no alteran cómo OCT4 reconoce y se une al nucleosoma de LIN28B. El ADN de LIN28B se sitúa de forma natural en varias posiciones posibles sobre el núcleo de histonas, pero la unión de OCT4 selecciona y estabiliza una posición preferida, haciendo que sitios de unión adicionales sean más accesibles para OCT4 y sus socios. Esta estrategia de “posicionamiento y estabilización del ADN” parece ser un modo general mediante el cual los factores pioneros acceden a la cromatina cerrada y promueven la unión cooperativa de otros reguladores. Para un público general, la conclusión es que el diseño básico del nucleosoma y la forma en que proteínas reguladoras clave como OCT4 interactúan con él están altamente conservados entre especies, lo que refuerza la idea de que los conocimientos obtenidos en organismos modelo pueden informar de forma fiable nuestra comprensión del control génico humano y de la biología de las células madre.
Cita: Sinha, K.K., Halic, M. Structural analysis of OCT4 binding to human LIN28B nucleosomes. Sci Rep 16, 5704 (2026). https://doi.org/10.1038/s41598-026-35959-8
Palabras clave: factores de transcripción pioneros, OCT4, estructura del nucleosoma, accesibilidad de la cromatina, regulación génica en células madre