Clear Sky Science · es
Marco de aprendizaje automático para el análisis del empalme alternativo del ARNm identifica una firma de progresión en el adenocarcinoma colorrectal
Por qué esta investigación importa para los pacientes
El cáncer colorrectal es uno de los tumores más frecuentes y mortales, y los médicos todavía tienen dificultades para predecir qué tumores permanecerán controlados y cuáles reaparecerán agresivamente tras el tratamiento. Este estudio introduce una nueva manera de leer señales ocultas en el ARN tumoral —los mensajes que las células usan para fabricar proteínas— y emplea aprendizaje automático para convertir esas señales en una puntuación de riesgo simple que podría ayudar a ajustar la intensidad del tratamiento para cada paciente.
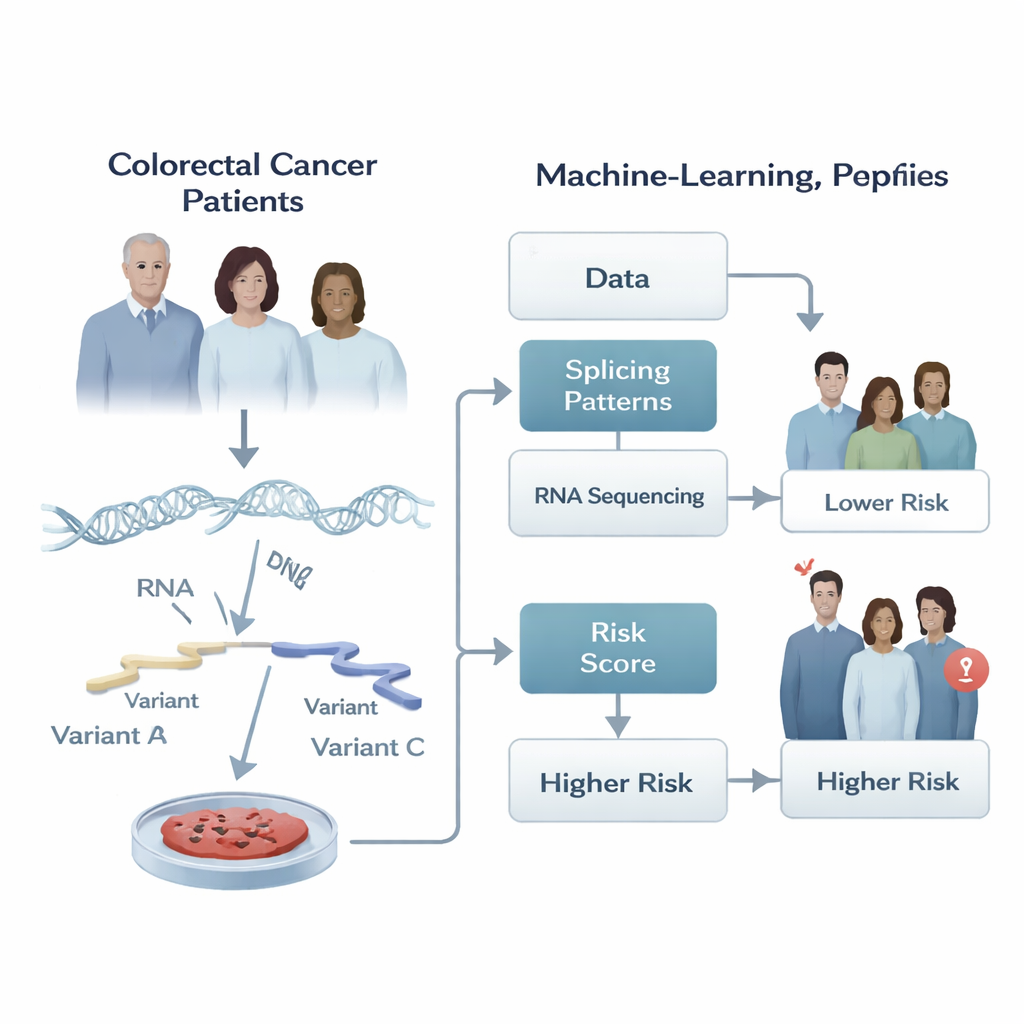
Cortes y ediciones ocultas en genes cancerosos
Nuestros genes no se leen de forma rígida. Cuando una célula copia el ADN en ARN, puede cortar y pegar fragmentos del mensaje de ARN en combinaciones distintas, un proceso llamado empalme alternativo. Esta edición permite que un mismo gen produzca varias versiones de una proteína, como diferentes herramientas de una misma caja. En células sanas, esta flexibilidad está estrictamente controlada. En el cáncer, sin embargo, el corte y el pegado pueden fallar, generando versiones de proteínas que ayudan a los tumores a crecer, diseminarse y resistir el tratamiento. Los autores supusieron que el patrón de estas ediciones del ARN en un tumor podría contener pistas potentes sobre cómo ese cáncer se comportará con el tiempo.
Convirtiendo patrones de ARN en una puntuación de riesgo
Los investigadores analizaron datos de secuenciación de ARN de tumores de 266 pacientes con adenocarcinoma colorrectal del Cancer Genome Atlas y de otros 348 pacientes de un estudio independiente. Para cada tumor, cuantificaron con qué frecuencia se utilizaban determinadas elecciones de empalme, resumiéndolas con un número entre cero y uno. Después construyeron una canalización de aprendizaje automático por pasos que primero cribó miles de eventos de empalme en busca de cualquier vínculo con el tiempo que los pacientes permanecieron libres de progresión tumoral, y luego redujo cuidadosamente esa lista evitando señales redundantes y solapadas. El resultado final fue una “firma” compacta de apenas cinco eventos de empalme específicos cuya conducta combinada mejor se correlacionó con que el cáncer del paciente progresara antes o después.
Clasificando a los pacientes en grupos de menor y mayor riesgo
Con esta firma de cinco eventos, el equipo definió una puntuación de riesgo numérica para cada paciente sumando las medidas de empalme, ponderadas según la fuerza con la que cada una se relacionaba con la progresión. Los pacientes cuyos tumores favorecían tres de los patrones de empalme tendieron a evolucionar peor, mientras que dos patrones se asociaron con mejores resultados. La puntuación dividió claramente a los pacientes en grupos de bajo y alto riesgo: tanto en la cohorte original como en el grupo de validación independiente, quienes tenían puntuaciones altas experimentaron la progresión del cáncer significativamente antes. Al graficar curvas de tiempo hasta la progresión, las dos líneas se separaron con claridad, lo que indica que este pequeño conjunto de ediciones del ARN capturó diferencias significativas en el comportamiento tumoral entre cientos de individuos.
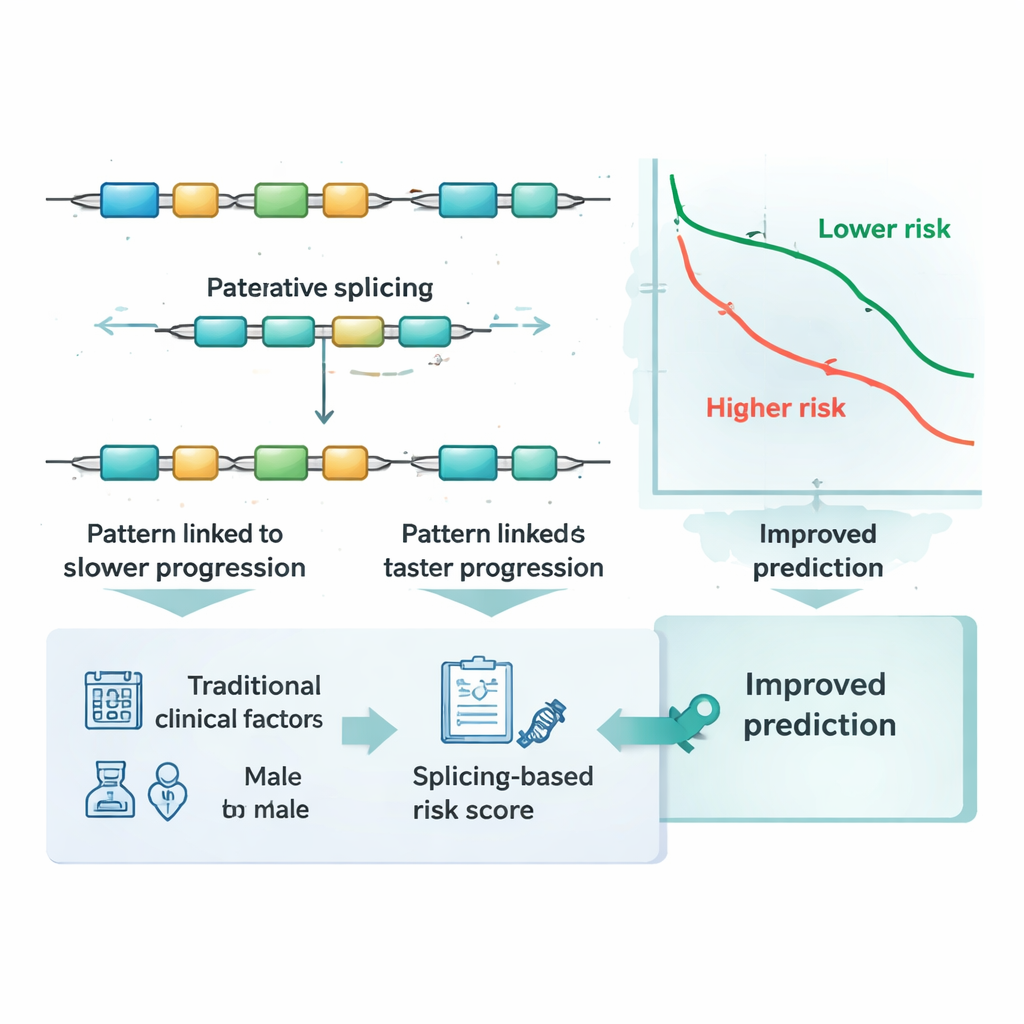
Más allá de la estadificación estándar y los marcadores conocidos
Los médicos actualmente se basan en la etapa tumoral, la edad y otras características clínicas para estimar el riesgo, y a veces en cambios específicos del ADN o en niveles de actividad génica. Los investigadores preguntaron si su puntuación basada en empalmes aportaba información adicional sobre estas medidas establecidas. Usando pruebas de precisión dependientes del tiempo, demostraron que las predicciones basadas solo en estadio, edad y sexo mejoraban notablemente cuando se incluía la puntuación de riesgo por empalme. También compararon la puntuación con docenas de marcadores moleculares conocidos en cáncer colorrectal y con varios enfoques estadísticos comunes. En ambos grupos principales de pacientes, la firma de cinco eventos por empalme igualó o superó a estas alternativas, y mejoró la predicción cuando se usó junto a ellas, lo que sugiere que captura información que otros marcadores no detectan.
Qué podría significar esto para la atención futura
Para un público no experto, el mensaje clave es que la forma en que un tumor “edita” su ARN puede revelar cuán peligroso es probable que sea. Este estudio muestra que seguir solo cinco ediciones específicas del ARN en tumores colorrectales puede clasificar a los pacientes en grupos con diferencias relevantes en sus probabilidades de mantenerse libres de progresión. Aunque este trabajo aún necesita traducirse a pruebas de laboratorio prácticas y evaluarse en ensayos clínicos prospectivos, apunta hacia un futuro en el que los médicos podrían usar tal puntuación en el diagnóstico para decidir quién necesita un tratamiento más agresivo y un seguimiento más estrecho, y quién podría evitar un tratamiento excesivo. Más ampliamente, ofrece un marco reutilizable para explotar patrones de empalme del ARN en otros cánceres con el fin de refinar el pronóstico y orientar una terapia realmente personalizada.
Cita: Maimekov, U., Nosrati, M., Mahmoud, A. et al. Machine learning framework for mRNA alternative splicing analysis identifies a signature of progression in colorectal adenocarcinoma. Sci Rep 16, 7106 (2026). https://doi.org/10.1038/s41598-026-35903-w
Palabras clave: cáncer colorrectal, empalme alternativo, secuenciación de ARN, aprendizaje automático, pronóstico del cáncer