Clear Sky Science · es
Desentrañando los efectos directos y pleiotrópicos de SNPs en alfalfa (Medicago sativa L.) mediante aprendizaje de grafos causales
Por qué importa para las granjas y la alimentación
La alfalfa es una herramienta fundamental de la agricultura moderna: alimenta al ganado lechero y contribuye a la salud del suelo. Sin embargo, la mejora de la alfalfa —plantas que resistan mejor el invierno, sufran menos daños y proporcionen forraje de alta calidad— se ha visto frenada por la enorme complejidad de su genética. Este estudio presenta una manera nueva de pasar de largas y confusas listas de marcadores de ADN a mapas claros de causa y efecto que muestran qué fragmentos del genoma realmente impulsan rasgos importantes del tallo y cuáles solo están asociados por otras razones.
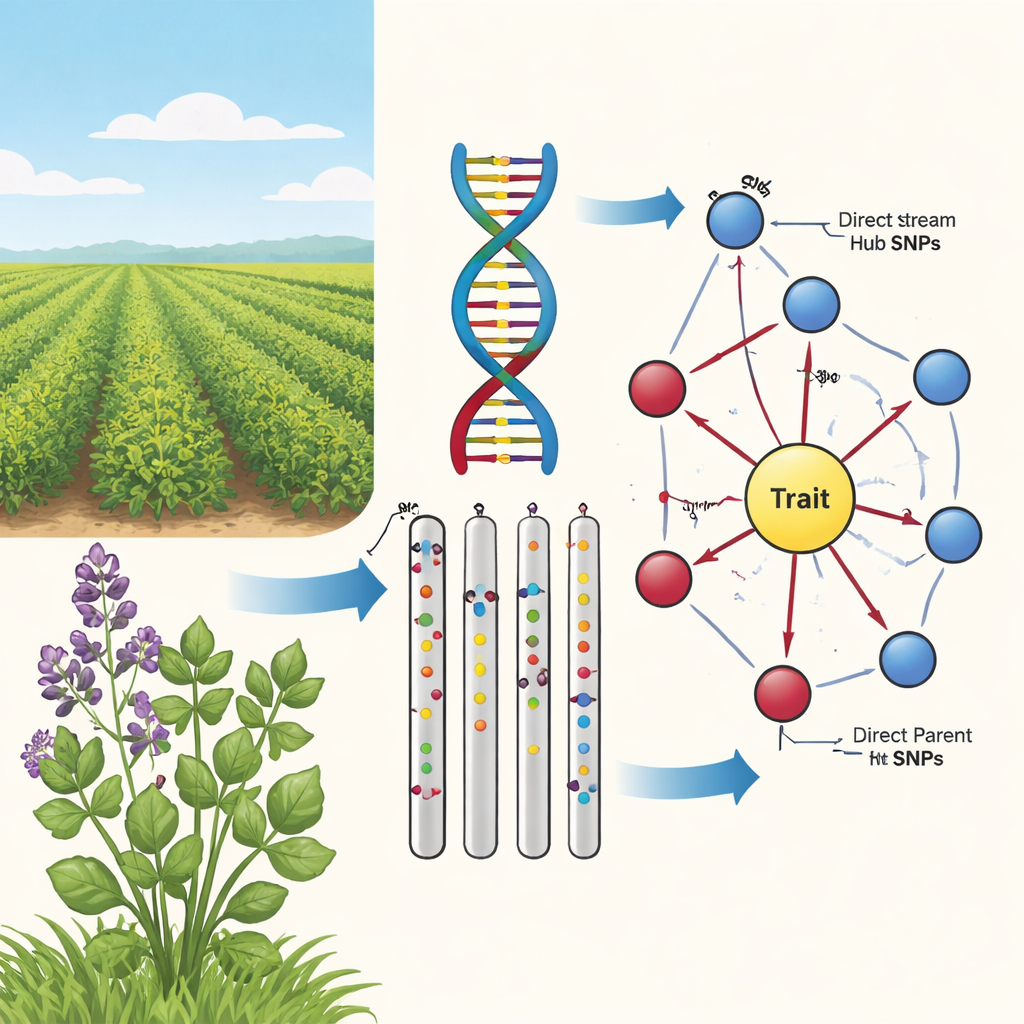
De vínculos superficiales a causa y efecto
Los estudios de asociación a escala genómica tradicionales exploran el genoma en busca de variaciones de ADN, llamadas SNPs, que tienden a aparecer junto a un rasgo, como el color del tallo o la supervivencia invernal. En la alfalfa, sin embargo, la situación es particularmente enrevesada: tiene cuatro copias de cada cromosoma, grandes segmentos de ADN se heredan juntos y las poblaciones están altamente mezcladas genéticamente. Esto crea una «niebla de correlación» en la que muchos marcadores parecen importantes, pero solo unos pocos influyen realmente en el rasgo. Los autores sostienen que los mejoradores necesitan algo más que enlaces estadísticos simples; necesitan saber qué marcadores se sitúan en las rutas causales reales desde el genotipo hasta los rasgos observables de la planta.
Cómo funciona el nuevo marco
Los investigadores construyeron un marco en dos etapas que combina técnicas modernas de aprendizaje automático con conceptos de la teoría de grafos causales. Primero, emplearon una técnica llamada Double Machine Learning para filtrar aproximadamente 2.400 SNPs en 500 genotipos de alfalfa. Este paso elimina la influencia de factores ocultos como la pertenencia familiar y la geografía, usando componentes principales del genoma como proxies. El resultado es una visión más limpia de qué marcadores siguen mostrando un efecto directo sobre rasgos como el color del tallo después de tener en cuenta estas influencias confusoras. En esta vista filtrada, aparecieron picos de señal fuertes y estables principalmente en los cromosomas 2 y 4, y marcadores clave mostraron tamaños de efecto cuyas bandas de confianza excluían claramente el cero, lo que sugiere una influencia causal real.
Convertir marcadores en mapas genéticos
En la segunda etapa, el equipo usó un algoritmo de aprendizaje de grafos causales, conocido como el algoritmo PC, para conectar los marcadores más prometedores en una red direccional. En estos diagramas, los nodos representan SNPs y el rasgo, y las flechas indican la dirección de influencia más probable. Al recortar las aristas que entran en conflicto con la biología básica (por ejemplo, los rasgos no pueden cambiar el ADN subyacente) y conservar solo los SNPs que alimentan al rasgo, los autores obtuvieron mapas compactos y biológicamente plausibles. Estas redes en forma de “girasol” revelan una estructura por capas: un anillo interno de SNPs Padres Directos que conectan directamente con el rasgo, y un anillo externo de SNPs Núcleo Ascendentes que influyen en varios padres pero no tocan el rasgo de forma directa.
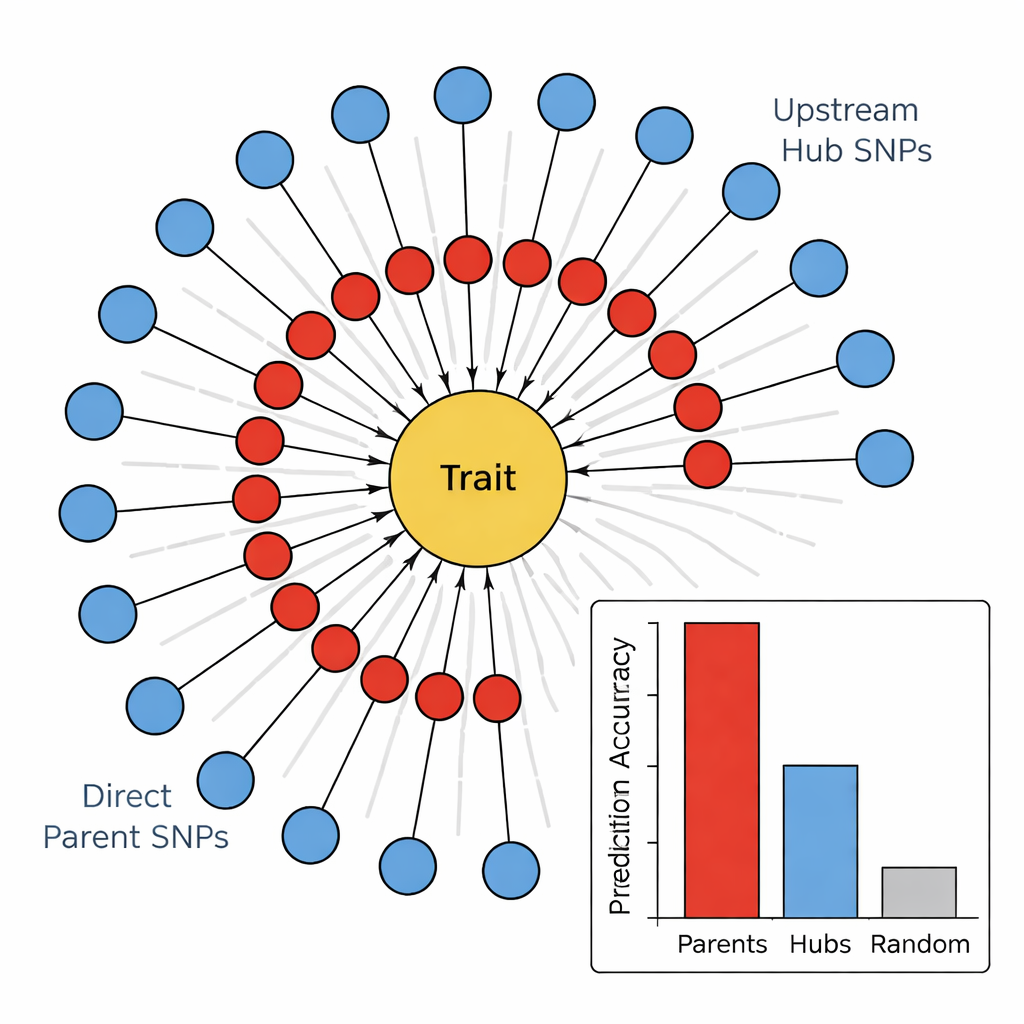
Ejecutores frente a directores en el genoma
Para comprobar si esta jerarquía tenía sentido, los autores compararon qué tan bien distintos grupos de marcadores podían predecir cuatro rasgos relacionados con el tallo: color, llenado, resistencia y daño invernal. En todos los rasgos, los SNPs Padres Directos fueron consistentemente los mejores predictores, a menudo explicando varias veces más variación que marcadores aleatorios o que los Núcleos Ascendentes. En contraste, los núcleos mostraron poder predictivo débil o incluso negativo, a pesar de estar muy conectados en la red. Cuando el equipo vinculó estos SNPs con genes conocidos, emergió un patrón: los Padres Directos a menudo coincidían con enzimas o proteínas estructurales que actúan directamente sobre las paredes celulares, pigmentos o daños por estrés, mientras que los Núcleos tendían a corresponder con factores de transcripción y proteínas regulatorias que ajustan de forma amplia múltiples vías a la vez.
Qué significa esto para la mejora futura de la alfalfa
Para mejoradores y genetistas, el estudio ofrece una forma de atravesar los resultados ruidosos de asociación y centrarse en los cambios de ADN que realmente mueven la aguja para rasgos específicos. Los autores muestran que combinar un cribado desconfundido con grafos causales puede servir como salvaguarda contra el sobreajuste, convirtiendo largas listas de candidatos en redes pequeñas e interpretables alineadas con la biología conocida. En términos prácticos, los SNPs Padres Directos se convierten en marcadores de alta precisión para seleccionar plantas con tallos mejores o mayor supervivencia invernal, mientras que los Núcleos Ascendentes señalan interruptores maestros que podrían remodelar respuestas al estrés más amplias, pero con posibles compensaciones. Esta visión estructural del genoma sienta las bases para una selección genómica más fiable en cultivos complejos e integrar capas futuras de datos, como expresión génica y metabolismo, en modelos coherentes de causa y efecto del rendimiento vegetal.
Cita: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
Palabras clave: genética de la alfalfa, aprendizaje de grafos causales, selección genómica, mejora de plantas, cultivos poliploides