Clear Sky Science · es
Métodos estructurados de PCA disociativa para la descomposición de señales neuroimagen de alta dimensión
Desenredando las señales ocultas del cerebro
Los escáneres cerebrales modernos pueden registrar actividad de cientos de miles de ubicaciones cada segundo, pero transformar este torrente de números en redes claras y significativas es extremadamente difícil. Diferentes procesos cerebrales a menudo se solapan en espacio y tiempo, como varias emisoras de radio que transmiten en frecuencias próximas. Este artículo presenta nuevas herramientas matemáticas que ayudan a separar estas señales enmarañadas de forma más limpia, prometiendo mapas de la función cerebral más nítidos tanto para la investigación básica como para estudios clínicos.
Por qué los métodos habituales se quedan cortos
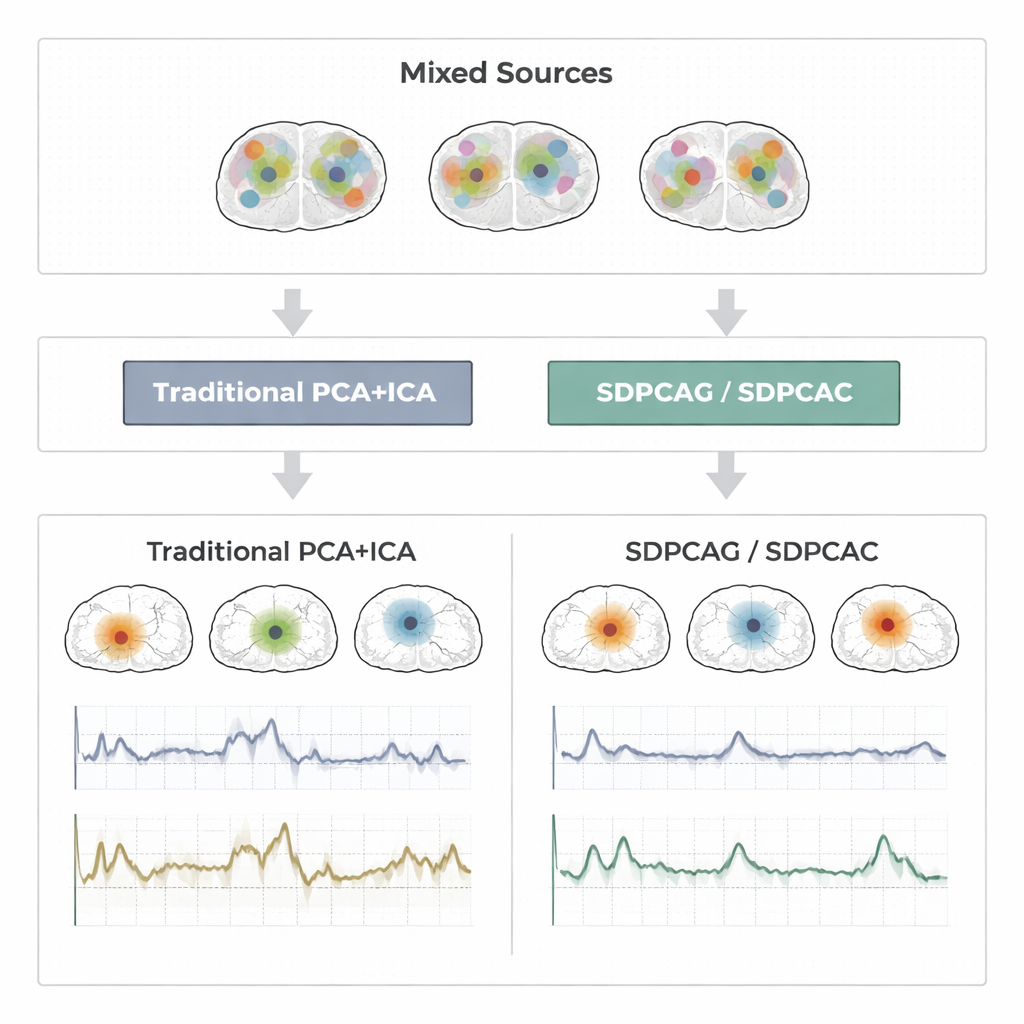
Durante décadas, los investigadores han recurrido a técnicas llamadas análisis de componentes principales (PCA), PCA disperso e análisis de componentes independientes (ICA) para comprimir y separar datos de resonancia magnética funcional (fMRI). El PCA encuentra patrones que explican la mayor parte de la variación en los datos, pero cada patrón mezcla información de casi todas las ubicaciones cerebrales, lo que dificulta la interpretación. El PCA disperso trata de corregir esto forzando que cada patrón use solo un subconjunto de ubicaciones, e ICA va más allá al asumir que las señales cerebrales subyacentes son estadísticamente independientes. En la práctica, sin embargo, las redes cerebrales reales se solapan e influyen entre sí. Cuando eso ocurre, las suposiciones de independencia y dispersión se rompen. El resultado puede ser mapas fragmentados y series temporales ruidosas que ya no coinciden con el comportamiento real de las redes cerebrales.
Una nueva forma de separar señales
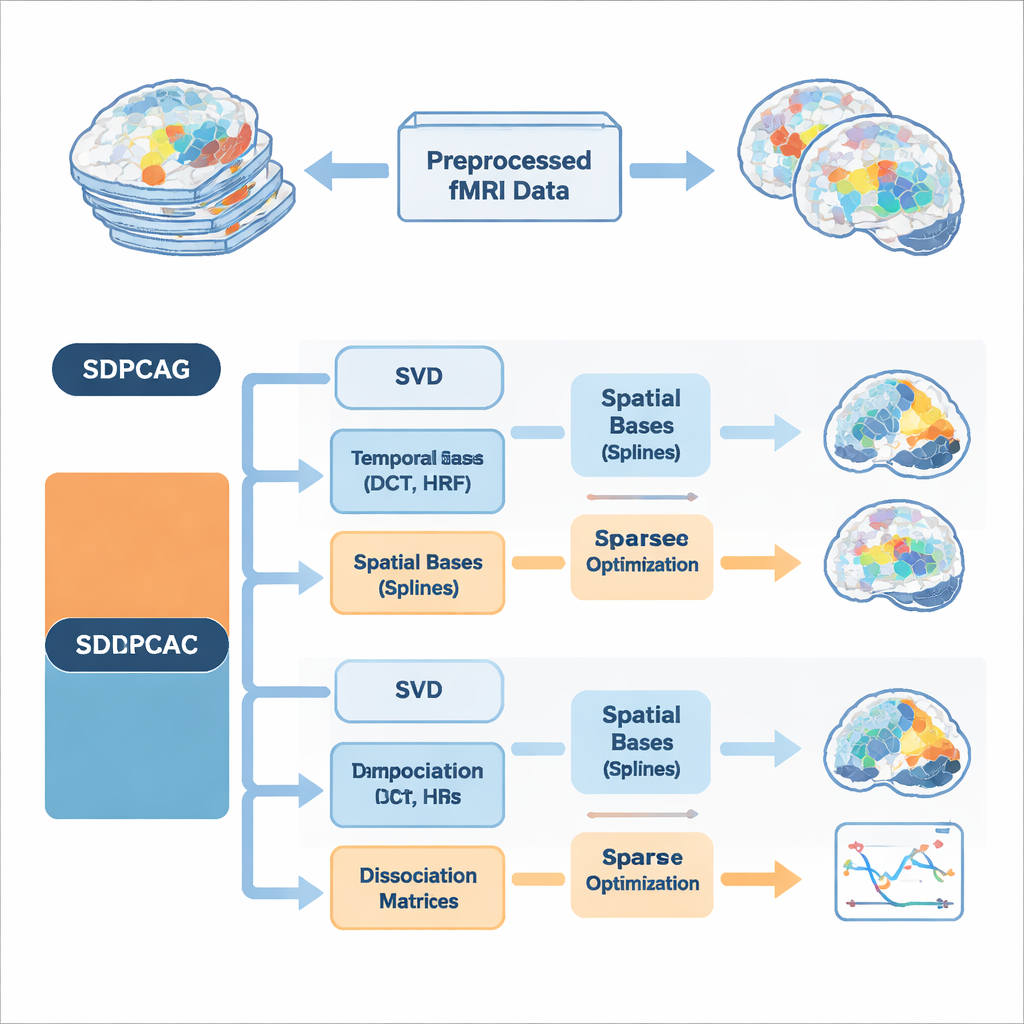
Los autores proponen un marco unificado llamado PCA disociativa estructurada, implementado en dos algoritmos denominados SDPCAG y SDPCAC. En lugar de tratar el espacio y el tiempo por separado, el método remodela todo el conjunto de datos fMRI mediante una única descomposición cuidadosamente diseñada. Parte de una descomposición estándar de bajo rango de los datos y luego introduce matrices especiales de “disociación” que reponderan y rotan mapas espaciales y cursos temporales conjuntamente. Al mismo tiempo, representa estos componentes usando conjuntos de bloques básicos lisos: ondas temporales tipo coseno, modelos de la respuesta hemodinámica del cerebro a la actividad neuronal y curvas espaciales lisas llamadas splines. Al aprender a combinar estos bloques básicos mientras se aplica dispersión—manteniendo solo las piezas más importantes—el método puede desenredar redes superpuestas sin imponer una independencia poco realista.
Incorporando conocimiento cerebral desde el inicio
Una innovación clave es que los algoritmos integran el conocimiento previo sobre señales cerebrales directamente en la descomposición, en lugar de limpiar los resultados a posteriori. En el aspecto temporal, usan funciones discretas de coseno para fomentar cursos temporales suaves e incluyen modelos estándar de la respuesta hemodinámica, la señal retrasada de oxigenación sanguínea medida por fMRI. En el aspecto espacial, las bases de splines favorecen patrones de activación contiguos y coherentes en lugar de puntos dispersos. Restricciones adicionales limitan cuántas funciones base temporales y espaciales puede usar cada componente, lo que reduce el sobreajuste al ruido y refleja la idea de que las redes cerebrales reales son relativamente compactas en espacio y tiempo. Se presentan dos estrategias de optimización complementarias: SDPCAG actualiza matrices completas por bloques, mientras que SDPCAC refina un componente a la vez usando errores residuales, cambiando un coste ligeramente mayor por ajustes más flexibles.
Probando el método
Para evaluar la eficacia de estas ideas, los autores realizan pruebas extensas en tres tipos de datos: señales fMRI sintéticas cuidadosamente diseñadas con verdad de terreno conocida; un experimento de diseño por bloques sobre motor del Human Connectome Project; y un estudio de eventos de golpeteo de dedos procedente de un laboratorio independiente. En estos escenarios comparan SDPCAG y SDPCAC frente a alternativas líderes que combinan descomposición matricial penalizada, PCA disperso, ICA y aprendizaje por diccionario. Miden cuán estrechamente las series temporales recuperadas coinciden con patrones de tarea conocidos, cuán bien los mapas espaciales se alinean con redes de reposo establecidas y con qué precisión se recuperan las fuentes bajo distintos niveles de ruido. Los nuevos métodos producen de forma consistente mapas cerebrales más limpios y localizados y series temporales menos ruidosas, manteniendo un rendimiento sólido incluso cuando los datos están fuertemente corrompidos. Uno de los algoritmos, SDPCAG, mejora la precisión de recuperación de fuentes en aproximadamente un 22% frente a un método competitivo robusto, además de ejecutarse más rápido que su hermano más detallado SDPCAC.
Qué significa esto para la investigación cerebral
En términos sencillos, este trabajo ofrece una mejor forma de “desmezclar” las señales dentro de los datos fMRI. Al modelar conjuntamente el espacio y el tiempo, usar priors realistas sobre cómo se comportan la actividad cerebral y el flujo sanguíneo y aplicar una dispersión inteligente, SDPCAG y SDPCAC generan redes cerebrales que son tanto más nítidas en las imágenes como más fieles a sus cursos temporales subyacentes. Esto puede conducir a una detección más fiable de activaciones relacionadas con tareas y a un mapeo más preciso de las redes en reposo, lo que a su vez apoya estudios de condiciones como la enfermedad de Alzheimer, trastornos psiquiátricos y otras enfermedades cerebrales. Aunque aún hay margen para acelerar y extender el enfoque—por ejemplo a estudios multi-sujeto o imágenes multimodales—representa un paso significativo hacia la conversión de datos de escaneo de alta dimensión en imágenes interpretables y fiables del cerebro humano en funcionamiento.
Cita: Khalid, M.U., Nauman, M.M., Rehman, S.U. et al. Structured dissociative PCA methods for high dimensional neuroimaging signal decomposition. Sci Rep 16, 6911 (2026). https://doi.org/10.1038/s41598-026-35764-3
Palabras clave: descomposición de señales fMRI, PCA disperso, mapeo de redes cerebrales, separación ciega de fuentes, conectividad en reposo