Clear Sky Science · es
Genómica comparativa de Pseudomonas aeruginosa multirresistente no susceptible a colistina revela linajes emergentes en Tailandia
Por qué este germen hospitalario importa a todo el mundo
Pseudomonas aeruginosa es un germen hospitalario que ataca a las personas cuando están más vulnerables: tras una cirugía, con respiradores, o en pacientes con quemaduras graves o enfermedades pulmonares. Durante años, los médicos han recurrido a un potente antibiótico de «último recurso» llamado colistina cuando otros fármacos fallan. Este estudio examina cepas de Pseudomonas procedentes de hospitales de Tailandia que ya no responden a la colistina ni a muchos otros antibióticos. Al leer el ADN completo de estas bacterias, los investigadores muestran cómo se propagan nuevos linajes altamente resistentes a los fármacos y por qué eso debe preocupar a pacientes, clínicos y sistemas sanitarios en todo el mundo.
Rastreando una infección difícil de tratar por toda Tailandia
El equipo se centró en 29 cepas de Pseudomonas aeruginosa recogidas en 2021–2022 en hospitales que participan en el programa nacional de vigilancia de la resistencia a antibióticos de Tailandia. Todas estas cepas eran multirresistentes: podían resistir varias clases principales de antibióticos, incluidos fármacos que se usan habitualmente para infecciones graves. Y, de forma crucial, tampoco eran totalmente susceptibles a la colistina, el medicamento que a menudo se reserva para casos potencialmente mortales. La mayoría de las muestras procedían de orina, pero otras se tomaron de sangre, esputo, pus y líquidos de drenaje quirúrgico, lo que refleja los muchos tipos de infecciones que este germen puede causar en pacientes hospitalizados.
Leyendo las «huellas genéticas» de las bacterias
Mediante una combinación de secuenciación de ADN de lecturas cortas y largas, los investigadores ensamblaron genomas de alta calidad para cada cepa. Después compararon estos genomas para clasificar las bacterias en familias genéticas, conocidas como tipos de secuencia. Se encontraron nueve tipos de secuencia distintos, lo que revela una diversidad considerable. Uno, denominado ST5340, no se había descrito antes. Resultó estar estrechamente relacionado con un clon internacional de alto riesgo conocido como ST357, difiriendo en solo uno de los siete genes de mantenimiento estándar. A pesar de esa relación cercana, el ST5340 destacó porque todas sus aisladas resistieron a todos los antibióticos probados, lo que lo señala como un linaje especialmente preocupante.
Linajes de alto riesgo emergentes y su propagación
Alineando pequeñas diferencias del ADN llamadas polimorfismos de nucleótido simple a través de 108 genomas de Pseudomonas tailandeses (las 29 nuevas más 79 de bases de datos públicas), el equipo construyó un árbol genealógico de las cepas que circulan en el país. Este análisis puso de manifiesto varios grupos dominantes centrados en ST5340, ST357, ST654 y ST235, linajes ya conocidos, o ahora emergentes, como «de alto riesgo» porque con frecuencia resisten múltiples fármacos y provocan brotes hospitalarios. ST5340, en particular, apareció en varias provincias y regiones, lo que sugiere que se está extendiendo ampliamente en lugar de estar confinado a un único hospital. También estuvieron presentes otros clones globales de alto riesgo, como ST654 y ST235, mientras que algunos linajes importantes a escala mundial, como ST244, estuvieron ausentes, probablemente porque el estudio incluía solo cepas no susceptibles a colistina.
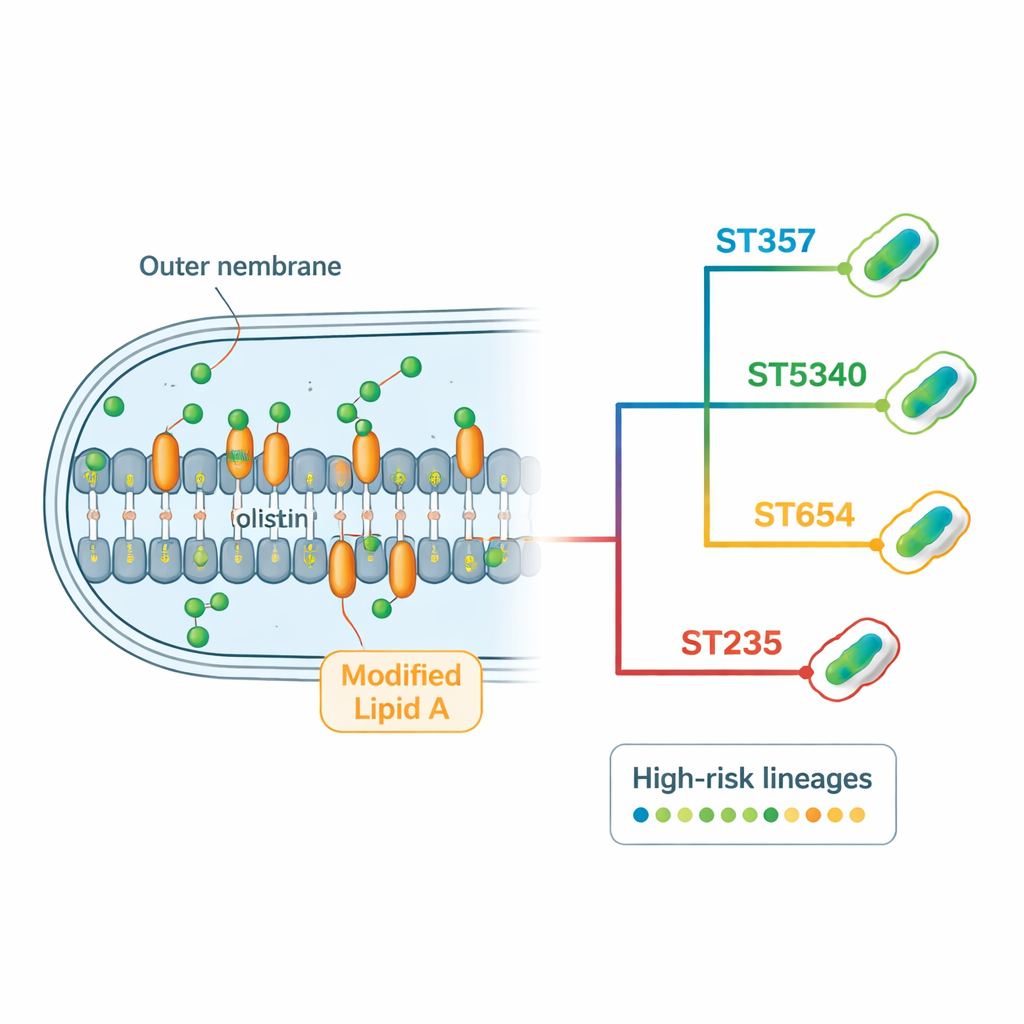
Cómo estas bacterias burlan a los antibióticos
El análisis genómico reveló un «resistoma» abundante: el conjunto completo de genes y mutaciones de resistencia que porta cada cepa. Muchas aisladas codificaban varios tipos de beta‑lactamasas, enzimas que degradan antibióticos comunes como penicilinas, cefalosporinas y carbapenémicos. El gen de carbapenemasa blaNDM‑1, asociado con resistencia a algunos de los fármacos hospitalarios más potentes, apareció en casi todas las cepas, a veces en múltiples copias. Las bacterias también portaban genes que modifican químicamente a los aminoglucósidos, así como bombas de expulsión potentes que funcionan como bombas moleculares para eyectar los fármacos fuera de la célula. En lo relativo a la colistina, el equipo no encontró genes móviles de resistencia, sino cambios recurrentes en genes cromosómicos implicados en la membrana externa y su regulación. Ciertas mutaciones en proteínas reguladoras y en enzimas que fabrican el lípido A se asociaron de forma contundente con la resistencia a colistina, sobre todo en los linajes dominantes ST357 y ST5340.
Qué significa esto para pacientes y hospitales
Combinando la vigilancia nacional con la secuenciación genómica moderna, este estudio muestra que los hospitales de Tailandia se enfrentan a una amenaza creciente por un clon de alto riesgo recién identificado, ST5340, junto con cepas problemáticas globales ya establecidas. Estas bacterias no solo son resistentes a la colistina, sino también a muchos otros fármacos clave, lo que reduce drásticamente las opciones de tratamiento cuando los pacientes desarrollan infecciones graves. Para el público general, el mensaje es claro: la resistencia a los antibióticos no es un riesgo del futuro sino una realidad presente que puede afectar directamente los resultados de cirugías, cuidados intensivos y tratamientos oncológicos. Los autores sostienen que es urgente mantener la vigilancia genómica, reforzar el control de infecciones y usar los antibióticos con mayor prudencia para evitar que estos linajes altamente resistentes se vuelvan aún más extendidos y difíciles de contener.
Cita: Wankaew, N., Arigul, T., Kruasuwan, W. et al. Comparative genomics of colistin-nonsusceptible multidrug-resistant Pseudomonas aeruginosa reveals emerging lineages in Thailand. Sci Rep 16, 5968 (2026). https://doi.org/10.1038/s41598-026-35520-7
Palabras clave: Pseudomonas aeruginosa, resistencia a antibióticos, colistina, vigilancia genómica, infecciones hospitalarias