Clear Sky Science · es
Diseño y evaluación, mediante inmunoinformática, de una vacuna multi-epítopo contra Vibrio fluvialis
Por qué importa una nueva vacuna para los amantes de los mariscos
Vibrio fluvialis es un pariente menos conocido de las bacterias que causan el cólera; vive en aguas costeras cálidas y puede contaminar mariscos y agua potable. Provoca diarrea severa e infecciones intestinales y se está volviendo más frecuente a medida que los océanos se calientan y los antibióticos pierden eficacia. Sin embargo, actualmente no existe una vacuna para las personas. Este estudio emplea métodos informáticos avanzados para diseñar un nuevo tipo de vacuna experimental, construida a partir de fragmentos diminutos y seleccionados de la bacteria, con el objetivo a largo plazo de proteger a quienes se exponen a través de alimentos, agua o inundaciones relacionadas con el clima.

De una amenaza oculta a un blanco claro
Vibrio fluvialis a menudo se ha confundido con otras especies de Vibrio, lo que sugiere que su papel en las enfermedades transmitidas por alimentos probablemente esté subestimado. Brotes se han vinculado a mariscos contaminados y agua poluida, y las tormentas e inundaciones recientes han llevado estas bacterias tierra adentro, enfermando a personas lejos de la costa. Muchos pacientes requieren atención hospitalaria y un número preocupante de cepas ahora resiste múltiples antibióticos. Dado que la superficie del microbio se parece a la de bacterias relacionadas, los médicos pueden diagnosticar mal las infecciones, retrasando el tratamiento adecuado. Todo ello crea una fuerte necesidad de prevención en lugar de depender solo de fármacos.
Diseñar una vacuna dentro de un ordenador
En lugar de cultivar bacterias enteras en el laboratorio, los investigadores recurrieron a la “inmunoinformática”: usar programas para predecir qué fragmentos pequeños de Vibrio fluvialis tienen más probabilidad de ser detectados y atacados por el sistema inmunitario humano. Se centraron en dos proteínas de membrana que se sitúan en la superficie bacteriana y son importantes para su supervivencia y su capacidad de causar enfermedad. A partir de estas proteínas, el equipo extrajo diez segmentos cortos, llamados epítopos, que pueden ser reconocidos tanto por células T como por células B, los principales efectivos de nuestras defensas inmunitarias. Luego unieron estas piezas en una sola cadena de 246 aminoácidos, añadiendo cortos segmentos espaciadores para que el sistema inmunitario pueda procesar cada parte correctamente, y un fragmento adyuvante para potenciar la respuesta global.
Comprobando potencia, seguridad y alcance global
Una vez construido virtualmente, el equipo realizó una serie de pruebas enteramente in silico, es decir, en ordenadores en lugar de en animales o personas. Los programas predijeron que el constructo combinado sería fuertemente “visible” para el sistema inmunitario pero poco probable que provocara alergia o toxicidad. Los epítopos elegidos coincidían con variantes comunes de genes inmunitarios de todo el mundo, lo que sugiere que alrededor del 99,97 por ciento de la población mundial debería poder responder, incluidas personas en regiones muy afectadas como el sur y el este de Asia. La proteína de la vacuna también pareció estable, lo bastante hidrofílica para disolverse bien y adecuada para una producción eficiente en bacterias de laboratorio estándar, lo que hace más práctica su eventual fabricación.
Cómo podría desencadenar protección la vacuna
Los investigadores se plantearon a continuación si la proteína diseñada podría interactuar de forma plausible con un sensor inmunitario real. Utilizando herramientas modernas de predicción estructural, construyeron un modelo tridimensional de la vacuna y luego simularon cómo podría acoplarse al receptor tipo Toll 2 (TLR2), una molécula en las células inmunitarias que detecta componentes bacterianos. El acoplamiento computacional sugirió un ajuste estrecho entre la vacuna y TLR2, respaldado por numerosos contactos moleculares estabilizadores. Simulaciones dinámicas largas y detalladas durante 100 nanosegundos indicaron que el par vacuna-receptor se mantenía estable y compacto en el tiempo. Simulaciones adicionales del sistema inmunitario predijeron fuertes oleadas de anticuerpos y actividad de células T, junto con la formación de células de memoria que, en principio, podrían proporcionar protección duradera contra Vibrio fluvialis.
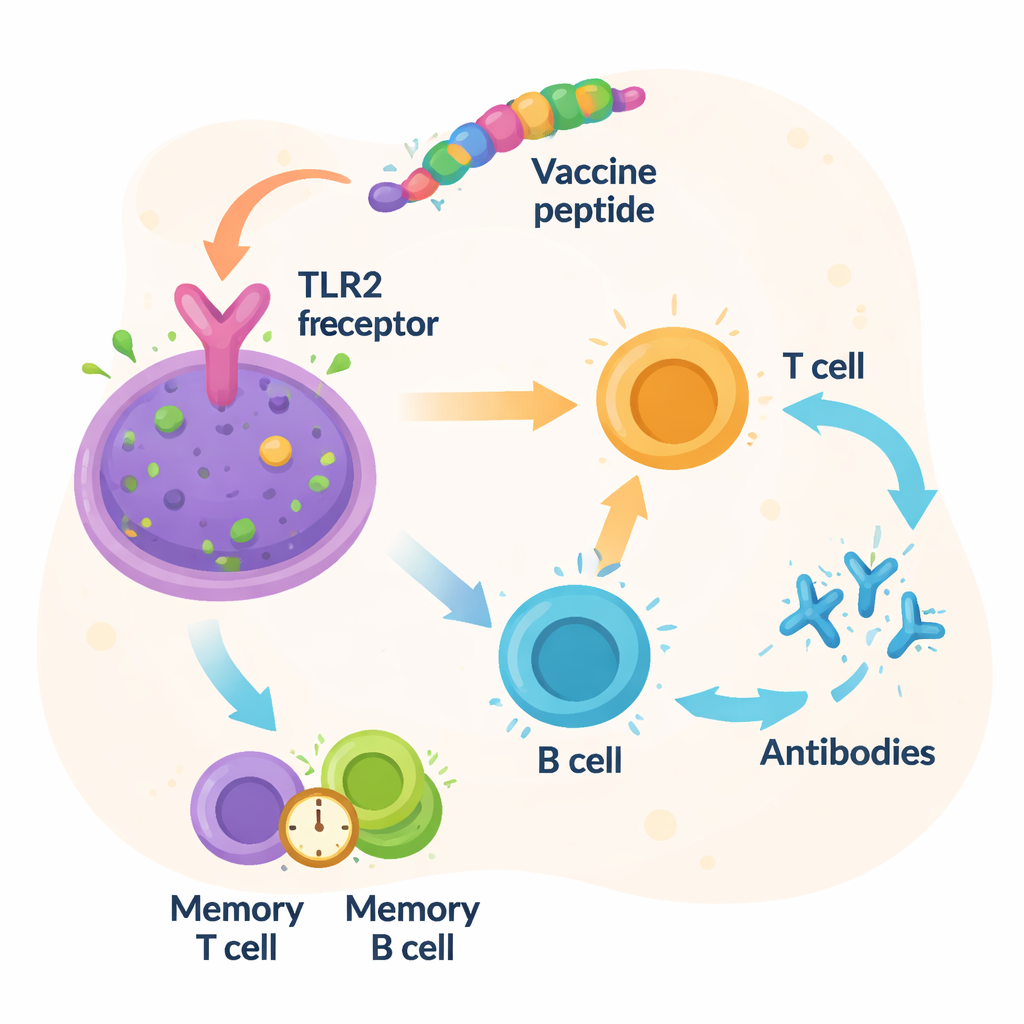
Del plano digital al escudo en el mundo real
En términos cotidianos, este trabajo ofrece un “plano” digital para una futura vacuna contra Vibrio fluvialis construida solo con las porciones más importantes de la bacteria, organizadas para ser eficaz a amplia escala y potencialmente más segura que las vacunas de célula completa. El estudio muestra que este constructo debería ser reconocible por la mayoría de los sistemas inmunitarios humanos, unirse bien a un sensor inmunitario clave y ser fabricable con herramientas estándar. Sin embargo, todos estos resultados provienen de modelos computacionales. Los siguientes pasos requerirán producir la vacuna en el laboratorio, probarla en células y animales y, finalmente, en ensayos humanos para confirmar que realmente protege frente a la infección sin causar daño. Si esas pruebas tienen éxito, tales vacunas multi-epítopo podrían convertirse en poderosas herramientas nuevas contra bacterias transmitidas por alimentos en un mundo que se calienta y se densifica cada vez más.
Cita: Naveed, M., Husnain, M., Aziz, T. et al. Immunoinformatics-based design and evaluation of a multi-epitope vaccine against Vibrio fluvialis. Sci Rep 16, 4100 (2026). https://doi.org/10.1038/s41598-026-35434-4
Palabras clave: Vibrio fluvialis, vacuna multi-epítopo, infección transmitida por alimentos, inmunoinformática, resistencia a antibióticos