Clear Sky Science · es
Un conjunto de datos de secuenciación pareada de ARNm y microARN en sangre durante el shock séptico agudo y la recuperación
Por qué esto importa para pacientes con infecciones graves
Cuando una infección grave se descontrola, las defensas del propio cuerpo pueden volverse dañinas, conduciendo a sepsis y shock séptico, condiciones que causan la muerte de cientos de miles de personas en todo el mundo cada año. Los médicos en la cama del paciente observan casos que empeoran de forma súbita o que mejoran lentamente, pero no pueden ver con facilidad lo que ocurre dentro de las células sanguíneas cuando el sistema inmunitario pasa de la crisis a la estabilidad. Este estudio presenta un conjunto de datos detallado que registra los cambios en la actividad génica en la sangre de los mismos pacientes durante la fase más peligrosa del shock séptico y de nuevo después de la mejoría, ofreciendo una nueva ventana sobre cómo el organismo recupera su equilibrio.
Una mirada más cercana dentro de la sangre durante la sepsis
El sistema inmunitario suele caminar por una cuerda floja: debe atacar bacterias, virus u hongos invasores sin causar daño duradero a los propios tejidos del organismo. En la sepsis, ese equilibrio se rompe. Las señales que impulsan la inflamación y las que la apagan dejan de coordinarse correctamente, y los órganos pueden comenzar a fallar. Los clínicos necesitan con urgencia marcadores sanguíneos rápidos y fiables que revelen qué pacientes están en verdadero peligro, cómo evoluciona su enfermedad y si los tratamientos funcionan. Las medidas tradicionales, como los niveles de la proteína procalcitonina, pueden variar mucho entre personas y no explican por completo quién se recupera y quién no. Por eso los investigadores recurren cada vez más al patrón completo de actividad génica del organismo —su “transcriptoma”— como una lectura más informativa.
Qué aporta este estudio respecto a trabajos previos
Estudios grandes anteriores ya han mostrado que los patrones de ARN mensajero (ARNm), las moléculas que llevan las instrucciones genéticas para fabricar proteínas, y de microARN, pequeños reguladores que afinan esas instrucciones, pueden distinguir a personas con sepsis de voluntarios sanos e incluso separar la sepsis de otras formas de inflamación grave. Algunas investigaciones también han usado estos patrones para estimar el riesgo futuro de desarrollar sepsis tras una cirugía mayor. Sin embargo, muchas de esas comparaciones se hicieron entre diferentes grupos de personas —pacientes frente a controles sanos, o sepsis frente a no sepsis—, lo que dificulta saber si las diferencias derivan de la propia enfermedad o de la variación natural entre individuos.
Seguir a los mismos pacientes desde la crisis hasta la recuperación
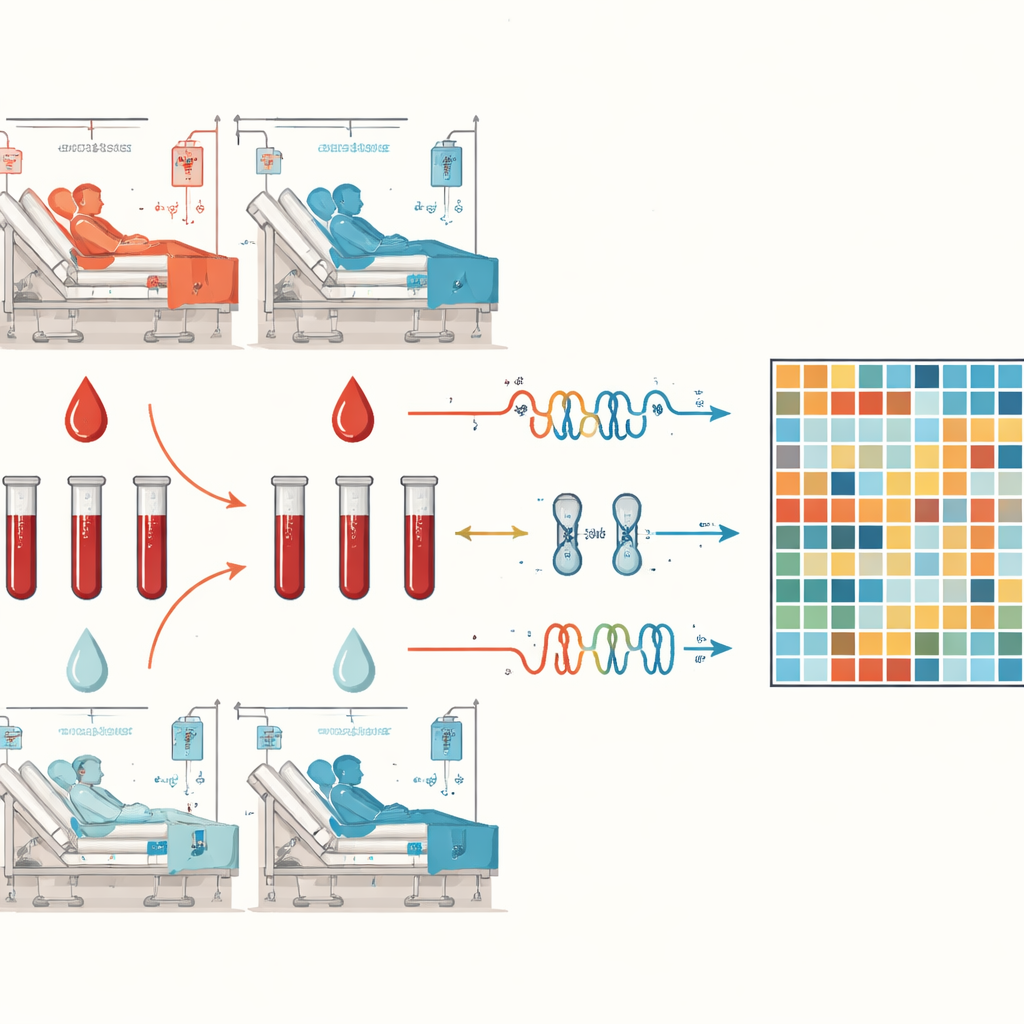
El nuevo conjunto de datos se centra en cambio en la variación dentro de cada persona. Seis adultos tratados en una unidad de cuidados intensivos en Budapest por shock séptico —tres con infecciones pulmonares y tres con infecciones del tracto urinario— proporcionaron cada uno dos muestras de sangre. Una se tomó en el momento álgido del shock séptico, cuando la función de los órganos estaba gravemente afectada y eran necesarios fármacos para mantener la presión arterial. La segunda se obtuvo días después, al alta de la unidad de cuidados intensivos, cuando los pacientes fueron considerados clínicamente estables y ya no precisaban fármacos vasopresores. Las puntuaciones clínicas estándar, como la escala SOFA que resume la función orgánica, mejoraron claramente entre los dos puntos temporales, confirmando el cambio de la crisis a la recuperación.
Cómo se creó el mapa de actividad genética
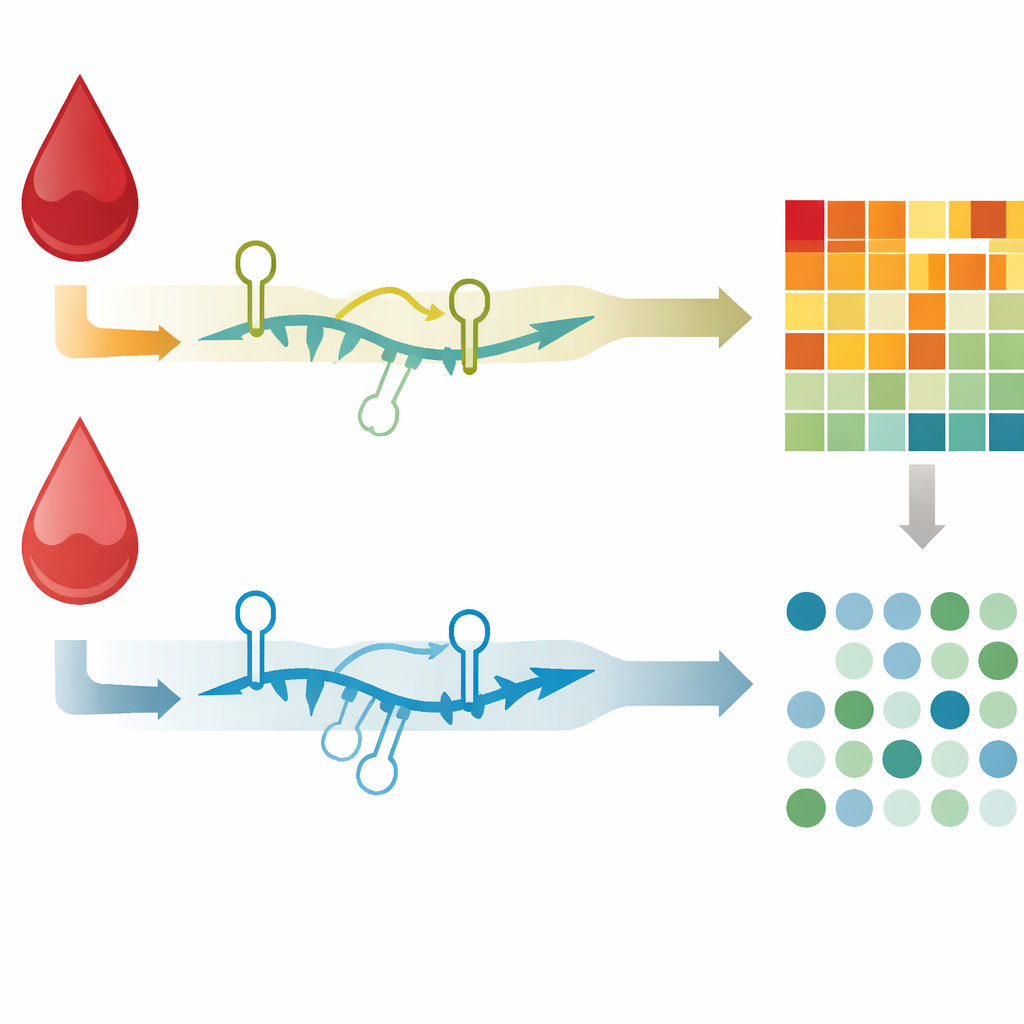
De cada muestra de sangre, el equipo extrajo ARN total y preparó dos tipos de bibliotecas de secuenciación: una que capturó ARNm y otra que capturó ARN pequeños, incluidos los microARN. Usando máquinas de secuenciación de nueva generación, obtuvieron en promedio 15 millones de lecturas de ARNm y 10 millones de lecturas de microARN por muestra, suficientes para construir una imagen detallada de qué genes estaban activos y con qué intensidad. Controles de calidad extensivos aseguraron que el ARN estuviera intacto y que las bibliotecas de secuenciación cumplieran con estándares estrictos. Las lecturas se alinearon luego con el genoma humano de referencia actual y se generaron recuentos de cuántas lecturas se asignaron a cada gen, dando como resultado perfiles pareados de actividad génica para cada paciente en los estados de shock y recuperación. Todos los archivos crudos de secuenciación, las tablas de recuentos y la información clínica vinculada se han depositado en una base de datos pública para que otros científicos la analicen.
Qué significa este recurso para la atención futura
Debido a que cada paciente sirve como su propio control, las diferencias en la actividad génica entre los dos puntos temporales tienen más probabilidades de reflejar el paso del estado de shock potencialmente mortal a la recuperación, en lugar de diferencias genéticas o de estilo de vida no relacionadas entre personas. El conjunto de datos es pequeño, por lo que por sí solo no es suficiente para definir pruebas diagnósticas definitivas ni para explicar por completo la biología de la sepsis. Aún así, ofrece una vista pareada poco frecuente de ARNm y microARN durante la fase más crítica de la enfermedad. Los investigadores pueden usarlo para explorar tendencias, generar nuevas hipótesis sobre cómo se desregulan las respuestas inmunitarias y buscar señales tempranas de mejora o deterioro. Con el tiempo, integrar estos mapas moleculares detallados con cohortes de pacientes más grandes podría ayudar a los clínicos a reconocer antes patrones inmunitarios peligrosos y orientar tratamientos más personalizados para personas con infecciones graves.
Cita: Molnár, K., Maricza, K., Elek, Z. et al. A dataset of paired blood mRNA and microRNA sequencing across acute septic shock and recovery. Sci Data 13, 453 (2026). https://doi.org/10.1038/s41597-026-06844-w
Palabras clave: sepsis, shock séptico, expresión génica, secuenciación de ARN en sangre, biomarcadores