Clear Sky Science · es
Ensamblaje del genoma a nivel cromosómico resuelto por haplotipos de un árbol de camelia oleosa autohexaploide Camellia osmantha
Por qué importa un árbol que produce aceite para cocinar
Mucha gente conoce las camelias como arbustos ornamentales, pero algunos de sus parientes son verdaderos caballos de batalla en la cocina. El aceite exprimido de semillas de camelia es muy apreciado en partes de Asia como un aceite para cocinar beneficioso para el corazón, rico en grasas saludables y compuestos vegetales protectores. Una estrella en ascenso es Camellia osmantha, un árbol resistente y de alto rendimiento que puede producir mucho más aceite por hectárea que las variedades tradicionales. Para aprovechar plenamente su potencial, los científicos necesitan entender su plano genético. Este estudio ofrece exactamente eso: un mapa detallado y de alta resolución del ADN del árbol, que abre la puerta a cosechas mejores, aceites más saludables y árboles que puedan prosperar en un mundo que se calienta.

Un nuevo árbol oleoso con gran potencial
Camellia osmantha es una especie de camelia oleosa reconocida recientemente. Combina varios rasgos que importan a los agricultores: fuerte tolerancia al calor, al frío y a la sequía, y una producción de aceite inusualmente alta —aproximadamente el doble que la de los árboles comerciales de camelia típicos a solo cinco años de edad. Como muchas plantas cultivadas seleccionadas por rendimiento, posee un genoma especialmente complejo: en lugar de las dos copias habituales de cada cromosoma, tiene seis. Esta naturaleza “autohexaploide” significa que su ADN es enorme, alrededor de cinco veces el tamaño del genoma humano, y está lleno de secuencias repetidas. Tal complejidad ha dificultado construir un mapa genómico limpio y preciso con tecnologías anteriores.
Resolver un rompecabezas genético muy grande
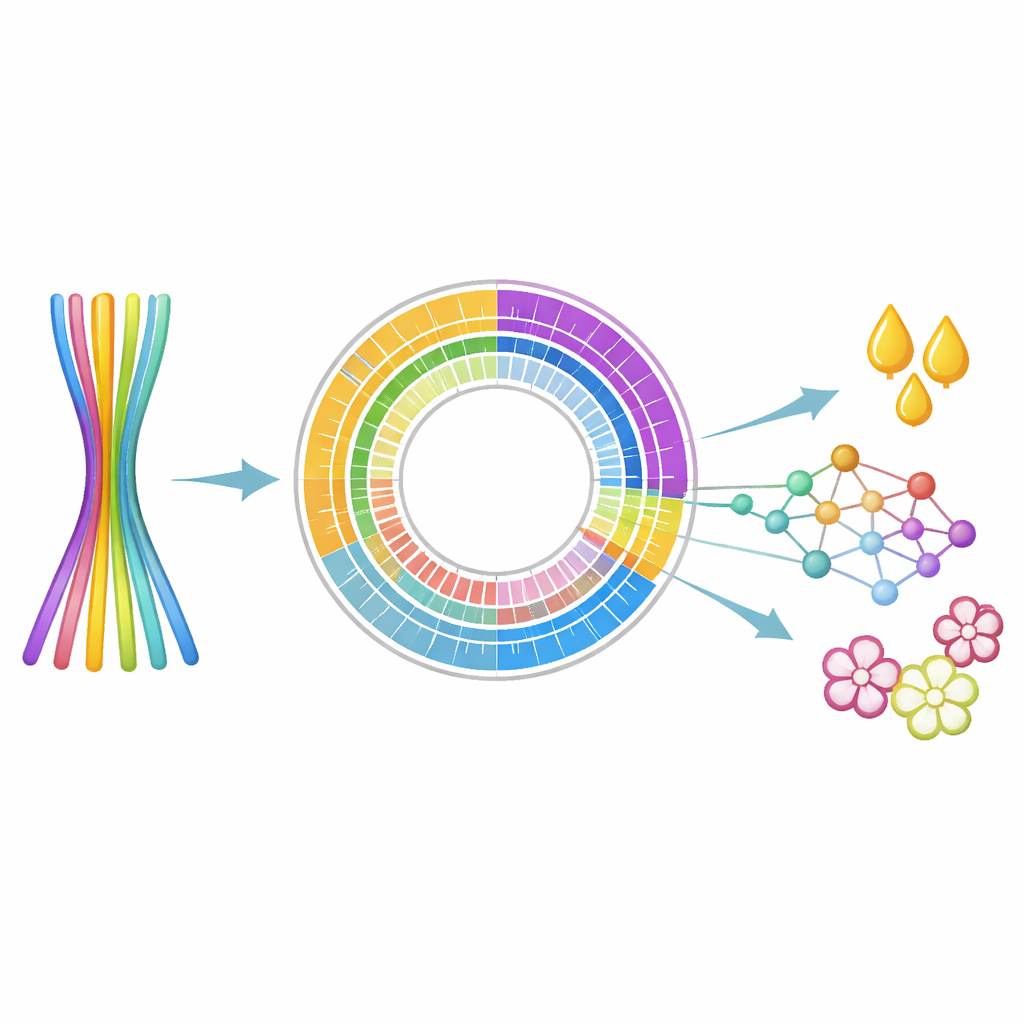
Para abordar este desafío, los investigadores combinaron varios métodos de secuenciación de ADN de vanguardia. Lecturas largas y altamente precisas de la plataforma PacBio HiFi proporcionaron segmentos de código genético de miles de letras, mientras que los datos Hi‑C capturaron cómo se pliegan y empaquetan los fragmentos de ADN dentro de la célula —pistas que ayudan a coser fragmentos en cromosomas completos. También recopilaron datos de ARN de hojas para ver qué genes están realmente activos. Usando nuevos algoritmos de ensamblaje diseñados para plantas poliploides, el equipo armó un genoma de 14,38 mil millones de pares de bases y, crucialmente, lo separó en seis “haplotipos” distintos pero coincidentes, cada uno representando un conjunto completo de cromosomas.
Seis copias completas, vistas con claridad por primera vez
El ensamblaje final ancló 11,08 mil millones de pares de bases en 90 andamios largos similares a cromosomas, agrupados ordenadamente en seis versiones de 15 cromosomas. Una versión, llamada Haplotipo 1, fue especialmente completa y limpia, con solo un pequeño número de huecos y evaluaciones que mostraron más del 95% de completitud. A lo largo del genoma, los científicos catalogaron un vasto paisaje de ADN repetido, especialmente elementos de repetición terminal larga que constituyen casi la mitad de la secuencia. Sobre este mapa estructural, identificaron 60.212 genes codificadores de proteínas y confirmaron que casi todos ellos contienen partes funcionales reconocibles, lo que sugiere que el conjunto génico es tanto amplio como fiable.
Genes relacionados con el aceite y la floración
Con el genoma en mano, el equipo buscó específicamente genes vinculados a rasgos de interés. Encontraron 3.269 factores de transcripción —claves “interruptores de control” para otros genes— y 2.655 genes similares a genes conocidos de resistencia a enfermedades, que pueden ayudar a los mejoradores a seleccionar árboles que resistan plagas y patógenos. Lo más emocionante desde el punto de vista agrícola fue la identificación de 80 genes implicados en la síntesis de aceites y grasas, incluidos enzimas que inician la síntesis de lípidos y otros que afinan los tipos de ácidos grasos almacenados en las semillas. También catalogaron 497 genes relacionados con el tiempo de floración y el desarrollo floral, palancas importantes para adaptar los árboles a diferentes climas y temporadas de cultivo.
Una base para mejores árboles y mejor aceite
Al resolver cada una de las seis copias cromosómicas y anotar cuidadosamente decenas de miles de genes, este trabajo convierte una masa enorme y enredada de ADN en un manual de referencia utilizable para Camellia osmantha. Los mejoradores de plantas y los biólogos moleculares pueden ahora rastrear qué versiones de genes se asocian con mayor rendimiento de aceite, mejor calidad del aceite, mayor resistencia a enfermedades o resiliencia al calor y la sequía. En términos prácticos, el estudio proporciona una hoja de ruta para desarrollar nuevas variedades de camelia oleosa más productivas, más robustas y mejor adaptadas a alimentar a la población en un clima cambiante —todo ello partiendo de una imagen más clara de lo que hay dentro de las células de este notable árbol.
Cita: Zhang, Z., Hao, B., Li, M. et al. Haplotype-resolved chromosome-level genome assembly of an autohexaploid oil camellia tree Camellia osmantha. Sci Data 13, 395 (2026). https://doi.org/10.1038/s41597-026-06786-3
Palabras clave: Camellia osmantha, genoma vegetal, cultivos poliploides, aceites comestibles, mejoramiento de cultivos