Clear Sky Science · es
Perfiles metabolómicos y transcriptómicos de dos especies estrechamente relacionadas del género Oldenlandia
Por qué importan estas humildes hierbas
Dos pequeñas plantas invasoras usadas en la medicina tradicional asiática, Oldenlandia diffusa y Oldenlandia corymbosa, se consumen ampliamente para problemas que van desde la inflamación hasta enfermedades hepáticas y el cáncer. Sin embargo, a pesar de su larga historia en remedios herbales y de que con frecuencia se mezclan en el mercado, sabemos sorprendentemente poco sobre en qué se diferencian realmente por dentro: qué ingredientes químicos producen, en qué órganos de la planta y qué genes controlan esos compuestos. Este estudio abre ese mundo oculto al proporcionar un mapa detallado tanto de las moléculas como de la actividad génica en distintos tejidos de las dos especies.
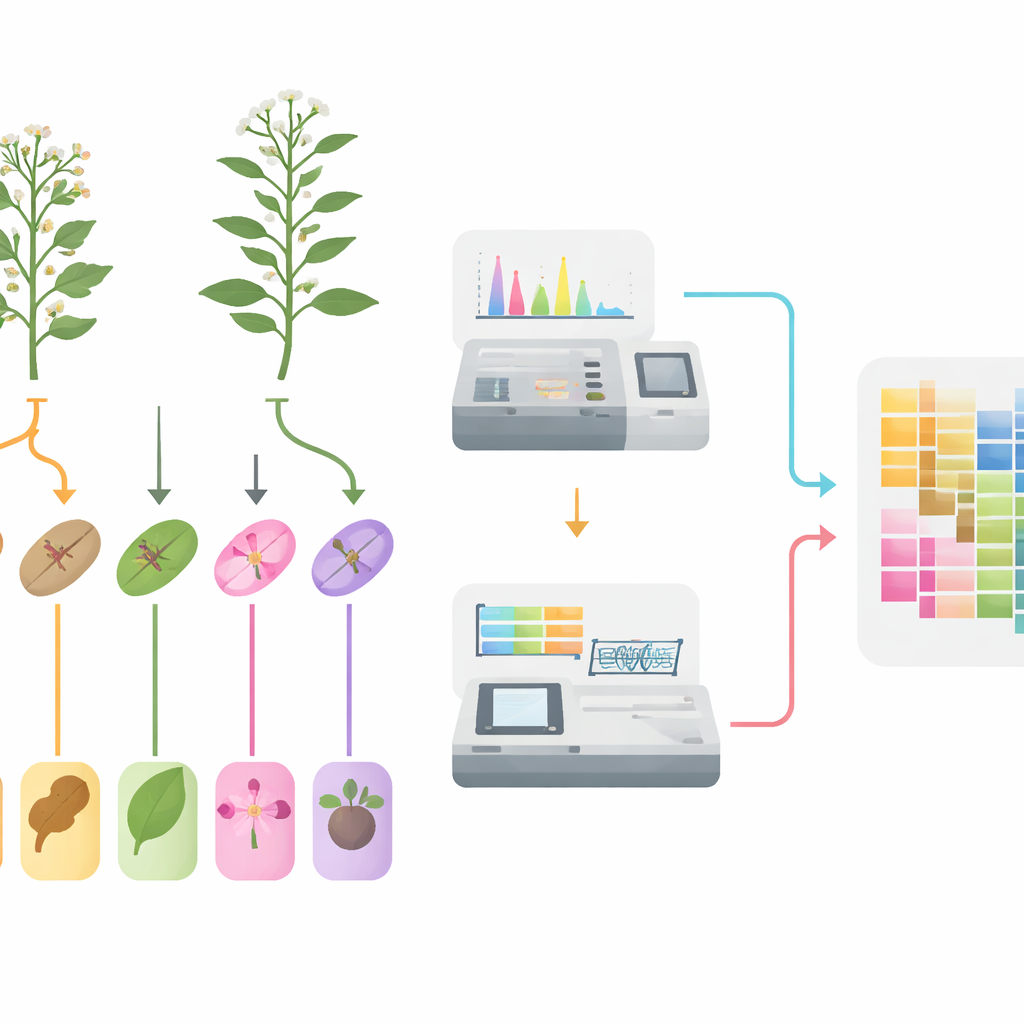
Del campo a las muestras congeladas
Los investigadores comenzaron cultivando ambas especies lado a lado en las mismas condiciones de campo para evitar sesgos ambientales. Durante la floración, separaron cuidadosamente cinco tejidos —raíces, tallos, hojas, flores y frutos— de múltiples plantas de cada especie. Para capturar una imagen fiable de la variación natural, agruparon material de muchos individuos y crearon seis réplicas biológicas por cada tipo de tejido. Cada muestra de tejido se dividió luego en dos: una parte para medir pequeñas moléculas y otra para leer qué genes estaban activos.
Inventario de miles de compuestos vegetales
Para catalogar la composición química de las plantas, el equipo utilizó un enfoque sensible basado en espectrometría de masas que puede rastrear un gran número de metabolitos vegetales conocidos en una sola corrida. En 60 muestras detectaron 1.342 moléculas distintas, dominadas por grupos ya sospechados de ser importantes para usos medicinales: casi una cuarta parte fueron flavonoides, seguidos por ácidos fenólicos, alcaloides y terpenoides. Los análisis estadísticos mostraron que las muestras de tejido se agruparon claramente por tipo, y los controles de calidad confirmaron que las mediciones eran estables y reproducibles. Al comparar el mismo tejido entre las dos especies se identificaron numerosas moléculas mucho más abundantes en una especie que en la otra, especialmente en rutas vinculadas a pigmentos de color, compuestos defensivos y otros metabolitos especializados.
Leyendo los manuales de instrucciones de las plantas
En paralelo, los científicos extrajeron ARN de los mismos tejidos para ver qué genes estaban activos, capturando así las instrucciones internas de las plantas en el momento del muestreo. La secuenciación de alto rendimiento generó más de 500 gigabases de datos de alta calidad y condujo a la identificación de 37.644 genes en Oldenlandia diffusa y 20.825 genes en Oldenlandia corymbosa. De nuevo, las muestras del mismo tejido se agruparon entre sí, lo que subraya la fiabilidad de los datos. Al comparar tejidos, el equipo encontró miles de genes que se comportaban de forma diferente entre raíces y partes aéreas, o entre tallos, hojas, flores y frutos. Muchos de estos genes participan en la captura de energía, el metabolismo básico y en enzimas que modifican compuestos vegetales —exactamente los tipos de actividades que determinarían dónde se sintetizan y almacenan los compuestos medicinales.
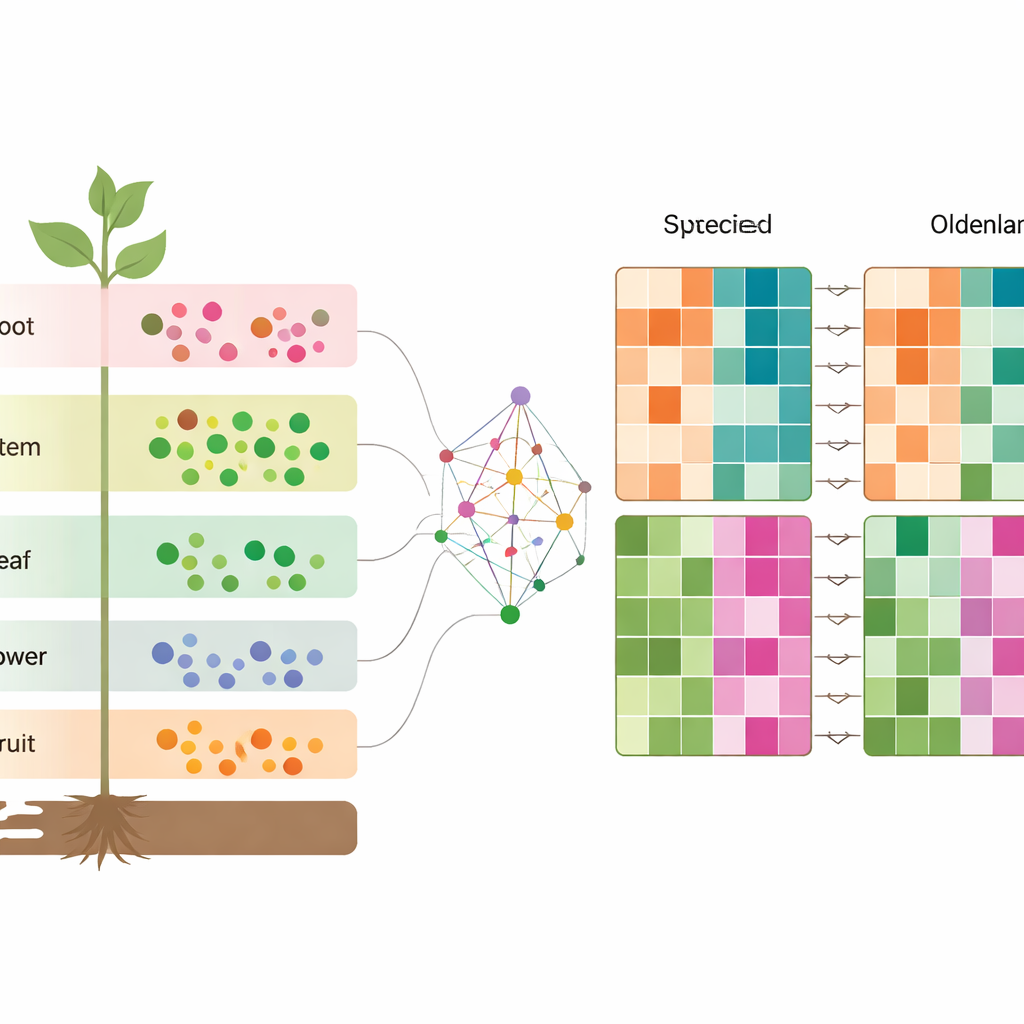
Analizando las diferencias entre las dos especies
Para entender qué separa verdaderamente a las especies, los autores emparejaron genes de O. diffusa y O. corymbosa que son contrapartes directas y luego compararon su actividad en cada tejido. Descubrieron miles de genes regulados al alza o a la baja en una especie respecto a la otra en raíces, tallos, hojas, flores y frutos. Estos genes pertenecían a rutas que sintetizan y procesan compuestos clave, incluidos terpenoides, fenilpropanoides y diversas moléculas que contienen nitrógeno. Al combinar estos hallazgos con los datos metabolómicos, se revela una imagen por capas: cada tejido tiene su propia huella química y genética, y esas huellas cambian de manera característica entre las dos hierbas estrechamente relacionadas.
Qué significa esto para la medicina y la investigación futura
Para el público general, la conclusión principal es que estas dos plantas medicinales de apariencia similar no son intercambiables. Bajo su aspecto parecido, sus raíces, tallos, hojas, flores y frutos difieren tanto en las cantidades de pequeñas moléculas importantes como en la actividad de los genes que las producen. Al publicar este gran conjunto de datos cuidadosamente validado, el estudio proporciona un atlas de referencia que otros científicos pueden explorar para identificar qué ingredientes pueden ser responsables de efectos concretos para la salud y qué genes podrían dirigirse para criar o diseñar plantas con propiedades más consistentes y potentes. En última instancia, este tipo de cartografía profunda puede ayudar a transformar las mezclas herbales tradicionales en medicinas mejor comprendidas y de uso más preciso.
Cita: Chen, P., Huang, Z., Wen, Y. et al. Metabolomic and Transcriptomic Profiling of Two Closely Related Species within the Genus Oldenlandia. Sci Data 13, 378 (2026). https://doi.org/10.1038/s41597-026-06745-y
Palabras clave: Oldenlandia, plantas medicinales, metabolómica, transcriptómica, metabolitos secundarios de plantas