Clear Sky Science · es
Colección de arqueas del intestino humano de la población estonia
Un mundo oculto dentro de nuestros intestinos
El intestino humano alberga billones de microbios que ayudan a digerir los alimentos, moldean nuestro sistema inmunitario e influyen en la salud de maneras sorprendentes. La mayor parte de la investigación se ha centrado en las bacterias, pero otro grupo de formas de vida microscópicas, llamadas arqueas, ha permanecido en gran medida en la sombra. Este estudio arroja luz sobre esos habitantes poco atendidos al construir un catálogo detallado de genomas de arqueas procedentes de personas que viven en Estonia, proporcionando a los científicos un nuevo mapa de ese mundo oculto y herramientas para explorar cómo afecta a nuestro organismo.
Por qué importan estos microbios poco conocidos
Las arqueas son formas de vida antiguas que, al mirarlas al microscopio, se parecen a las bacterias pero son fundamentalmente diferentes. En el intestino humano, muchas arqueas se especializan en convertir hidrógeno y dióxido de carbono en gas metano. Su presencia ya se ha asociado con un tránsito intestinal más lento, ciertas formas del síndrome del intestino irritable, obesidad e incluso cáncer colorrectal. Sin embargo, hasta ahora los científicos contaban con relativamente pocos genomas de referencia para estudiarlas, y la mayor parte de lo que sabemos proviene de un reducido número de especies bien estudiadas. Esa carencia dificulta detectar todas las especies de arqueas en el intestino de una persona o entender cómo podrían contribuir a la salud o la enfermedad.
Construir una biblioteca de genomas a partir de toda una población
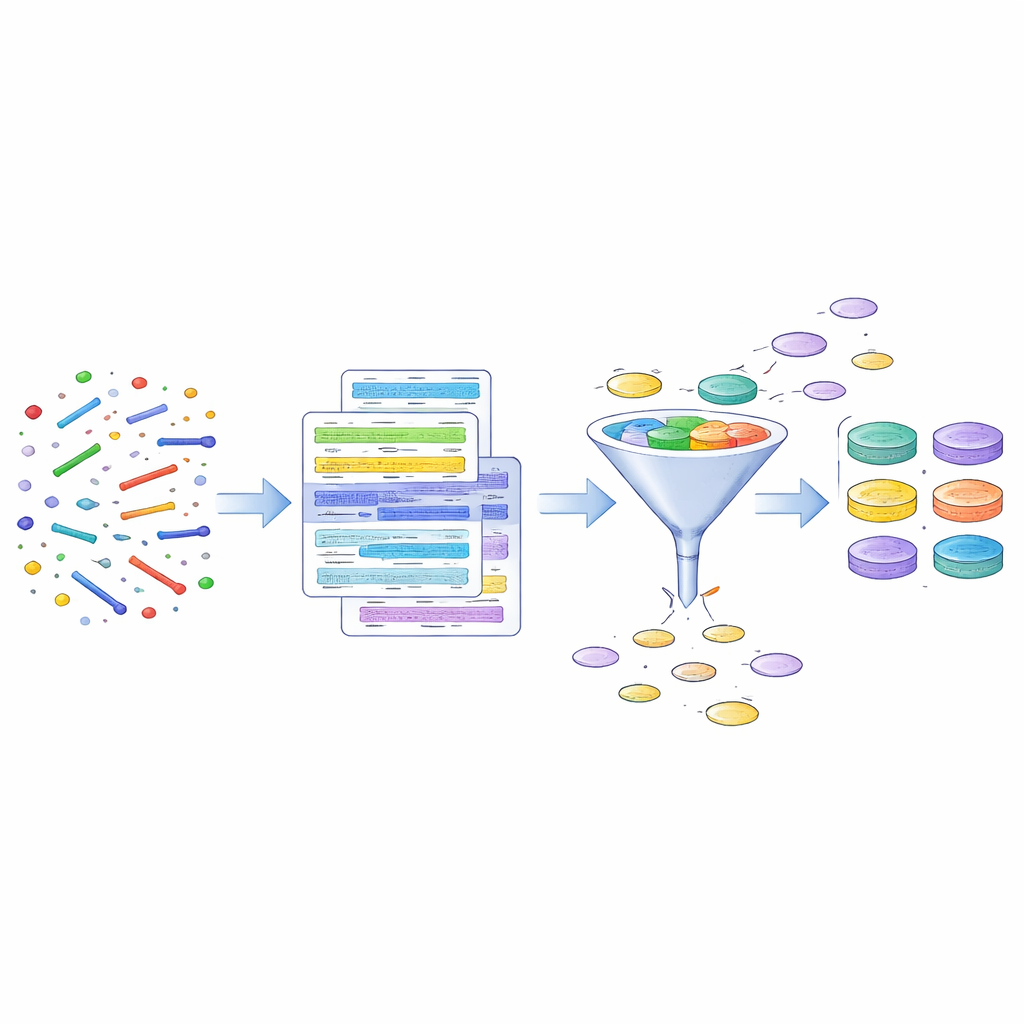
Los investigadores empezaron con datos del microbioma intestinal de 1.878 voluntarios del cohorte Estonian Microbiome, un gran estudio de salud que incluye personas de distintas edades y ambos sexos. En lugar de cultivar microbios en el laboratorio, utilizaron fragmentos de ADN recogidos de muestras de heces y los ensamblaron computacionalmente hasta obtener genomas casi completos, un método conocido como metagenómica. De más de 84.000 genomas reconstruidos de todo tipo de microbios, se centraron en los 316 que inicialmente se identificaron como arqueas. Tras controles de calidad exhaustivos, ese conjunto se redujo a 273 genomas de arqueas, formando una colección curada que llaman “EstMB MAGdb Archaea-273”.
Limpiar los datos para evitar falsos descubrimientos
Reconstruir genomas a partir de fragmentos brutos de ADN es un poco como recomponer decenas de libros triturados a la vez, y los errores pueden dar lugar a quimeras: genomas falsos cosidos con piezas que no pertenecen juntas. Para evitarlo, el equipo fue más allá de las métricas de calidad estándar. Comprobaron qué tan completo era cada genoma y cuánta contaminación contenía, examinaron el tamaño general del genoma y analizaron si los fragmentos más pequeños dentro de cada genoma apuntaban a un origen biológico coherente. Se eliminaron genomas sospechosos, como los de tamaño anormalmente grande o con señales taxonómicas inconsistentes. Un caso llamativo implicó tres genomas que parecían pertenecer a un grupo de arqueas muy inusual y raramente visto en humanos; análisis adicionales mostraron que probablemente eran artefactos técnicos, lo que subraya lo fácil que es que se cuelen errores en los catálogos de genomas.
De cientos de genomas a los representantes clave
Para facilitar el uso de su recurso, los autores agruparon los 273 genomas en conglomerados a nivel de especie según la similitud de sus secuencias de ADN. Este proceso dio lugar a 21 especies de arqueas distintas, y el equipo eligió un genoma bien ensamblado y de alta calidad para representar cada especie. Estos 21 representantes, denominados colectivamente “Archaea ESTrep-21”, pueden servir como panel de referencia para estudios futuros. Usando estos genomas como plantilla, los investigadores estimaron a continuación qué tan comunes es cada especie y qué abundancia tiende a presentar en la población estonia. La colección también incluye múltiples genomas para algunas especies, lo que abre la puerta a explorar variaciones a nivel de cepa—diferencias que, en última instancia, podrían ayudar a explicar por qué la misma especie puede ser inofensiva en una persona pero estar asociada con enfermedad en otra.
Qué significa esto para la investigación sanitaria futura
Para el público no especializado, la conclusión clave es que este trabajo no afirma haber descubierto un nuevo microbio causante de enfermedades. En cambio, proporciona el material de referencia de alta calidad en el que se apoyarán muchos estudios futuros. Al ofrecer una biblioteca depurada y bien documentada de genomas de arqueas del intestino humano, los autores facilitan que los científicos de todo el mundo detecten estos microbios con precisión, comparen su presencia entre poblaciones y vinculen arqueas o cepas específicas con rasgos como el hábito intestinal, el peso o el riesgo de enfermedad. De la misma manera que un buen mapa permite a los exploradores navegar un nuevo terreno, esta colección de genomas de arqueas de Estonia equipa a los investigadores para explorar un rincón previamente poco cartografiado de nuestro ecosistema interno.
Cita: Pantiukh, K., Org, E. Human gut archaea collection from Estonian population. Sci Data 13, 366 (2026). https://doi.org/10.1038/s41597-026-06742-1
Palabras clave: microbioma intestinal, arqueas, metagenómica, salud humana, catálogo de genomas