Clear Sky Science · es
Secuenciación del genoma, ensamblaje de novo y anotación del bambú comercialmente importante, Bambusa tulda Roxb
Una hierba de crecimiento rápido con gran potencial
El bambú puede parecer una planta de jardín sencilla, pero en realidad es un recurso natural poderoso para la construcción, la fabricación de papel e incluso futuros biocombustibles. Una especie de uso extendido, Bambusa tulda o bambú bengalí, crece con rapidez, acumula grandes cantidades de material leñoso y florece solo en raras ocasiones. Hasta ahora, los científicos carecían de un “manual de instrucciones” completo para esta especie. Este artículo describe cómo los investigadores decodificaron y organizaron la secuencia completa del ADN de B. tulda, creando un recurso fundamental que ayudará a mejorar el bambú para la industria, la conservación y tecnologías respetuosas con el clima.
¿Por qué descodificar el ADN de un bambú?
Bambusa tulda es común en el subcontinente indio y en partes del sudeste asiático, donde sus colmos (tallos) fuertes se emplean en construcción rural, mobiliario y artesanía. También despierta interés como fuente de pulpa para papel y energía renovable. Sin embargo, B. tulda presenta comportamientos enigmáticos: puede crecer muy rápido, acumular mucho material leñoso y luego esperar alrededor de 50 años antes de florecer, a veces con todas las plantas de una zona floreciendo a la vez. Sin una secuencia genómica completa, los científicos solo podían suponer qué genes controlan estos rasgos. Al leer y ensamblar su ADN, los autores buscaron construir un mapa de referencia que los futuros investigadores puedan usar para estudiar el crecimiento, la floración, la resistencia a enfermedades y más.
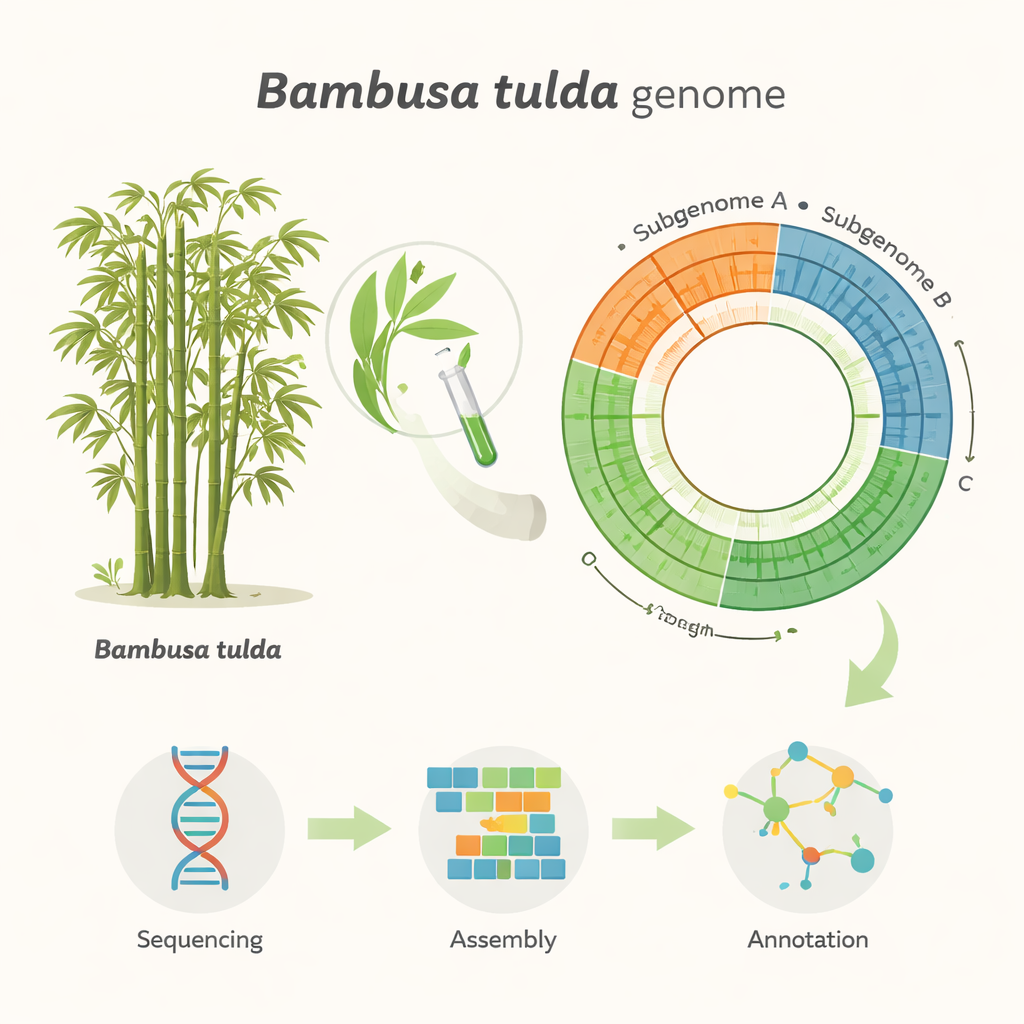
Midiendo y leyendo un genoma gigante
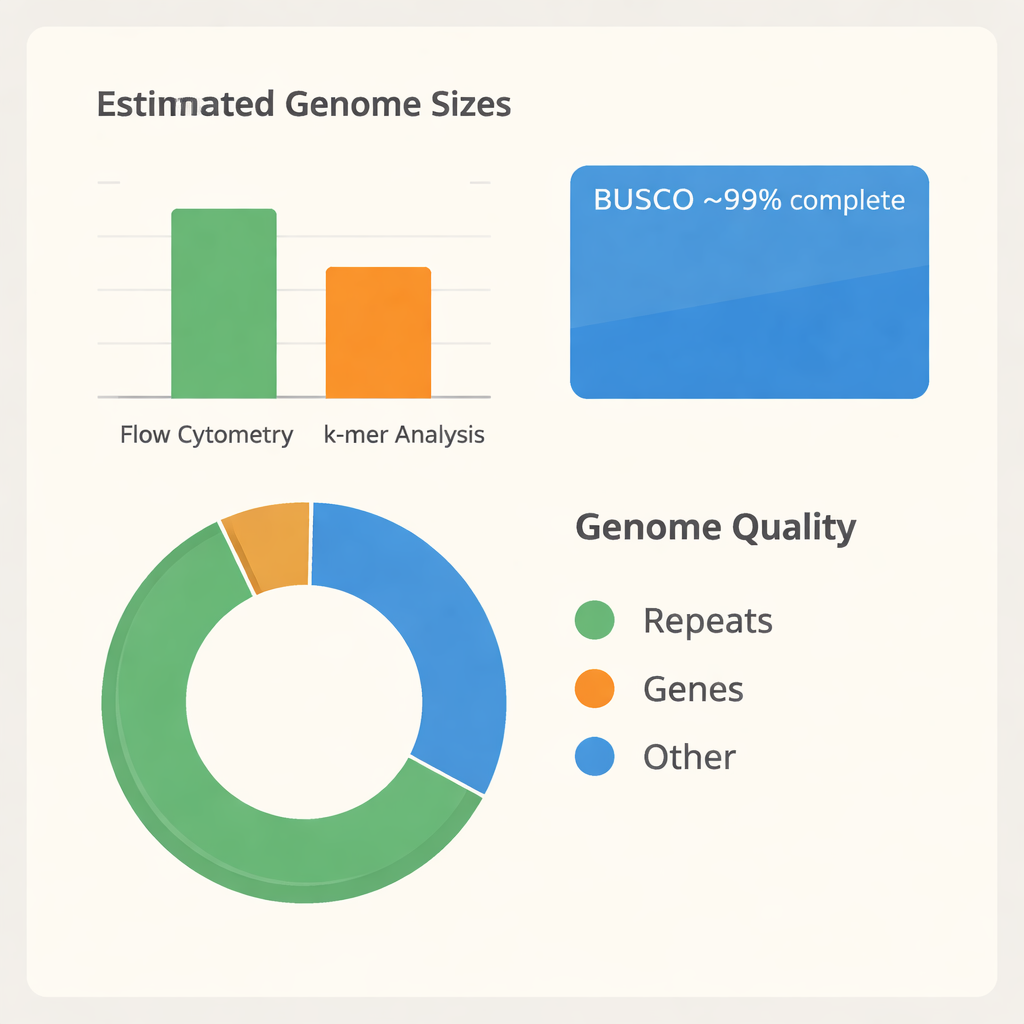
El equipo primero necesitó entender cuán grande es el genoma de B. tulda. Usando una técnica llamada citometría de flujo, compararon el contenido de ADN de las células foliares de B. tulda con el de tomate y maíz, dos plantas cuyos tamaños genómicos ya se conocen. Esto sugirió un tamaño genómico diploide de aproximadamente 3 mil millones de “letras” de ADN. Luego usaron un segundo enfoque independiente basado en cómo se solapan fragmentos cortos de ADN (análisis de k-mer), que estimó un tamaño algo menor, de aproximadamente 2,34 mil millones de letras, y reveló que gran parte del genoma es repetitivo y probablemente duplicado. Con estas medidas, extrajeron ADN muy largo y de alta calidad de hojas jóvenes y lo secuenciaron usando la avanzada tecnología PacBio HiFi, generando más de 116 mil millones de bases de datos sin procesar, suficiente para leer el genoma decenas de veces.
Uniendo el plano del bambú
Convertir millones de lecturas de ADN en un genoma ordenado es como montar un rompecabezas gigantesco sin la imagen de la caja. Los investigadores usaron software especializado para construir tanto un ensamblaje primario combinado como dos haplotipos separados, reflejando las dos copias parentales del genoma. Tras eliminar fragmentos duplicados y derivados de orgánulos, consiguieron un ensamblaje “haploide” depurado de 43 grandes segmentos, que cubren alrededor de 1,37 mil millones de bases. Estos segmentos se agrupan en tres subgenomas, etiquetados A, B y C, consistentes con el origen complejo y poliploide de B. tulda. Una prueba de calidad ampliamente usada llamada BUSCO mostró que aproximadamente el 99% de los genes vegetales esperados están presentes e intactos, lo que indica que el ensamblaje es tanto completo como fiable para estudios posteriores.
Genes, repeticiones y pistas evolutivas
Una vez ensamblado el genoma, el siguiente paso fue identificar sus partes funcionales. Combinando tres líneas de evidencia —predicciones a partir de la propia secuencia de ADN, similitud con genes de otros bambús y datos de ARN de genes expresados activamente— el equipo anotó 56.890 genes codificadores de proteínas, que ocupan aproximadamente una quinta parte del genoma. También catalogaron gran número de ARN no codificantes, incluyendo más de mil genes de ARN de transferencia y ARN ribosómico que sostienen la producción de proteínas. De manera llamativa, alrededor de dos tercios del genoma consiste en elementos repetitivos, especialmente segmentos de ADN móvil que se copian y desplazan. Estas repeticiones ayudan a explicar por qué las estimaciones de tamaño anteriores diferían y apuntan a una historia evolutiva dinámica. La comparación de familias proteicas entre otras doce especies de bambú, junto con maíz y plátano como parientes, sitúa a B. tulda firmemente entre los bambús leñosos paleotropicales con un fondo hexaploide, confirmando que su genoma se construyó a partir de múltiples copias ancestrales.
Una nueva base para la investigación futura del bambú
Para quienes no son especialistas, el resultado clave es que B. tulda ya dispone de un genoma de referencia de alta calidad: un plano indexado y buscable de su ADN. Este recurso permitirá a los científicos localizar genes que controlan el crecimiento rápido, la lignificación y la floración retardada, y compararlos con los de otras gramíneas. También apoyará esfuerzos para criar o diseñar variedades de bambú mejor adaptadas a la construcción, la producción de papel o la energía, al tiempo que se preservan las poblaciones naturales. En resumen, al cartografiar el paisaje genético de este bambú de importancia comercial, el estudio sienta las bases para un uso más inteligente de una de las plantas más versátiles del mundo.
Cita: Kundu, S., Rupp, O., Dey, S. et al. Genome sequencing, de novo assembly and annotation of the commercially important bamboo, Bambusa tulda Roxb. Sci Data 13, 175 (2026). https://doi.org/10.1038/s41597-026-06679-5
Palabras clave: genoma de bambú, Bambusa tulda, genética vegetal, gramíneas leñosas, biomateriales renovables