Clear Sky Science · es
Un ensamblaje genómico a nivel cromosómico de Homatula variegata de la cuenca del río Yangtsé
Un pez de arroyo diminuto con una gran historia genética
En los arroyos rápidos y pedregosos que alimentan la parte alta del río Yangtsé de China vive una pequeña locha rayada llamada Homatula variegata. Es apreciada tanto para la mesa como para acuarios domésticos, pero hasta ahora se sabía muy poco sobre su plano genético. Este estudio ofrece el primer mapa casi completo, cromosoma por cromosoma, del genoma de la especie, abriendo la puerta a una conservación más inteligente, una cría más eficiente y una mayor comprensión de cómo la vida se adapta a aguas frías y rápidas de montaña.
¿Por qué mapear el ADN de un pez de aspecto modesto?
Aunque esta locha alcanza solo alrededor de 14 centímetros, desempeña un papel desproporcionado en los ecosistemas fluviales locales y en la acuicultura regional. Prosperan en arroyos de altitud media con fondos de guijarros y corrientes constantes, alimentándose de insectos, detritos orgánicos y peces pequeños. Por ser a la vez sabrosa y colorida, existe un interés creciente en su cría como especie ornamental y alimentaria autóctona. Sin embargo, criar y proteger una especie es mucho más difícil sin una referencia genética precisa. Un genoma completo actúa como una lista detallada de piezas y un diagrama de cableado, revelando los genes que determinan el crecimiento, el color, la resistencia a enfermedades y la capacidad de soportar aguas rápidas y frías. Hasta ahora, ninguna locha de esta rama de la familia de peces contaba con una referencia de tan alta calidad, dejando un importante punto ciego en la genética de peces de agua dulce.
Construyendo un mapa de ADN cromosoma por cromosoma
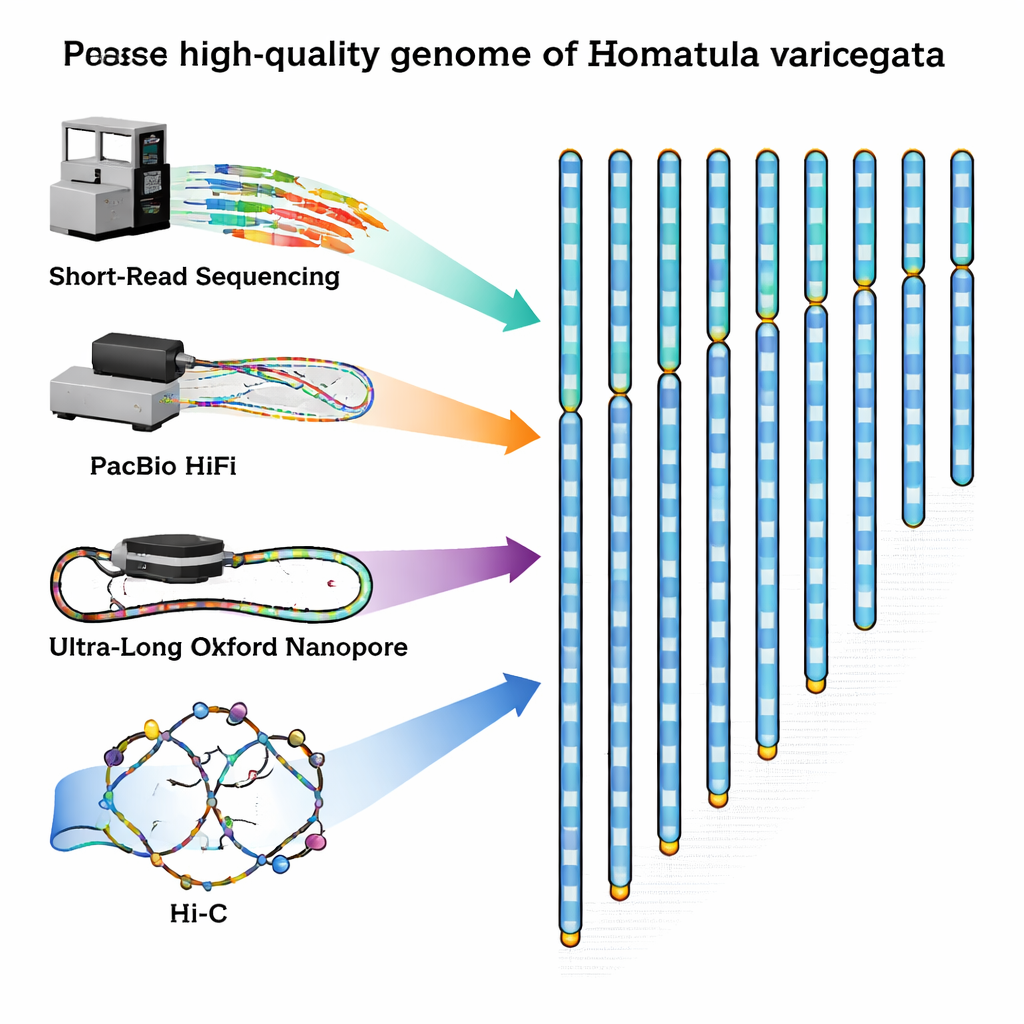
Para llenar este vacío, los investigadores capturaron un macho adulto sano de la locha en el río Qingyi, un afluente del Yangtsé, y extrajeron cuidadosamente ADN y ARN de su sangre. Luego combinaron varios métodos de secuenciación de última generación, cada uno con fortalezas distintas. Máquinas de lecturas cortas de Illumina produjeron enormes cantidades de fragmentos de ADN de alta precisión. La tecnología PacBio HiFi ofreció fragmentos algo más largos con excelente exactitud, mientras que los dispositivos de Oxford Nanopore generaron hebras ultra largas capaces de atravesar regiones repetitivas difíciles de descifrar. Finalmente, un método llamado Hi‑C capturó cómo las hebras de ADN se pliegan e interactúan dentro del núcleo celular, proporcionando un mapa de contactos 3D que ayuda a unir fragmentos en cromosomas completos en el orden correcto.
Qué revela el nuevo genoma
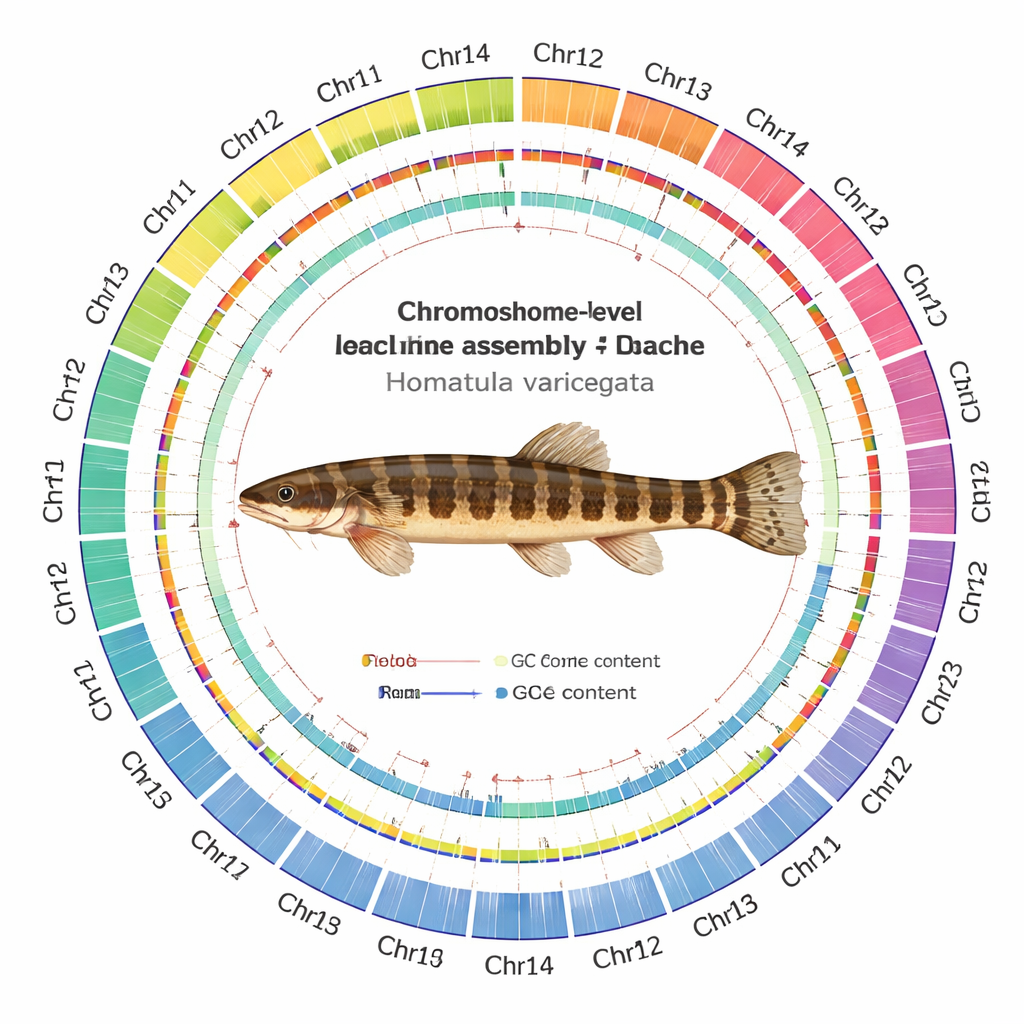
Al entrelazar estos datos con software de ensamblaje moderno y controles de calidad cuidadosos, el equipo produjo un genoma de 641 millones de letras de ADN, ordenado en 24 cromosomas. Sorprendentemente, cada cromosoma está ensamblado como una pieza continua; 22 de ellos sin huecos y solo con pequeñas lagunas en dos. Pudo localizarse 24 centrómeros probables —el “cinturón” central de cada cromosoma— y detectarse la mayoría de las tapas teloméricas protectoras en los extremos cromosómicos. Los científicos catalogaron 24.479 genes codificadores de proteínas y pudieron asignar funciones probables a aproximadamente el 93% de ellos mediante comparación con grandes bases de datos internacionales. También cartografiaron el paisaje del ADN repetitivo, encontrando que más de una cuarta parte del genoma consiste en elementos genéticos móviles, especialmente transposones de ADN, que pueden saltar por el genoma y, a veces, impulsar la evolución.
Comprobando la calidad bajo el capó
Los indicadores a alto nivel solo tienen sentido si el mapa subyacente es fiable. Por ello, el equipo sometió el ensamblaje a una batería de pruebas. Las lecturas de todas las plataformas de secuenciación se alinearon con el nuevo genoma a tasas muy altas, con cobertura uniforme a lo largo de la mayor parte de los cromosomas. Herramientas independientes que cuentan patrones cortos de ADN sugirieron que casi todo el contenido de secuencia esperado está presente, y las pruebas estándar de integridad génica mostraron que la gran mayoría de los genes universales de peces están intactos. Los mapas de contacto Hi‑C formaron patrones limpios y cuadrangulares a lo largo de cada cromosoma, con poca señal dispersa entre ellos, lo que indica que los segmentos están correctamente unidos y no revueltos.
Del mapa de ADN al impacto en el mundo real
Para un no especialista, este trabajo puede sonar como un triunfo técnico por sí mismo, pero sus implicaciones son prácticas y amplias. Contar con un genoma casi completo para Homatula variegata proporciona a los científicos una referencia contra la cual comparar poblaciones silvestres, vigilar la diversidad genética y detectar signos de endogamia o adaptación local. Los criadores pueden buscar marcadores de ADN vinculados a rasgos deseables como crecimiento rápido, resistencia o coloración llamativa, acelerando la cría selectiva sin sacrificar el carácter natural de la especie. Los ecólogos pueden explorar cómo ha evolucionado esta locha para vivir en arroyos de montaña fríos y de fuerte corriente, lecciones que también pueden informar la gestión de especies emparentadas. En resumen, este genoma a nivel cromosómico convierte a un modesto pez de río en un modelo poderoso para comprender —y proteger— la rica vida de los ecosistemas de agua dulce asiáticos.
Cita: Tang, Y., Wu, Q., Wang, Y. et al. A chromosome level genome assembly of Homatula variegata from the Yangtze River basin. Sci Data 13, 303 (2026). https://doi.org/10.1038/s41597-026-06667-9
Palabras clave: genoma de pez, ensamblaje cromosómico, biodiversidad de agua dulce, genética de acuicultura, locha del río Yangtsé