Clear Sky Science · es
Un recurso curado de genomas quimolitotrofoautótrofos y genes marcadores para la predicción de vías de fijación de CO₂
Microbios que ayudan a equilibrar el presupuesto de carbono de la Tierra
Ocultos en suelos, océanos y ambientes extremos, ciertos microbios pueden construir su propia biomasa usando dióxido de carbono (CO₂) como su principal fuente de carbono. Estos microquímicos microscópicos son cruciales para mantener el ciclo del carbono de la Tierra en equilibrio y pueden inspirar nuevas formas de capturar el CO₂ industrial. Sin embargo, hasta ahora los científicos carecían de una forma simple y fiable para mirar el ADN de un microbio y decir qué estrategia de fijación de CO₂ emplea. Este estudio presenta un catálogo de genes curado y una nueva herramienta informática, AutoFixMark, diseñada para cubrir esa laguna.
Muchas rutas para convertir el aire en biomasa
No todos los organismos que fijan CO₂ lo hacen de la misma manera. Los microbios han evolucionado al menos siete vías naturales que convierten el CO₂ en materia orgánica. Algunas, como el ciclo de Calvin–Benson–Bassham común en plantas y muchas bacterias, son bien conocidas; otras, como la vía reductiva de la glicina descubierta solo en 2020, todavía están poco cartografiadas. Estas vías están dispersas a lo largo de muchas ramas del árbol de la vida y con frecuencia reutilizan enzimas similares, lo que dificulta sorprendentemente diferenciarlas solo por la secuencia del genoma. El software existente puede predecir capacidades metabólicas generales, pero no ha sido optimizado ni probado a fondo para identificar con precisión las rutas exactas de fijación de CO₂.
Construyendo un mapa de referencia limpio de microbios fijadores de CO₂
Los investigadores empezaron reuniendo dos colecciones de genomas cuidadosamente comprobadas. Primero, seleccionaron 15 microbios bien estudiados cuyas vías de fijación de CO₂ se han descrito en detalle. Estos organismos de referencia, que abarcan varios grupos bacterianos y arqueales, sirvieron como planos para definir las enzimas clave que son verdaderamente distintivas de cada vía. A continuación, crearon un conjunto de referencia de 347 genomas quimolitotrofoautótrofos —microbios que obtienen energía de químicos inorgánicos y construyen biomasa a partir de CO₂—. Cada genoma de este conjunto mayor fue vinculado, manualmente a partir de la bibliografía, a vías específicas de fijación de CO₂, proporcionando un conjunto de verdad sólido para evaluar las predicciones.
Genes marcadores y reglas simples en lugar de cajas negras
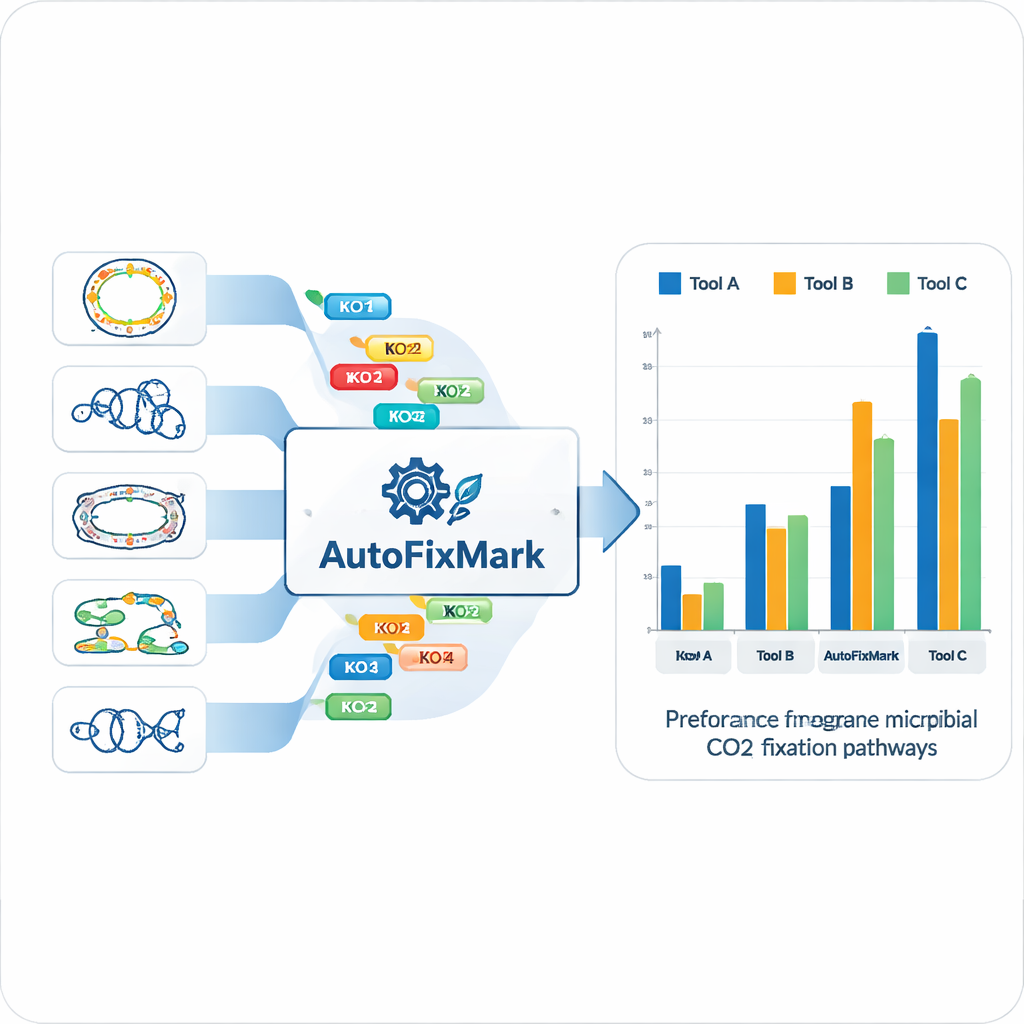
Usando los 15 genomas de referencia, el equipo identificó “genes marcadores” para cada una de las siete vías de fijación de CO₂ y los mapeó a identificadores estandarizados de KEGG Orthology (KO). En lugar de depender de aprendizaje automático opaco, codificaron reglas transparentes sobre cómo se combinan estos marcadores. Algunas reacciones pueden ser llevadas a cabo por cualquiera de varias enzimas alternativas, resueltas mediante una regla “one_of”. Otras dependen de complejos multisubunidad y deben tener “all_of” un conjunto definido de KOs. Para la vía reductiva de la glicina, donde no se entienden completamente todos los componentes, la herramienta usa reglas “at_least” que requieren un número mínimo de subunidades presentes. Estas reglas lógicas se almacenan en un archivo JSON legible por máquina que forma la base de conocimiento central de AutoFixMark.
Una herramienta ligera que supera al software establecido
AutoFixMark en sí es un programa pequeño basado en reglas escrito en Python. Toma como entrada una lista de IDs KO de los genes del genoma de un microbio, típicamente producida por una herramienta separada llamada KofamScan, y luego verifica qué reglas marcadoras se cumplen para cada una de las siete vías. Los autores compararon AutoFixMark con dos herramientas de anotación metabólica ampliamente usadas, METABOLIC y gapseq, usando su conjunto de referencia de 347 genomas. Las tres herramientas tuvieron buen rendimiento en vías clásicas como el ciclo de Calvin, el ciclo tricarboxílico reductivo y la vía de Wood–Ljungdahl. Sin embargo, AutoFixMark destacó claramente frente a las demás para vías más nuevas o menos comunes, como el ciclo 3-hidroxipropionato/4-hidroxibutirato, el ciclo dicarboxilato/4-hidroxibutirato y la vía reductiva de la glicina, algunas de las cuales ni siquiera están cubiertas por el software competidor.
Qué significan estos resultados para estudios sobre clima y ecología
Los conjuntos de genes curados, el programa AutoFixMark y la colección completa de genomas de referencia están disponibles públicamente. Esto significa que los investigadores pueden ahora rastrear tanto microbios aislados como genomas ensamblados a partir de metagenomas para ver qué estrategias de fijación de CO₂ están genéticamente en condiciones de usar. Es importante destacar que los autores subrayan que AutoFixMark predice potencial genético, no si una vía está activa en condiciones del mundo real. Muchas de estas rutas bioquímicas pueden funcionar en sentido inverso, dependiendo del balance energético de la célula. Aun así, disponer de un método robusto y transparente para señalar microbios fijadores de CO₂ ayudará a los científicos a mapear dónde y cómo la vida extrae carbono de la atmósfera, guiará experimentos sobre vías emergentes y respaldará el diseño de futuras biotecnologías basadas en CO₂.
Cita: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
Palabras clave: fijación microbiana de carbono, metabolismo autótrofo, anotación del genoma, captura de CO2, metagenómica