Clear Sky Science · es
Un conjunto de datos anotado de tinciones de Gram de hemocultivos positivos
Por qué importan las respuestas rápidas en infecciones
Cuando bacterias u hongos entran en el torrente sanguíneo, cada hora sin el tratamiento adecuado puede marcar la diferencia entre la vida y la muerte. Los médicos dependen de una prueba de laboratorio rápida llamada tinción de Gram para identificar qué tipo de microorganismo está presente y elegir antibióticos tempranos. Pero interpretar estas laminillas teñidas al microscopio es un trabajo manual y especializado que requiere tiempo y puede variar entre tecnólogos. Este estudio describe una nueva colección de imágenes de diapositivas de hemocultivos de hospital, cuidadosamente anotada, diseñada para ayudar a que los ordenadores aprendan a leer tinciones de Gram automáticamente y así apoyar una atención más rápida y fiable.
Convertir diapositivas reales de hospital en datos
Los investigadores reunieron 57 tipos distintos de bacterias y hongos que se habían cultivado a partir de frascos de hemocultivo positivos de pacientes como parte del trabajo rutinario del hospital. De enero a mayo de 2024, cuando un hemocultivo señalaba positivo, el personal preparó extendidos teñidos por Gram en portaobjetos de vidrio y confirmó la especie exacta usando un método de identificación de alta precisión llamado espectrometría de masas MALDI-TOF. Sin alterar las rutinas normales ni recoger muestras adicionales, el equipo capturó imágenes digitales de alta resolución de campos típicos bajo un microscopio con inmersión en aceite a 100×, obteniendo 505 imágenes en color de gran tamaño que reflejan lo que los tecnólogos ven en la práctica real.
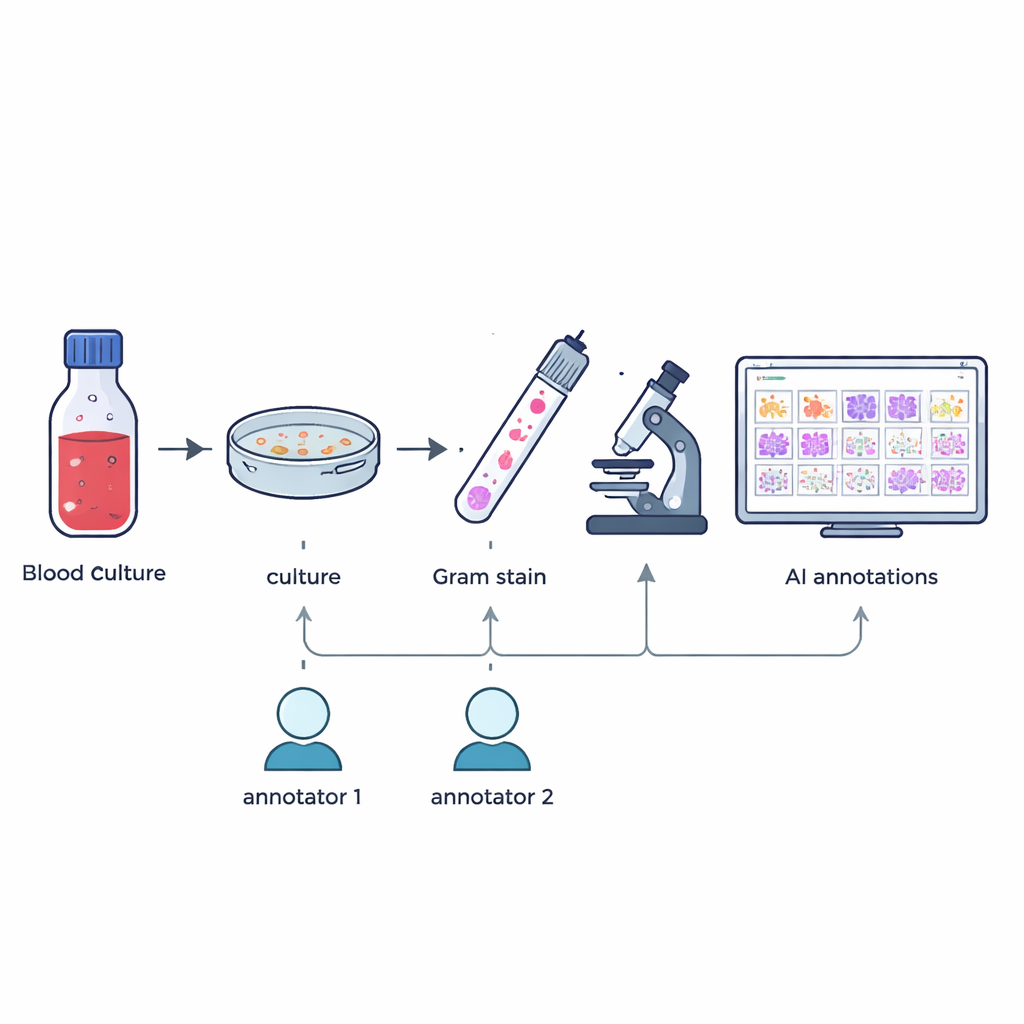
Etiquetado cuidadoso de formas diminutas
Construir un conjunto de enseñanza útil para la inteligencia artificial implica saber exactamente dónde está cada microbio en cada imagen. Dos tecnólogos en microbiología con experiencia dibujaron de forma independiente cajas alrededor de células microbianas individuales o agrupaciones en cada imagen, guiándose únicamente por lo que veían al microscopio. Una herramienta de software personalizada comparó los dos conjuntos de marcas: las cajas que se solaparon lo suficiente se fusionaron y cualquier discrepancia o desacuerdo se marcó. Un experto sénior con más de 20 años de experiencia revisó manualmente estos casos. Este proceso en varios pasos produjo 7.528 anotaciones verificadas que destacan cocos (células redondeadas), bacilos (células en forma de bastón) y hongos, excluyendo objetos parciales o dudosos.
Qué contiene el conjunto de datos
El recurso acabado combina varias capas de información. Las 505 imágenes se proporcionan como archivos JPEG de alta resolución, y las cajas finales verificadas por expertos se almacenan en el formato JSON COCO estándar, ampliamente usado en investigación de visión por ordenador. Archivos adicionales enlazan cada imagen con su especie microbiana, si es Gram-positiva o Gram-negativa, su grupo morfológico amplio, el tipo de frasco de hemocultivo del que procedía y cuánto tardó el cultivo en dar positivo. Debido a que cada imagen contiene solo una especie, todas las cajas dentro de una misma imagen comparten las mismas características biológicas. Los usuarios pueden elegir entre un único archivo grande de anotaciones o archivos separados por imagen, y se incluye un script sencillo en Python para visualizar cualquier imagen con sus cajas superpuestas.
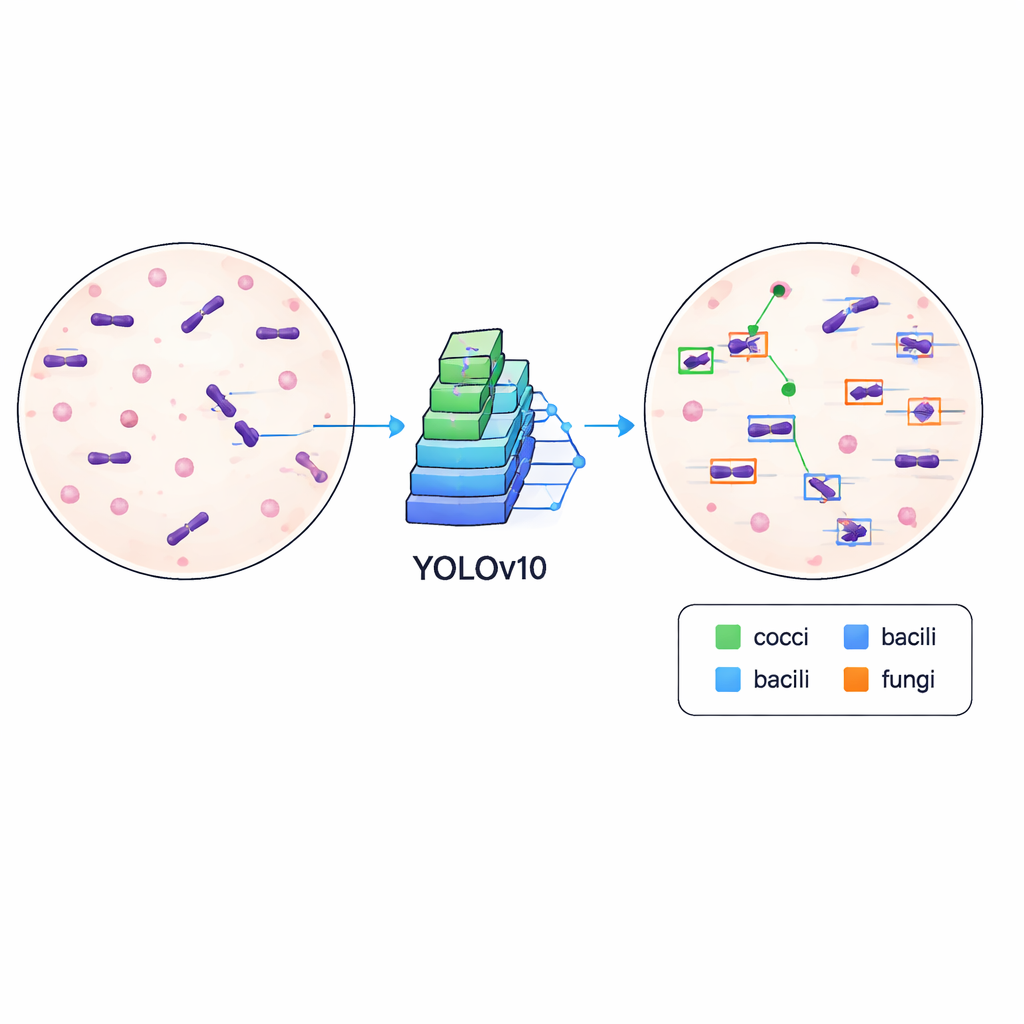
Enseñar a los ordenadores a detectar gérmenes
Para demostrar que el conjunto de datos es no solo ordenado sino también práctico, los autores entrenaron un algoritmo moderno de detección de objetos conocido como YOLOv10 para localizar y clasificar microbios en las imágenes. Dividieron los datos en conjuntos de entrenamiento y validación y ejecutaron el modelo durante 500 rondas de entrenamiento en una tarjeta gráfica de gama alta, monitorizando cuánto había aprendido a dibujar cajas precisas y a distinguir entre distintos tipos celulares. El sistema entrenado alcanzó una precisión media aproximada del 84,6 % en un umbral de correspondencia estándar, lo que indica que puede localizar y etiquetar microbios de forma fiable a través de apariencias variadas de las laminillas, incluyendo diferencias en la intensidad de la tinción, restos de fondo y enfoque.
Cómo se puede usar este recurso
Como los datos siguen formatos comunes, pueden integrarse en muchas canalizaciones de visión por ordenador existentes. Los investigadores podrían primero entrenar un sistema simplemente para distinguir microbios verdaderos de restos (debris), ayudando a los laboratorios a filtrar señales de hemocultivo falsos positivos. También pueden agrupar microbios en formas amplias, acorde con lo que los clínicos necesitan para un informe inicial de «nivel 1» que orienta la elección temprana de antibióticos. Un objetivo más ambicioso es distinguir especies individuales mediante señales visuales sutiles. Los autores señalan limitaciones: algunas células están agrupadas, algunas laminillas proceden de una única fuente por especie y el enfoque puede variar—tal como ocurre en la vida real. Aun así, cada caja incluida ha sido cuidadosamente verificada, lo que hace del conjunto de datos un punto de partida fiable.
Qué significa esto para los pacientes
En términos sencillos, este trabajo convierte las laminillas rutinarias de hemocultivo en un terreno de entrenamiento compartido para software inteligente. Al publicar tanto las imágenes como las marcas de los expertos, el estudio reduce la barrera para que equipos de todo el mundo construyan y prueben herramientas de IA que puedan leer tinciones de Gram de forma rápida y coherente. Aunque dichos sistemas no reemplazarán a los microbiólogos humanos, podrían ayudar a señalar infecciones peligrosas antes, reducir errores de interpretación y favorecer un mejor uso de los antibióticos. Para los pacientes, eso podría traducirse en un tratamiento más rápido y preciso cuando más importa.
Cita: Yi, Q., Gou, X., Zhu, R. et al. An annotated dataset of Gram stains from positive blood cultures. Sci Data 13, 294 (2026). https://doi.org/10.1038/s41597-026-06651-3
Palabras clave: infecciones del torrente sanguíneo, tinción de Gram, conjunto de datos de imágenes médicas, inteligencia artificial, diagnóstico en microbiología