Clear Sky Science · es
Primer ensamblaje y anotación del genoma a nivel cromosómico de una raya de agua dulce en peligro (Fontitrygon garouaensis) de África
Un habitante fluvial raro recibe un foco genómico
En los ríos turbios del África occidental vive una raya poco habitual que ha hecho algo que casi ninguno de sus parientes tiburones y rayas ha hecho: se ha establecido permanentemente en agua dulce. Esta raya de agua dulce de cuerpo liso, Fontitrygon garouaensis, además está en peligro y ha sido poco estudiada. El artículo detrás de esta nota presenta el primer mapa completo de su ADN a nivel cromosómico, ofreciendo una herramienta potente para entender cómo una línea marina tan antigua se ha adaptado a la vida en los ríos y cómo podríamos protegerla mejor.
Por qué importa esta raya
Los tiburones y las rayas pertenecen a una de las ramas más antiguas del árbol evolutivo de los vertebrados, que se separó de los ancestros de los peces óseos hace cientos de millones de años. Sin embargo, pese a su importancia evolutiva, sus genomas siguen siendo poco cartografiados, sobre todo en especies que viven en aguas africanas. Fontitrygon garouaensis es especialmente singular: es la única raya conocida totalmente adaptada a los sistemas de agua dulce africanos, y muestra rasgos corporales distintivos como una fila reducida o ausente de espinas en el dorso. Dado que el paso del mar salado a los ríos de agua dulce es raro y supone un desafío fisiológico para tiburones y rayas, esta especie ofrece un experimento natural sobre cómo los animales reconfiguran su biología para afrontar nuevos entornos.
Construyendo un mapa de referencia genético
Para desentrañar el plano genético de la raya, los investigadores recolectaron una hembra adulta del río Níger en Nigeria y extrajeron ADN y ARN de alta calidad de múltiples tejidos. Luego emplearon una estrategia “híbrida” que combina tres enfoques de secuenciación de vanguardia. La secuenciación de lecturas cortas Illumina proporciona un enorme número de pequeños fragmentos de ADN; la secuenciación de lecturas largas PacBio HiFi genera tramos mucho más largos y continuos; y la secuenciación Hi-C captura cómo se pliega e interactúa el ADN dentro del núcleo celular. Al entretejer estos conjuntos de datos con software especializado, el equipo ensambló un genoma de aproximadamente 4,19 mil millones de letras de ADN, organizado en 41 piezas a escala cromosómica —comparable en tamaño a algunos de los genomas de tiburón más grandes conocidos.
Qué revela el genoma
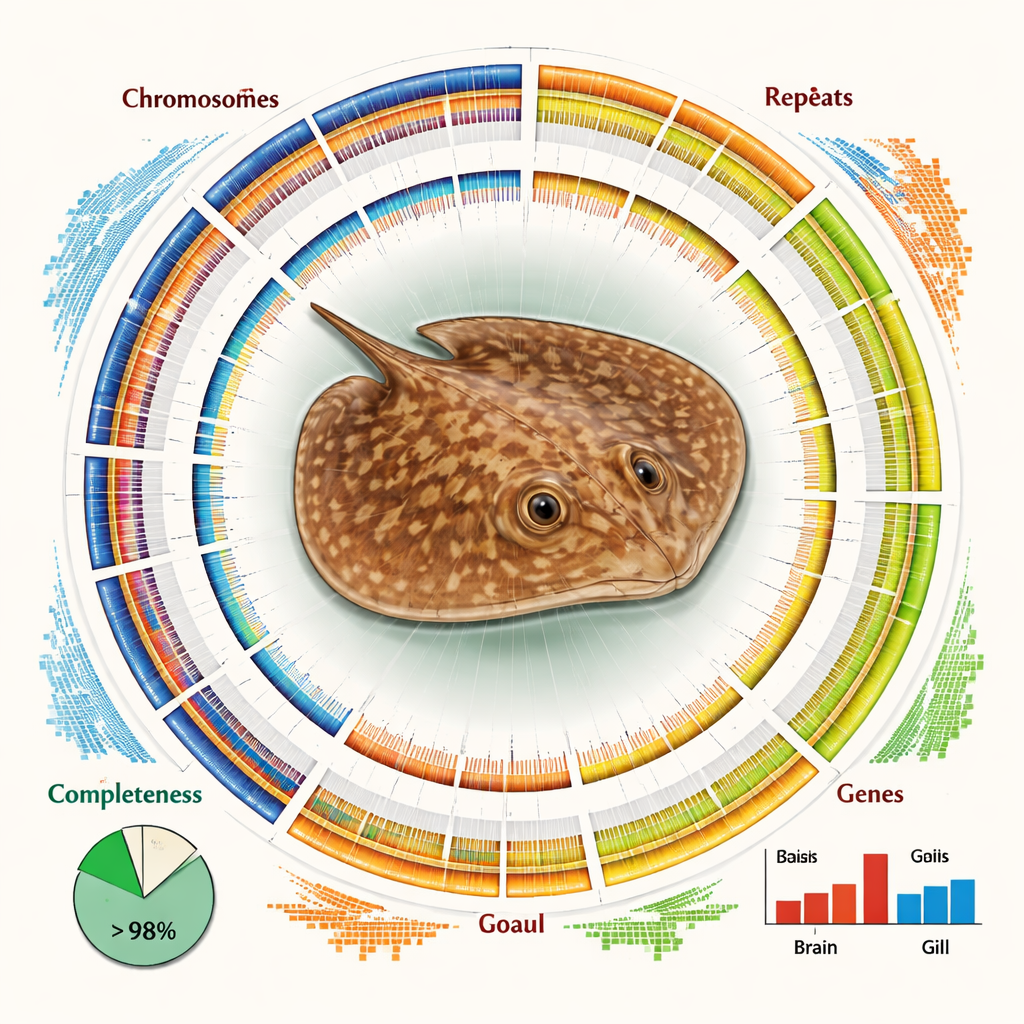
El ensamblaje final es tanto grande como notablemente completo. Controles de calidad independientes muestran que más del 93 por ciento de los genes vertebrados centrales esperados están presentes e intactos, y más del 84 por ciento de la secuencia total de ADN está asignada con confianza a cromosomas específicos. El genoma está dominado por ADN repetitivo —tramos de secuencia que aparecen muchas veces— que constituyen aproximadamente dos tercios de su longitud. Muchos de estos repeticiones pertenecen a elementos genéticos móviles como LINEs y LTRs, que se han copiado e insertado a lo largo del genoma a lo largo del tiempo evolutivo. A pesar de esta complejidad, los investigadores identificaron casi 30 000 genes codificantes de proteínas y pudieron asignar funciones probables a más del 98 por ciento de ellos usando bases de datos internacionales de proteínas y vías metabólicas.
Pistas sobre la vida en agua dulce y la evolución
Tener un mapa a nivel cromosómico permitió al equipo hacer más que listar genes. Al comparar los cromosomas de la raya con los de tiburones y rayas emparentados, descubrieron una historia de reordenamientos estructurales —roturas, fusiones y reorganizaciones de segmentos cromosómicos completos— que distingue a esta línea. Estos cambios podrían haber contribuido a modelar los rasgos únicos de la especie y su nicho ecológico. Los autores también examinaron la actividad génica en dos tejidos clave: las branquias, que median la respiración y el equilibrio salino con el agua circundante, y el cerebro. Encontraron diferencias claras en qué genes están activados, con genes de las branquias enriquecidos en vías relacionadas con el uso de energía y el metabolismo de grasas, lo que sugiere los ajustes bioquímicos necesarios para sobrevivir en agua dulce.
Una nueva base para la conservación
En esencia, este trabajo convierte a una raya fluvial oscura y amenazada en uno de los peces cartilaginosos mejor caracterizados a nivel del ADN. Para quienes no son especialistas, eso significa que los científicos cuentan ahora con un manual de referencia detallado de la especie, desde sus cromosomas hasta genes individuales. Esta referencia puede orientar estudios futuros sobre cómo afronta cambios en la calidad del agua, cómo están estructuradas sus poblaciones a lo largo de los ríos y cómo se relaciona con otras rayas. Igualmente importante, proporciona una base genómica para la planificación conservacionista, ofreciendo nuevas formas de monitorear la diversidad genética, identificar poblaciones distintas que merezcan protección y entender cómo esta rara especialista de agua dulce podría responder a las presiones ambientales continuas.
Cita: Nneji, L.M., Oladipo, S.O., Oyebanji, O.O. et al. First Chromosome-level Genome Assembly and Annotation of an Endangered Freshwater Stingray (Fontitrygon garouaensis) from Africa. Sci Data 13, 302 (2026). https://doi.org/10.1038/s41597-026-06646-0
Palabras clave: raya de agua dulce, ensamblaje del genoma, evolución de los elasmobranquios, genómica de la conservación, biodiversidad fluvial africana