Clear Sky Science · es
Datos temporales multiómica de expresión génica durante la diferenciación de células polihormonales derivadas de células madre embrionarias humanas
Cómo las células aprenden a convertirse en órganos
Nuestros cuerpos comienzan como pequeños racimos de células idénticas que, de alguna manera, aprenden a convertirse en tejidos muy distintos, desde el cerebro hasta el páncreas. Este estudio sigue ese proceso de aprendizaje en el laboratorio, usando células madre embrionarias humanas que se guían para convertirse en células pancreáticas tempranas. Al rastrear la actividad de miles de genes a lo largo del tiempo y en múltiples niveles, el trabajo crea un mapa de referencia rico que puede ayudar a los científicos a comprender mejor el desarrollo humano y, a largo plazo, mejorar estrategias para tratar enfermedades como la diabetes.
Observando cómo las células eligen un camino
Las células madre embrionarias humanas son especiales porque pueden transformarse en casi cualquier tipo celular del cuerpo. En este estudio, los investigadores dirigieron estas células hacia un destino específico: una línea pancreática llamada células polihormonales, que pueden producir hormonas clave como la insulina y el glucagón. Reprodujeron el desarrollo temprano en un plato al modificar el medio de cultivo paso a paso, moviendo primero las células a un estado primitivo similar al intestino llamado endodermo, y luego hacia células pancreáticas productoras de hormonas durante 17 días. Se recogieron muestras en diez puntos temporales cuidadosamente elegidos para capturar todo el recorrido desde la célula madre pluripotente hasta la célula especializada en producir hormonas. 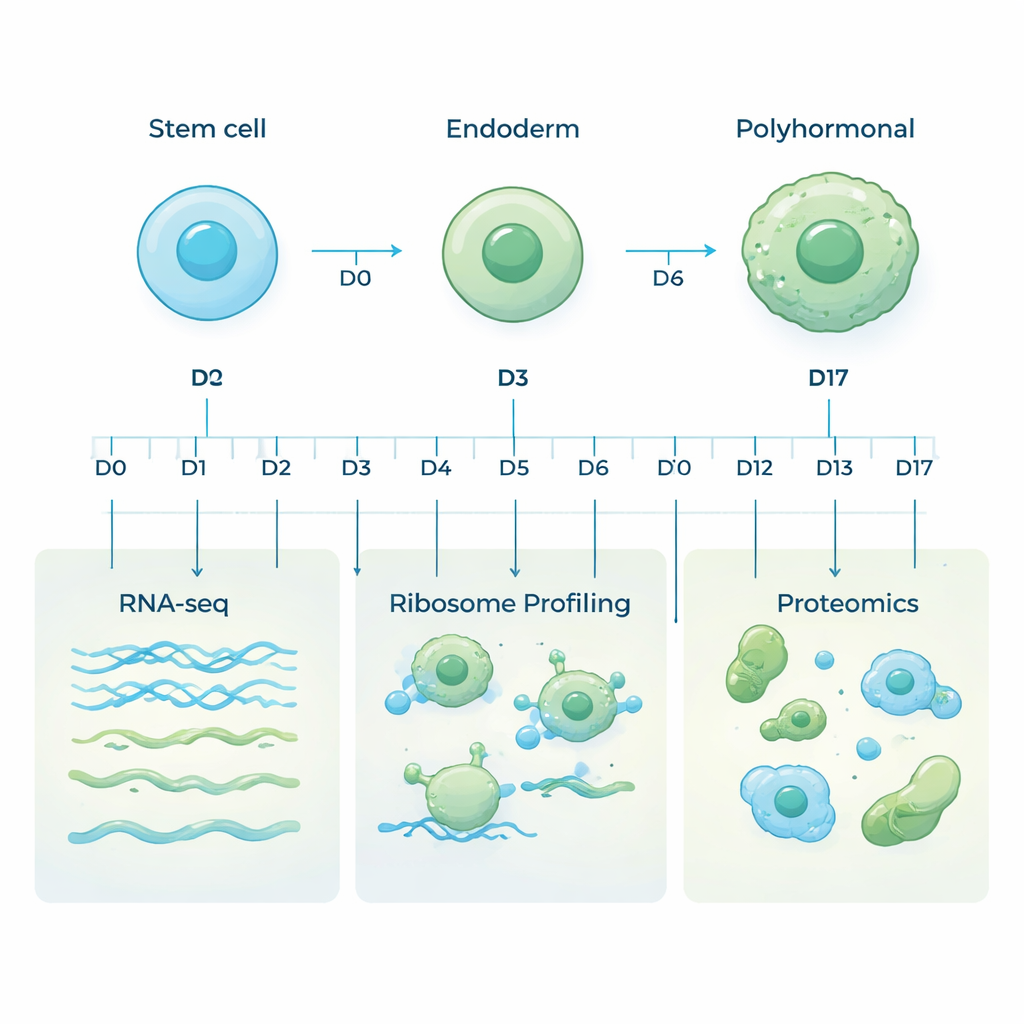
Mirando bajo el capó en tres niveles
La mayoría de los estudios solo observan el ARN mensajero (ARNm), las moléculas que transportan las instrucciones génicas. Pero el ARNm es solo parte de la historia: no todos los mensajes se traducen en proteína, y las propias proteínas pueden formarse o degradarse a ritmos distintos. Para obtener una visión más completa, el equipo usó tres enfoques complementarios en las mismas muestras. La secuenciación de ARN midió qué genes se estaban transcribiendo a ARNm. El perfilado de ribosomas siguió qué mensajes estaban siendo leídos activamente por las máquinas celulares que fabrican proteínas. La proteómica basada en espectrometría de masas midió después las proteínas reales presentes. Juntos, estos niveles revelan cómo se controla la actividad génica a medida que las células cambian de identidad.
Siguiendo señales clave de identidad celular
Para comprobar que las células realmente siguieron la ruta de desarrollo prevista, los científicos monitorizaron genes marcadores bien conocidos. Al principio, marcadores clásicos de células madre como OCT4 y NANOG eran altos y luego disminuyeron a medida que avanzaba la diferenciación. Cuando las células entraron en la etapa de endodermo, aumentaron marcadores como KIT y SOX17. En las etapas finales, los marcadores polihormonales insulina (INS) y glucagón (GCG) aparecieron con fuerza tanto a nivel de ARN como de proteína, confirmando que las células habían adoptado una identidad pancreática productora de hormonas. Aunque uno de los réplicas biológicas avanzó por estas etapas algo más despacio que el otro, ambos siguieron el mismo recorrido general, reflejando pequeñas diferencias naturales más que problemas técnicos. 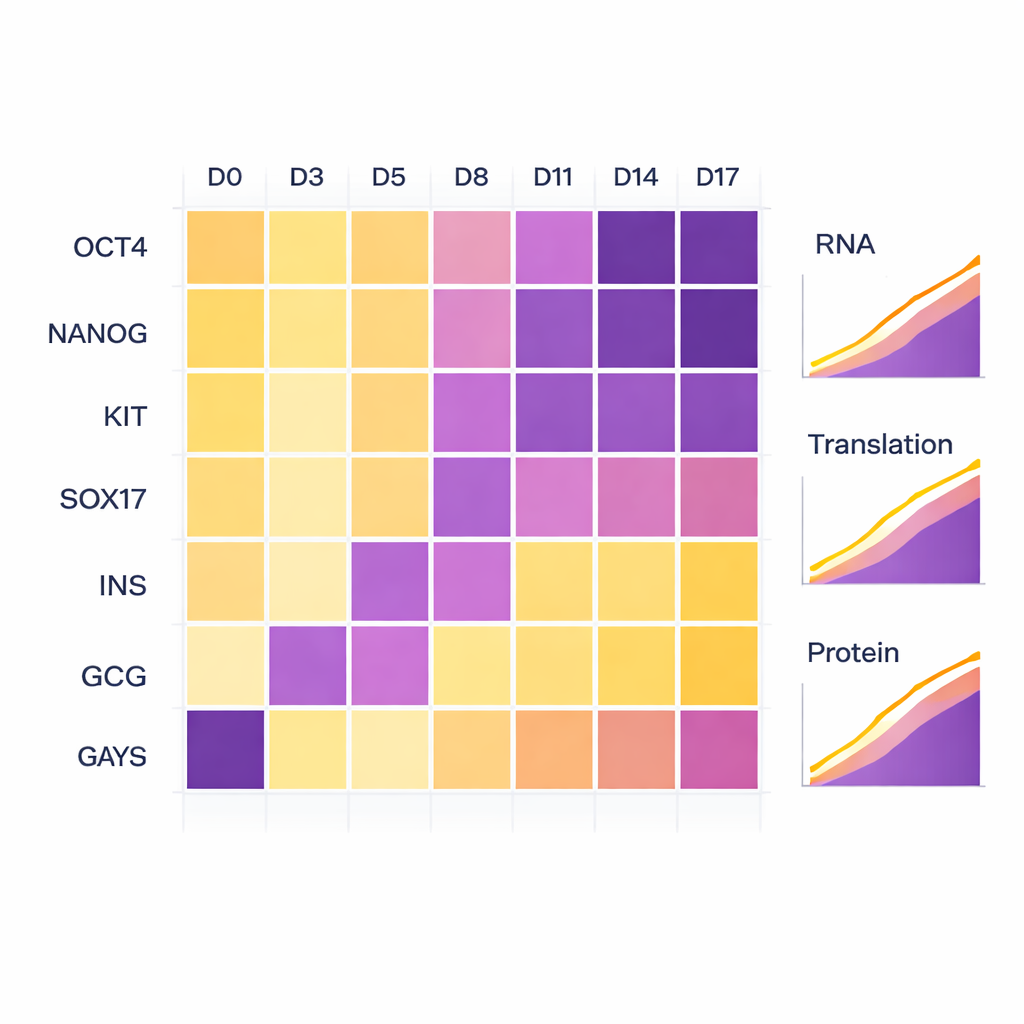
Controles de calidad para un recurso de confianza
Dado que este trabajo está pensado para servir como recurso comunitario, los autores dedicaron un esfuerzo extenso a comprobar la calidad y consistencia de los datos. Para cada uno de los tres métodos, evaluaron la precisión de la secuenciación y las medidas, la cobertura de genes y el grado de concordancia entre experimentos repetidos. Las etapas de células madre y polihormonales mostraron diferencias claras y reproducibles a través de los niveles de ARN, traducción y proteína. Los análisis de componentes principales —mapas estadísticos que agrupan muestras similares— mostraron que los puntos temporales se ordenaron secuencialmente, con etapas tempranas y tardías claramente separadas y réplicas biológicas agrupándose de forma ajustada. Solo los datos de proteómica siguieron de manera fiable casi 7.500 proteínas a lo largo de todos los puntos temporales, con relativamente pocas mediciones perdidas, lo que subraya la profundidad del conjunto de datos.
Una base para descubrimientos futuros
Los autores ponen a disposición pública todos los datos crudos y procesados, junto con scripts de análisis y archivos de referencia, para que otros investigadores puedan reutilizar y reanalizar el conjunto de datos. Más allá de describir cómo un tipo celular se convierte en otro, este trabajo ofrece una imagen detallada y resuelta en el tiempo de cómo interactúan los mensajes génicos, su traducción y las proteínas resultantes durante una transición del desarrollo importante. Para el público no especializado, la conclusión principal es que el destino celular está controlado por varias capas de regulación que actúan conjuntamente a lo largo del tiempo, y que este conjunto de datos proporciona una “película” de alta resolución de esos cambios. Los científicos pueden ahora usar este recurso para investigar por qué algunos genes cambian temprano y otros tarde, cómo diferentes órganos pueden seguir reglas similares o distintas, y cómo guiar mejor a las células madre hacia destinos de interés médico.
Cita: Keskin, A., Shayya, H.J., Patel, A. et al. Temporal multiomics gene expression data across human embryonic stem cell-derived polyhormonal cell differentiation. Sci Data 13, 278 (2026). https://doi.org/10.1038/s41597-026-06606-8
Palabras clave: células madre, desarrollo del páncreas, expresión génica, multiómica, células polihormonales