Clear Sky Science · es
Ensamblado genómico sin huecos, de telómero a telómero, de Opsariichthys evolans (Cypriniformes: Cyprinidae)
Un pez de arroyo con una historia genómica
Los arroyos montañosos y rápidos del sureste de China y Taiwán albergan a un pequeño y colorido pez llamado Opsariichthys evolans. Aunque es poco conocido fuera de la región, esta especie es una pieza clave ecológica y una obra de arte natural, con franjas brillantes y colores nupciales llamativos. Durante más de un siglo, los científicos debatieron cómo clasificarlo y cómo encaja en el árbol genealógico de los peces de agua dulce. Este estudio aporta una pieza clave de ese rompecabezas: el primer genoma completo y sin huecos de O. evolans, leído de un extremo cromosómico al otro.
Por qué importa este pez
O. evolans vive en arroyos claros y con corriente, donde contribuye a mantener el equilibrio de las redes tróficas y actúa como un indicador sensible de la calidad del agua. Los machos desarrollan franjas laterales vívidas y tubérculos granulares en la cabeza y alrededor de los ojos durante la época de cría, además de un hocico oscuro, negro-púrpura. Estos rasgos llamativos, junto con la preferencia de la especie por aguas rápidas, la convierten en un modelo ideal para estudiar cómo los animales se adaptan a su entorno. Al mismo tiempo, los cambios impulsados por el ser humano—contaminación, fragmentación del hábitat y especies invasoras—están reduciendo sus poblaciones, por lo que comprender su biología es importante para la conservación.
Una confusión de nombres que duró décadas
Durante décadas, los biólogos lucharon por decidir si O. evolans pertenecía al género Opsariichthys o a Zacco. Los primeros taxónomos describieron la especie como Zacco evolans, basándose en gran medida en rasgos externos como la forma de las aletas y las franjas del cuerpo. Estudios posteriores, más detallados, mostraron que su patrón de franjas y los tubérculos nupciales difieren de los de la similar Zacco platypus. Los estudios de ADN mitocondrial sugerían que O. evolans encaja mejor dentro de Opsariichthys, pero algunos datos de genes nucleares insinuaban una relación más próxima con Zacco. Sin un genoma completo, la imagen evolutiva permanecía borrosa y el debate sobre su lugar correcto en el árbol familiar de los peces continuó.

Leer cada letra del genoma
Para resolver estas preguntas, los investigadores recogieron un ejemplar macho silvestre de un río de la provincia de Anhui, China, y preservaron cuidadosamente nueve tejidos distintos. A continuación combinaron varias tecnologías de secuenciación de ADN de vanguardia, cada una con sus fortalezas, para leer el código genético del animal. Fragmentos cortos y altamente precisos ayudaron a pulir la secuencia, mientras que lecturas largas y ultralargas de las plataformas PacBio y Oxford Nanopore cubrieron regiones difíciles y cosieron los cromosomas de extremo a extremo. La tecnología Hi-C, que captura cómo se pliega el ADN dentro de la célula, se empleó para organizar las piezas en cromosomas de longitud completa. El resultado final es un genoma de telómero a telómero, sin huecos, de aproximadamente 0,89 mil millones de pares de bases, ordenado en 39 cromosomas con una pieza continua de ADN por cada uno.
Lo que revela el genoma
El genoma terminado superó controles de calidad estrictos, capturando más del 99% de los genes conservados esperados y alineándose de cerca con secuencias de ADN conocidas de peces relacionados. Casi la mitad del genoma consiste en secuencias repetidas, muchas de ellas «genes saltarines» que pueden moverse y remodelar el genoma a lo largo del tiempo evolutivo. El equipo identificó casi 30 000 genes codificadores de proteínas y miles de ARN no codificantes, la mayoría de los cuales pudieron vincularse a funciones conocidas mediante grandes bases de datos biológicas. Al comparar este nuevo genoma con los de dos parientes cercanos—Opsariichthys bidens y Zacco platypus—los científicos hallaron que la estructura cromosómica global es muy similar, confirmando estrechos lazos evolutivos. Dentro de este marco, identificaron genes candidatos y vías probablemente implicados en la coloración de las franjas corporales y en las adaptaciones a vivir en corrientes rápidas, ofreciendo pistas sobre cómo evolucionaron su aspecto distintivo y su estilo de vida.
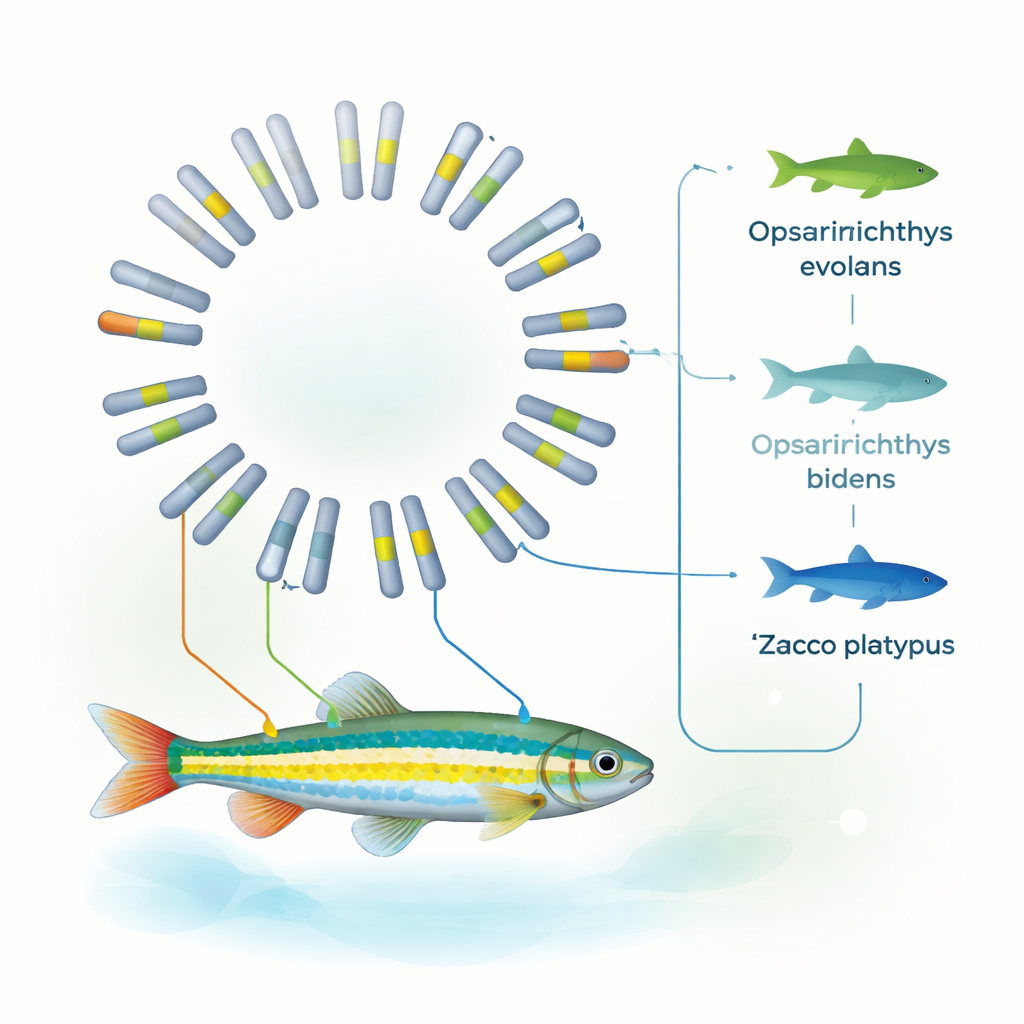
Aclarando su lugar en el árbol familiar de los peces
Usando familias de genes compartidas entre diez especies de peces diferentes, el equipo reconstruyó un árbol evolutivo detallado. Su análisis indica que O. evolans se separó de Z. platypus hace aproximadamente entre 8 y 19 millones de años y que su estructura genómica es especialmente cercana a la de O. bidens. Junto con la evidencia mitocondrial previa, estos patrones apoyan ubicar firmemente a O. evolans en el género Opsariichthys, y no en Zacco. En otras palabras, el genoma completo ahora respalda lo que la observación minuciosa de las franjas, el color del hocico y las estructuras nupciales ya sugería: las apariencias pueden engañar, pero cuando la morfología y un genoma completo coinciden, las líneas taxonómicas se aclaran mucho.
Por qué un genoma completo cambia las reglas del juego
Para los no especialistas, el logro aquí es como pasar de un mapa borroso y rasgado a un atlas nítido y de alta resolución de una especie. Con un genoma completo y sin huecos, los científicos pueden ahora rastrear los orígenes de los colores llamativos de O. evolans, su forma aerodinámica para la vida en aguas rápidas y sus relaciones con otros ciprínidos del este asiático con una precisión sin precedentes. Este recurso ayudará a refinar la clasificación de peces, guiar los esfuerzos de conservación de ecosistemas de arroyos vulnerables y profundizar nuestra comprensión de cómo pequeñas diferencias en el ADN pueden generar la rica diversidad observada en los peces de agua dulce.
Cita: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
Palabras clave: ensamblado del genoma, pez de agua dulce, de telómero a telómero, evolución de peces, genómica comparativa