Clear Sky Science · es
Cereblon induce la degradación neosustrato de G3BP2 mediante mimetismo de superficie molecular
Convertir la limpieza celular en un sistema de orientación inteligente
Los medicamentos modernos intentan cada vez más corregir la enfermedad no solo bloqueando proteínas problemáticas, sino eliminándolas por completo. Este artículo explora una forma ingeniosa de reprogramar una de las máquinas de "limpieza" de la célula para que, cuando se combina con una pequeña molécula, pueda reconocer y destruir una proteína vinculada al cáncer y a otros trastornos. El trabajo revela un truco inesperado: la máquina de limpieza remodela parte de su superficie para imitar a uno de los socios naturales de la proteína, lo que le permite engancharse y enviar la proteína a la basura celular.
El recolector de basuras celular con flexibilidad oculta
Nuestras células etiquetan constantemente las proteínas desgastadas o no deseadas para su destrucción, usando un sistema centrado en ligasas E3: complejos proteicos grandes que deciden qué debe desecharse. Uno de esos complejos depende de un componente llamado cereblon, que actúa como sensor que reconoce rasgos específicos ("degrones") en otras proteínas. Ciertos fármacos ya aprobados explotan cereblon actuando como "pegamentos moleculares": se unen a cereblon y crean una nueva superficie de anclaje que atrae proteínas relacionadas con la enfermedad, las cuales son entonces etiquetadas y degradadas. Hasta ahora, la mayoría de los objetivos conocidos utilizaban un patrón estructural particular, lo que hacía parecer limitada la gama de proteínas que podían eliminarse de esta manera.
Descubrir un nuevo objetivo fuera de las reglas antiguas
En el nuevo estudio, los autores cribaron una colección de pegamentos moleculares centrados en cereblon en células humanas e identificaron un compuesto llamado MRT-5702. Esta pequeña molécula provocó la pérdida rápida de una proteína llamada G3BP2, que ayuda a gestionar ARN y forma parte de gránulos de estrés —ensamblajes vinculados al cáncer, problemas cardíacos y enfermedades neurodegenerativas. Es importante destacar que G3BP2 carece del patrón de degrón habitual que reconoce cereblon. Experimentos celulares de seguimiento, incluidos ensayos sensibles basados en luz para medir proximidad entre proteínas, confirmaron que MRT-5702 acerca a cereblon y G3BP2 en un complejo de tres partes que conduce a la degradación de G3BP2, mientras que respeta a su proteína hermana estrechamente relacionada G3BP1, a menos que se intercambie su dominio clave.
La imitación como estrategia de unión
Profundizando, los investigadores se preguntaron cómo G3BP2 podía unirse a cereblon sin el motivo de reconocimiento estándar. En lugar de buscar similitudes entre G3BP2 y los objetivos conocidos de cereblon, invirtieron la cuestión: ¿podría cereblon parecerse a uno de los socios habituales de G3BP2? Las proteínas G3BP suelen interactuar con otras moléculas a través de un punto caliente en una región llamada dominio NTF2-like, que normalmente reconoce motivos de secuencia cortos. Usando modelos estructurales del socio natural de G3BP2, USP10, el equipo escaneó computacionalmente la superficie de cereblon y encontró un parche en una región menos conocida, el dominio LON, que imita de forma aproximada la forma y la química del motivo de unión de USP10. Mutar solo unos pocos aminoácidos clave en este parche, o en el punto caliente de G3BP2, debilitó el complejo de tres partes, lo que sugiere que cereblon está efectivamente suplantando a USP10 para anclarse a G3BP2.
Capturar la nueva interfaz en detalle atómico
Para visualizar esta interacción inusual, el equipo utilizó microscopía crioelectrónica de alta resolución para resolver la estructura de un complejo que contenía cereblon, otro componente central de la ligasa, MRT-5702 y el dominio NTF2-like de G3BP2. Las imágenes revelaron que un lazo flexible en el dominio LON de cereblon se dobla y remodela para formar casi la mitad de la superficie de contacto con G3BP2. La forma activa de imagen especular de MRT-5702 se asienta en el bolsillo habitual de unión de fármacos de cereblon pero, junto con el lazo, ayuda a crear una amplia plataforma de aterrizaje que acoge la mitad de la dímero de G3BP2. De forma llamativa, este arreglo usa apenas el sitio canónico de cereblon que maneja los objetivos previos tipo pegamento, mostrando que cereblon puede involucrar regiones muy diferentes de su superficie dependiendo del pegamento y la proteína implicados. Al mismo tiempo, la mitad intacta del dímero de G3BP2 permanece disponible para unirse a otros socios, ofreciendo una vía plausible para la degradación “colateral” de proteínas que resulten estar asociadas.
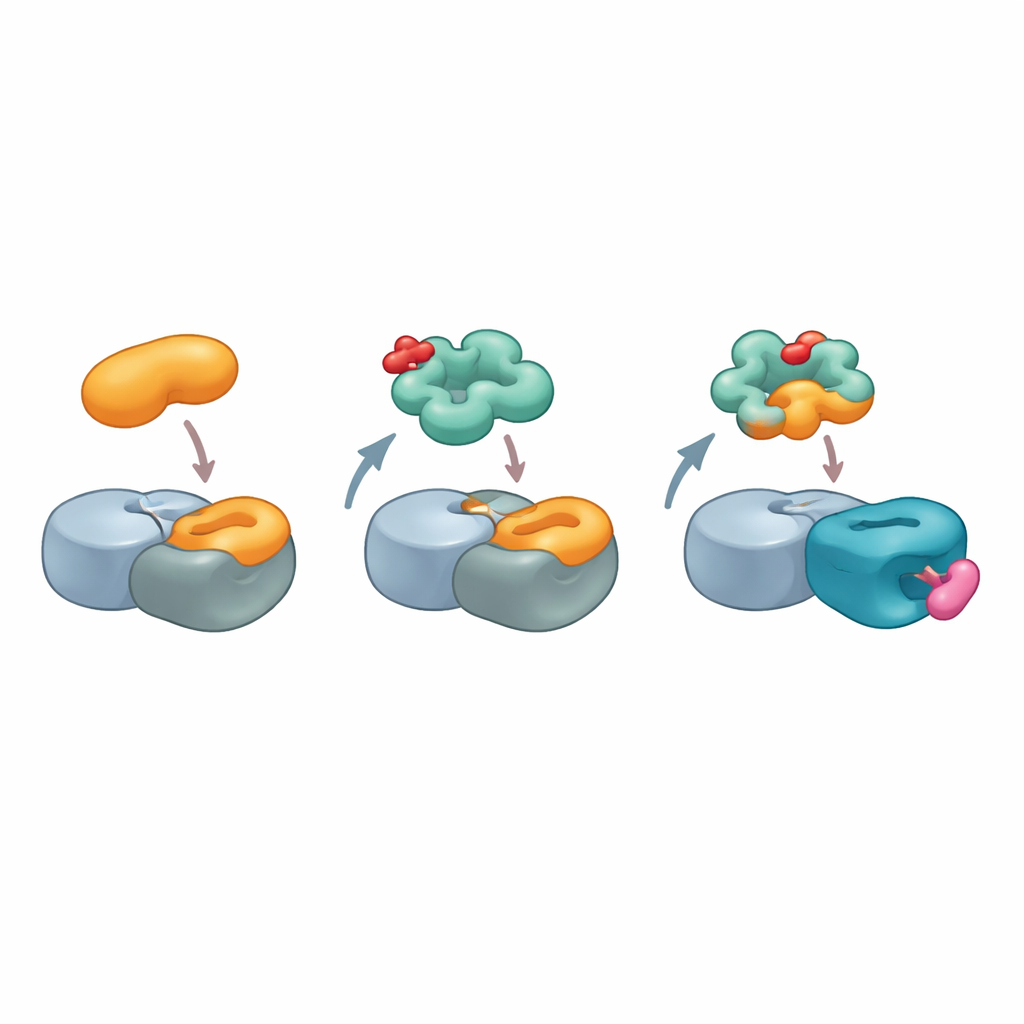
Huellas de pegamento para el diseño de fármacos futuros
En conjunto, los hallazgos presentan a cereblon como un mediador mucho más versátil de lo que se apreciaba. En lugar de exigir que los objetivos lleven un único tipo de degrón, cereblon puede, cuando está armado con el pegamento molecular adecuado, moldear una superficie compuesta que imita contactos proteína‑proteína naturales en otras partes de la célula. Los autores proponen que tales superficies combinadas de proteína y pegamento, a las que denominan "huellas de pegamento" (glueprints), podrían mapearse y diseñarse para imitar puntos calientes de interacción existentes en muchas proteínas vinculadas a enfermedades. Para un lector no especializado, el mensaje clave es que los desarrolladores de fármacos podrían no necesitar descubrir bolsillos de unión completamente nuevos en proteínas problemáticas; en su lugar, pueden enseñar a la propia maquinaria de reciclaje celular a reconocer esas proteínas copiando con ingenio las formas de sus socios habituales, ampliando considerablemente el abanico de objetivos que pueden eliminarse de forma segura y selectiva.
Cita: Annunziato, S., Quan, C., Donckele, E.J. et al. Cereblon induces G3BP2 neosubstrate degradation using molecular surface mimicry. Nat Struct Mol Biol 33, 479–487 (2026). https://doi.org/10.1038/s41594-025-01738-8
Palabras clave: degradadores tipo pegamento molecular, cereblon, degradación proteica dirigida, G3BP2, interacciones proteína-proteína