Clear Sky Science · es
Un modelo base generalizable para el análisis de resonancias magnéticas cerebrales humanas
Enseñar a las máquinas a leer exploraciones cerebrales
La resonancia magnética (RM) permite a los médicos observar el cerebro vivo sin cirugía, pero interpretar esas imágenes sigue dependiendo en gran medida de expertos humanos y de grandes conjuntos de datos etiquetados. Este estudio presenta BrainIAC, una especie de «motor cerebral» de uso general que aprende a partir de decenas de miles de exploraciones cerebrales no etiquetadas y que luego puede adaptarse rápidamente a muchas preguntas médicas —desde estimar la edad cerebral hasta delinear tumores—, a menudo con solo unos pocos ejemplos. Para los pacientes, esta tecnología podría traducirse en diagnósticos más rápidos, una mejor planificación del tratamiento y acceso a herramientas avanzadas de imagen incluso en hospitales con experiencia especializada limitada.
Por qué las exploraciones cerebrales son difíciles para las máquinas
La RM cerebral es rica pero compleja. Una misma persona puede ser escaneada con varios ajustes diferentes, cada uno resaltando distintos tejidos o rasgos de enfermedad. Los hospitales usan una variedad de aparatos y protocolos, por lo que las imágenes pueden variar mucho de un lugar a otro. Además, las etiquetas detalladas de expertos —por ejemplo, trazar con precisión los bordes de un tumor o registrar la supervivencia a largo plazo— son costosas y poco frecuentes. Los sistemas tradicionales de inteligencia artificial suelen entrenarse para una tarea muy concreta sobre un conjunto de datos curado. Tienden a tener dificultades cuando se les pide trabajar en nuevos hospitales, enfermedades raras o cuestiones para las que no fueron diseñados específicamente.
Un único modelo central para muchas tareas cerebrales
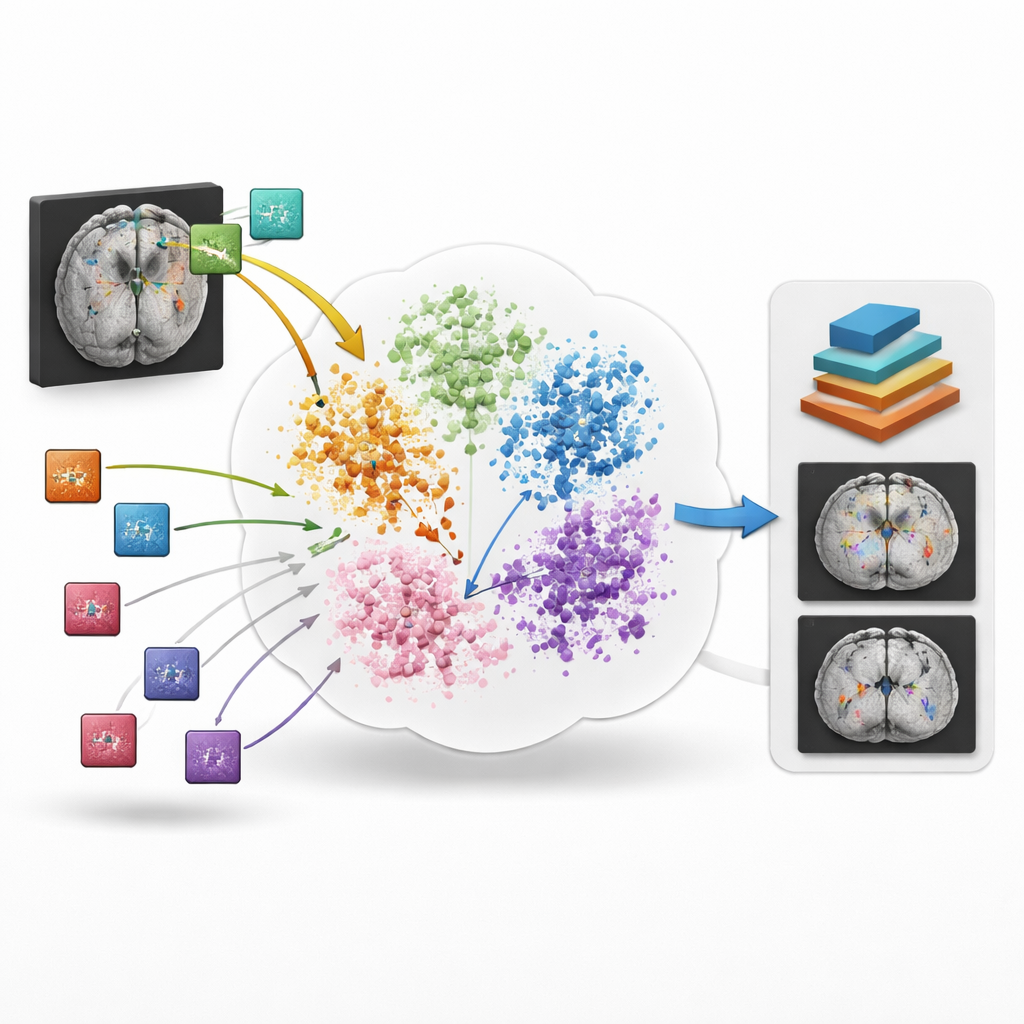
BrainIAC toma una ruta distinta: en lugar de aprender una tarea a la vez, primero aprende el «lenguaje» general de la estructura cerebral y la enfermedad a partir de 32.015 exploraciones de RM procedentes de 34 conjuntos de datos y diez condiciones neurológicas, totalizando casi 49.000 exploraciones en la piscina completa. El modelo se entrena de forma auto-supervisada, lo que significa que no necesita etiquetas humanas. Observa muchos pequeños parches tridimensionales extraídos de escaneos cerebrales completos y aprende a distinguir cuándo dos versiones aumentadas de manera distinta provienen de la misma ubicación frente a cuando provienen de cerebros diferentes. Al acercar en su espacio interno los parches coincidentes y alejar los no relacionados, BrainIAC construye una representación flexible de cómo lucen habitualmente los cerebros sanos y enfermos a través de edades, aparatos y hospitales.
Poniendo el motor cerebral a trabajar
Una vez aprendida esta representación central, los investigadores prueban BrainIAC en siete tareas concretas que reflejan problemas clínicos reales. Estas incluyen clasificar exploraciones por tipo de secuencia de RM, estimar la edad aparente del cerebro, predecir si un tumor cerebral porta una mutación genética clave, pronosticar la supervivencia en pacientes con tumores agresivos, distinguir problemas de memoria iniciales del envejecimiento normal, estimar hace cuánto tiempo ocurrió un ictus y delinear tumores en las imágenes. Para cada tarea comparan tres estrategias: entrenar un modelo desde cero para esa tarea, partir de modelos de imagen médica previos diseñados para otros fines, o ajustar finamente las características cerebrales ya aprendidas por BrainIAC. En general, BrainIAC iguala o supera a las alternativas, especialmente cuando hay pocos datos etiquetados disponibles.
Funciona bien cuando los datos escasean
Una prueba clave es cómo se comporta el sistema cuando los datos etiquetados son extremadamente escasos, como suele ocurrir en enfermedades raras o en estudios de imagen costosos. El equipo explora escenarios donde solo se usa el 10 % de las exploraciones de entrenamiento habituales e incluso entornos más exigentes de «pocos ejemplos» donde hay solo uno o cinco ejemplos etiquetados por clase. En estas condiciones restrictivas, BrainIAC ofrece de forma constante predicciones más precisas que los modelos entrenados desde cero u otros modelos base disponibles. Por ejemplo, distingue mejor tipos sutiles de secuencias de RM, predice con mayor precisión la genética tumoral y la supervivencia, y traza contornos de tumores más limpios usando muchas menos imágenes anotadas. El modelo también demuestra mayor estabilidad cuando se agregan de forma artificial artefactos comunes de RM, como cambios de contraste o distorsiones relacionadas con el escáner, lo que sugiere que ha aprendido características robustas en lugar de atajos frágiles.
Qué podría significar esto para pacientes y clínicos
Para comprender si BrainIAC se concentra en regiones clínicamente relevantes, los autores generan «mapas de atención» visuales que muestran dónde mira el modelo al tomar decisiones. Estos mapas resaltan estructuras como el hipocampo para problemas de memoria tempranos, regiones de la materia blanca para la estimación de la edad y el núcleo del tumor para predicciones genéticas y de supervivencia —áreas que coinciden con la intuición de expertos humanos. Dado que BrainIAC se puede integrar en distintas canalizaciones de análisis y adaptarse con un entrenamiento adicional mínimo, ofrece una columna vertebral flexible para futuras herramientas de imagen, incluidas posibles combinaciones con registros clínicos o datos genéticos.
Un paso hacia una imagen cerebral más inteligente y accesible
En conjunto, el estudio demuestra que un único modelo base, cuidadosamente entrenado, puede servir como un punto de partida sólido para muchas tareas distintas de RM cerebral, superando a menudo a sistemas especializados que deben reconstruirse desde cero cada vez. Para los no especialistas, la conclusión clave es que BrainIAC actúa como un «lector cerebral» ampliamente formado que puede adquirir nuevas habilidades rápidamente con solo unos pocos ejemplos. Si bien no sustituye a modelos a medida ni al juicio médico, establece una base importante para que las predicciones basadas en imágenes sean más precisas, más robustas y más accesibles, incluso en situaciones donde recopilar grandes conjuntos de datos etiquetados sería de otro modo imposible.
Cita: Tak, D., Garomsa, B.A., Zapaishchykova, A. et al. A generalizable foundation model for analysis of human brain MRI. Nat Neurosci 29, 945–956 (2026). https://doi.org/10.1038/s41593-026-02202-6
Palabras clave: resonancia magnética cerebral, IA médica, modelos base, aprendizaje auto-supervisado, neuroimagen