Clear Sky Science · es
MaAsLin 3: afinando y ampliando modelos lineales multivariables generalizados para el descubrimiento de asociaciones meta-ómicas
Por qué importan los diminutos vecinos del intestino
Nuestros cuerpos albergan billones de microbios que ayudan a digerir los alimentos, entrenan el sistema inmunitario e incluso pueden influir en nuestro estado de ánimo. A medida que la secuenciación de ADN ha facilitado el catálogo de estas comunidades microbianas, ha surgido una pregunta crucial: ¿qué microbios específicos se asocian con enfermedades como la enfermedad inflamatoria intestinal, o con rasgos cotidianos como la edad y la dieta? Responder a esto resulta sorprendentemente difícil. Los datos son ruidosos, están llenos de ceros y se informan como porcentajes en lugar de recuentos reales. Este artículo presenta MaAsLin 3, una nueva herramienta estadística diseñada para extraer señales más claras de datos de microbioma desordenados, de modo que los investigadores puedan vincular con mayor fiabilidad los microbios con la salud humana y el medio ambiente.
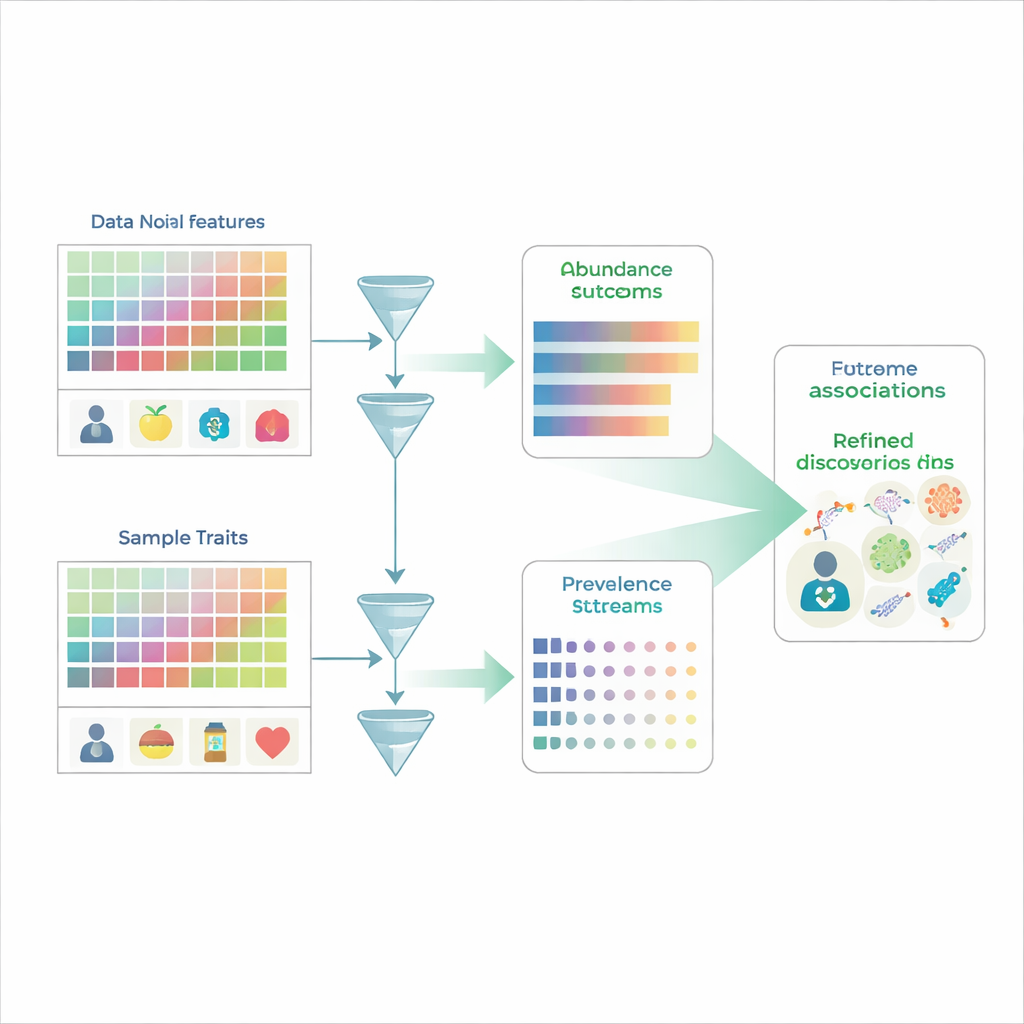
Buscando patrones en una multitud ruidosa
Los estudios tradicionales de microbioma funcionan un poco como contar caras en una multitud: los investigadores miden la abundancia relativa de cientos o miles de especies microbianas en muchas personas y luego preguntan qué especies difieren entre, por ejemplo, grupos enfermos y sanos. Pero los datos de microbioma están restringidos a porcentajes que deben sumar 100 %, por lo que si una especie sube, al menos otra parece bajar aunque su cantidad real no haya cambiado. Además, muchas especies simplemente no se detectan en una muestra dada, lo que produce muchos ceros que pueden reflejar tanto ausencia real como límites de detección. Los métodos de análisis comunes suelen mezclar dos preguntas distintas: si un microbio está presente en absoluto y cuánto hay cuando está presente, lo que facilita interpretar mal la biología subyacente.
Separar presencia de cantidad
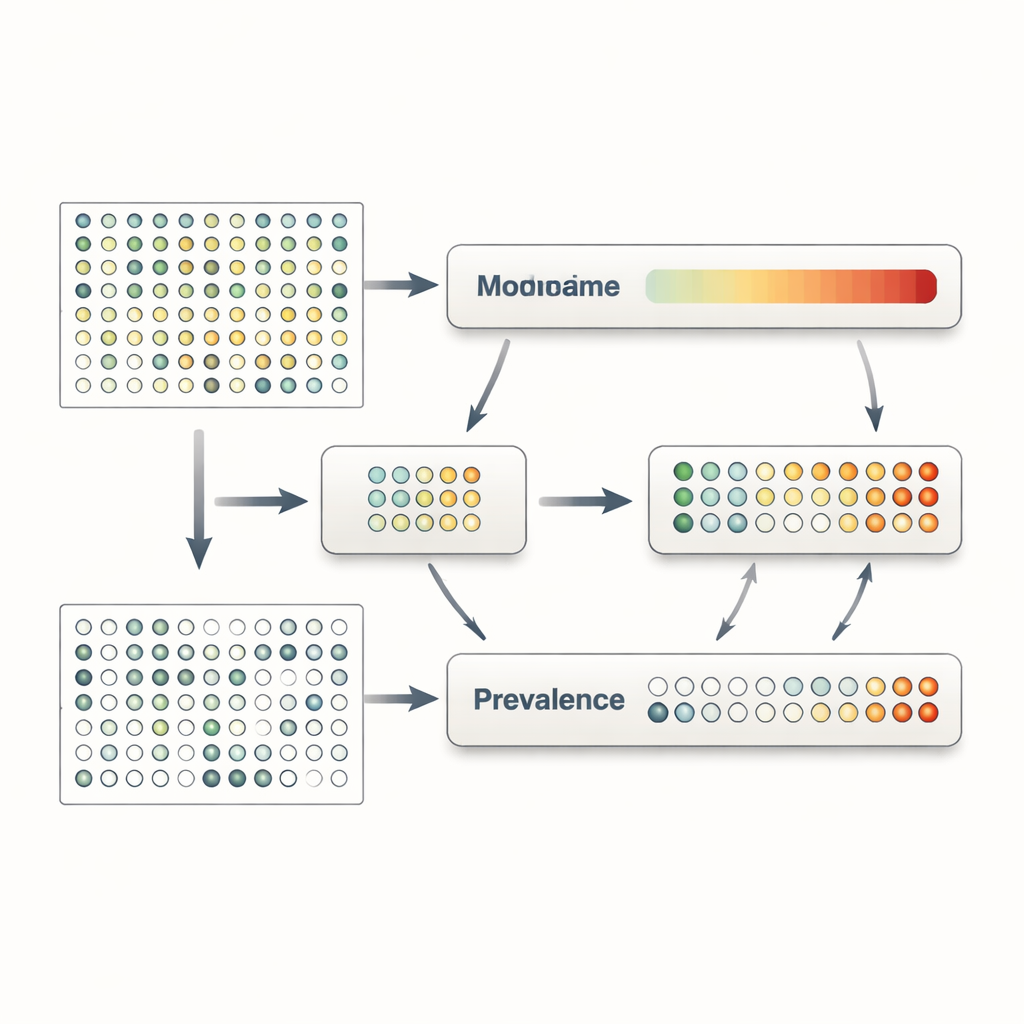
MaAsLin 3 aborda estos problemas tratando explícitamente la presencia y la cantidad como fenómenos separados pero relacionados. Para cada rasgo microbiano—como una especie, un gen o una vía metabólica—construye dos modelos en paralelo. Un modelo examina la prevalencia, preguntando con qué frecuencia se detecta el rasgo en muestras con distintos rasgos clínicos o ambientales. El otro modelo se centra en la abundancia, preguntando cómo cambia el nivel del rasgo entre solo las muestras en las que se detecta. Al dividir los datos de esta manera, MaAsLin 3 evita el atajo común de rellenar ceros con números pequeños arbitrarios, lo que puede distorsionar los resultados. Luego combina los dos efectos en una visión general de cómo cada rasgo se relaciona con cada variable, permitiendo al mismo tiempo que los investigadores vean si una asociación se debe principalmente a la presencia, a la cantidad o a ambas.
Acercándose a cantidades reales
Una complicación adicional en la ciencia del microbioma es que la mayoría de las mediciones son relativas: nos indican qué fracción de la comunidad total ocupa una especie, no cuántas células hay realmente. Sin embargo, las preguntas biológicas a menudo dependen de la abundancia absoluta —por ejemplo, si el recuento celular de un patógeno supera un umbral que podría desencadenar enfermedad. MaAsLin 3 ofrece dos soluciones complementarias. Cuando los experimentos incluyen información adicional, como cantidades conocidas de un organismo de referencia o estimaciones de la carga microbiana total, el método puede transformar los porcentajes relativos en estimaciones de recuentos absolutos y modelarlos directamente. Cuando esos datos no están disponibles, MaAsLin 3 compara el comportamiento de cada rasgo con el patrón típico de todos los rasgos, lo que bajo supuestos realistas aproxima lo que se vería en una escala absoluta. Amplias simulaciones por ordenador y pruebas en conjuntos de datos reales con abundancias absolutas medidas experimentalmente muestran que esta estrategia recupera con precisión las tendencias subyacentes y supera a varias herramientas de uso común.
Revelando señales ocultas en las enfermedades intestinales
Para mostrar lo que estos avances significan en la práctica, los autores aplicaron MaAsLin 3 a una gran cohorte bien estudiada de personas con y sin enfermedades inflamatorias intestinales como la enfermedad de Crohn y la colitis ulcerosa. Trabajos previos ya habían identificado muchos cambios microbianos en estas condiciones, pero MaAsLin 3 aportó varias capas de matiz. Confirmó la mayoría de las asociaciones conocidas, a la vez que aclaró que alrededor de tres cuartas partes de las asociaciones involucraban cambios en si los microbios estaban presentes en absoluto, más que en cuán abundantes eran cuando estaban presentes. En otras palabras, la inflamación intestinal a menudo coincidía con la pérdida completa de ciertos microbios beneficiosos o con la incapacidad de detectarlos, en lugar de una disminución leve en sus niveles. El método también reveló microbios cuya mera presencia —independientemente de su cantidad— se correlacionó fuertemente con la alteración de la comunidad intestinal relacionada con la enfermedad.
Qué significa esto para futuros estudios y la atención clínica
Para el público general, el mensaje clave es que la forma en que analizamos los datos de microbioma puede moldear radicalmente qué microbios consideramos relevantes para la salud. Al manejar mejor los ceros, separar presencia de cantidad y aproximar los recuentos celulares reales, MaAsLin 3 ofrece una lente más nítida para descubrir marcadores microbianos fiables de enfermedad, dieta y ambiente. Sus resultados en la enfermedad inflamatoria intestinal sugieren que muchos cambios de relevancia clínica implican microbios que desaparecen o aparecen de nuevo, no solo los que aumentan o disminuyen gradualmente en abundancia. Esta distinción es importante para diseñar terapias: si la enfermedad está vinculada a la pérdida absoluta de especies beneficiosas, las estrategias que reintroduzcan o protejan esos microbios pueden ser más efectivas que los enfoques que solo intentan ajustar el equilibrio global de la comunidad. MaAsLin 3, por tanto, equipa a los investigadores con un conjunto de herramientas más preciso y flexible para convertir mediciones complejas del microbioma en ideas biológicas accionables.
Cita: Nickols, W.A., Kuntz, T., Shen, J. et al. MaAsLin 3: refining and extending generalized multivariable linear models for meta-omic association discovery. Nat Methods 23, 554–564 (2026). https://doi.org/10.1038/s41592-025-02923-9
Palabras clave: microbioma, enfermedad inflamatoria intestinal, modelado estadístico, abundancia absoluta, prevalencia microbiana